Clear Sky Science · es
Construcción de secuencias de ADN complejas y diversas usando uniones de tres vías de ADN
Construyendo nuevas historias genéticas
La biología moderna puede leer y editar ADN a una velocidad asombrosa, pero escribir secuencias genéticas largas y a medida sigue quedando rezagado. Esta brecha ralentiza desde el diseño de nuevos medicamentos hasta la creación de materiales más sostenibles. Este estudio presenta “Sidewinder”, una nueva forma de coser fragmentos de ADN que pretende hacer que escribir genes complejos y personalizados sea tan fiable y escalable como leerlos.
Por qué el ensamblaje de ADN necesita repensarse
Cada célula funciona gracias al ADN, una larga cadena de “letras” químicas que codifican las instrucciones de la vida. Los científicos solo pueden sintetizar químicamente tramos cortos de ADN, por lo que los genes más largos deben ensamblarse a partir de muchas piezas pequeñas, como oraciones reconstruidas a partir de palabras recortadas. Los métodos actuales usan bordes coincidentes en esas piezas para guiar qué fragmentos se unen. Pero esos bordes coincidentes pasan a formar parte del ADN final, lo que significa que no se pueden optimizar libremente para un ensamblaje perfecto sin alterar también el gen. A medida que los diseños se vuelven más largos y complejos, este compromiso incorporado provoca más errores, bajos rendimientos y límites prácticos sobre lo que puede construirse.
Un camino lateral que guía sin dejar rastro
Sidewinder aborda este problema añadiendo una tercera hebra auxiliar de ADN que nunca aparece en el producto final. Las piezas de ADN se preparan con dos características en sus extremos: «toeholds» (anzuletas) cortos que formarán la conexión final y perfecta, y «códigos de barras» más largos diseñados solo para comunicarse con sus parejas previstas. Al mezclarse a una temperatura controlada, los códigos de barras de piezas adyacentes se reconocen y se enrollan en una hélice lateral temporal, formando una unión de tres vías que posiciona las anzuletas coincidentes. Una enzima luego sella las piezas principales de ADN. Finalmente, los códigos de barras auxiliares se eliminan, dejando una secuencia continua y limpia sin cicatrices ni etiquetas adicionales. 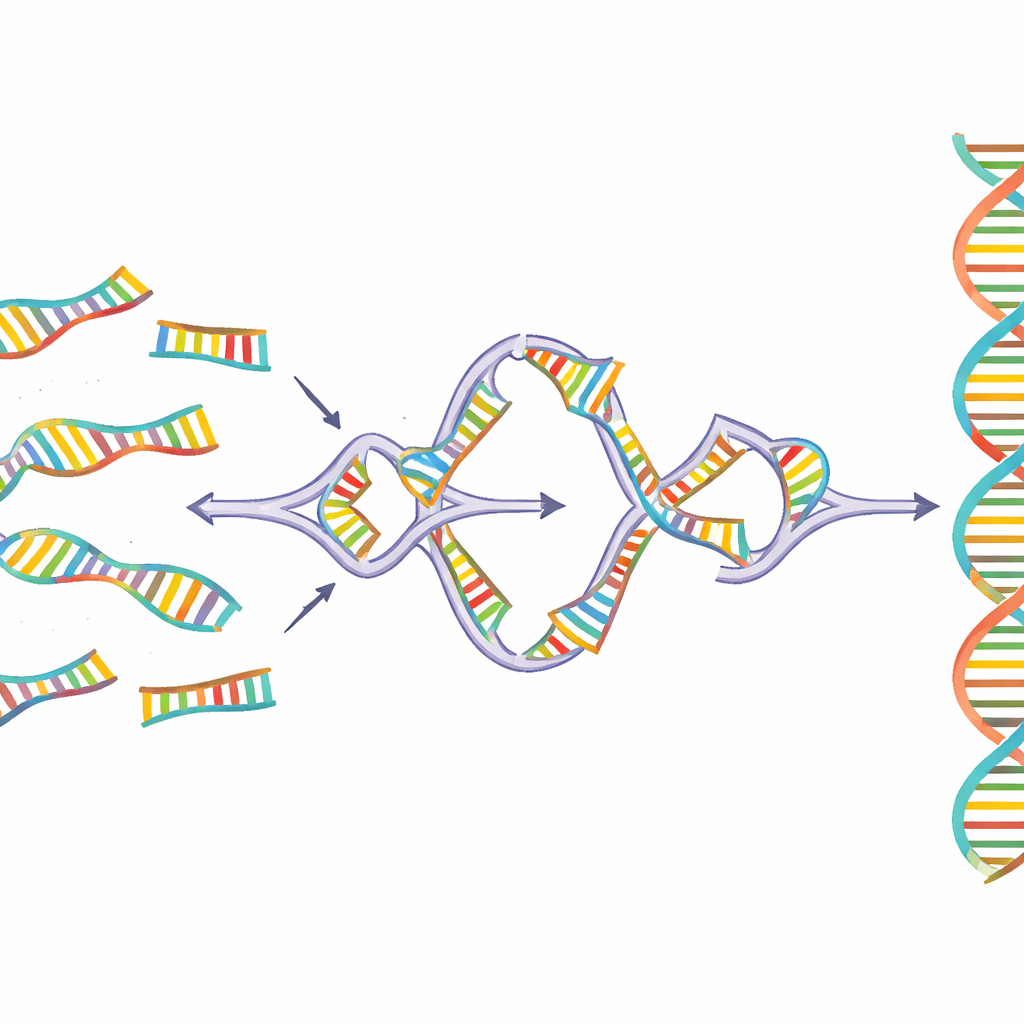
De docenas de fragmentos a genes difíciles
Para demostrar lo que Sidewinder puede manejar, los autores construyeron constructos de ADN a partir de 5, 10, 20 e incluso 40 fragmentos separados en una sola reacción. Los métodos de última generación competidores flaquearon más allá de unas pocas piezas, produciendo mezclas caóticas o fallando por completo, mientras que Sidewinder dio de forma consistente un único producto del tamaño correcto. La secuenciación de lectura larga confirmó que, en una prueba de 40 fragmentos, más del 96 % de las lecturas eran productos auténticos de Sidewinder y cada uno de ellos estaba ensamblado en el orden perfecto. El equipo luego puso a prueba el método con secuencias en “modo difícil”: un gen humano con un contenido extremadamente alto de G y C, y un segmento de proteína similar a la seda cargado de repeticiones. Tales secuencias suelen derrotar a los ensamblajes estándar porque se adhesivan entre sí de formas confusas. Sidewinder siguió produciendo ensamblajes casi perfectos, incluso cuando todas las junturas compartían deliberadamente la misma secuencia de anzuleta, algo que sería casi imposible de controlar con técnicas antiguas.
Muchos genes a la vez y océanos de variantes
Puesto que los códigos de barras de Sidewinder definen de forma única quién puede emparejarse con quién, varios genes pueden construirse en el mismo tubo sin contaminación cruzada. Los investigadores mezclaron fragmentos para tres proteínas marcadoras de color distinto y las ensamblaron en una sola reacción. Con los cebadores adecuados, pudieron amplificar selectivamente cualquier gen individual o la mezcla, y la secuenciación mostró que los cruces incorrectos entre diseños fueron extremadamente raros. 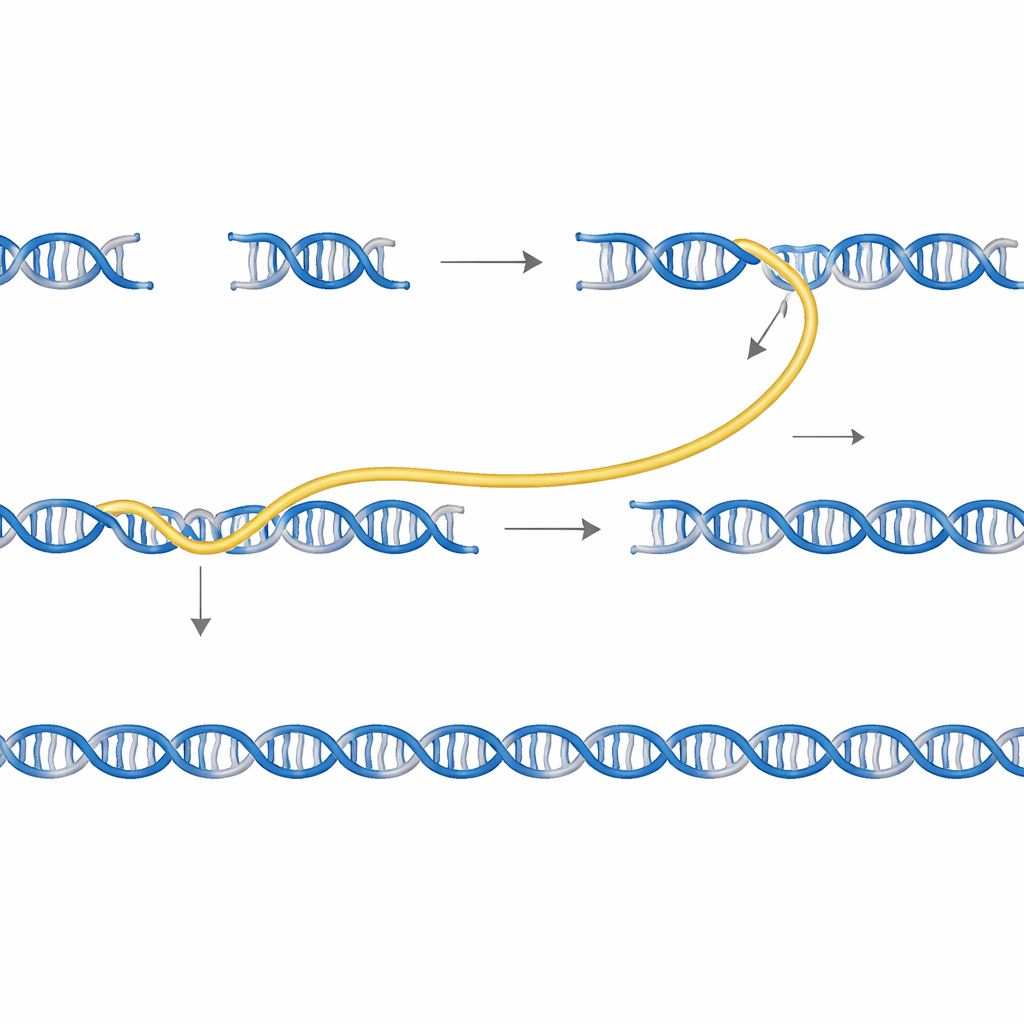
Qué significa esto para la bioingeniería futura
El logro clave de Sidewinder es separar las «instrucciones de ensamblaje» de la historia final del ADN. Al mover la información guía a una hebra lateral extraíble, los científicos pueden diseñar uniones extraordinariamente específicas y fiables sin verse obligados a comprometer el gen en sí. El resultado es un método de uso general para construir secuencias de ADN largas, complejas y muy variadas con una precisión que iguala, y en ciertos aspectos mejora, la calidad de las piezas de partida. A medida que herramientas como la IA propongan diseños genéticos cada vez más audaces, técnicas como Sidewinder pueden volverse esenciales para convertir esos diseños en moléculas reales para la medicina, materiales, agricultura y otros campos.
Cita: Robinson, N.E., Zhang, W., Ghosh, R. et al. Construction of complex and diverse DNA sequences using DNA three-way junctions. Nature 651, 491–500 (2026). https://doi.org/10.1038/s41586-025-10006-0
Palabras clave: ensamblaje de ADN, biología sintética, bibliotecas de genes, nanotecnología del ADN, ingeniería de proteínas