Clear Sky Science · es
Inferencia basada en simulación de la dinámica de migración celular en entornos espaciales complejos
Cómo las células inmunitarias encuentran su camino a través de tejidos densos
Nuestras células inmunitarias a menudo tienen que abrirse paso por tejidos densos y laberínticos para llegar a sitios de infección o a los ganglios linfáticos. Este estudio plantea una pregunta aparentemente simple con grandes implicaciones: ¿cómo navegan estas células en entornos tan abarrotados y cómo podemos inferir de manera fiable su comportamiento a partir de datos de microscopía ruidosos? Al combinar “laberintos” de laboratorio diseñados con precisión con simulaciones por ordenador avanzadas y herramientas modernas de aprendizaje automático, los autores muestran una nueva manera de descifrar las reglas que guían el movimiento celular en entornos complejos.
Construir un pequeño laberinto para células inmunitarias
Para investigar cómo el entorno moldea el movimiento, los investigadores se centraron en las células dendríticas: centinelas inmunitarias que deben viajar desde tejidos periféricos hasta los ganglios linfáticos, guiadas por atrayentes químicos llamados quimiocinas. Construyeron un chip microfabricado: un “bosque de pilares” plano de postes regularmente espaciados hechos de caucho de silicona (PDMS), con huecos estrechos de 10 micrómetros que imitan los espacios reducidos de los tejidos reales. Un lado del chip se cargó con decenas de miles de células dendríticas; el lado opuesto contenía una fuente de la quimiocina CCL19, que crea un gradiente estable a través de los pilares. Mediante microscopía en lapso de tiempo, rastrearon los núcleos de células individuales cada 30 segundos mientras intentaban moverse hacia la fuente de quimiocina. 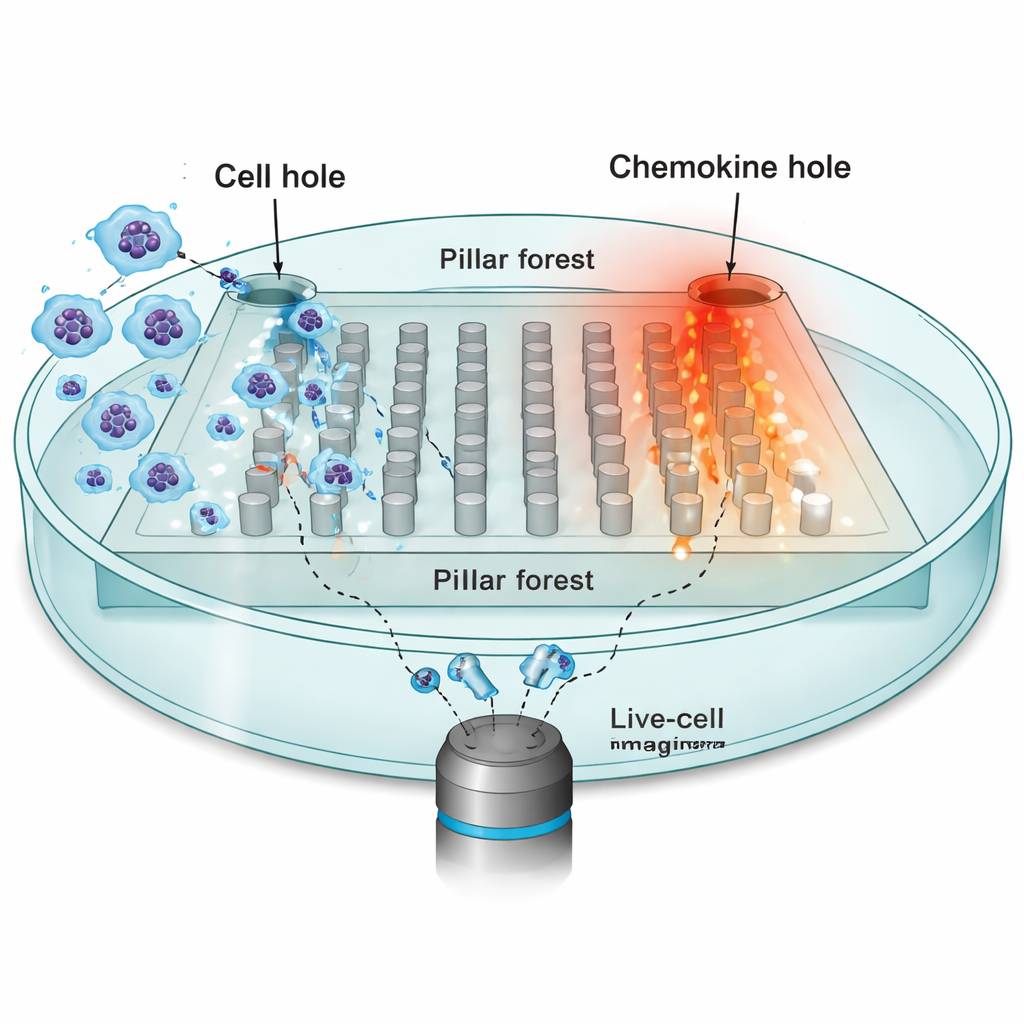
Convertir la biología en un experimento virtual
Para dar sentido a esta diversidad, el equipo construyó un modelo computacional detallado de la migración celular usando un marco conocido como modelo de Potts celular. En lugar de tratar a la célula como un simple punto, este enfoque representa cada célula como un parche extendido en una rejilla, lo que le permite cambiar de forma, comprimirse entre los pilares y responder a señales químicas. El modelo incluye cuatro ingredientes clave: cuánto tira la célula el gradiente de quimiocina (mdir), cuánto tiende a persistir en su dirección actual de movimiento (mrand), con qué frecuencia se reorienta (capturado por una tasa λ) y su tamaño efectivo (a). Al ajustar estos parámetros y ejecutar simulaciones, el modelo produce trayectorias sintéticas que pueden compararse directamente con los recorridos celulares registrados en el bosque de pilares.
Por qué las medidas escogidas a mano se quedan cortas
Tradicionalmente, los investigadores resumen estos datos de movimiento con un puñado de estadísticas familiares: cuánta distancia recorre una célula (desplazamiento), qué tan rápido se mueve (velocidad) y cómo cambia su dirección con el tiempo (ángulos de giro). Los autores emplearon primero estas medidas diseñadas manualmente dentro de una técnica llamada computación bayesiana aproximada (ABC), que busca conjuntos de parámetros que hagan que las trayectorias simuladas se parezcan a las experimentales. Encontraron que, si bien estos resúmenes capturan tendencias generales, pierden gran parte de la estructura fina en los datos. Como resultado, algunos parámetros del modelo, especialmente los que gobiernan la persistencia aleatoria y el momento de las reorientaciones, quedaron mal acotados o incluso sesgados. Además, ABC requirió cientos de miles de simulaciones y muchas horas de cómputo para alcanzar ajustes aceptables.
Dejar que las redes neuronales aprendan qué es relevante
Para superar estas limitaciones, el estudio recurrió a una familia más reciente de métodos llamada estimación de la posterior neuronal (NPE). Aquí, una red neuronal se entrena directamente con muchos pares de datos simulados y parámetros subyacentes. Una parte de la red aprende automáticamente su propio conjunto compacto de “características resumen” a partir de colecciones enteras de trayectorias celulares; otra parte aprende cómo esas características se mapean de vuelta a valores probables de los parámetros. Crucialmente, estas características aprendidas se optimizan explícitamente para la inferencia precisa de parámetros, no para la interpretabilidad humana. Luego, los autores reutilizaron los resúmenes aprendidos dentro de un marco ABC, creando una canalización híbrida que combina la robustez de ABC con la flexibilidad de las redes neuronales. 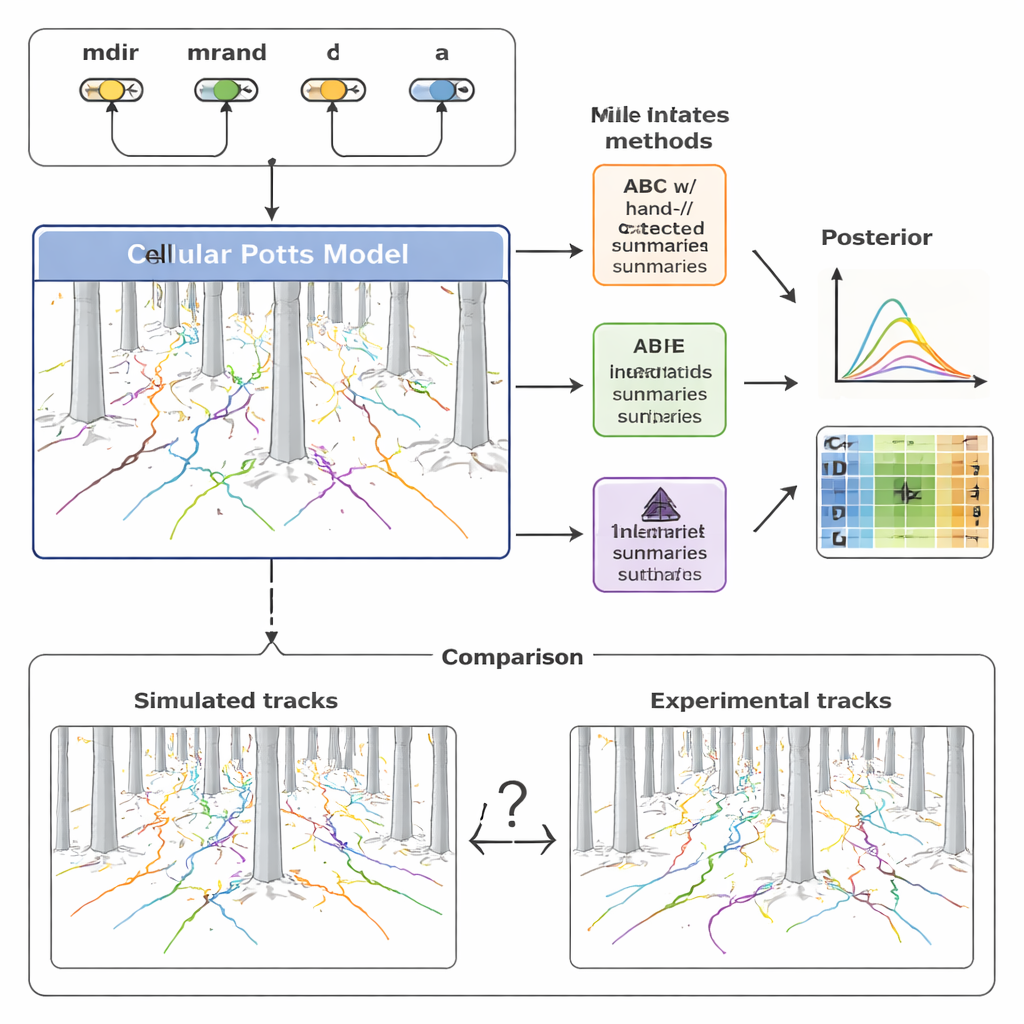
Lo que el nuevo enfoque revela sobre la navegación celular
Con este modelo calibrado, los investigadores exploraron cómo las señales de quimiocinas y los obstáculos físicos modelan conjuntamente la migración. El tamaño celular inferido sugirió que las células dendríticas efectivamente se encogen y deforman para caber por los huecos de 10 micrómetros, coherente con su flexibilidad conocida. Las simulaciones indicaron que el movimiento persistente aleatorio es un factor importante en la amplitud de dispersión de las células, incluso sin guía de quimiocina, y que el bosque de pilares puede atrapar células cuando señales direccionales fuertes y persistencia actúan conjuntamente. Sorprendentemente, el modelo predice que una señal de quimiocina que esté activa brevemente al principio puede, en algunos casos, ayudar a que más células lleguen al objetivo que una señal constante, porque la atracción prolongada puede mantener a las células dando vueltas dentro de los obstáculos en vez de escapar de ellos.
Por qué esto importa para la biología y el modelado
Para los no especialistas, el mensaje clave es doble. Primero, la migración de las células inmunitarias en tejidos no es solo seguir un rastro químico; surge de una interacción sutil entre las señales de guía, las propias tendencias de movimiento de las células y la disposición física de su entorno. Segundo, extraer estas reglas a partir de datos de imagen requiere dejar que el ordenador aprenda qué patrones en los datos son más informativos, en lugar de confiar exclusivamente en medidas simples diseñadas por humanos. Al integrar experimentos micro‑ingenierizados, simulaciones que resuelven la forma y una inferencia basada en redes neuronales, este trabajo proporciona un esquema potente para estudiar cómo células de muchos tipos se mueven por entornos complejos, con posibles aplicaciones que van desde entender la vigilancia inmunitaria hasta diseñar mejores terapias contra el cáncer.
Cita: Arruda, J., Alamoudi, E., Mueller, R. et al. Simulation-based inference of cell migration dynamics in complex spatial environments. npj Syst Biol Appl 12, 20 (2026). https://doi.org/10.1038/s41540-026-00648-9
Palabras clave: migración celular, células dendríticas, gradientes de quimiocinas, inferencia basada en simulación, bosques de pilares microfluídicos