Clear Sky Science · es
La N-acetiltransferasa B asociada al ribosoma coordina la proteostasis global y la autofagia en plantas creando Ac/N-degrones
Cómo las plantas mantienen el equilibrio de sus proteínas
Cada célula de una planta está llena de proteínas que deben construirse, repararse y eliminarse constantemente. Cuando este acto de equilibrio falla, el crecimiento se ralentiza y el estrés puede resultar mortal. Este estudio desvela cómo una pequeña etiqueta química colocada en el extremo inicial de muchas proteínas ayuda a las plantas a decidir qué proteínas reciclar rápidamente y con qué intensidad activar un proceso interno de limpieza llamado autofagia. Comprender este sistema de control revela cómo las plantas sobreviven largos periodos sin luz o nutrientes y podría, algún día, ayudarnos a obtener cultivos que resistan mejor condiciones adversas.
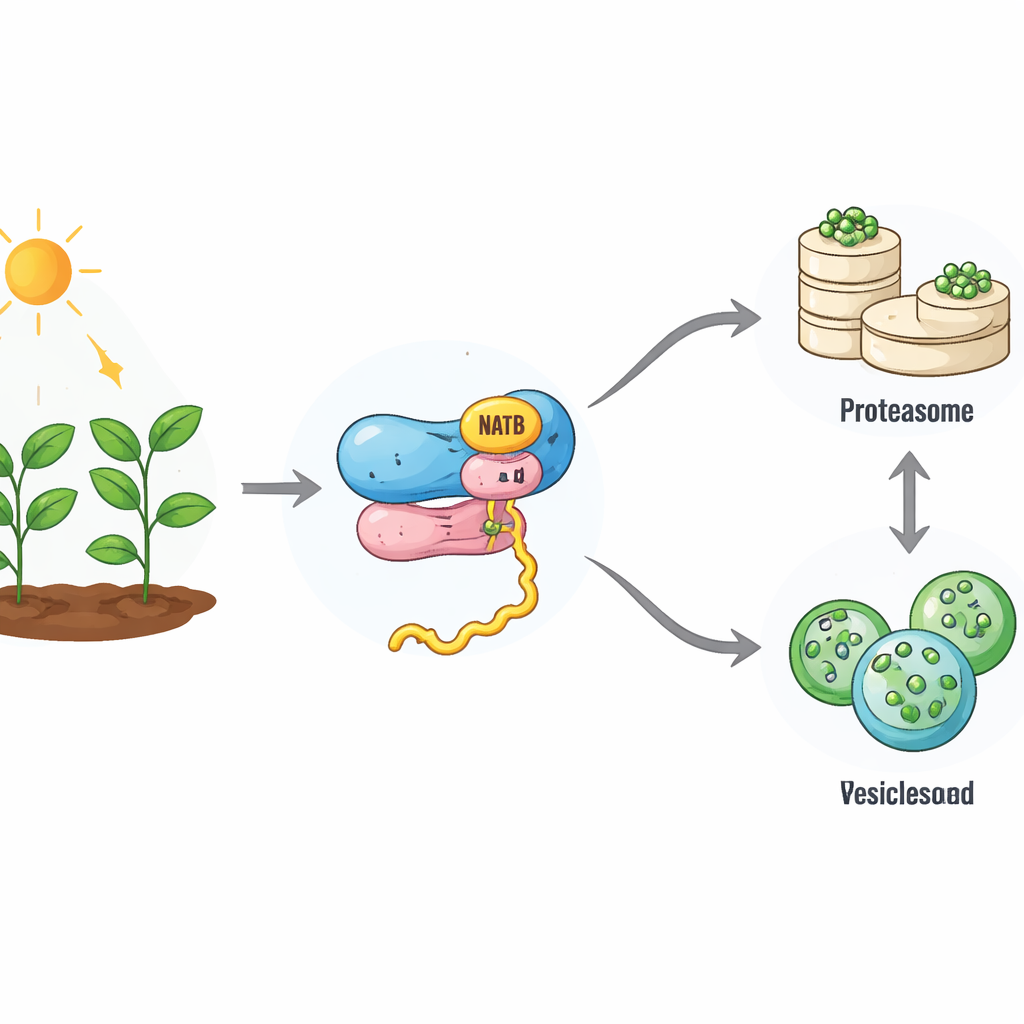
Una pequeña etiqueta con grandes consecuencias
Mientras se sintetizan nuevas proteínas en los ribosomas, pueden recibir un “tapón” químico en su extremo inicial. En las plantas, un complejo enzimático ligado al ribosoma llamado NatB añade este tapón a aproximadamente una quinta parte de todas las proteínas. Hasta ahora, los científicos no comprendían del todo qué implica este etiquetado tan extendido para el destino de esas proteínas. Empleando edición genética CRISPR para desactivar la parte catalítica de NatB en Arabidopsis, los autores crearon plantas que carecen en gran medida de esta modificación en los blancos habituales de NatB. Sorprendentemente, estas plantas eran enanas pero sobrevivían, a diferencia de los animales deficientes en NatB, lo que sugiere que las células vegetales pueden compensar en parte la pérdida. Aun así, muchas proteínas que normalmente llevan la etiqueta NatB quedaron solo parcialmente o nada modificadas, lo que ofrece una ventana para entender cómo funciona este sistema.
Ralentización del recambio proteico y un cambio en el sistema de reciclaje celular
Cuando el equipo midió la velocidad con la que se destruyen las proteínas, descubrió que las plantas deficientes en NatB presentan una maquinaria de reciclaje celular lenta. La vía principal de destrucción proteica, el sistema ubiquitina-proteasoma, funcionó con menos eficiencia: su actividad disminuyó y las proteínas dirigidas a esta ruta llevaban menos de las marcas habituales de “destrúyeme”. Al mismo tiempo, la tasa global de producción de proteínas nuevas también se redujo. Estudios detallados de proteínas mostraron que muchas proteínas dependientes de NatB eran ahora más estables y se acumulaban en la célula, lo que indica que la etiqueta NatB normalmente ayuda a convertir algunas proteínas en componentes de vida corta. Sin embargo, no todos los blancos de NatB se comportaron igual, lo que apunta a un efecto más selectivo moldeado por la secuencia y el contexto de cada proteína.
La autofagia entra en acción como plan de respaldo
El estudio reveló que, a medida que la ruta del proteasoma se ralentiza, otra vía de reciclaje se activa. Este segundo sistema, la autofagia, encierra porciones de la célula en burbujas de membrana que se entregan a un compartimento donde los contenidos se descomponen y se reutilizan. Las plantas deficientes en NatB mostraron niveles más altos de proteínas centrales de la autofagia y un flujo mayor de material a través de esta vía, especialmente durante la oscuridad cuando la energía escasea. Las plantas sin NatB sobrevivieron mucho más tiempo en oscuridad prolongada o bajo privación de nitrógeno y azufre que las plantas normales, pero esta ventaja desapareció cuando se desactivaron genes de la autofagia. Esto indica que la autofagia potenciada ayuda a compensar el debilitamiento del sistema del proteasoma, evitando que la economía proteica celular colapse.
Un sensor clave de energía en el centro del conmutador
Para entender qué inclina el equilibrio del uso del proteasoma hacia la autofagia, los autores se centraron en un complejo sensor de energía llamado SnRK1. Dos subunidades estrechamente relacionadas, KIN10 y KIN11, comienzan con secuencias que las hacen probables clientas de NatB. Los investigadores demostraron que NatB puede etiquetar directamente estas proteínas en ensayos in vitro. En plantas carentes de NatB, solo KIN11 se acumuló de forma marcada, y su forma activa, fosforilada, fue más abundante. El seguimiento cuidadoso de la degradación proteica reveló que cuando KIN11 lleva la etiqueta NatB, es más fácilmente marcada para destrucción por el proteasoma, mientras que KIN11 no etiquetada persiste. Las plantas que carecían tanto de NatB como de KIN11 perdieron su resistencia adicional al estrés por oscuridad, mientras que plantas modificadas para sobreproducir solo KIN11 se volvieron más tolerantes a la oscuridad prolongada. Estos hallazgos sitúan a KIN11 como un mensajero crucial que, cuando se estabiliza, impulsa a la célula a favorecer la autofagia y la conservación de energía.
Qué significa esto para la supervivencia de las plantas
En pocas palabras, NatB escribe una marca removible de “usar y desechar” en proteínas específicas, incluido el sensor energético KIN11. Cuando NatB está activo, KIN11 se mantiene bajo control, el recambio proteico a través del proteasoma es rápido y las plantas crecen con vigor en condiciones favorables. Cuando la actividad de NatB se pierde o reduce, KIN11 se salva de la destrucción rápida, la autofagia se incrementa y las plantas entran en un modo de supervivencia que conserva recursos y afronta mejor largos periodos de oscuridad o mala nutrición. Este trabajo revela a NatB como un coordinador central entre dos grandes sistemas de reciclaje en las células vegetales y explica cómo una etiqueta química sutil en el inicio de una proteína puede inclinar la balanza entre crecimiento y resistencia.
Cita: Gong, X., Pożoga, M., Boyer, JB. et al. The ribosome-associated N-terminal acetyltransferase B coordinates global proteostasis and autophagy in plants by creating Ac/N-degrons. Nat Commun 17, 3116 (2026). https://doi.org/10.1038/s41467-026-71208-2
Palabras clave: control de calidad de proteínas, autofagia, tolerancia al estrés en plantas, modificación postraduccional, degradación de proteínas