Clear Sky Science · es
SMART: agregación multiómica espacial mediante redes neuronales de grafos y aprendizaje métrico
Ver los tejidos como mapas de vecindario
Nuestros cuerpos están formados por bulliciosos vecindarios celulares, donde genes, proteínas y la organización del ADN funcionan juntos en ubicaciones precisas. Nuevos microscopios y herramientas de secuenciación pueden ahora leer muchas de estas capas moleculares directamente dentro de cortes finos de tejido, pero convertir este torrente de datos espaciales y multilayer en imágenes claras de cómo están organizados los órganos es un enorme desafío computacional. Este estudio presenta SMART, un método informático que ayuda a los científicos a fusionar estas señales complejas en mapas detallados de dónde viven distintas comunidades celulares y cómo se disponen.
Por qué es difícil mapear los vecindarios celulares
Las tecnologías modernas de «multi-ómicas espaciales» pueden medir varios tipos de información molecular a la vez —como ARN, proteínas de la superficie celular y el grado de accesibilidad de la cromatina— conservando la posición exacta de cada medición en un corte de tejido. Cada tipo, u “ómica”, ofrece una vista distinta del comportamiento celular, pero son ruidosas, de alta dimensionalidad y no se alinean de forma natural entre sí. Además, las células del mismo tipo no siempre están agrupadas; pueden aparecer como islas dispersas a lo largo de un órgano. Las herramientas de software existentes a menudo ignoran el diseño espacial, simplifican en exceso las relaciones entre omicas o tienen dificultades para escalar a los conjuntos de datos muy grandes que los nuevos instrumentos pueden generar.
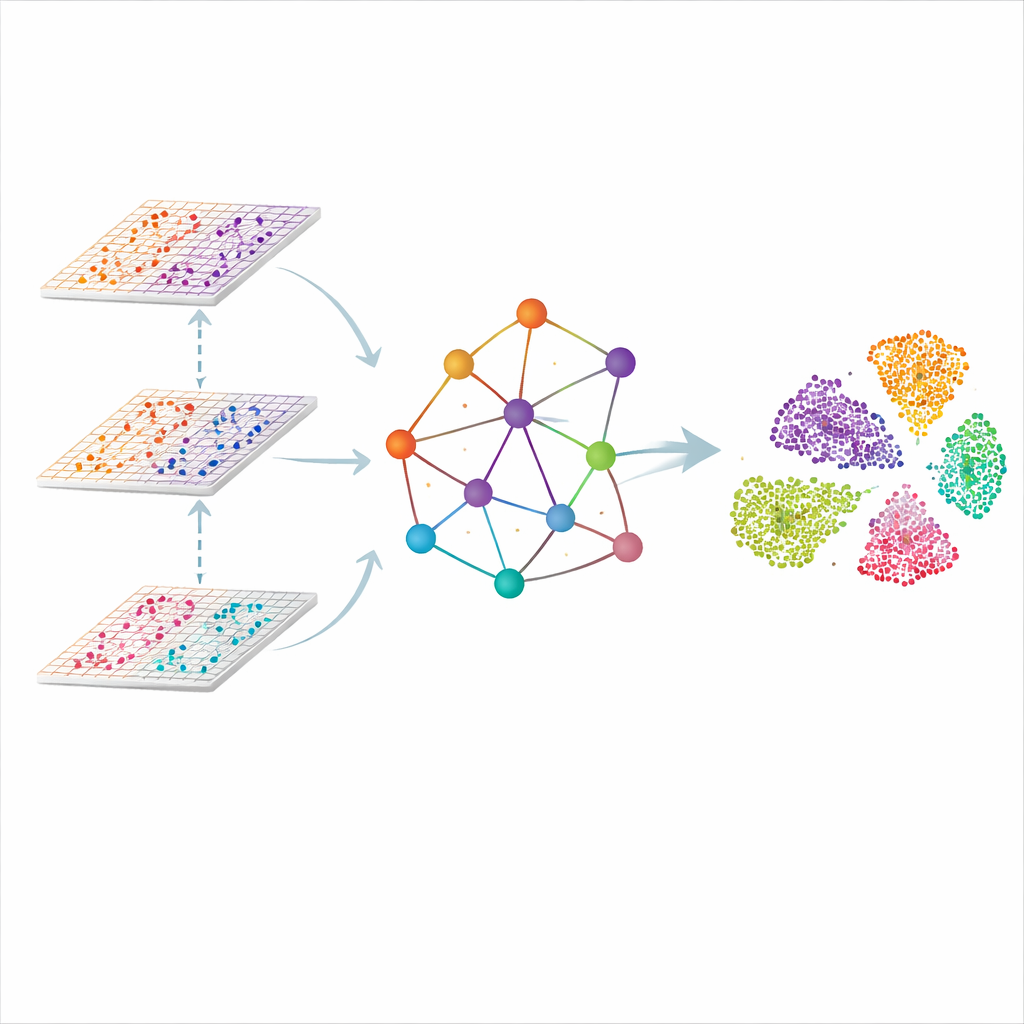
Un grafo del tejido, no solo una lista de células
SMART aborda el problema tratando cada punto de medición en el tejido como un vértice en una red. Los puntos próximos se enlazan para formar un grafo espacial, y las lecturas moleculares de cada omica se comprimen primero en un conjunto más pequeño de características coordinadas que capturan patrones generales en lugar de genes individuales. Un tipo de red neuronal diseñado para grafos pasa después la información a lo largo de los enlaces, permitiendo que cada punto «escuche» a sus vecinos mientras mantiene el rastro de cómo contribuye cada omica. El resultado es una representación compartida y de baja dimensión en la que regiones similares del tejido —como capas distintas del cerebro o zonas de un ganglio linfático— se agrupan de forma natural.
Enseñar al modelo qué debe considerarse similar
Seguir simplemente los vecinos físicos no es suficiente, porque las células del mismo tipo pueden estar muy separadas. SMART añade un segundo ingrediente tomado de los sistemas de reconocimiento facial: aprendizaje métrico con tripletas. Para cada punto, el método encuentra automáticamente otro punto con patrones moleculares muy parecidos (un «positivo») y otro claramente distinto (un «negativo»). A continuación ajusta la representación interna para que los positivos se acerquen y los negativos se alejen, incluso si están distantes en el corte de tejido. Esta dinámica se ejecuta junto a un paso de reconstrucción que fuerza a SMART a preservar los detalles clave de cada capa omica, equilibrando la continuidad espacial con la especificidad molecular.
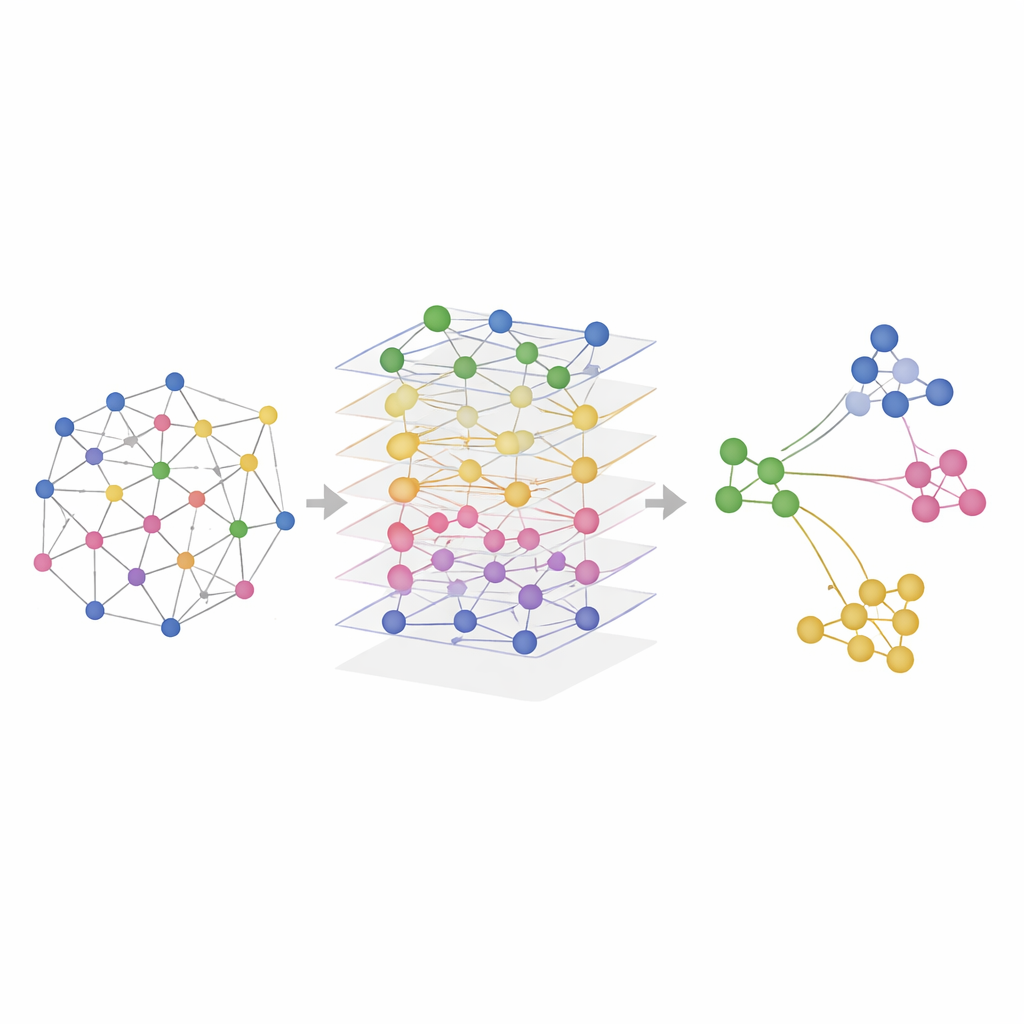
Poner SMART a prueba en tejidos reales
Los investigadores probaron SMART tanto en datos simulados como en experimentos reales que midieron combinaciones de ARN, proteínas y accesibilidad de la cromatina en cerebros de ratón, bazo de ratón, y ganglios linfáticos y amígdalas humanas. En simulaciones controladas donde se conocían las regiones espaciales verdaderas, SMART recuperó con mayor precisión los patrones de referencia y mantuvo las relaciones presentes en cada capa omica. En conjuntos de datos reales, SMART identificó de forma consistente estructuras anatómicas finas —como regiones cerebrales específicas o zonas de células inmunitarias en órganos linfoides— con mayor nitidez que métodos competidores, al tiempo que mantenía bajas las demandas computacionales. Una versión relacionada, llamada SMART-MS, extiende las mismas ideas a través de múltiples secciones tisulares, alineando cortes del mismo órgano y corrigiendo diferencias técnicas entre experimentos.
Mapas rápidos para la próxima ola de biología espacial
En términos sencillos, SMART es un motor de cartografía para la próxima generación de atlas moleculares. Al combinar un modelado de estilo de red del diseño tisular con un sentido incorporado de lo que debe contarse como «similar», puede convertir vastas y desordenadas colecciones de mediciones multi-ómicas espaciales en mapas coherentes de vecindarios de los órganos. Esto permite a los investigadores localizar con más facilidad dónde residen tipos celulares y microambientes particulares, cómo cambian durante el desarrollo o la enfermedad y cómo encajan las nuevas tecnologías experimentales. A medida que los datos espaciales continúen creciendo en tamaño y complejidad, herramientas como SMART y SMART-MS serán clave para transformar mediciones en bruto en conocimiento biológico.
Cita: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Palabras clave: multi-ómicas espaciales, redes neuronales de grafos, microambiente tisular, integración de datos, biología unicelular