Clear Sky Science · es
Perfilado mecanístico basado en solubilidad de terapias farmacológicas combinadas
Por qué importa combinar medicamentos
La atención oncológica moderna suele basarse en combinaciones de fármacos, pero determinar qué medicamentos funcionan mejor juntos sigue siendo en gran medida ensayo y error. Este estudio se centra en la leucemia mieloide aguda, un cáncer sanguíneo agresivo que con frecuencia reaparece tras el tratamiento. Los investigadores presentan una nueva forma de observar, de manera masiva, cómo responden las proteínas de las células cuando se administran dos fármacos simultáneamente. Su enfoque ayuda a explicar por qué ciertas combinaciones son a la vez más eficaces y menos tóxicas, y ofrece una hoja de ruta para diseñar terapias combinadas más inteligentes y precisas contra cánceres difíciles.
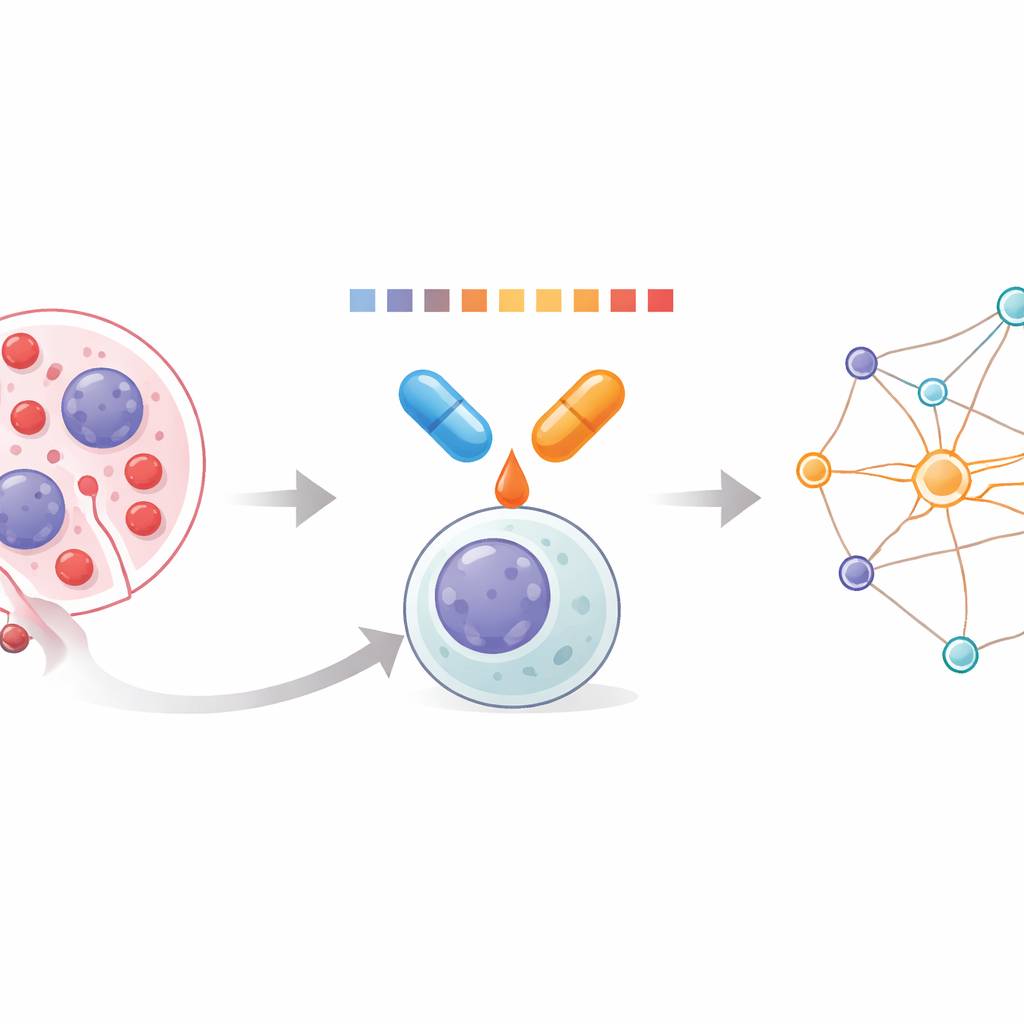
Mirando dentro de las células leucémicas
La leucemia mieloide aguda (LMA) surge cuando células sanguíneas blancas inmaduras en la médula ósea crecen de forma descontrolada y desplazan la formación sana de sangre. Debido a que la LMA está impulsada por numerosos cambios genéticos distintos, los fármacos únicos rara vez funcionan durante mucho tiempo. Las combinaciones pueden funcionar mejor, pero los médicos han tenido herramientas limitadas para ver cómo actúan los pares de fármacos a nivel de miles de proteínas dentro de la célula. El equipo detrás de este trabajo se propuso medir esos efectos combinados directamente, usando un método que detecta qué tan fácilmente las proteínas se disuelven o se agregan cuando se calientan. Los cambios en la solubilidad revelan qué proteínas se estabilizan o desestabilizan con el tratamiento, ofreciendo una ventana al verdadero impacto de los fármacos.
Una nueva forma de perfilar pares de fármacos
Los investigadores desarrollaron un flujo de trabajo que llaman Análisis Integral de Alteración de Solubilidad/Estabilidad del Proteoma Combinatorio, o CoPISA. Células, o sus extractos proteicos, se exponen al fármaco A, al fármaco B, a la combinación de A y B, o a ningún fármaco. Cada muestra se calienta brevemente a través de una serie de temperaturas, y las proteínas aún disueltas se capturan y cuantifican mediante espectrometría de masas. En lugar de ajustar curvas complejas proteína por proteína, el método usa el área total bajo el perfil de fusión de cada proteína como medida compacta de su comportamiento. Comparar estas áreas entre tratamientos muestra qué proteínas se vuelven más o menos solubles en cada condición, revelando patrones únicos de fármacos individuales frente a combinaciones.
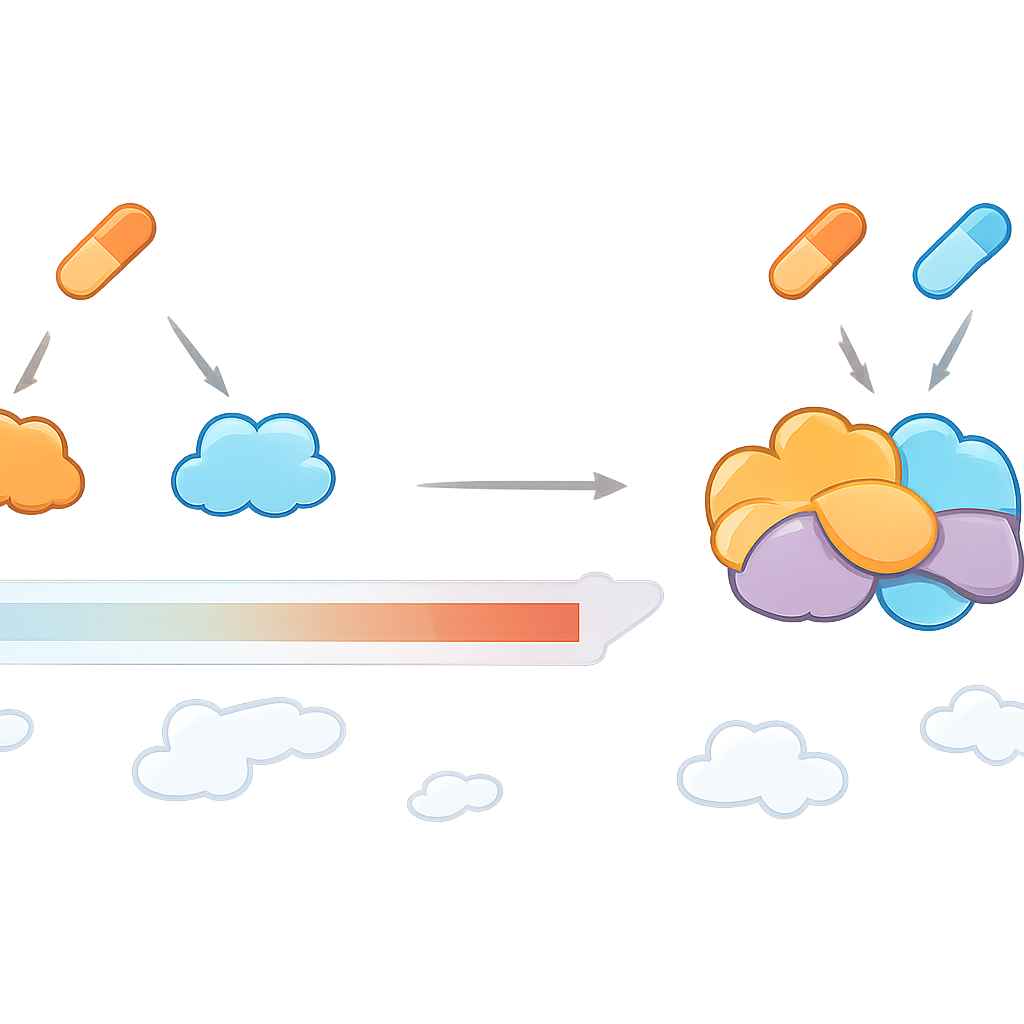
Encontrar objetivos que solo aparecen con ambos fármacos
CoPISA se aplicó a dos pares de fármacos para LMA cuidadosamente seleccionados: LY3009120 con sapanisertib (denominado LS), y ruxolitinib con ulixertinib (RU). Estos pares ya habían mostrado una fuerte actividad y toxicidad relativamente baja en muestras de pacientes, líneas celulares y modelos en pez cebra. CoPISA descubrió no solo proteínas afectadas por cada fármaco por separado, sino también un conjunto distinto de proteínas cuya solubilidad cambiaba solo cuando estaban presentes ambos fármacos. Los autores describen esto como “diana de conjunción”, similar a una puerta lógica AND: la proteína responde únicamente si ambas entradas (fármacos) están activas. Para LS, estos efectos exclusivos de la combinación convergieron en procesos como el empaquetamiento del ADN, pequeñas etiquetas proteicas llamadas SUMO que controlan la estabilidad del genoma, y cómo las células leucémicas se adhieren a su tejido circundante. Para RU, los objetivos únicos apuntaron a puntos de control de daño en el ADN debilitados, producción de energía mitocondrial perjudicada y un procesamiento del ARN alterado.
Mapear los puntos débiles del cáncer
Al superponer sus datos de solubilidad sobre grandes mapas de genes y vías relacionados con la LMA, los investigadores pudieron ver cómo cada tratamiento remodelaba la red interna del cáncer. Muchos genes bien conocidos de la LMA —como DNMT3A, NPM1 y TP53— se vieron afectados de maneras que aparecían solo con la terapia combinada, reforzando la idea de que los fármacos pareados pueden exponer vulnerabilidades invisibles para agentes individuales. El equipo también examinó modificaciones químicas en las proteínas, como la acetilación, metilación y fosforilación, que actúan como interruptores moleculares. Encontraron que ciertas formas modificadas de proteínas clave, incluyendo NPM1 y el factor de reparación del ADN BLM, eran impactadas específicamente por las combinaciones, lo que sugiere que la alteración de la localización y la señalización proteica contribuye al efecto potenciado.
Qué significa esto para tratamientos futuros
En conjunto, el estudio muestra que las combinaciones de fármacos pueden crear su propio paisaje único de objetivos proteicos, en lugar de limitarse a sumar los efectos de cada fármaco. CoPISA proporciona una manera práctica de cartografiar ese paisaje, destacando proteínas y vías que solo se vuelven vulnerables cuando dos medicamentos actúan en conjunto. Para los pacientes, esto podría traducirse en terapias combinadas elegidas no solo porque reducen tumores en un ensayo in vitro, sino porque atacan los puntos débiles más profundos del cáncer mientras limitan la toxicidad innecesaria. Aunque se demuestra aquí en LMA, el enfoque es de amplia aplicabilidad y puede ayudar a guiar el diseño racional de tratamientos combinados en muchas enfermedades complejas.
Cita: Gholizadeh, E., Zangene, E., Vadadokhau, U. et al. Solubility based mechanistic profiling of combinatorial drug therapy. Nat Commun 17, 2744 (2026). https://doi.org/10.1038/s41467-026-70394-3
Palabras clave: leucemia mieloide aguda, combinaciones de fármacos, proteómica, solubilidad de proteínas, terapia dirigida