Clear Sky Science · es
Identificación de elementos cis-reguladores aporta información sobre la regulación génica específica de tejidos en el genoma ovino
Por qué el genoma de la oveja importa en la vida cotidiana
Las ovejas alimentan a millones de personas y sostienen economías rurales, pero todavía sabemos sorprendentemente poco sobre cómo se activan y desactivan sus genes en distintas partes del cuerpo. Este estudio crea un mapa detallado de los interruptores de control que ajustan la actividad génica en 24 tejidos de una única oveja, desde el cerebro y el pulmón hasta el músculo y la ubre. Al cartografiar estos interruptores ocultos, el trabajo sienta las bases para animales más sanos, mejores rasgos de producción como la grasa de la leche y una comprensión más profunda de cómo los cuerpos mamíferos, incluido el nuestro, regulan los genes.
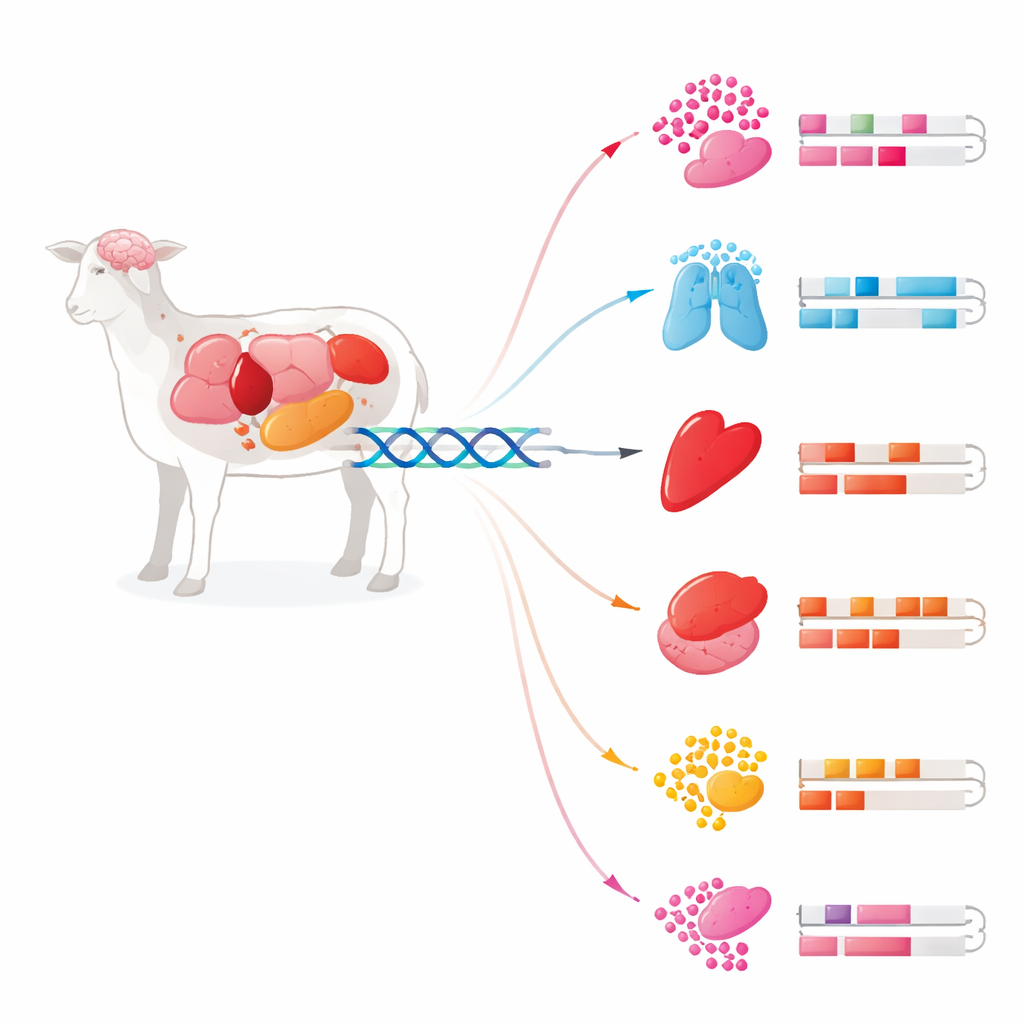
Interruptores ocultos en el ADN
Nuestro ADN no solo contiene genes; también alberga extensos tramos de código regulador que actúan como atenuadores, decidiendo cuándo y dónde se activan los genes. Dos tipos clave de elementos son los promotores, junto a los genes, y los enhancers, que pueden estar lejos pero aún así controlarlos. Los investigadores combinaron seis métodos de vanguardia que leen distintos aspectos de la actividad del genoma: marcas proteicas en las proteínas que empaquetan el ADN, cromatina accesible, inicios de transcripción, metilación del ADN y salida de ARN. Usando estas pistas superpuestas, identificaron más de 270.000 enhancers y casi 26.000 promotores en 24 tejidos de la misma oveja Rambouillet utilizada para construir el genoma de referencia actual. Este mapa unificado muestra dónde está cableado el genoma para la regulación, no solo qué genes existen.
Diferentes tejidos, distinta lógica de control
Aunque casi todas las células contienen el mismo ADN, los tejidos se comportan de manera muy diferente porque usan conjuntos distintos de enhancers. El estudio halló que los promotores son relativamente estables: muchos se comparten entre tejidos y sus patrones están conservados entre especies. Los enhancers, en contraste, son muy variables y mucho más específicos por tejido. Los tejidos cerebrales, como el cerebelo y la corteza cerebral, destacaron por paisajes de enhancers especialmente ricos y diversos. Algunos genes neuronales tenían más de diez enhancers cada uno, lo que sugiere que funciones cruciales como el crecimiento nervioso y la comunicación están gestionadas por un control regulador fuertemente estratificado en lugar de un interruptor único de encendido/apagado.
Acercándonos a la especialización del cerebro y de los órganos
Al correlacionar la actividad de enhancers con los niveles de expresión génica, los autores vincularon casi 9.000 enhancers con alrededor de 4.300 genes y descubrieron muchas parejas control específicas de tejidos. En el cerebelo, por ejemplo, una región enhancers única parece impulsar un factor cerebral llamado BDNF de forma distinta a la corteza cercana, ayudando a explicar diferencias sutiles entre partes del cerebro que comparten el mismo gen. Patrónes similares surgieron en corazón, intestino y glándulas suprarrenales: los órganos pueden usar conjuntos de genes superpuestos, pero enhancers distintos en cada tejido afinan cuándo y con qué intensidad se emplean esos genes. El análisis de la metilación del ADN mostró que las marcas químicas en los enhancers generalmente atenúan la actividad génica, reforzando su papel como reguladores sensibles más que como tramos pasivos de ADN.
Qué hace diferentes a las ovejas y a otros mamíferos
Para ver cómo se comparan las ovejas con otros mamíferos, el equipo cruzó su mapa con datos regulatorios de humanos, ratones, cerdos y vacas. Los promotores resultaron altamente conservados, pero los enhancers variaron mucho más entre especies, lo que refleja la idea de que la evolución reconfigura el control génico más que cambia los propios genes. Los autores identificaron conjuntos de pares enhancer–promotor presentes solo en rumiantes como ovejas y vacas, enriquecidos en procesos como la descomposición de azúcares en el rumen y el manejo de ácidos grasos de cadena larga. Esto sugiere que los sistemas digestivos y el metabolismo especializados de estos animales están impulsados en parte por cableados regulatorios únicos, más que por genes exclusivos.
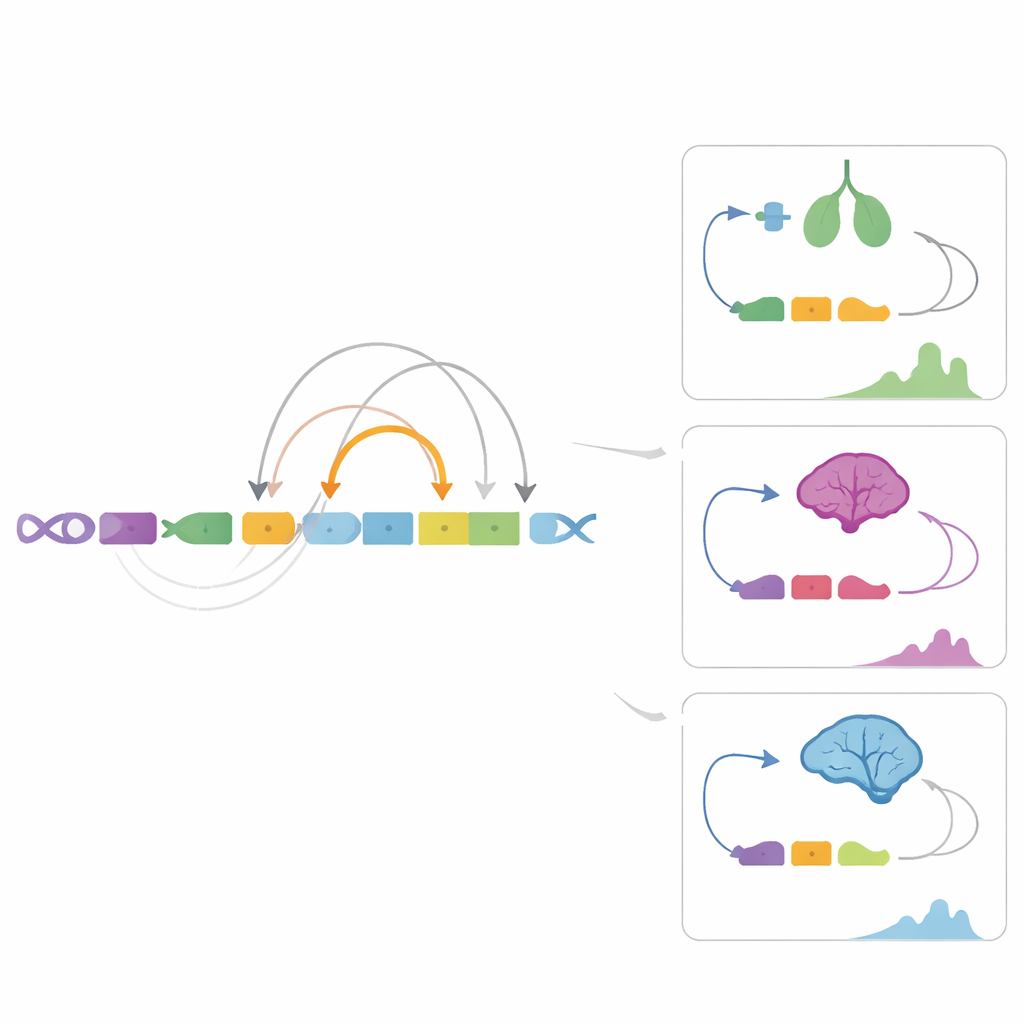
Conexiones con rasgos que interesan a los ganaderos
Dado que muchos rasgos de importancia económica dependen de cambios sutiles en la regulación génica, el equipo superpuso millones de variantes genéticas y regiones asociadas a rasgos conocidos sobre su mapa regulatorio. Descubrieron variantes dentro de enhancers que probablemente influyen en el rendimiento de grasa de la leche al alterar el control de un gen implicado en el metabolismo del cobre y de las grasas, COMMD1. También hallaron variantes asociadas al peso al nacer dentro de un enhancer específico del cerebelo que se predice regula el gen XKR4, ofreciendo una vía plausible desde el cambio en el ADN hasta rasgos de crecimiento. Estos ejemplos muestran cómo los mapas de enhancers pueden convertir señales anónimas de estudios de asociación del genoma en hipótesis biológicas concretas sobre cómo surgen los rasgos.
Qué significa esto para el futuro
Para el público general, el mensaje principal es que este estudio transforma el genoma de la oveja de una lista estática de piezas en un diagrama de cableado, mostrando cómo y dónde se controlan los genes en tejidos reales. Al catalogar cientos de miles de interruptores regulatorios, aclarar su actividad en distintos órganos y vincularlos con rasgos y diferencias entre especies, el trabajo ofrece una base potente para criar animales más sanos y productivos y para entender cómo emergen los rasgos complejos a partir de la regulación génica. Mapas similares en otras especies, incluidos los humanos, profundizarán nuestra comprensión de la salud, la enfermedad y la evolución al centrarse en cómo se gestionan los genes, no solo en qué genes están presentes.
Cita: Xie, S., Davenport, K.M., Salavati, M. et al. Identification of cis-regulatory elements provides insights into tissue-specific gene regulation in the sheep genome. Nat Commun 17, 2413 (2026). https://doi.org/10.1038/s41467-026-70382-7
Palabras clave: regulación génica específica de tejidos, genómica ovina, enhancers y promotores, genómica funcional en ganado, evolución de los rumiantes