Clear Sky Science · es
La proteómica subcelular revela un plano para la integración de endosimbiontes en el trypanosomatido Angomonas deanei
Socios ocultos dentro de la vida unicelular
Muchos organismos unicelulares no están verdaderamente solos. Algunos albergan bacterias que viven en su interior como inquilinos permanentes, intercambiando alimentos y servicios en relaciones que recuerdan el origen de nuestras propias mitocondrias. Este estudio explora una de esas asociaciones en Angomonas deanei, un parásito microscópico de insectos, para revelar cómo una bacteria que fue libre se ha entretejido profundamente en el funcionamiento interno de la célula anfitriona.
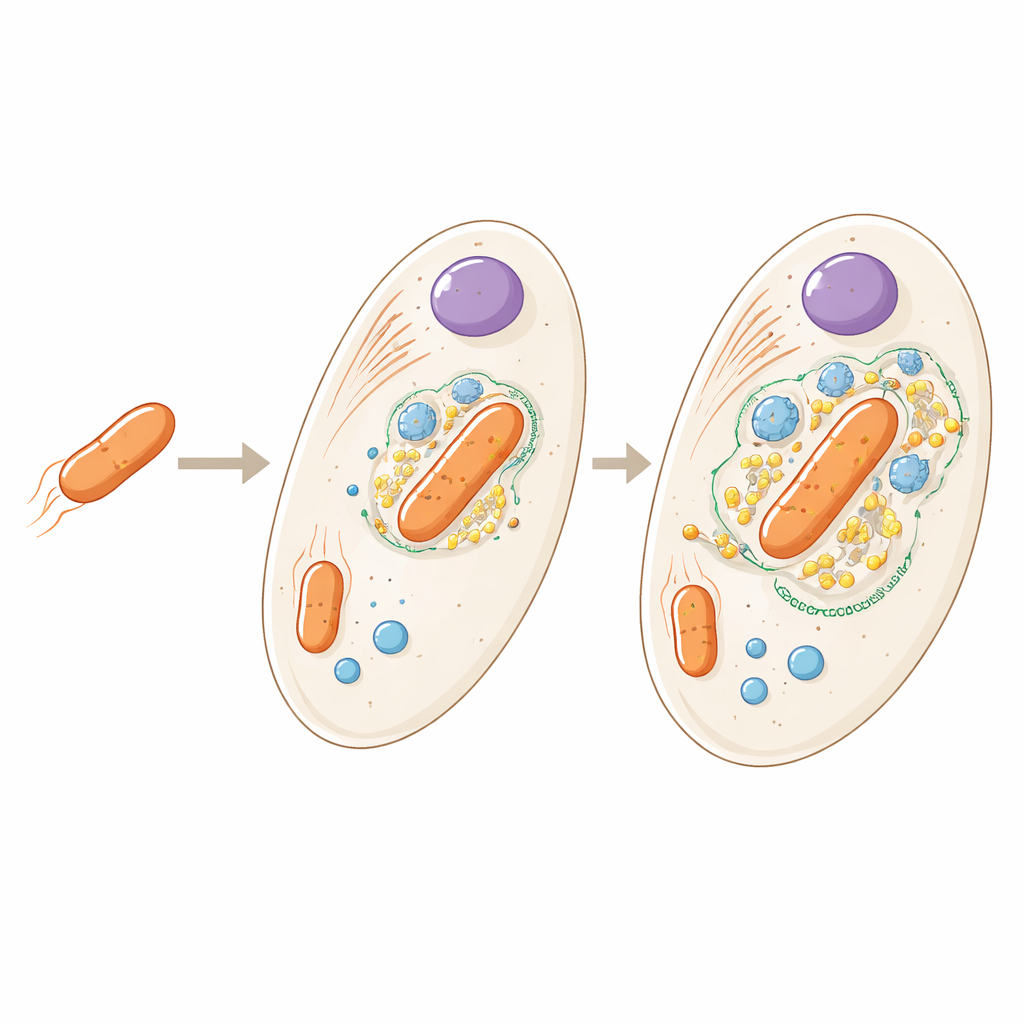
De huésped a parte integrada
La bacteria que vive dentro de Angomonas deanei es pariente distante de microbios del suelo de vida libre, pero aquí existe como una única copia por célula huésped y ya no puede sobrevivir por sí sola. Trabajos anteriores mostraron que el huésped produce proteínas especiales que viajan hacia la bacteria e incluso ayudan a controlar cuándo se divide. El nuevo estudio plantea una pregunta más amplia: si observamos toda la célula, ¿dónde se localizan exactamente todas las proteínas del huésped y de la bacteria, y qué nos dice eso sobre el grado de integración entre ambos socios?
Cartografiando la ciudad interior de la célula
Para responder, los investigadores lisaron grandes cantidades de células con mucha suavidad para que las estructuras internas quedaran mayormente intactas. Luego separaron esos fragmentos haciéndolos girar a distintas velocidades e identificaron miles de proteínas en cada fracción mediante espectrometría de masas de alta resolución. Al comparar cómo las proteínas se agrupaban a lo largo de las fracciones y contrastar los datos con marcadores conocidos y microscopía fluorescente, crearon una detallada "guía de direcciones" para la célula, asignando casi 3.000 proteínas a 21 regiones distintas como el núcleo, la mitocondria, cuerpos de almacenamiento especializados y el propio endosimbionte bacteriano.
Herramientas del huésped dirigidas a la bacteria residente
Dentro de este atlas, el equipo descubrió un conjunto de proteínas producidas por el huésped que viajaban de forma consistente con el endosimbionte, ampliando la colección conocida de las llamadas proteínas dirigidas al endosimbionte. Un ejemplo recién confirmado, denominado ETP10, recubre la bacteria de manera similar a otra proteína descrita antes, lo que sugiere un andamiaje de factores del huésped envuelto alrededor del socio microbiano. Otro pequeño grupo de proteínas compartía un comportamiento físico inusual con una proteína tipo dinamina ya conocida por estrangular la bacteria durante su división. En conjunto, estos hallazgos apuntan a una maquinaria especializada construída por el huésped dedicada a posicionar, moldear y reproducir el endosimbionte dentro de la célula.
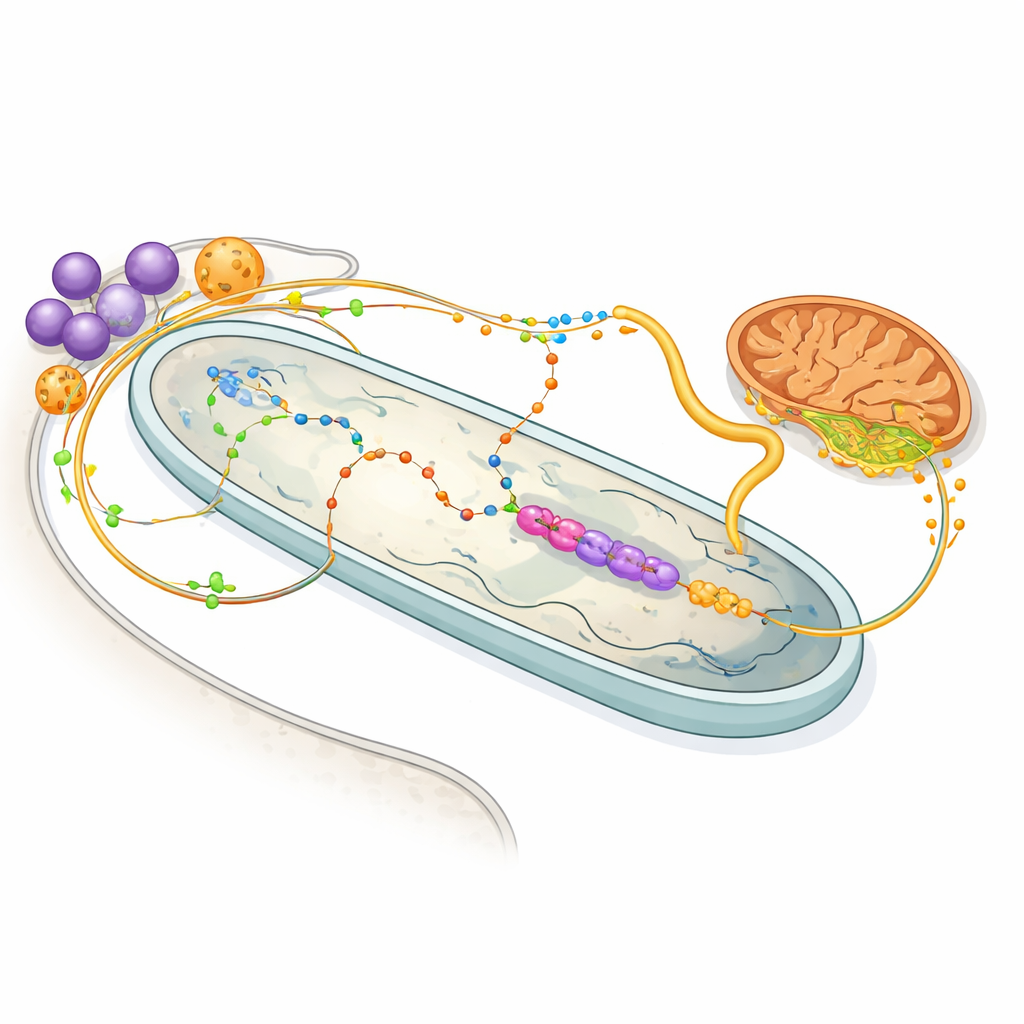
Compartir energía y rutas químicas de intercambio
El mapa de proteínas también ilumina el bullicioso intercambio de moléculas entre huésped y bacteria. Enzimas de las glicosomas del huésped —orgánulos encargados del metabolismo de azúcares y aminoácidos— parecen ajustadas para alimentar a la bacteria con el aminoácido prolina y con 2‑oxoglutarato, ambos compuestos valiosos como fuentes de energía. Dentro de la bacteria, un conjunto simplificado de enzimas usa 2‑oxoglutarato para generar NADH, que impulsa una cadena respiratoria mínima, y luego entrega succinato de vuelta a la mitocondria del huésped. Otras vías muestran que la bacteria realiza la mayoría de los pasos en la síntesis de hemo, un pigmento vital necesario por el huésped, mientras también aporta bloques de construcción cruciales para nucleótidos. En efecto, cada socio ha delegado tareas metabólicas específicas en el otro, creando un sistema compartido e interdependiente.
Nuevas vías de comunicación dentro de la célula
Más allá del metabolismo, el estudio revela enlaces físicos y probablemente de señalización entre el endosimbionte y otros orgánulos. Un grupo distinto de proteínas del huésped forma lo que los autores denominan un clúster de "sitio de contacto", enriquecido en componentes de la envoltura nuclear y del retículo endoplásmico que co-sedimentan físicamente con la bacteria. Dos tipos de orgánulos de almacenamiento —glicosomas y acidocalciscosomas— aparecen en dos poblaciones: algunos permanecen libres en el citoplasma, mientras que otros viajan de forma consistente con la bacteria. La microscopía confirma que subgrupos de estos orgánulos se aposentan estrechamente contra el endosimbionte. Los acidocalciscosomas son reservorios conocidos de calcio y fosfato, por lo que su proximidad sugiere una ruta bidireccional de señalización y tráfico iónico que conecta la bacteria, estos depósitos y el retículo endoplásmico cercano.
Un plano de cómo la vida se fusiona dentro de la vida
En conjunto, este trabajo proporciona un rico plano a escala celular de cómo una bacteria puede volverse funcionalmente fusionada con su huésped sin haberse transformado aún en un orgánulo completo como las mitocondrias. Angomonas deanei depende de su endosimbionte para nutrientes clave, mientras que la bacteria, a su vez, depende de proteínas y moléculas ricas en energía producidas por el huésped y está anclada a orgánulos del huésped para comunicación y control. Para el público general, la lección es que la evolución puede cablear gradualmente la cooperación entre formas de vida muy diferentes, paso a paso, hasta que separarlas se vuelve imposible. Este sistema ofrece una instantánea en vivo de ese proceso en acción, ayudando a los científicos a comprender mejor cómo las células complejas como la nuestra emergieron una vez de comienzos más simples.
Cita: Hammond, M., Chmelová, Ľ., van Geelen-Kuenzel, N.A. et al. Subcellular proteomics reveals a blueprint for endosymbiont integration in trypanosomatid Angomonas deanei. Nat Commun 17, 2241 (2026). https://doi.org/10.1038/s41467-026-70084-0
Palabras clave: endosimbiosis, metabolismo celular, evolución de orgánulos, biología de protistas, interacciones huésped-microbio