Clear Sky Science · es
La distribución dinámica de amplificaciones genéticas en tándem en una población heterorresistente de Escherichia coli revelada por secuenciación de lecturas largas ultra-profundas
Bolsillos ocultos de supervivencia
Cuando los médicos tratan infecciones bacterianas con antibióticos, asumen que todo el conjunto de microbios responderá de la misma manera. Pero a veces, una fracción muy pequeña de la población resiste en silencio, sobrevive al tratamiento y allana el camino para el fracaso o la recaída. Este estudio desentraña cómo surgen esos supervivientes raros y cómo cambian con el tiempo en Escherichia coli, e introduce una forma potente de observar estos cambios genéticos desarrollarse célula por célula.
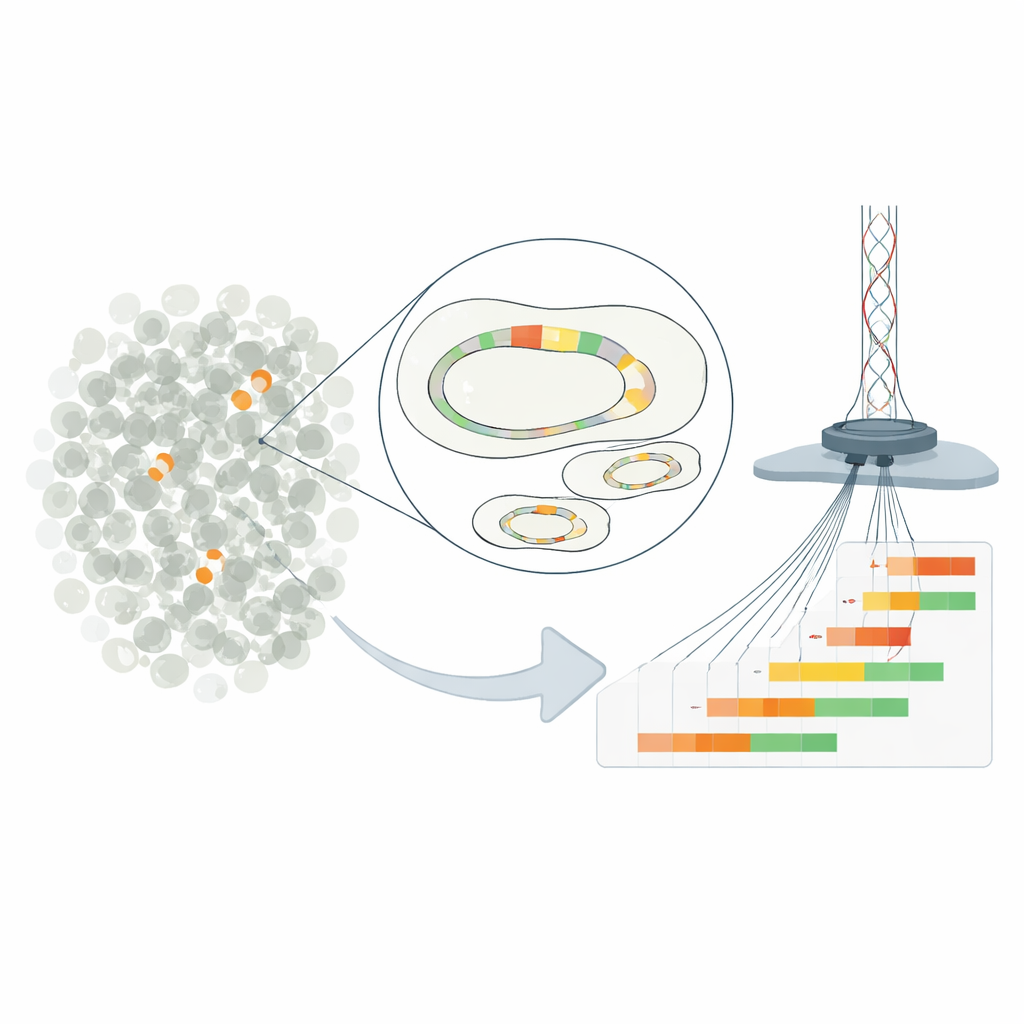
Repeticiones genéticas pequeñas, grandes consecuencias
El trabajo se centra en la “heterorresistencia”, una situación en la que la mayoría de las bacterias de una muestra parecen susceptibles a un fármaco, pero una pequeña minoría puede soportar dosis mucho mayores. En la cepa de E. coli estudiada, este comportamiento proviene de copias repetidas de un gen de resistencia en un plásmido: un pequeño círculo de ADN separado del cromosoma principal. Al duplicar un segmento corto de ADN que contiene un gen de beta-lactamasa, las bacterias pueden aumentar la producción de una enzima que descompone el antibiótico piperacilina-tazobactam. Cuantas más repeticiones porta una célula, más enzima produce y mayores son sus probabilidades de supervivencia en presencia del fármaco.
Leer círculos de ADN con un detalle sin precedentes
Los métodos tradicionales solo pueden estimar el número medio de copias de un gen en toda una población bacteriana, enmascarando la rica diversidad entre células individuales. Para superar esto, los investigadores diseñaron el plásmido clínico para que pudiera cortarse en un punto preciso y aislarse del resto del genoma. Emplearon secuenciación Nanopore de lecturas largas ultra-profundas para leer moléculas plasmídicas completas de extremo a extremo, contando exactamente cuántas unidades repetidas de resistencia contenía cada una. Este enfoque alcanzó una resolución de hasta una célula entre 100.000, revelando plásmidos con desde cero hasta más de una docena de copias coexistiendo en el mismo cultivo. Comprobaciones con otras técnicas confirmaron que, en promedio, el nuevo método informaba números de copias precisos.
Cómo los antibióticos remodelan la población
Con esta herramienta en mano, el equipo siguió lo que ocurrió cuando expusieron cultivos de E. coli a dosis crecientes de piperacilina-tazobactam y luego retiraron el fármaco. A medida que aumentaban los niveles de antibiótico, la distribución global se desplazó hacia plásmidos con más copias del gen de resistencia, pero las células con menos copias nunca desaparecieron por completo. Cuando se retiró el fármaco y las bacterias se cultivaron durante cientos de generaciones, la población solo volvió gradualmente hacia números de copias más bajos y nunca recuperó por completo su estado inicial. Ensayos de crecimiento separados mostraron que cada copia génica adicional proporcionaba un aumento medible en la tolerancia al fármaco, vinculado de forma estrecha las distribuciones genéticas observadas con el patrón visible de heterorresistencia en los ensayos de laboratorio estándar.

Protección de los vecinos y costes silenciosos
Para explicar por qué las células de baja copia persistían incluso bajo tratamiento intenso, los autores construyeron un modelo matemático que combinaba crecimiento bacteriano, degradación del antibiótico y los eventos aleatorios que añaden o eliminan copias génicas. Las simulaciones mostraron que la “resistencia indirecta” desempeña un papel clave: las células altamente resistentes expulsan suficiente beta-lactamasa para reducir la concentración del fármaco en el entorno compartido, protegiendo incidentalmente a vecinos menos resistentes. Siempre que las copias génicas adicionales impongan solo un pequeño coste de crecimiento en ausencia de fármaco, este efecto protector ayuda a mantener una amplia distribución de números de copias, ralentizando el retorno a una población totalmente susceptible. El modelo también mostró cómo la adaptación ordinaria al medio de cultivo —mutaciones no relacionadas que mejoran el crecimiento— puede fijar determinados estados de número de copias al hacer que algunas subpoblaciones sean más aptas que otras.
Por qué esto importa para los pacientes y más allá
Para quienes no son especialistas, el mensaje es que un cultivo bacteriano no es un enemigo uniforme: es una mezcla en constante cambio de individuos con distintas capacidades para sobrevivir a los antibióticos. Al contar directamente las copias génicas en miles de moléculas de ADN individuales, este estudio vincula esa diversidad oculta con la resistencia relevante para el tratamiento de forma cuantitativa. Tales conocimientos podrían mejorar cómo se utiliza la secuenciación genómica para predecir heterorresistencias difíciles de detectar, ayudar a identificar cepas bacterianas que tienen más probabilidades de causar fracaso terapéutico y orientar mejores pruebas diagnósticas. Dado que las amplificaciones génicas en tándem también impulsan la adaptación rápida en virus, tumores y otros organismos, la misma estrategia podría adaptarse mucho más allá de E. coli, ofreciendo una nueva ventana sobre cómo fragmentos repetidos de ADN ayudan a la vida a sortear amenazas.
Cita: Jonsson, S., Guliaev, A., Berryhill, B.A. et al. The dynamic distribution of genetic tandem amplifications in a heteroresistant Escherichia coli population revealed by ultra-deep long read sequencing. Nat Commun 17, 2113 (2026). https://doi.org/10.1038/s41467-026-70044-8
Palabras clave: heterorresistencia a antibióticos, amplificación génica, Escherichia coli, secuenciación de lecturas largas, beta-lactamasa