Clear Sky Science · es
Descubrimiento de péptidos antimicrobianos dirigidos a Acinetobacter baumannii mediante una canalización basada en aprendizaje de pocos disparos preentrenada y afinada
Por qué esto importa para la salud cotidiana
Las infecciones resistentes a los fármacos están aumentando tan rápidamente que, para mediados de siglo, podrían matar a más personas cada año que el cáncer. Uno de los culpables más preocupantes es Acinetobacter baumannii, un germen hospitalario resistente que hace caso omiso de muchos antibióticos y a menudo infecta a personas con ventiladores. Este estudio muestra cómo los científicos combinaron inteligencia artificial con experimentos de laboratorio para descubrir rápidamente nuevas moléculas pequeñas candidatas a fármaco que pueden matar a esta bacteria causando mucho menos daño al organismo que nuestro medicamento actual de último recurso.
Un supermicrobio hospitalario difícil de eliminar
Acinetobacter baumannii es una bacteria Gram negativa que prospera en las unidades de cuidados intensivos, particularmente en pacientes dependientes de ventiladores. Su resistente envoltura externa y su genoma de rápida evolución la hacen resistente a muchos antibióticos habituales. Hoy en día, una de las pocas opciones restantes es un fármaco llamado polimixina B, pero puede dañar gravemente los riñones y la bacteria aún puede desarrollar resistencia. Al mismo tiempo, se ha explorado una prometedora clase de fragmentos proteicos pequeños llamados péptidos antimicrobianos contra otros microbios, pero se han encontrado muy pocos que funcionen específicamente bien contra A. baumannii. El cribado tradicional por prueba y error es simplemente demasiado lento y costoso para filtrar el número astronómico de posibles secuencias cortas de péptidos.
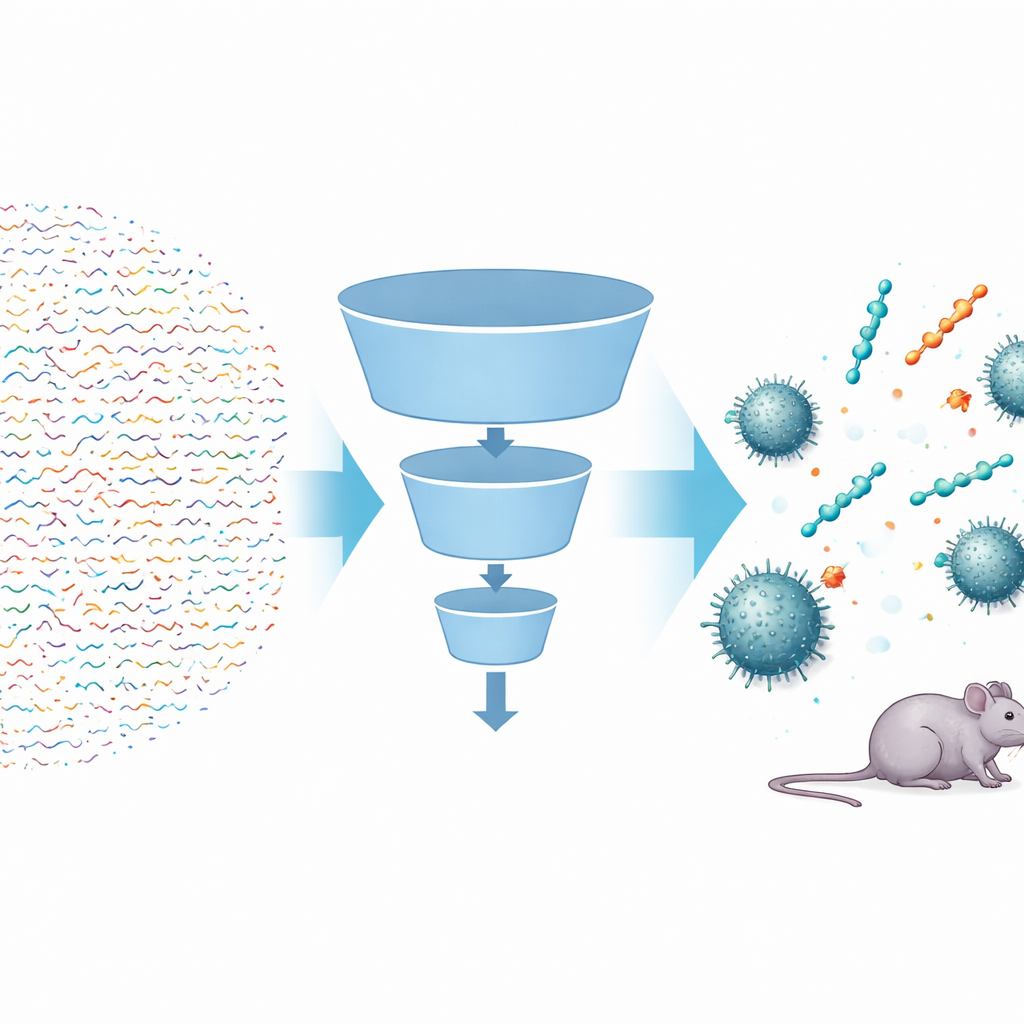
Usar algoritmos inteligentes para explorar un espacio enorme
Los investigadores construyeron una canalización de inteligencia artificial en varios pasos, llamada FSLSMEP, para escanear bibliotecas enteras de péptidos cortos —aquellos con seis, siete u ocho bloques básicos— que suman decenas de miles de millones de candidatos. El reto fue que solo disponían de 148 péptidos conocidos que actúan contra A. baumannii, muy pocos para los métodos de aprendizaje automático estándar. Para sortear esto, comenzaron con un modelo preentrenado potente que ya había “leído” cientos de millones de secuencias proteicas naturales y aprendido reglas generales sobre cómo se comportan esas moléculas. Luego afinaron este modelo en dos etapas: primero con un conjunto más grande de péptidos activos contra una bacteria relacionada, Pseudomonas aeruginosa, y finalmente con los escasos datos de A. baumannii. En el proceso, tres módulos vinculados—uno para separar péptidos probables de improbables, otro para clasificarlos y otro para estimar cuán potentes podrían ser—actuaron como filtros sucesivos en un embudo.
De las predicciones computacionales a éxitos en el tubo de ensayo
Tras descartar primero los péptidos menos prometedores mediante reglas químicas simples, el equipo introdujo casi cuatro millones de candidatos en su canalización. El clasificador eliminó la mayoría de las secuencias que no parecían antimicrobianas; el modelo de ordenación favoreció aquellas cuyas características sugerían actividad fuerte; y el modelo de regresión predijo la concentración mínima de fármaco necesaria para detener el crecimiento bacteriano. De sesenta y cuatro millones de péptidos de seis unidades, el sistema propuso solo diez candidatos principales. Cuando se sintetizaron y probaron en el laboratorio, nueve de estos mostraron actividad antibacterial real, una tasa de acierto impresionante en el descubrimiento de fármacos. Los mismos modelos entrenados se aplicaron entonces, sin volver a entrenar, a los espacios mucho mayores de péptidos de siete y ocho unidades, de los que los investigadores escogieron secuencias adicionales mejor clasificadas para su prueba. De nuevo, la mayoría resultó ser activa, incluidos heptapéptidos tan potentes como la polimixina B frente a algunas cepas.
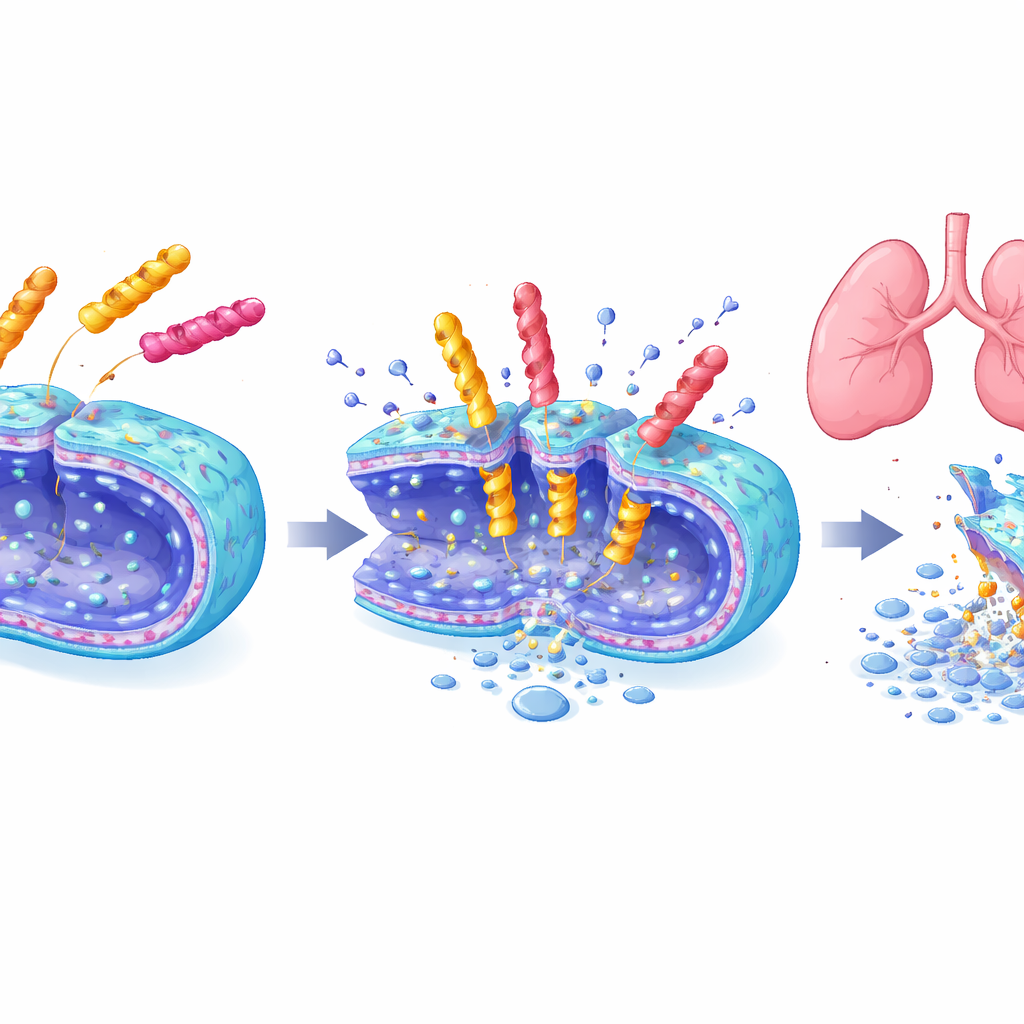
Asesinos potentes con un toque más suave
Tres péptidos líderes —uno de cada una de las bibliotecas de seis, siete y ocho unidades— fueron examinados en detalle. Eliminaban rápidamente poblaciones de A. baumannii en minutos u horas, dañaban las membranas bacterianas como se observó con microscopía electrónica y también funcionaban contra varios otros microbios peligrosos. Al mismo tiempo, causaban poco daño a células de mamífero cultivadas o a los glóbulos rojos, en contraste con algunos péptidos antimicrobianos existentes. En pruebas de exposición a largo plazo, las bacterias no desarrollaron resistencia con facilidad a estas nuevas moléculas, mientras que la resistencia a la polimixina B aumentó rápidamente. Lo más llamativo fue que, en un modelo de neumonía en ratón, una dosis inhalada del heptapéptido EME7(7) eliminó las infecciones pulmonares con tanta eficacia como la polimixina B pero no dañó los riñones, mientras que la polimixina B causó daño renal claro y aumentos en marcadores sanguíneos de estrés renal.
Qué significa esto para futuros medicamentos
Este trabajo demuestra que una canalización de IA cuidadosamente diseñada puede convertir un conjunto de datos pequeño e incompleto en un motor potente para descubrir nuevos péptidos antimicrobianos. Al combinar un preentrenamiento amplio, afinado por pasos y múltiples capas de filtrado, los investigadores exploraron eficientemente bibliotecas enteras de péptidos cortos y encontraron candidatos que tanto combaten un peligroso supermicrobio hospitalario como parecen más seguros para órganos vitales. La misma estrategia también tuvo éxito en encontrar péptidos activos contra el patógeno fúngico Candida albicans, lo que sugiere que podría reutilizarse para buscar muchos otros tipos de péptidos terapéuticos. Para los pacientes, este enfoque podría eventualmente traducirse en nuevos medicamentos que traten infecciones persistentes sin los fuertes efectos secundarios y la rápida aparición de resistencia que afectan a los antibióticos de última línea actuales.
Cita: Huang, J., Zhang, W., Wang, A. et al. Discovery of antimicrobial peptides targeting Acinetobacter baumannii via a pre-trained and fine-tuned few-shot learning-based pipeline. Nat Commun 17, 2475 (2026). https://doi.org/10.1038/s41467-026-69306-2
Palabras clave: péptidos antimicrobianos, resistencia a los antibióticos, Acinetobacter baumannii, descubrimiento de fármacos con aprendizaje automático, aprendizaje de pocos disparos