Clear Sky Science · es
Propiedades electrostáticas de las regiones desordenadas controlan la búsqueda de factores de transcripción y la actividad pionera
Cómo las “colas” proteicas ayudan a activar genes
Cada célula de tu cuerpo debe decidir rápidamente qué genes activar, a pesar de que su ADN está empaquetado de forma apretada en cromatina. Este artículo explora cómo las extensiones flexibles y cargadas eléctricamente de proteínas clave en el control génico actúan como ayudantes integrados de búsqueda, permitiendo que algunas proteínas encuentren interruptores de ADN enterrados y abran el material circundante, mientras que otras tienen dificultades para hacerlo. Comprender esta capa oculta de control arroja luz sobre cómo las células madre mantienen su flexibilidad y cómo las células cambian de identidad.
Interruptores génicos en un paisaje de ADN congestionado
Los factores de transcripción son proteínas que localizan secuencias cortas de ADN y activan genes cercanos. En las bacterias, el ADN está relativamente expuesto, y los modelos clásicos describen a estas proteínas como entidades que saltan repetidamente a la solución y luego se deslizan a lo largo del ADN desnudo hasta encontrar su objetivo. En las células animales, sin embargo, el ADN se enrolla alrededor de proteínas en forma de carrete para formar nucleosomas y se pliega en cromatina compacta. Esta congestión hace incierto cómo los factores de transcripción logran encontrar los sitios correctos lo suficientemente rápido como para controlar miles de genes.
Regiones proteicas flexibles con influencia oculta
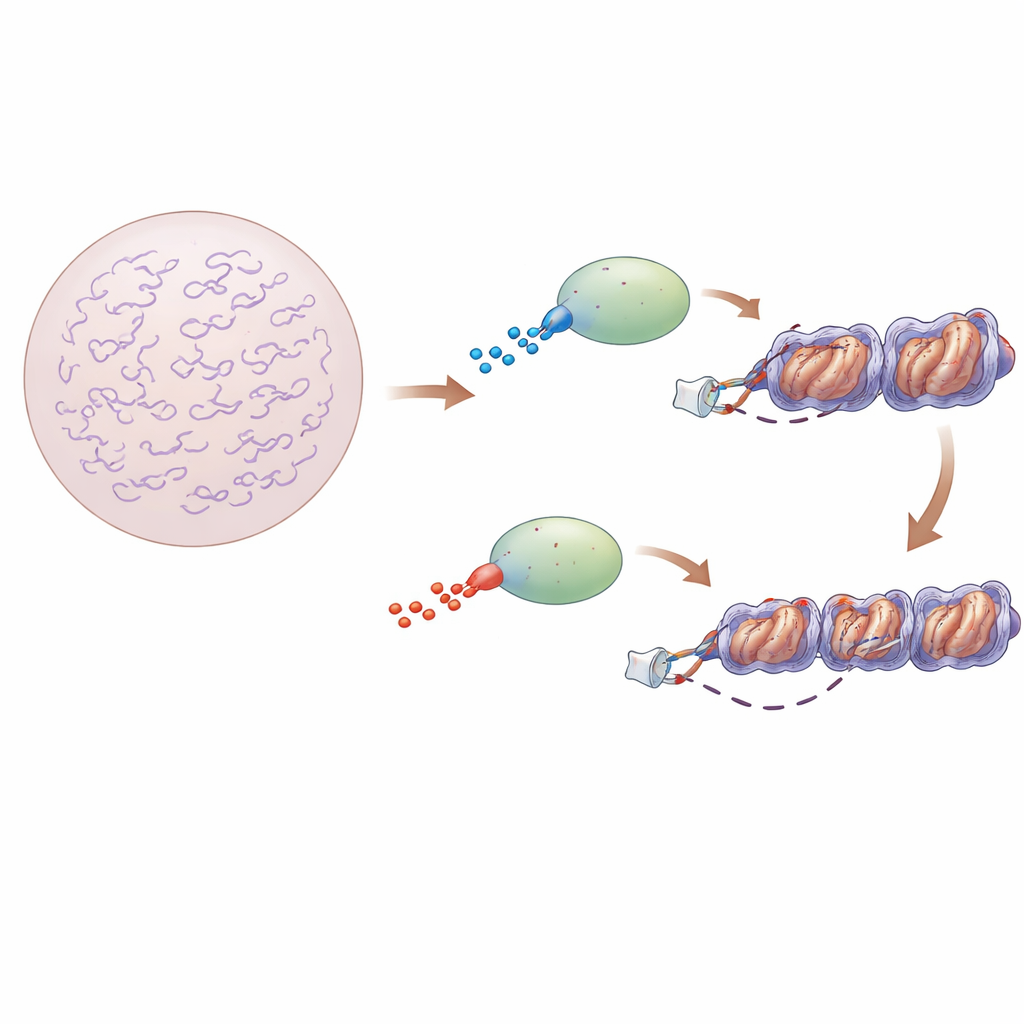
Muchos factores de transcripción contienen un núcleo estructurado que se agarra al ADN, flanqueado por largos tramos desordenados de aminoácidos. Estas regiones flexibles no se pliegan en formas fijas, pero sí portan cargas eléctricas. Los autores se centraron en dos factores estrechamente relacionados, Sox2 y Sox17, que comparten casi el mismo núcleo de unión al ADN pero se comportan de forma muy distinta en las células. Sox2 es un factor “pionero” clásico capaz de unirse al ADN oculto en cromatina compacta y es esencial para mantener a las células madre en un estado pluripotente y flexible. Sox17, en contraste, actúa normalmente más tarde durante el desarrollo y es mucho menos capaz de unirse a ADN fuertemente empaquetado. La diferencia clave: la región justo después del núcleo de unión al ADN de Sox2 es más cargada positivamente, mientras que la región equivalente en Sox17 es más cargada negativamente.
Observando moléculas individuales buscar ADN
Para ver cómo estas diferencias de carga afectan el proceso de búsqueda, los investigadores usaron microscopía de molécula única tanto en células madre de ratón vivas como con componentes purificados sobre superficies de vidrio. Diseñaron versiones de Sox2 y Sox17 que intercambian estas “colas” cargadas, y también versiones que contienen solo el núcleo de unión al ADN. En las células, siguieron proteínas marcadas con fluorescencia una por una, midiendo qué tan rápido se difunden, cuánto tiempo permanecen unidas y con qué frecuencia aterrizan en el ADN. Las proteínas que llevaban la cola positivamente cargada de Sox2 se unieron a la cromatina con más frecuencia y pasaron más tiempo en interacciones de larga duración que las que llevaban la cola de Sox17, aunque todas las versiones reconocían esencialmente las mismas letras del ADN.
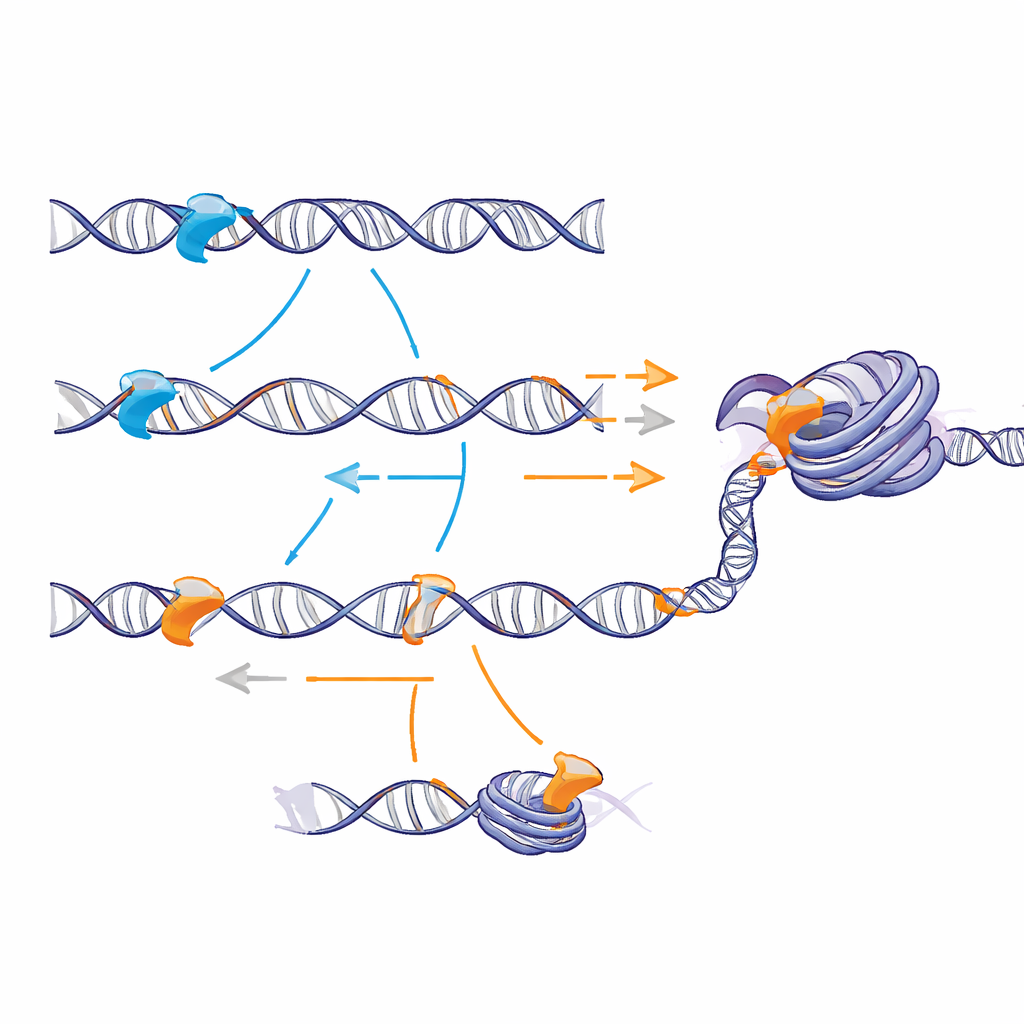
Deslizamiento lento pero mejor reconocimiento
En experimentos de tubo de ensayo cuidadosamente controlados con fragmentos de ADN desnudo, las colas cargadas no cambiaron con qué frecuencia las proteínas colisionaban inicialmente con el ADN desde la solución. En cambio, alteraron lo que sucedía una vez que una proteína había aterrizado. Combinando experimentos con modelos matemáticos, los autores mostraron que la cola de Sox2 hace que la proteína se deslice más despacio a lo largo del ADN pero sea más propensa a “detectar” su objetivo específico cuando lo atraviesa. La cola de Sox17 permite un movimiento más rápido pero aumenta la probabilidad de simplemente deslizarse por el sitio correcto sin fijarse. Esto revela una compensación entre velocidad y reconocimiento: una cola más pegajosa y cargada positivamente suaviza el paisaje energético lo suficiente como para aumentar las probabilidades de captura exitosa del objetivo.
Invadiendo y abriendo la cromatina compacta
Cuando el equipo reconstruyó nucleosomas y fibras cortas de cromatina in vitro, el contraste se volvió más marcado. La cola de Sox2 promovió contactos frecuentes y de corta duración tanto con el ADN envuelto como con los carretes de histonas, que ocasionalmente se convertían en una unión más larga y específica en sitios objetivo enterrados. En fibras de cromatina modelo, esto condujo a una unión más estable y mayor acceso a sitios internos que con la cola de Sox17. En células madre, la expresión artificial de Sox2 aumentó la unión en regiones de cromatina naturalmente cerradas y hizo que esas regiones fueran más accesibles, según un ensayo que detecta qué tan fácilmente las enzimas pueden cortar el ADN. La versión de Sox2 que llevaba la cola de Sox17 se unió menos y abrió la cromatina con menos eficiencia, aunque seguía reconociendo los mismos motivos de ADN.
Qué significa esto para la identidad celular
En conjunto, el estudio muestra que la carga eléctrica de las “colas” proteicas desordenadas puede ajustar cómo los factores de transcripción buscan el ADN y cuán eficazmente pueden invadir y aflojar la cromatina compacta. Una cola más cargada positivamente, como en Sox2, favorece contactos inespecíficos frecuentes y agudiza el reconocimiento del objetivo, apoyando una fuerte actividad pionera y ayudando a mantener el paisaje de cromatina abierto en células madre. Estos principios probablemente se extienden a muchas otras proteínas de control génico, añadiendo una nueva regla de diseño sobre cómo las células programan y reprograman su actividad genética.
Cita: Sakong, S., Fierz, B. & Suter, D.M. Electrostatic properties of disordered regions control transcription factor search and pioneer activity. Nat Commun 17, 2512 (2026). https://doi.org/10.1038/s41467-026-69284-5
Palabras clave: factores de transcripción, cromatina, Sox2, regiones intrínsecamente desordenadas, actividad pionera