Clear Sky Science · es
Multiplicidad heterogénea de variantes blaCTX-M en el mismo plásmido mejora la adaptabilidad evolutiva en Klebsiella pneumoniae clínica
Por qué importa para la medicina moderna
Las infecciones resistentes a los antibióticos son una amenaza creciente en los hospitales de todo el mundo, y los médicos recurren cada vez más a fármacos de último recurso para salvar a los pacientes. Este estudio explica cómo una bacteria hospitalaria común, Klebsiella pneumoniae, puede emplear un truco genético sutil para resistir combinaciones potentes de antibióticos que fueron diseñadas para superar la resistencia. Al desvelar esta estrategia, la investigación ayuda a explicar por qué algunas infecciones reaparecen a pesar de tratamientos agresivos, y aporta pistas sobre cómo los médicos podrían adelantarse un paso.
Un germen hospitalario bajo presión
La historia comienza en una unidad de cuidados intensivos, donde dos pacientes fueron infectados por cepas casi idénticas de K. pneumoniae. Una cepa respondió bien al tratamiento con la combinación moderna ceftazidima/avibactam, mientras que la otra mostró fuerte resistencia. Las comparaciones genéticas mostraron que ambas cepas portaban la misma familia amplia de enzimas de resistencia, llamadas β-lactamasas, en un plásmido compartido —un pequeño círculo de ADN móvil dentro de la bacteria. Pero en la cepa resistente una de estas enzimas había cambiado de forma sutil, y esa variante, denominada CTX-M-249, permitió que la bacteria resistiera la combinación de fármacos que debería haberla matado.
Un cambio pequeño con grandes consecuencias
Pruebas bioquímicas más detalladas revelaron que CTX-M-249 intercambia un tipo de protección por otro. La versión habitual, CTX-M-65, es excelente rompiendo ciertos antibióticos como el cefotaxima, pero sigue siendo vulnerable al inhibidor avibactam. CTX-M-249, alterada en solo dos posiciones de la proteína, mejora su capacidad frente a la combinación ceftazidima más avibactam, pero pierde gran parte de su eficacia contra el cefotaxima. En teoría, esto parece un intercambio evolutivo clásico: ganar una defensa mientras se debilita otra. Sin embargo, la cepa clínica evitó este inconveniente al llevar varias copias estrechamente relacionadas del gen a la vez, de modo que diferentes versiones de la enzima podían coexistir en la misma línea bacteriana.
Muchas copias, muchas opciones
Empleando secuenciación de lectura larga y métodos de conteo precisos, los investigadores encontraron que el plásmido en la cepa resistente llevaba dos sitios separados de blaCTX-M, y uno de ellos podía existir en múltiples versiones ligeramente distintas. Sin presión de fármacos, aproximadamente la mitad de la población portaba la versión más antigua CTX-M-65 y casi la mitad portaba CTX-M-249, con una pequeña fracción con formas intermedias. Cuando las bacterias se expusieron a dosis crecientes de ceftazidima/avibactam, tanto el número de copias del gen como la proporción de CTX-M-249 aumentaron bruscamente. A veces esto ocurrió por un aumento del número de plásmidos por célula; a niveles de fármaco más altos, el propio plásmido generó repeticiones en tándem cortas del gen de resistencia. En efecto, las bacterias usaron la duplicación de ADN como un mando que podían subir o bajar para adaptarse a los antibióticos circundantes.
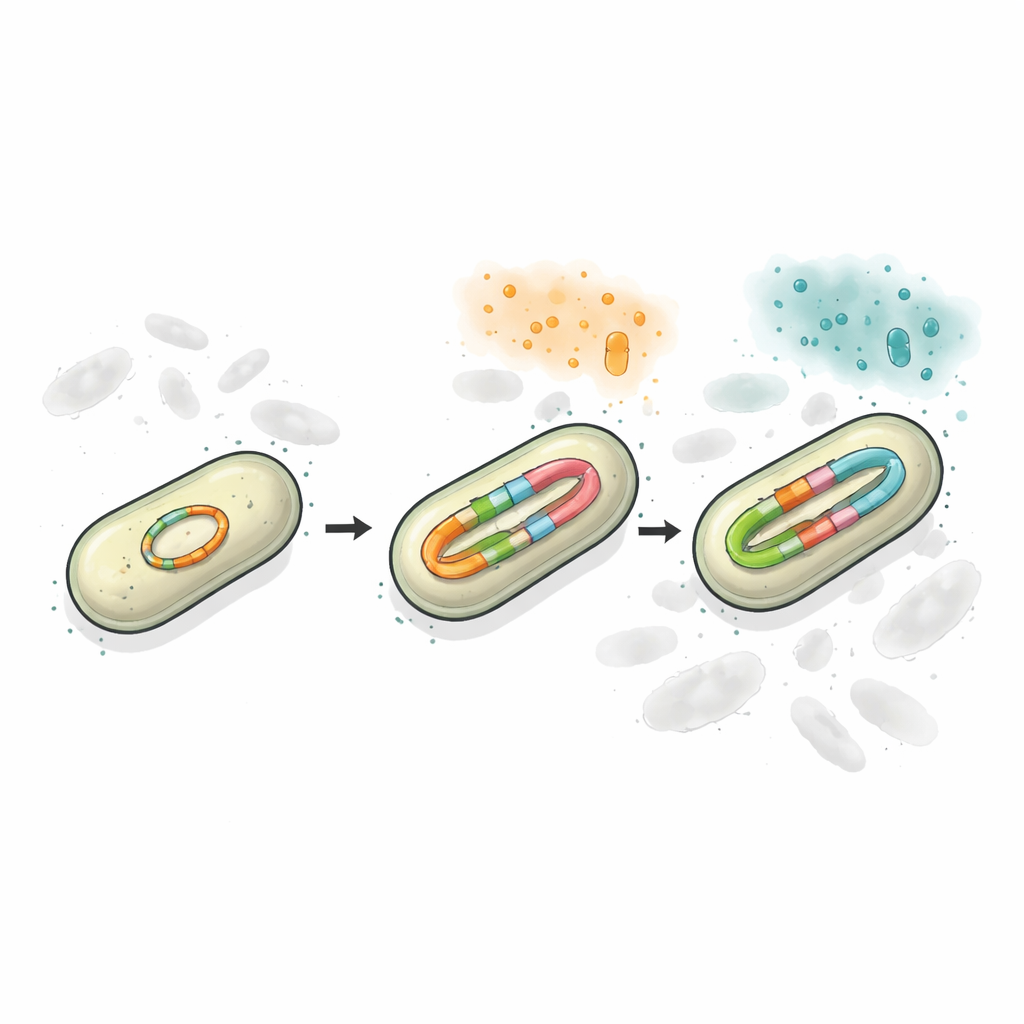
Mantener la diversidad en un solo círculo de ADN
Para probar cómo esta disposición afecta la supervivencia, el equipo construyó modelos de laboratorio simplificados en los que las bacterias llevaban bien una versión de resistencia, dos versiones en plásmidos separados, o ambas versiones codificadas juntas en un único plásmido. Al desafiarse con dos cefalosporinas diferentes, los sistemas mixtos superaron a las cepas con un solo gen, porque al menos una versión de la enzima podía hacer frente a cada fármaco. Sin embargo, la configuración en la que ambas variantes del gen estaban en el mismo plásmido resultó ser la más estable. Cuando se aplicaron antibióticos durante varios días o se cambió de un fármaco a otro, las células con dos plásmidos separados a menudo perdieron uno de ellos, sacrificando parte de su protección. En contraste, el plásmido “dos en uno” se heredaba como un paquete, preservando ambas opciones de resistencia incluso cuando imponía un coste de crecimiento a corto plazo.
Un patrón más amplio en bacterias peligrosas
Modelos matemáticos reprodujeron estos experimentos, mostrando que, por encima de ciertos niveles de antibiótico, las bacterias con un solo plásmido que lleva múltiples variantes de resistencia acaban dominando poblaciones mixtas. Los investigadores buscaron luego miles de genomas de K. pneumoniae procedentes de hospitales, granjas, alimentos y el medio ambiente. Con frecuencia encontraron múltiples copias ligeramente diferentes de genes clave de resistencia —especialmente en aislados clínicos humanos que enfrentan una fuerte exposición a fármacos. Esto sugiere que construir “heterogeneidad multicopia” en plásmidos no es una rareza, sino una táctica generalizada que las bacterias usan para cubrir sus apuestas frente a tratamientos cambiantes.
Qué significa esto para los pacientes y el tratamiento
Para un público no especialista, el mensaje central es que algunas bacterias no llevan simplemente un único gen de resistencia; llevan familias de versiones relacionadas agrupadas en el mismo elemento de ADN móvil, lo que les da un conjunto de herramientas flexible contra distintos fármacos. Esta disposición les permite mantener la resistencia durante largos periodos, incluso cuando los médicos cambian terapias, y ayuda a explicar por qué ciertas infecciones son tan difíciles de eliminar. Al mismo tiempo, el estudio muestra que combinaciones de fármacos bien elegidas —como emparejar ceftazidima/avibactam con cefotaxima— pueden explotar debilidades en este sistema y suprimir incluso estas cepas bien armadas. Comprender cómo las bacterias construyen y usan estos plásmidos multicopia es, por tanto, crucial para diseñar estrategias antibióticas más inteligentes y frenar el avance de la resistencia.
Cita: Weng, R., Zhu, J., Wu, X. et al. Heterogeneous multicopy of blaCTX-M variants on the same plasmid enhances evolutionary adaptability in clinical Klebsiella pneumoniae. Nat Commun 17, 2460 (2026). https://doi.org/10.1038/s41467-026-69266-7
Palabras clave: resistencia a los antibióticos, Klebsiella pneumoniae, plásmidos, beta-lactamasas, terapia multimedicamentosa