Clear Sky Science · es
PRICE: detección directa y robusta de microARNs con resolución de un solo nucleótido
Por qué importan los mensajes genéticos diminutos
Dentro de cada célula hay un enjambre de diminutas moléculas de ARN llamadas microARNs que ayudan a afinar qué genes se activan o se silencian. Un cambio de apenas una “letra” en estas moléculas cortas puede inclinar la balanza hacia la salud o la enfermedad, incluidos los cánceres. Médicos e investigadores desearían poder leer esas pequeñas diferencias directamente en sangre o tejido, pero los métodos actuales suelen ser lentos, caros y no lo bastante precisos para detectar de forma fiable un cambio de una sola letra. Este artículo presenta una nueva técnica de laboratorio, llamada PRICE, que promete leer esos errores microscópicos en los microARNs de manera más simple y precisa, abriendo la puerta a una detección precoz del cáncer y a un mejor seguimiento del comportamiento de los tumores.
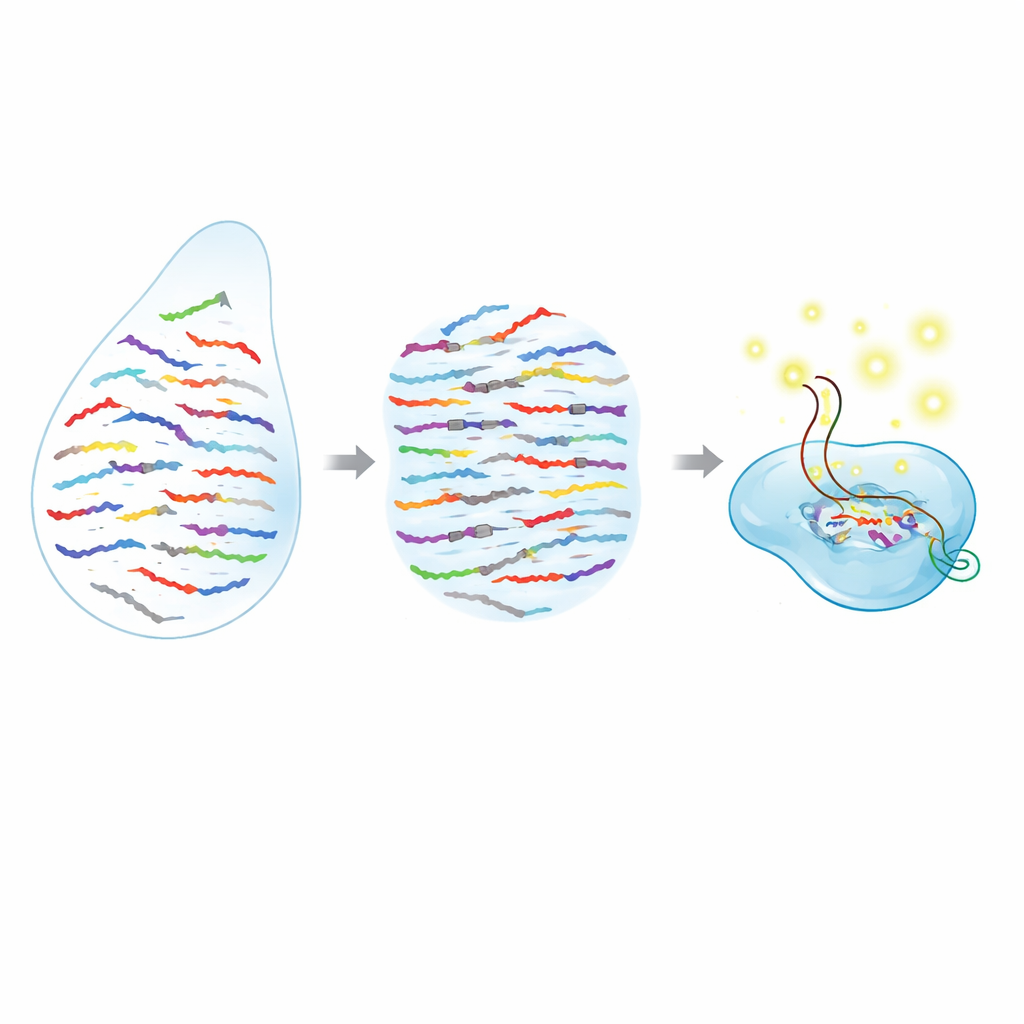
Una nueva forma de distinguir moléculas que se parecen
Los microARNs son extremadamente cortos, lo que dificulta diferenciarlos cuando sus secuencias difieren por un único componente. Muchas herramientas actuales, como la PCR y la secuenciación de ARN, hacen un buen trabajo contando microARNs en conjunto, pero flaquean cuando dos versiones son casi idénticas o requieren preparación compleja de la muestra y equipos costosos. Los autores combinan dos ideas potentes para superar esto: unas “tijeras” moleculares programables de la familia CRISPR y piezas sintéticas parecidas al ADN llamadas ácidos nucleicos peptídicos (PNA). La enzima CRISPR Cas13a puede ser dirigida para reconocer un ARN específico y, una vez que encuentra su blanco, empieza a cortar moléculas reporteras cercanas, produciendo una señal fluorescente intensa. Los PNA, por su parte, son hebras cortas que se unen con especial afinidad a secuencias de ARN coincidentes, pero pierden esa unión de forma brusca si incluso una sola letra es incorrecta.
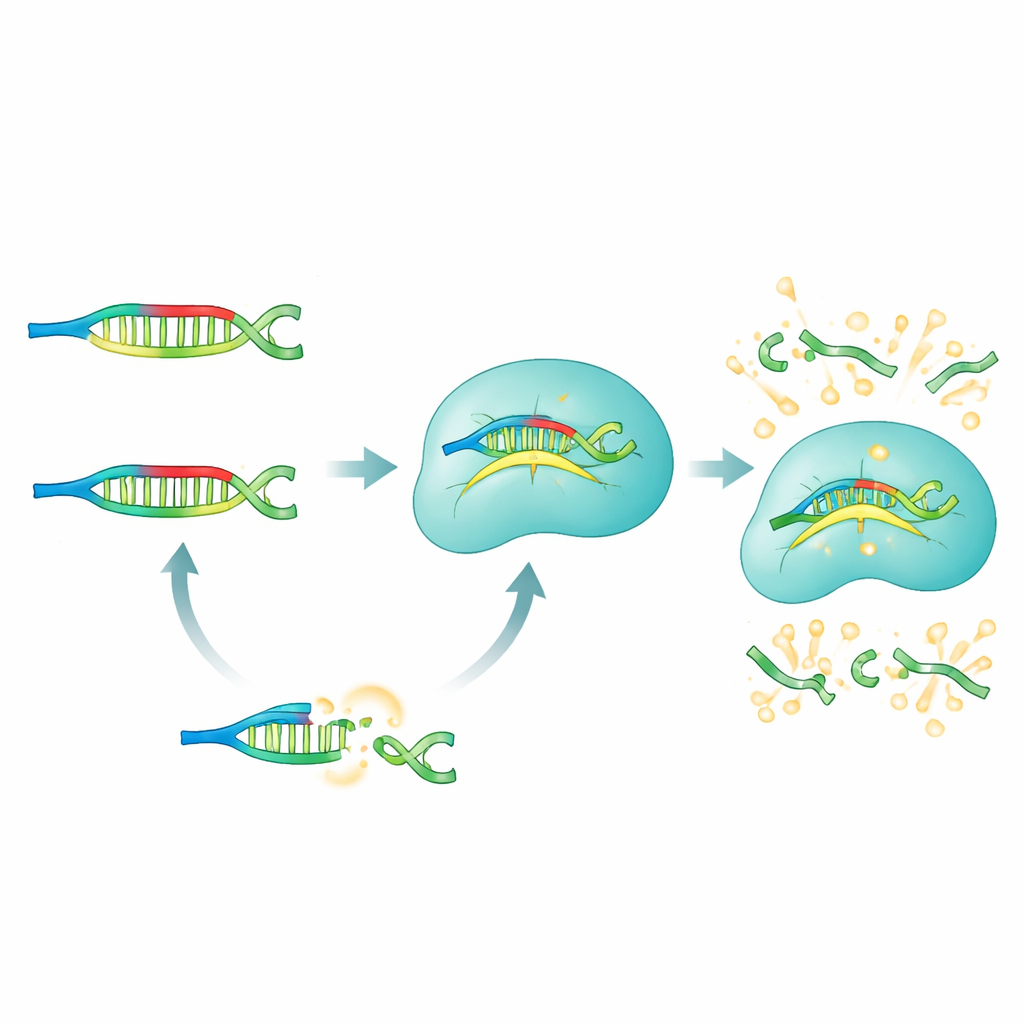
Cómo funciona el método PRICE
En el sistema PRICE, los PNA actúan como bloqueadores selectivos que silencian todo lo que los investigadores no quieren ver. Para un microARN de interés, el equipo diseña un panel de bloqueadores PNA que coinciden perfectamente con todas las versiones “equivocadas” —aquellas con cambios de una sola letra no deseados— mientras deliberadamente presentan un desajuste con el objetivo elegido. Cuando una muestra biológica (suero, células o tejido) se mezcla con estos PNA, los microARNs no objetivos quedan fuertemente unidos y efectivamente enmascarados. El verdadero objetivo queda sin unir y libre para interactuar con el complejo Cas13a, que ha sido preprogramado con un ARN guía que reconoce ese microARN. Solo este objetivo desbloqueado puede activar a Cas13a en su modo cortante, lo que a su vez fragmenta las moléculas reporteras fluorescentes y genera un brillo fuerte y fácil de medir.
Afinando la precisión de una sola letra
Los autores exploraron sistemáticamente cómo diseñar bloqueadores PNA que sean lo bastante fuertes para capturar el microARN erróneo, pero lo bastante débiles para ignorar el deseado que difiere en solo una letra. Encontraron que dos reglas de diseño análogas a la temperatura son cruciales: el PNA debe formar un emparejamiento estable con el mutante no deseado a la temperatura corporal o por encima de ella, pero debe formar un emparejamiento mucho más débil con el objetivo que se disocie bien por debajo de esa temperatura. Con estas reglas, apoyadas por un modelo predictivo simple, construyeron PNA que reducen las señales falsas de microARNs mutantes en más del 70 por ciento mientras dejan la señal verdadera casi intacta. Es importante que los PNA añadidos no disminuyeron la sensibilidad global: PRICE aún pudo detectar microARNs a concentraciones de solo unas pocas decenas de femtomolares, comparable con las mejores pruebas basadas en amplificación pero sin los pasos adicionales de copiado.
Poner la prueba a trabajar en muestras de cáncer
Para demostrar que PRICE es más que un artefacto teórico, el equipo se centró en la familia let‑7 de microARNs, que está muy implicada en la biología del cáncer. Demostraron que PRICE puede identificar microARNs objetivo en mezclas que contienen muchos miembros familiares casi idénticos e incluso detectar variantes raras que constituyen apenas el 5 por ciento de una muestra. Los investigadores luego pasaron a material clínico real: líneas celulares de cáncer de hígado, biopsias de tejido y suero de pacientes. Tanto en tejido tumoral como en sangre, PRICE detectó consistentemente niveles más bajos de determinados microARNs let‑7 en pacientes en comparación con controles no cancerosos, en concordancia con estudios previos. Al compararlo directamente con la RT‑qPCR estándar, PRICE mostró una capacidad al menos similar y a menudo mejor para distinguir casos cancerosos de no cancerosos, especialmente en muestras de suero con baja abundancia donde los resultados de PCR se volvían ruidosos.
Por qué esto importa para los diagnósticos futuros
En esencia, este trabajo demuestra que es posible leer directamente diferencias de una sola letra en pequeños ARN reguladores de forma práctica y escalable. Al permitir que los PNA bloqueen secuencias parecidas no deseadas y delegar la lectura final a una enzima CRISPR, PRICE ofrece una caja de herramientas flexible para diseñar pruebas que pueden reorientarse simplemente intercambiando el panel de bloqueadores y el ARN guía. Más allá del cáncer de hígado y la familia let‑7, la misma estrategia podría extenderse a muchas otras enfermedades donde importan pequeños cambios en ARN, e incluso a variantes de ADN cuando se combine con enzimas CRISPR relacionadas. Los autores también demuestran un lector compacto multicanal que puede ejecutar ensayos PRICE fuera de grandes laboratorios centrales, sugiriendo pruebas futuras en el punto de atención. Si se desarrolla más, PRICE podría convertirse en una forma práctica de monitorizar cambios genéticos sutiles que señalan cáncer y otras enfermedades mucho antes de que aparezcan los síntomas.
Cita: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Palabras clave: diagnóstico por microARN, CRISPR Cas13a, ácido nucleico peptídico, variación de un solo nucleótido, biomarcadores de cáncer de hígado