Clear Sky Science · es
Motivos Shine–Dalgarno extendidos gobiernan el inicio de la traducción en Staphylococcus aureus
Cómo un germen hospitalario ajusta sus fábricas de proteínas
Staphylococcus aureus es un germen común que puede causar desde infecciones cutáneas leves hasta enfermedades potencialmente mortales. Para sobrevivir en el organismo y resistir los tratamientos, debe reconfigurar constantemente qué proteínas produce. Este artículo revela cómo S. aureus controla el paso inicial de la producción proteica de una manera que difiere de bacterias de libro de texto como Escherichia coli, y muestra cómo este control está vinculado a la formación de biopelículas, un factor importante en las infecciones crónicas y tolerantes a antibióticos.
Un “apretón de manos” oculto entre gen y ribosoma
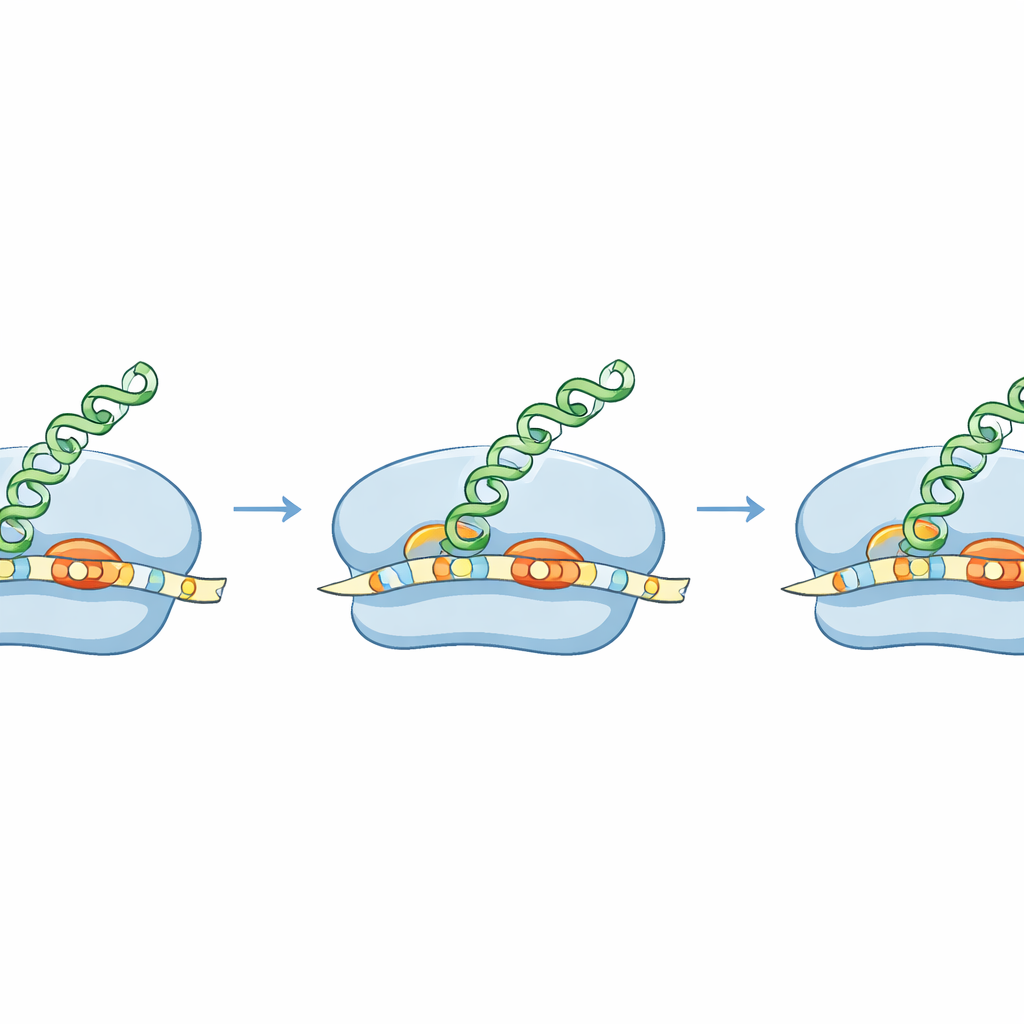
Para convertir un gen en proteína, las bacterias emplean ribosomas, máquinas moleculares que examinan el ARN mensajero (ARNm) para encontrar dónde empezar a leer. Muchos ARNm bacterianos contienen una secuencia corta, conocida desde hace tiempo como la región Shine–Dalgarno, que ayuda al ribosoma a acoplarse en el lugar correcto. Al inmovilizar ribosomas en el momento en que inician la traducción y secuenciar los fragmentos de ARN protegidos, los autores crearon un mapa de alta resolución de los sitios de inicio a lo largo del genoma de S. aureus. Descubrieron que S. aureus utiliza con frecuencia una versión inusualmente larga de esta secuencia de acoplamiento, situada muy cerca de la señal de inicio, formando un “cremallera” extendida entre el ARNm y el ARN ribosómico. Este apareamiento extendido es mucho más prominente que en E. coli y parece ser una característica distintiva de cómo S. aureus elige dónde empezar.
Reglas específicas de la especie para iniciar la síntesis proteica
El equipo demostró que este eje de acoplamiento extendido tiene consecuencias reales. En varios genes naturales de S. aureus, las primeras letras pueden leerse de más de una manera, ofreciendo lugares rivales para iniciar la traducción. Usando ribosomas purificados, sistemas libres de células y células vivas, los investigadores compararon cómo S. aureus y E. coli manejan estos inicios ambiguos. Los ribosomas de S. aureus eligieron de forma fiable el mismo inicio “correcto” utilizado en la propia bacteria, guiados por la larga hélice de acoplamiento y el espaciado preferido entre esa hélice y la señal de inicio. Los ribosomas de E. coli, en cambio, favorecieron un inicio cercano distinto que produciría una proteína alternativa. Esto significa que el mismo ARNm puede dirigir la síntesis de proteínas diferentes en distintas especies, lo que abre la puerta a diseñar mensajes que solo sean legibles por bacterias seleccionadas.
Nuevas proteínas diminutas y señales de inicio débiles
Puesto que su método localiza con precisión la llegada de ribosomas a los sitios de inicio, los autores pudieron también descubrir muchos genes cortos previamente perdidos. Identificaron docenas de pequeños marcos de lectura abiertos, incluidas secuencias “ascendentes” cortas que se sitúan justo antes de genes más grandes ya conocidos. Algunas de estas regiones cortas probablemente codifican diminutas proteínas con funciones propias; otras parecen actuar principalmente como reguladores. El estudio además reveló que S. aureus a veces inicia la traducción en tripletes de inicio “no canónicos” que normalmente se consideran señales pobres. En esos casos, motivos de acoplamiento fuertes y extendidos parecen compensar el inicio débil, limitando la producción de proteína de modo que ciertos factores, incluidos reguladores metabólicos, se fabriquen solo en pequeñas cantidades o en respuesta a condiciones de crecimiento.
Un sensor molecular que enlaza nutrientes y crecimiento de biopelículas
Un elemento corto ascendente, denominado rbfL, emergió como un ejemplo llamativo de control translacional ligado a la virulencia. Se encuentra justo antes de rbf, un gen que codifica un factor de transcripción que promueve la formación de biopelículas. La secuencia rbfL codifica un pequeño péptido “líder” rico en arginina, que incluye codones de arginina muy raros decodificados por ARN de transferencia escasos. Cuando la arginina escasea, estos codones se traducen lentamente y los ribosomas se detienen sobre la región que solapa el sitio de acoplamiento de rbf, bloqueando físicamente que nuevos ribosomas inicien la traducción de rbf. Cuando la arginina o su ARNt correspondiente son abundantes, la detención se alivia y rbf se produce con mayor eficiencia. En experimentos de crecimiento, añadir arginina extra aumentó la formación de biopelículas, vinculando este sensor molecular directamente a un modo de vida comunitario que resiste a los antibióticos.
Por qué importan estos hallazgos
Este trabajo muestra que S. aureus ha evolucionado motivos de acoplamiento extendidos y elementos ascendentes diminutos para afinar dónde y cuándo comienza la síntesis de proteínas. Estas características no solo lo distinguen de bacterias modelo como E. coli, sino que además acoplan la detección de nutrientes al control de reguladores de biopelículas. Para un lector general, la conclusión clave es que los “botones de inicio” de la producción proteica de la bacteria son más complejos de lo que se pensaba —y que estos interruptores especializados ayudan a determinar cuándo S. aureus se vuelve más peligroso. Entender estas reglas únicas de iniciación podría orientar el diseño de antibióticos específicos por especie o herramientas genéticas que destruyan selectivamente bacterias nocivas preservando las beneficiosas.
Cita: Kohl, M.P., Bahena-Ceron, R., Chane-Woon-Ming, B. et al. Extended Shine-Dalgarno motifs govern translation initiation in Staphylococcus aureus. Nat Commun 17, 2678 (2026). https://doi.org/10.1038/s41467-026-69079-8
Palabras clave: Staphylococcus aureus, inicio de la traducción, Shine-Dalgarno, pequeños ORF, regulación de biopelículas