Clear Sky Science · es
Un atlas de cuantificación absoluta de pequeños ARN no codificantes en diversos tejidos y líneas celulares de mamíferos
Por qué importan las moléculas de ARN diminutas
Dentro de cada célula, ejércitos de diminutas moléculas de ARN ayudan a decidir qué genes se activan o se silencian. Estos pequeños ARN no codificantes actúan como reguladores de intensidad para nuestros programas genéticos, moldeando el desarrollo, la función de los órganos y la enfermedad. Sin embargo, a pesar de las potentes tecnologías de secuenciación, los científicos han tenido dificultades para medir con exactitud cuántas de estas moléculas están presentes en distintos tipos celulares y tejidos. Este estudio presenta una forma más precisa de contarlas y construye un atlas detallado que muestra su verdadera abundancia en numerosos tejidos de mamíferos y líneas celulares de laboratorio comunes.
Una forma más clara de contar pequeños ARN
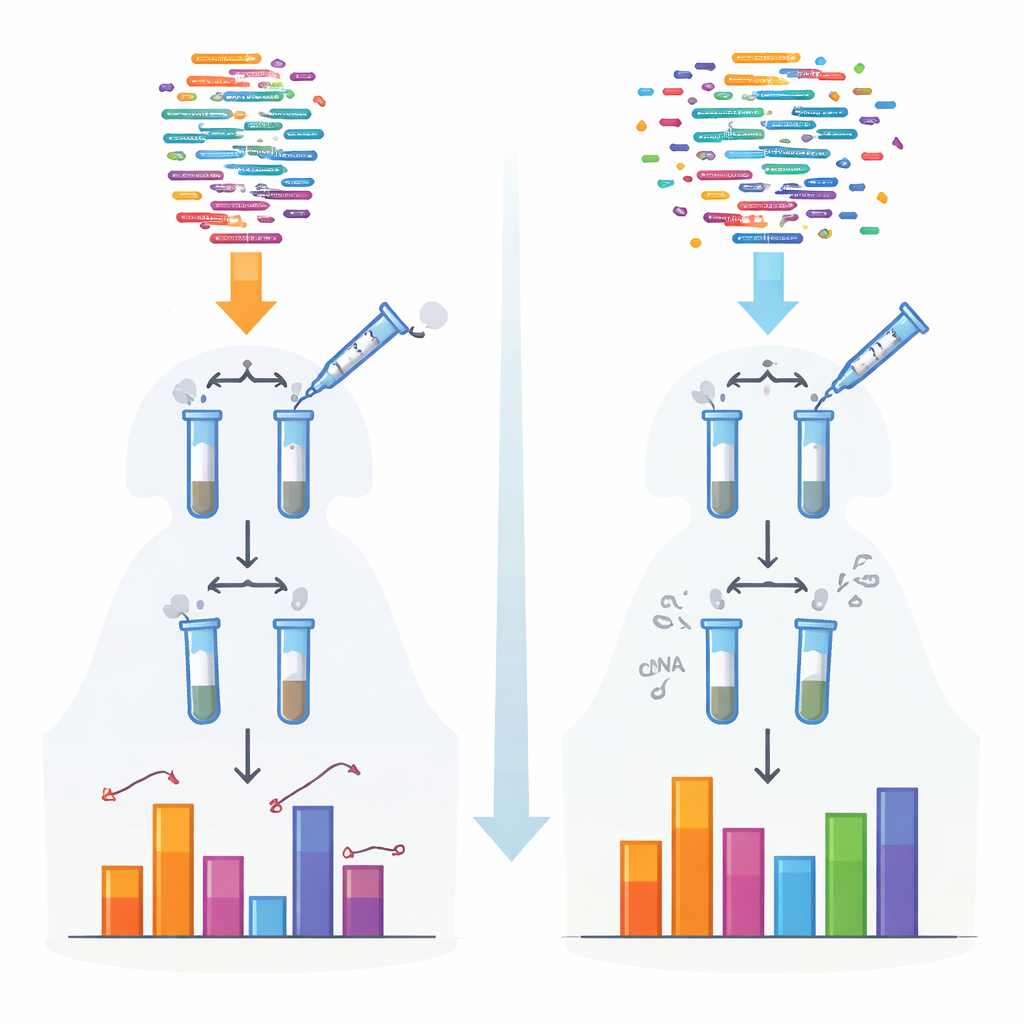
Los métodos tradicionales para secuenciar pequeños ARN dependen de enzimas que unen adaptadores antes de leer las moléculas. Esas enzimas prefieren ciertas conformaciones y terminaciones químicas, de modo que algunos ARN se capturan de forma eficiente mientras que otros se pierden o se subcuentan. Este sesgo es especialmente severo para clases particulares como los piARN y los pequeños ARN vegetales, que llevan capuchones químicos protectores en sus extremos. Los autores crearon un nuevo protocolo, llamado 4NBoost, que rediseña los adaptadores y las condiciones de reacción para nivelar estas preferencias y añade códigos moleculares incorporados para distinguir moléculas verdaderas de copias generadas durante la amplificación.
Convertir un protocolo en una herramienta de medición
Para transformar 4NBoost de una lectura relativa a una herramienta de medición real, el equipo añadió ARN sintéticos “spike‑in” diseñados con precisión a concentraciones conocidas que abarcan un rango muy amplio. Comparando cuántas veces cada spike‑in fue leído por el secuenciador con la cantidad originalmente añadida, construyeron curvas estándar que convierten los recuentos de lecturas en números absolutos de moléculas. Pruebas con diferentes mezclas de spike‑in y ARN de control añadidos mostraron que 4NBoost podía rastrear la abundancia con precisión a través de varios órdenes de magnitud, incluidos ARN con modificaciones químicas problemáticas. Incluso partiendo de tan solo un nanogramo de ARN total, el método seguía capturando fielmente el paisaje de pequeños ARN.
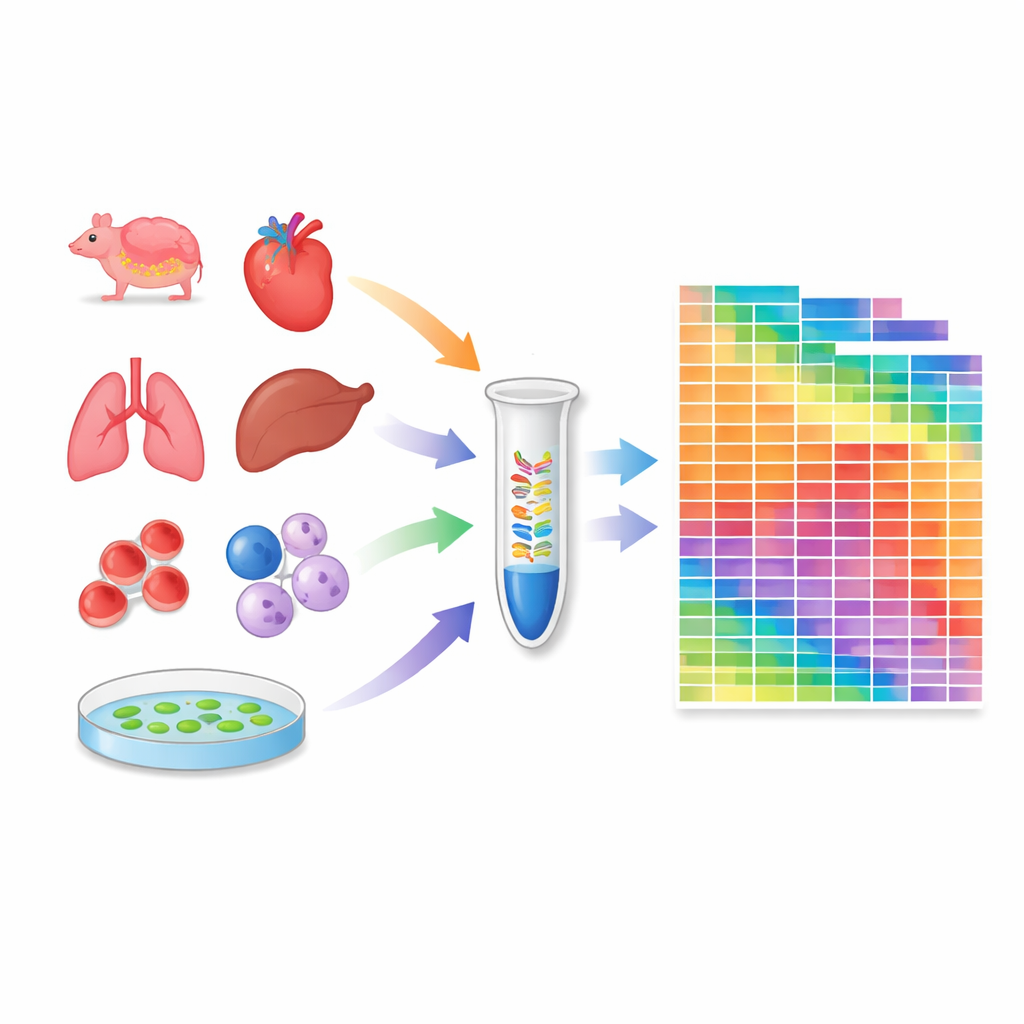
Construcción de un atlas a través de tejidos y líneas celulares
Con este protocolo calibrado, los investigadores analizaron 259 muestras: 20 tejidos de ratón, 18 de macaco cangrejero, 24 líneas celulares humanas y de ratón de uso extendido y varios tejidos de la planta modelo Arabidopsis. Para cada muestra estimaron el número absoluto de moléculas de miles de microARN y piARN. Esto reveló cuántas especies diferentes de microARN están presentes en cada contexto y cómo sus cantidades totales varían entre tejidos y especies. Algunas líneas celulares y órganos poseen repertorios de microARN especialmente ricos, mientras que otros, como las células sanguíneas, están dominados por unas pocas especies de alta abundancia. El atlas también evidenció diferencias sustanciales entre tejidos de ratón y mono, subrayando que la regulación por pequeños ARN puede ser específica por especie.
Corregir datos antiguos y revisar suposiciones comunes
Al comparar el nuevo atlas con bases de datos populares de pequeños ARN construidas con métodos convencionales, aparecieron desajustes llamativos. Varias familias importantes de microARN—como miR‑19 y miR‑29—resultaron ser mucho más abundantes de lo que se pensaba, mientras que otras—como las ampliamente estudiadas familias let‑7 y miR‑10—frecuentemente habían sido sobreestimadas. El estudio también reexaminó qué “brazo” de cada horquilla precursora se utiliza realmente en las células, descubriendo casos en los que las anotaciones actuales listan la hebra mayor equivocada. Para rescatar la riqueza de conjuntos de datos sesgados existentes, los autores entrenaron un modelo de aprendizaje automático que aprende cómo las mediciones convencionales se desvían de 4NBoost y luego las corrige matemáticamente para reflejar mejor las abundancias reales.
Un recurso público para explorar los pequeños ARN
Todas las mediciones de 4NBoost y el modelo de corrección están disponibles gratuitamente a través de una plataforma en línea llamada SmRNAQuant. Los investigadores pueden explorar o descargar niveles absolutos de pequeños ARN para tejidos, líneas celulares o microARN específicos, y pueden subir sus propios datos preparados con un kit común para obtener valores corregidos por sesgo. Para los no especialistas, el mensaje clave es que contar importa: diferencias diminutas en el número de copias de pequeños ARN pueden marcar la diferencia entre una regulación génica activa y ningún efecto en absoluto. Al ofrecer números más fiables y una manera de corregir datos antiguos, este trabajo establece una base cuantitativa más sólida para entender cómo los pequeños ARN moldean la biología normal y la enfermedad.
Cita: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
Palabras clave: cuantificación de microARN, pequeño ARN no codificante, sesgo en secuenciación de ARN, atlas de expresión en tejidos, corrección mediante aprendizaje automático