Clear Sky Science · es
Comparativa exhaustiva de métodos de puntuación poligénica de una y múltiples ancestrías con la plataforma PGS-hub
Por qué importa tu puntuación de riesgo genética
Los médicos son cada vez mejores leyendo nuestro ADN para estimar quiénes tienen más probabilidades de desarrollar enfermedades comunes como cardiopatía, diabetes o esquizofrenia. Estas estimaciones, llamadas puntuaciones poligénicas, combinan los pequeños efectos de muchos variantes genéticas en un solo número. Pero hoy existen muchas formas de calcular esas puntuaciones y no funcionan igual de bien para personas de distintos orígenes ancestrales. Este estudio se propuso comparar de forma directa los principales métodos y construir un servicio en línea, PGS-hub, que permita a los investigadores calcular estas puntuaciones de manera coherente y sencilla.
Un punto único para calculadoras de riesgo genético
Los autores crearon PGS-hub, una plataforma web que oculta gran parte de la complejidad técnica asociada a las puntuaciones poligénicas. Los usuarios suben resultados de estudios genéticos que resumen cómo millones de marcadores de ADN se relacionan con una enfermedad o rasgo. A continuación eligen el trasfondo ancestral de la población que les interesa—por ejemplo, europea o africana—y seleccionan entre un menú de métodos de puntuación populares. Tras bambalinas, PGS-hub convierte la entrada a los formatos adecuados, incorpora paneles de referencia preconstruidos que describen cómo se correlacionan marcadores cercanos y ejecuta numerosos trabajos en un sistema de cálculo de alto rendimiento. El resultado es un archivo compacto de pesos que se puede aplicar a genomas individuales para generar una puntuación por persona. 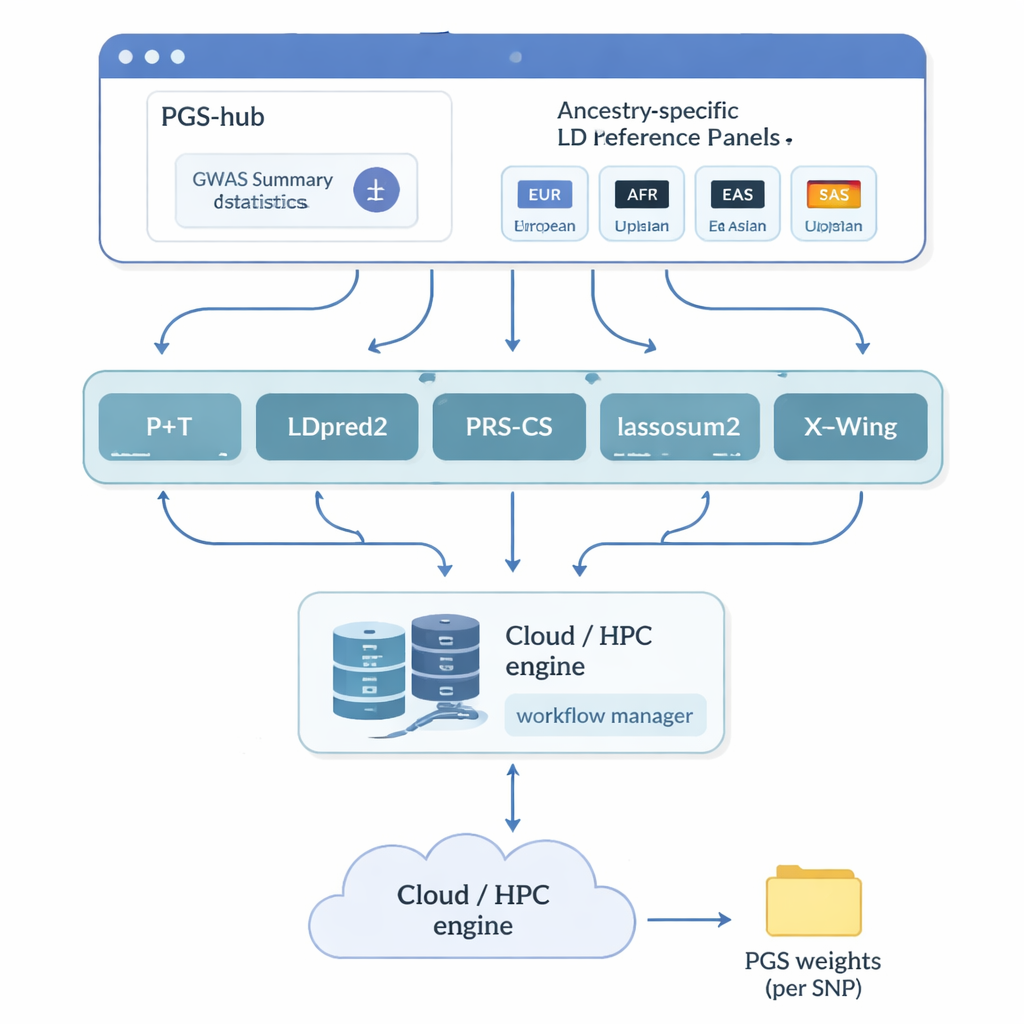
Poniendo a prueba 13 métodos de puntuación
Para ver qué enfoques funcionan mejor, el equipo comparó 13 métodos de vanguardia en 36 enfermedades y rasgos en casi 380.000 personas de ascendencia europea y poco más de 8.000 personas de ascendencia africana del UK Biobank. Evaluaron no solo qué tan bien cada puntuación predecía quién tenía una enfermedad o un valor superior en un rasgo, sino también cuánto tiempo de cómputo y memoria consumía cada método. En europeos, un método llamado LDpred2 proporcionó en general las puntuaciones más precisas, superando a menudo a los demás por un margen claro. Un puñado de alternativas—lassosum2, PRS-CS y SDPR—rindieron casi igual en muchos rasgos, mientras que algunos métodos más antiguos quedaron rezagados. Para rasgos como la estatura o la enfermedad de Crohn, las mejores puntuaciones explicaron una parte considerable del riesgo genético; para otros, como la función renal, todos los métodos tuvieron dificultades, reflejando señales genéticas subyacentes más débiles.
Perspectivas para poblaciones diversas y métodos combinados
Una preocupación importante en la predicción genética es que los métodos entrenados mayoritariamente en europeos pueden no transferirse bien a personas con otras ancestrías. Cuando los autores repitieron sus comparativas usando estudios genéticos de ascendencia africana, todos los métodos tuvieron un rendimiento inferior, lo que subraya la falta de estudios de gran tamaño en estas poblaciones. Aun así, LDpred2 y SDPR tendieron a estar entre las mejores opciones. El equipo también examinó enfoques "multiancestría" que combinan explícitamente información entre poblaciones. Aquí, una estrategia relativamente simple—combinar linealmente las mejores puntuaciones específicas por ancestría generadas por LDpred2 en una única puntuación LDpred2-multi—superó a modelos multiancestría más elaborados como PRS-CSx y X-Wing tanto para grupos europeos como africanos. Además, los autores demostraron que construir un conjunto (ensemble), que mezcla las puntuaciones más fuertes de múltiples métodos, mejoró aún más la predicción en todos los rasgos, especialmente para enfermedades con alta heredabilidad como la esquizofrenia y la enfermedad coronaria. 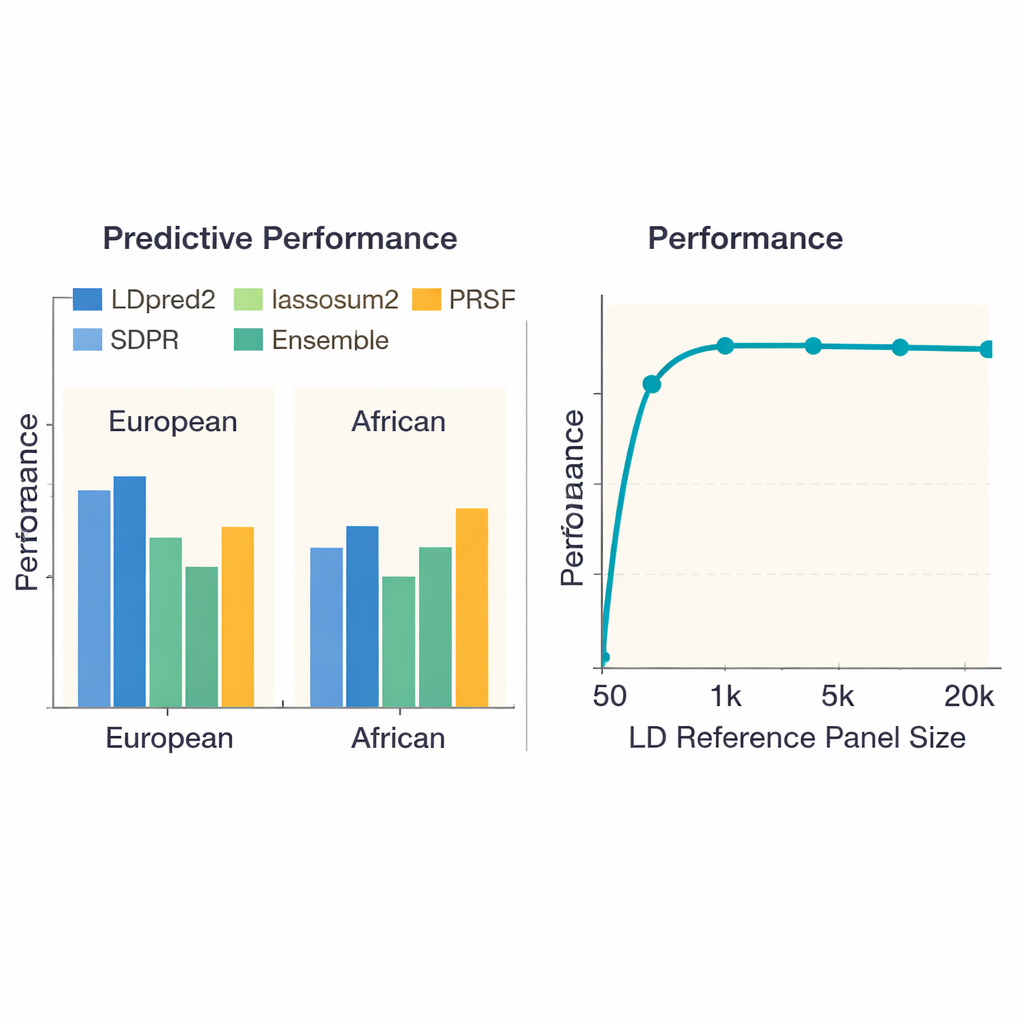
Cómo las elecciones de datos y los límites de cálculo moldean las puntuaciones
El estudio investigó cómo el tamaño del panel de referencia—el conjunto de personas usado para aprender cómo co-varían los marcadores de ADN cercanos—afecta el rendimiento. Cuando este panel era muy pequeño (menos de 1.000 individuos), las puntuaciones eran notablemente menos precisas. A medida que el panel creció hasta alrededor de 5.000 personas, el rendimiento mejoró de forma pronunciada y luego se estabilizó, lo que sugiere que paneles cada vez mayores aportan rendimientos decrecientes. Sorprendentemente, simplemente añadir más marcadores de ADN no siempre ayudó: usar alrededor de 6,6 millones de variantes a veces empeoró las predicciones respecto a usar un conjunto cuidadosamente seleccionado de aproximadamente 1,1 millones, probablemente porque los marcadores adicionales añadían más ruido que señal útil. Los autores también documentaron grandes diferencias en el coste computacional. Métodos simples como el clásico pruning-and-thresholding terminaron en menos de una hora por rasgo, mientras que algunos enfoques bayesianos requirieron cientos de horas de CPU, información relevante para proyectos grandes o grupos con recursos limitados.
Qué significa esto para la predicción futura basada en ADN
Para los no especialistas, el mensaje principal es que no todas las puntuaciones de riesgo genético se crean igual, y los detalles de cómo se construyen influyen fuertemente en quiénes se benefician de ellas. Este trabajo ofrece orientación práctica: métodos como LDpred2 y ensamblajes bien diseñados tienden a proporcionar las predicciones más fiables en grandes conjuntos de datos europeos, y las combinaciones multiancestría pueden superar a modelos cruzados más complejos. Al mismo tiempo, la caída de precisión en individuos de ascendencia africana subraya la urgente necesidad de estudios genéticos más grandes y diversos. Al agrupar muchos métodos en una única plataforma en línea estandarizada, PGS-hub reduce la barrera para que investigadores de todo el mundo generen y comparen puntuaciones poligénicas, un paso importante hacia el uso de estas puntuaciones de forma justa y eficaz en medicina.
Cita: Chen, X., Wang, F., Zhao, H. et al. Comprehensive benchmarking single and multi ancestry polygenic score methods with the PGS-hub platform. Nat Commun 17, 2014 (2026). https://doi.org/10.1038/s41467-026-68599-7
Palabras clave: puntuaciones poligénicas, predicción de riesgo genético, plataforma PGS-hub, genómica multiancestral, UK Biobank