Clear Sky Science · es
Descubrimiento a escala del genoma y fenotipado de transcritos no codificantes en A. fumigatus revela lncRNA con un papel en la sensibilidad a antifúngicos
Por qué importa un moho en nuestros hogares
La mayoría pensamos en el moho como una molestia en el pan o en rincones húmedos, pero un moho común, Aspergillus fumigatus, causa más de dos millones de muertes cada año: más que la malaria y el VIH juntos. Los médicos disponen de un arsenal limitado de fármacos antifúngicos para controlar este patógeno, y la resistencia a estos tratamientos está aumentando rápidamente. Este estudio explora una capa oculta del genoma del hongo: los ARN largos no codificantes, o lncRNA, que no producen proteínas pero pueden influir en cómo el hongo responde al tratamiento. Comprender estos elementos genéticos “silenciosos” podría abrir nuevas vías para predecir, rastrear y, en última instancia, contrarrestar la resistencia a antifúngicos.
Mensajes ocultos en el ADN fúngico
Tradicionalmente se ha pensado en los genes como fragmentos de ADN que codifican proteínas, las encargadas del trabajo celular. En la última década, los científicos han descubierto que vastas regiones del genoma se transcriben en moléculas de ARN que nunca llegan a ser proteínas. Estos ARN largos no codificantes pueden, no obstante, afectar el comportamiento celular, incluida la respuesta a fármacos. Aunque los lncRNA han sido cartografiados en humanos y en levaduras, en los mohos patógenos como A. fumigatus estaban en gran medida por explorar. Los autores se propusieron cambiar eso construyendo un catálogo a escala del genoma de estos transcritos misteriosos y preguntándose si alguno de ellos inclina la balanza entre sensibilidad y resistencia a los fármacos.
Escuchando al hongo bajo ataque farmacológico
Para descubrir lncRNA, el equipo expuso A. fumigatus a seis compuestos antifúngicos distintos, incluidos azoles de uso común que afectan la membrana celular fúngica, y luego secuenciaron todos los ARN producidos. Usando una canalización bioinformática personalizada, ensamblaron decenas de miles de transcritos y eliminaron sistemáticamente todo lo que correspondía a genes codificantes de proteínas conocidos o ARN domésticos cortos. Tras varias rondas de filtrado y curación manual, obtuvieron un conjunto de alta confianza de 1.089 nuevos ARN largos no codificantes distribuidos por el genoma. La mayoría se localizaba entre genes conocidos o se solapaba con ellos en la dirección opuesta, y en conjunto ampliaron la fracción del genoma fúngico conocida por ser activamente transcrita de aproximadamente dos tercios a más de cuatro quintas partes.
Respuestas coordinadas y puntos calientes conservados
Cuando los investigadores compararon cómo cambiaban estos lncRNA bajo distintas dosis de fármaco, encontraron que el hongo no los despliega al azar. En su lugar, los lncRNA se agruparon en alrededor de 15 patrones de respuesta distintos, algunos compartidos entre varios fármacos y otros únicos para tratamientos particulares. Por ejemplo, fármacos que atacan vías bioquímicas similares tendieron a activar firmas de lncRNA solapadas, mientras que un inhibidor de la síntesis de proteínas produjo muchas respuestas únicas. Muchos lncRNA estaban muy próximos a genes ya conocidos por influir en la sensibilidad a azoles, como los implicados en la captación de hierro o en la biosíntesis de ergosterol, un componente clave de las membranas fúngicas. En varios casos, un lncRNA cercano y un gen de respuesta al fármaco se regulaban al alza o a la baja de manera conjunta, insinuando que estos elementos no codificantes pueden ayudar a coordinar programas de supervivencia cruciales.
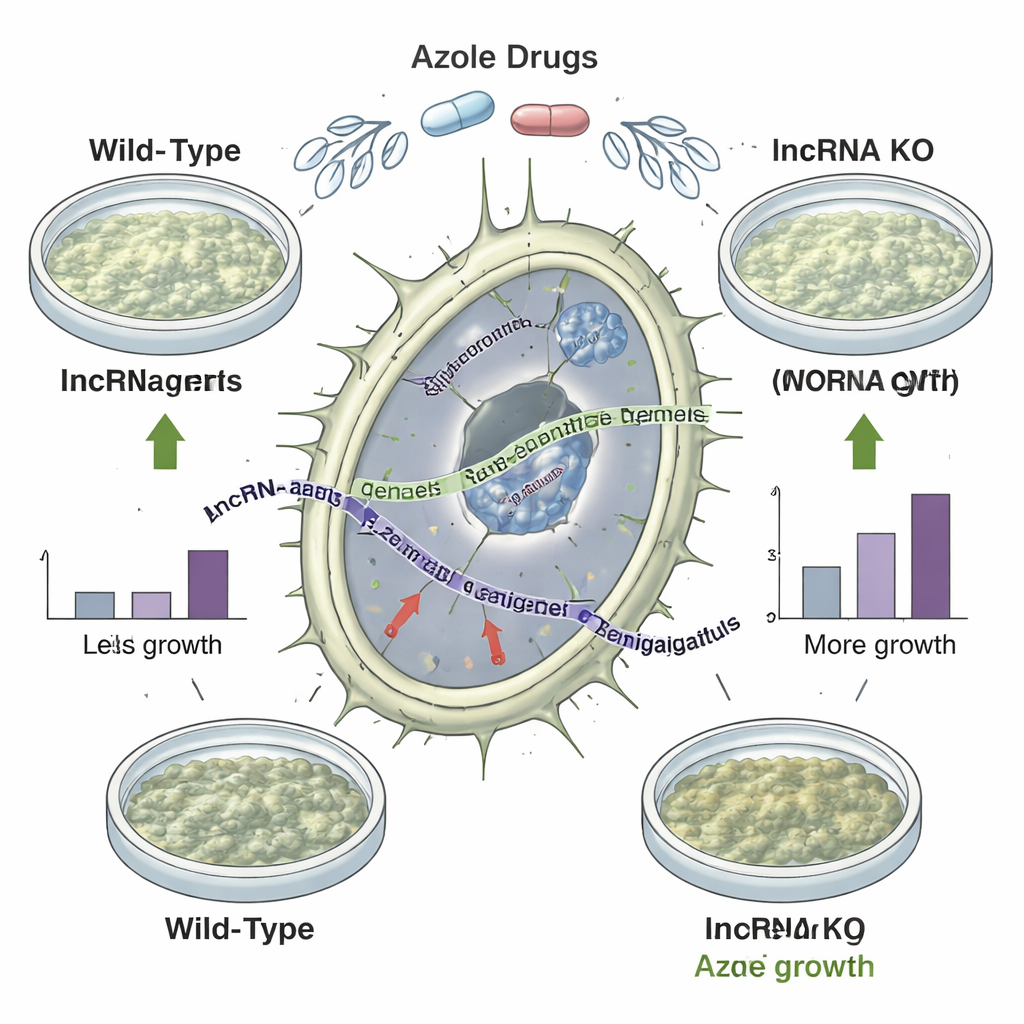
Eliminar genes “silenciosos” cambia la sensibilidad a fármacos
Catalogar lncRNA es una cosa; demostrar que importan es otra. El equipo eliminó 92 regiones lncRNA seleccionadas del genoma fúngico y comparó cómo crecían los mutantes bajo una serie de estreses, incluida alta temperatura, bajo hierro y exposición a tres azoles distintos. Sesenta mutantes mostraron cambios de aptitud específicos según la condición, y 35 en realidad crecieron mejor que la cepa original cuando se enfrentaron a azoles. Una cepa de eliminación destacada mostró un crecimiento mejorado frente a todos los azoles probados sin que ello supusiera un simple aumento de la expresión de genes codificantes de proteínas cercanos, lo que sugiere con fuerza que el lncRNA ausente por sí mismo restringía la tolerancia al fármaco. Al examinar numerosas aisladas clínicas y ambientales con perfiles de susceptibilidad conocidos, los autores también hallaron que la presencia o ausencia de ciertos genes lncRNA se correlacionaba con la facilidad con la que cada cepa era inhibida por los azoles.
Qué significa esto para combatir infecciones fúngicas mortales
Para no especialistas, el mensaje clave es que partes del genoma fúngico que antes se desestimaban como “basura” están moldeando activamente cuán peligroso puede ser A. fumigatus y cuán efectivos son nuestros fármacos contra él. Al construir el primer mapa integral de ARN largos no codificantes en este patógeno mayor y vincular docenas de ellos a cambios medibles en la respuesta a fármacos, este trabajo abre una nueva clase de marcadores genéticos y posibles dianas. A largo plazo, los lncRNA podrían ayudar a explicar por qué algunas cepas son intrínsecamente más difíciles de tratar, orientar el diseño de diagnósticos más eficaces e inspirar terapias que desarmen la resistencia no matando al hongo por completo, sino silenciando a los reguladores silenciosos que le permiten perdurar.
Cita: Weaver, D., Qi, T., Chown, H. et al. Genome-wide discovery and phenotyping of non-coding transcripts in A. fumigatus reveals lncRNAs with a role in antifungal drug sensitivity. Nat Commun 17, 1832 (2026). https://doi.org/10.1038/s41467-026-68543-9
Palabras clave: Aspergillus fumigatus, resistencia a antifúngicos, ARN largo no codificante, fármacos azoles, genómica fúngica