Clear Sky Science · es
Reduciendo imágenes médicas voluminosas mediante redes neuronales profundas que desacoplan forma y textura
Por qué importa reducir el tamaño de las imágenes médicas
Los hospitales modernos generan cantidades enormes de exploraciones 3D detalladas procedentes de máquinas de TC y RM. Estas imágenes son esenciales para el diagnóstico y la investigación, pero son inmensas: un solo conjunto de datos puede ocupar cientos de gigabytes, lo que hace que almacenar, compartir y analizar sea lento y caro. Este artículo presenta una nueva forma de reducir drásticamente estos archivos voluminosos conservando casi intacto el detalle diagnóstico, lo que podría acelerar el trabajo clínico, las consultas remotas y los estudios médicos a gran escala.
Dos tipos de información en una misma exploración
Cuando miras una exploración corporal, en realidad estás viendo dos tipos de información a la vez. Primero, la forma general de órganos y huesos: dónde curva la columna, el tamaño del hígado, la disposición del abdomen. Segundo, la textura fina: pequeñas variaciones de intensidad que sugieren tipos de tejido o enfermedades sutiles. Los autores sostienen que la mayoría de las herramientas de compresión existentes tratan estos dos ingredientes como si estuvieran mezclados, lo que hace la compresión más lenta y menos eficiente. Su idea clave es separar forma y textura y comprimir cada una con una estrategia adecuada.
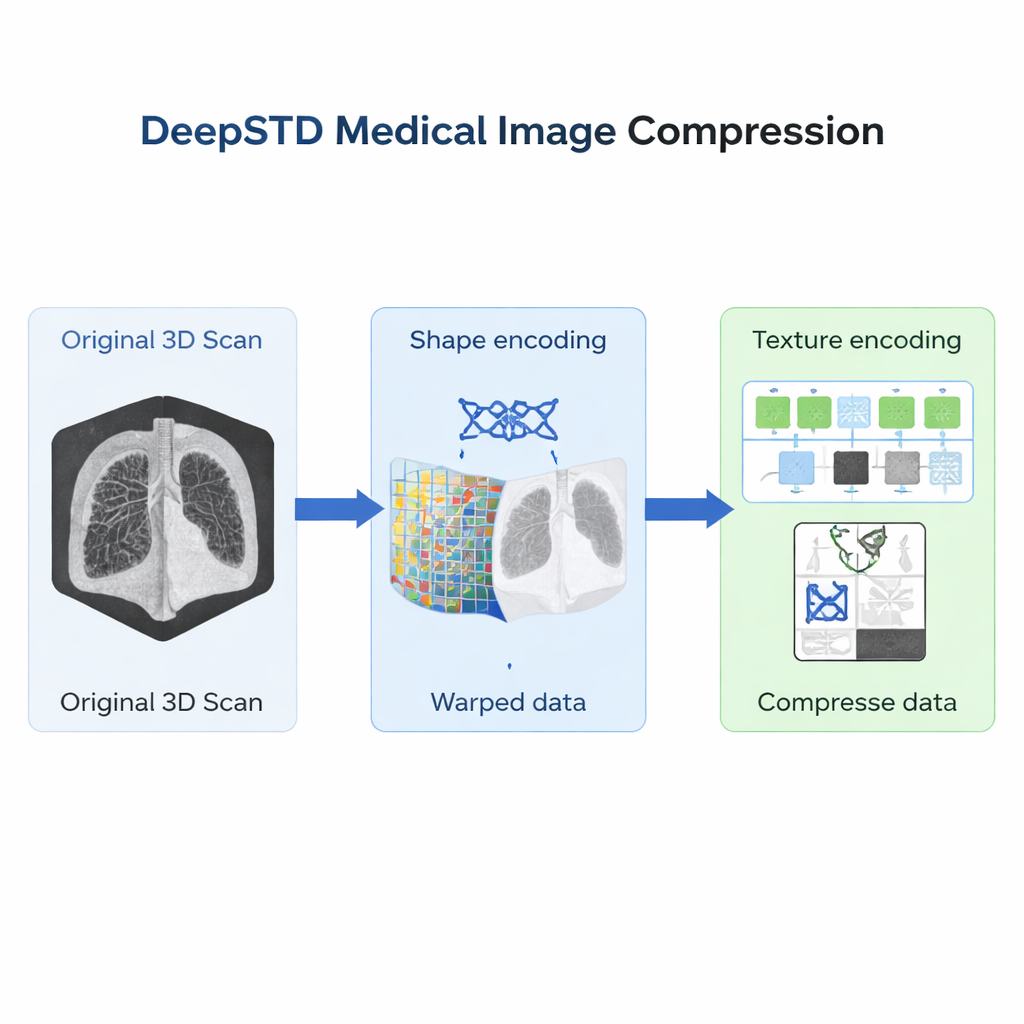
Un plano de referencia basado en plantillas del cuerpo
El nuevo método, llamado Compresión Desacoplada Forma-Textura (DeepSTD), comienza eligiendo una “plantilla” para una región corporal y tipo de imagen concretos, como TC de torso o RM abdominal. Esta plantilla funciona como un mapa estándar de esa anatomía. Para cada nueva exploración, DeepSTD primero determina cómo debe deformarse suavemente el cuerpo de esa persona para alinearse con la plantilla. Ese campo de deformación describe las diferencias de forma: quizá un paciente sea más alto, otro tenga el hígado ligeramente desplazado, o la columna tenga distinta curvatura. Los autores representan este campo de deformación usando un tipo compacto de red neuronal que sobresale en codificar deformaciones 3D suaves, de modo que la información de forma puede almacenarse eficientemente.
Capturar texturas sutiles tras la alineación
Una vez que una exploración se ha transformado para coincidir con la forma de la plantilla, lo que queda son principalmente diferencias de textura: los patrones sutiles de intensidad que distinguen a un paciente de otro. Como todas las exploraciones están ahora en el mismo esquema geométrico, estas texturas resultan más sencillas de modelar y comprimir. DeepSTD alimenta los datos alineados a una segunda red neuronal que combina capas convolucionales (buenas para detalles locales) con bloques Transformer (buenos para captar estructura a largo alcance) en plena 3D. Esta red aprende, a partir de muchos ejemplos, qué detalles de textura son comunes y cuáles son únicos, permitiendo almacenar solo lo esencial en un “código latente” compacto. El archivo comprimido final es simplemente el código de forma más el código de textura.
Pruebas en colecciones reales de TC y RM
El equipo evaluó DeepSTD en grandes conjuntos de datos públicos, incluidos escaneos detallados de columna por TC y volúmenes abdominales de RM. Lo compararon con herramientas tradicionales (como JPEG, HEVC y estándares de vídeo más recientes) y con métodos neuronales de última generación. A niveles de compresión de hasta 256 veces más pequeños que los archivos originales, DeepSTD preservó tanto la similitud a nivel de píxel como características médicamente importantes, como segmentaciones automáticas de órganos, con mucho mejor rendimiento que las alternativas. Al mismo tiempo, codificó exploraciones decenas e incluso más de cien veces más rápido que el mejor sistema neuronal previo basado únicamente en representaciones neuronales implícitas. En términos prácticos, un conjunto de datos de TC que antes tardaba días en descargarse con una conexión lenta podría transferirse en menos de media hora con DeepSTD, con casi ninguna pérdida visible.
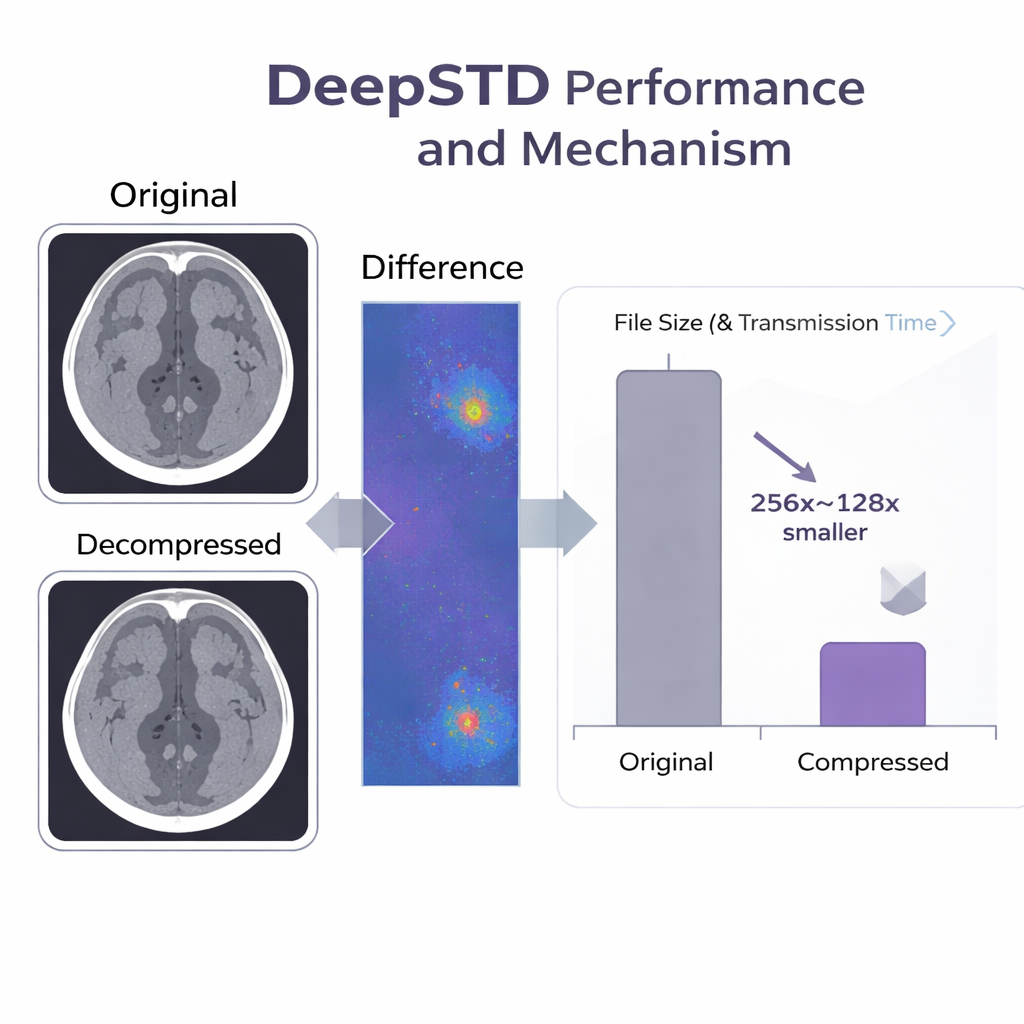
Diseñado para el uso clínico cotidiano
Más allá de los números, los autores diseñaron DeepSTD con las restricciones del mundo real en mente. El método puede usar múltiples tarjetas gráficas en paralelo, reduciendo aún más los tiempos de codificación y decodificación para grandes colecciones. Permite un control preciso sobre la tasa de compresión, de modo que los hospitales puedan ajustar el tamaño de los archivos al almacenamiento disponible o al ancho de banda de la red. El sistema también funciona cuando los datos de entrenamiento son limitados, gracias a aumentos de datos inteligentes y técnicas de “destilación de conocimiento” que transfieren lo aprendido desde conjuntos de datos más ricos. Pruebas en radiografías de tórax adicionales y en exploraciones de RM de cerebro y rodilla sugieren que el enfoque es aplicable de forma amplia a distintos tipos de imagen.
Qué significa esto para pacientes y médicos
Para un público no especializado, la conclusión es simple: DeepSTD es una forma más inteligente de empaquetar imágenes médicas. Al codificar por separado cómo está formada la anatomía de un paciente y cómo se ven sus tejidos, comprime exploraciones más de cien veces mientras conserva la información de la que dependen médicos y algoritmos. Esto podría facilitar enormemente almacenar registros de imagen a largo plazo, compartir datos entre hospitales y realizar estudios de IA a gran escala, todo sin sacrificar la calidad diagnóstica.
Cita: Yang, R., Xiao, T., Cheng, Y. et al. Reducing bulky medical images via shape-texture decoupled deep neural networks. Nat Commun 17, 1573 (2026). https://doi.org/10.1038/s41467-026-68292-9
Palabras clave: compresión de imágenes médicas, aprendizaje profundo, datos de TC y RM, representación neuronal, almacenamiento de datos de salud