Clear Sky Science · es
Categorización de 34 métodos computacionales para detectar genes espacialmente variables a partir de datos de transcriptómica espacialmente resuelta
Por qué la ubicación importa para nuestros genes
Nuestros cuerpos están formados por células que no solo difieren en lo que hacen, sino también en el lugar que ocupan dentro de los tejidos y órganos. Las nuevas tecnologías de "transcriptómica espacial" pueden ahora leer qué genes están activos conservando al mismo tiempo la dirección de cada célula en un mapa tisular. Este artículo de revisión explica cómo los científicos detectan genes cuya actividad cambia según el lugar—los llamados genes espacialmente variables—y por qué ponerse de acuerdo sobre cómo encontrarlos es vital para comprender el cáncer, el funcionamiento cerebral y muchas otras enfermedades.
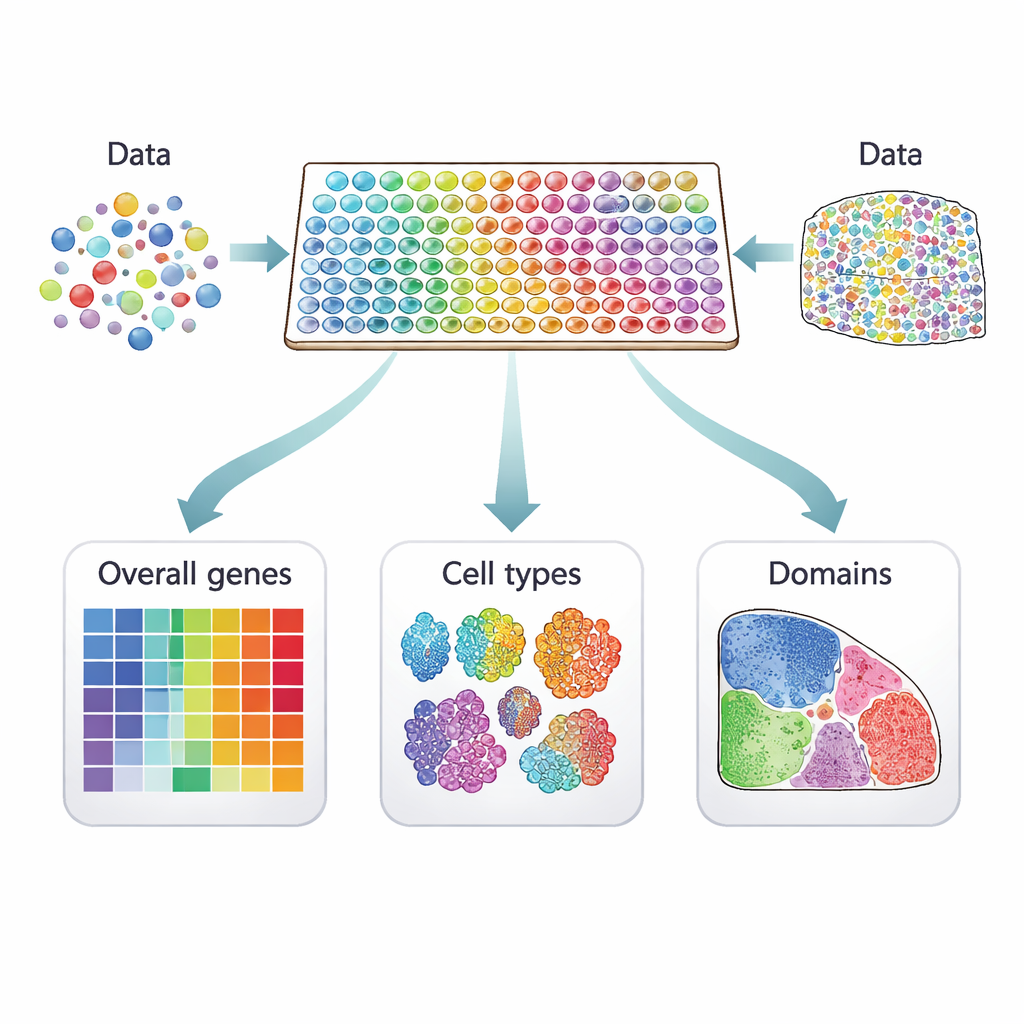
De células dispersas a mapas vivos
Los estudios tradicionales de una sola célula miden la actividad génica en miles de células individuales pero pierden información sobre de dónde provenían esas células. La transcriptómica espacial rellena este vacío al medir la actividad génica directamente en cortes finos de tejido. Cada medida está ligada a un "punto" en el corte, que puede contener una célula o varias, según la tecnología. Los métodos basados en imagen localizan unas pocas centenas de genes seleccionados con un detalle espacial muy alto, mientras que las plataformas basadas en secuenciación capturan casi todos los genes con menor resolución. Juntas, estas aproximaciones convierten una sección de tejido en un mapa colorido de actividad génica que puede revelar estructuras ocultas, como capas en el cerebro o regiones dentro de un tumor.
Tres tipos de genes sensibles a la ubicación
Se han propuesto muchos métodos computacionales para identificar genes que muestran patrones significativos en estos mapas tisulares, pero no todos buscan lo mismo. Los autores clasifican 34 métodos actuales en tres categorías claras. El primer grupo busca genes espacialmente variables "globales", cuya actividad cambia a lo largo del tejido de cualquier manera no aleatoria—quizá formando rayas, cúmulos o gradientes. El segundo grupo se centra en genes espaciales "específicos de tipo celular" que varían dentro de un único tipo de célula, ayudando a distinguir, por ejemplo, subtipos de neuronas o distintos estados de células inmunitarias. El tercer grupo rastrea genes "marcadores de dominio" que se activan fuertemente en regiones o capas particulares, lo que los convierte en etiquetas útiles para esas zonas tisulares.
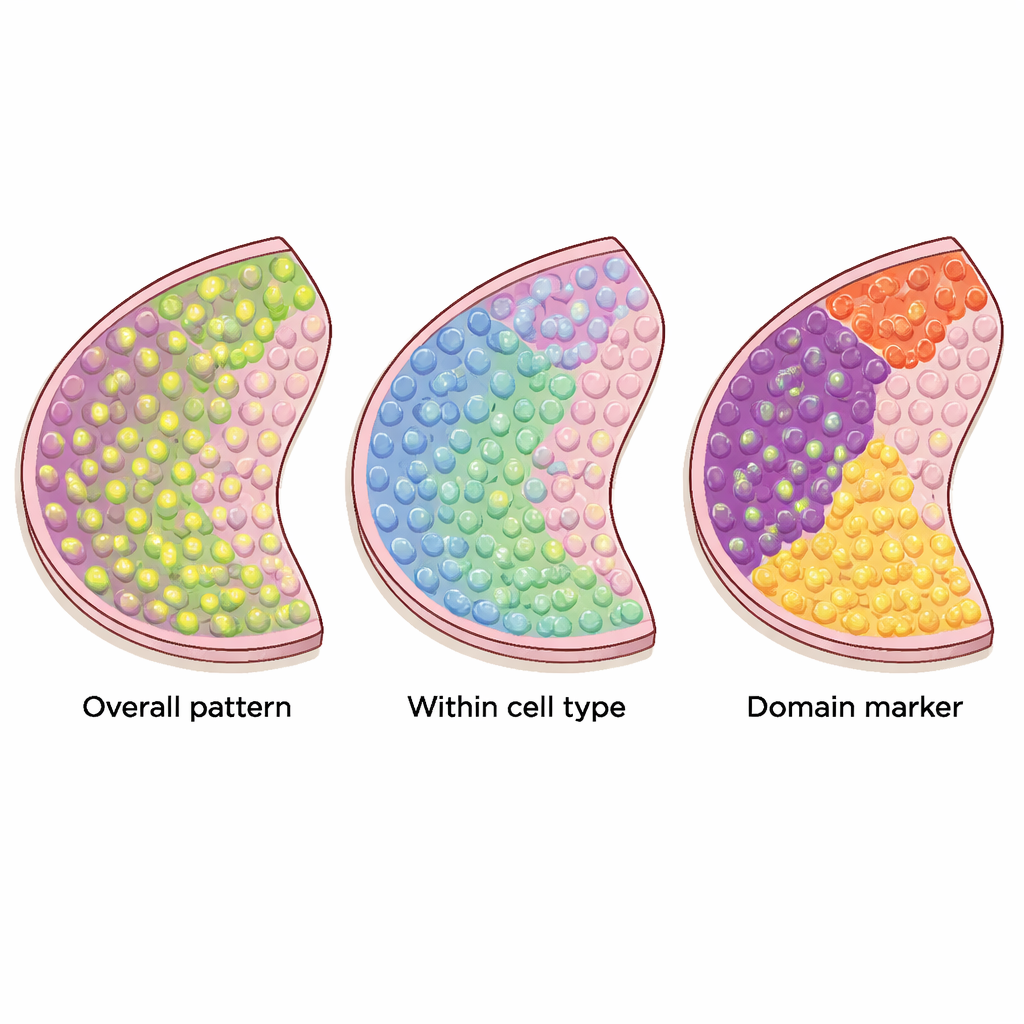
Diferentes herramientas para diferentes patrones
La revisión explica cómo funcionan estos métodos en el fondo. Algunos tratan el corte tisular como puntos en un espacio bidimensional regular y usan "kernels" matemáticos para buscar patrones como manchas u ondas. Otros primero enlazan ubicaciones cercanas en una red, o grafo, y luego preguntan si la expresión alta tiende a agruparse a lo largo de los enlaces de ese grafo. Ciertas herramientas se apoyan en pruebas estadísticas formales con tasas de error bien definidas, mientras que otras clasifican principalmente los genes según la fuerza con la que destacan sus patrones. Los métodos que se dirigen a patrones muy específicos pueden ser potentes cuando los datos coinciden con sus expectativas, pero pueden pasar por alto formas más irregulares o complejas, como las que se observan en muchos cánceres. También existe un compromiso entre flexibilidad y velocidad: algunos enfoques escalan a cientos de miles de puntos, mientras que otros tienen dificultades con conjuntos de datos muy grandes.
Lo que estos genes pueden revelar
Una vez identificados los genes espacialmente variables, se convierten en materia prima para descubrimientos biológicos más profundos. Los genes espaciales globales suelen usarse como primer filtro para reducir el número de genes antes de agrupar los puntos en "dominios espaciales": regiones cuyos cells comparten perfiles de expresión similares. Estos dominios pueden coincidir con estructuras tisulares conocidas, sugerir nuevas subregiones o resaltar vecindarios celulares distintos, como frentes invasivos en tumores. Los genes marcadores de dominio ayudan luego a explicar qué hace única a cada región y pueden reutilizarse para etiquetar estructuras similares en otras muestras. Mientras tanto, los genes espaciales específicos de tipo celular prometen una visión más fina de cómo ciertos tipos celulares varían a lo largo de un tejido, lo que puede iluminar las interacciones tumor‑inmunes o circuitos especializados en el cerebro.
Retos y el camino por delante
Los autores subrayan que ningún método único es el mejor para todas las tareas, y que comparar herramientas de forma justa requiere pensar con cuidado qué tipo de gen espacial está realmente diseñado para encontrar cada método. Piden mejores bancos de pruebas usando conjuntos de datos realistas, estándares estadísticos más claros para evitar descubrimientos falsos y nuevos enfoques que respeten las diferencias entre tecnologías y tipos de tejido. Para los no expertos, el mensaje clave es que los genes espacialmente variables convierten listas planas de genes en mapas vivos, vinculando la actividad molecular con la estructura tisular. Formas robustas de detectar e interpretar estos genes serán fundamentales para convertir la transcriptómica espacial en hallazgos prácticos sobre el desarrollo, la función cerebral y la enfermedad.
Cita: Yan, G., Hua, S.H. & Li, J.J. Categorization of 34 computational methods to detect spatially variable genes from spatially resolved transcriptomics data. Nat Commun 16, 1141 (2025). https://doi.org/10.1038/s41467-025-56080-w
Palabras clave: transcriptómica espacial, genes espacialmente variables, patrones de expresión génica, microambientes tisulares, genómica computacional