Clear Sky Science · de
Label-freie virtuelle Mehrfachfärbung ganzer Objektträger mittels dualer Anregungs-Photonenabsorptions-Fernsensorikmikroskopie
Gewebe sehen, ohne es zu zerstören
Wenn Ärztinnen und Ärzte Krankheiten wie Krebs oder Nierenschäden diagnostizieren, verlassen sie sich häufig auf dünne Gewebeschnitte, die mit chemischen Farbstoffen behandelt wurden. Diese Färbungen machen verborgene Strukturen sichtbar, verändern das Präparat jedoch dauerhaft oder verbrauchen es — ein Problem, wenn nur eine winzige Biopsie vorliegt. Diese Studie stellt eine Methode vor, Gewebe „digital zu färben“ mithilfe von Licht und künstlicher Intelligenz, sodass vertraute pathologische Bilder entstehen, ganz ohne jegliche Farbstoffe.
Warum traditionelle Färbungen Fluch und Segen zugleich sind
Chemische Färbungen wie Hämatoxylin und Eosin oder spezielle Farbstoffe für Kollagen, Kohlenhydrate und Nierenstrukturen sind die Arbeitspferde der modernen Pathologie. Sie machen transparentes Gewebe sichtbar und sind unverzichtbar zur Diagnose von Krebs, Infektionen und Organschäden. Diese Färbungen sind jedoch destruktiv: derselbe Schnitt kann in der Regel nicht erneut gefärbt oder für weiterführende Tests verwendet werden, und mehrere Färbungen verbrauchen schnell kostbares Biopsiematerial. Jede Färbung erfordert zudem sorgfältige Laborarbeit, geschultes Personal und kann Stunden oder Tage zur Diagnosestellung hinzufügen.
Lichtbasierte Bildgebung, die das Gewebe direkt liest
Die Forschenden verwendeten ein spezialisiertes Mikroskop namens Photon Absorption Remote Sensing (PARS), das misst, wie Gewebemoleküle Energie aus ultraviolettem Licht absorbieren und abgeben. In dieser Arbeit kombinierten sie zwei UV‑Farben, eine mit kürzerer und eine mit etwas längerer Wellenlänge, und bestrahlten abwechselnd dieselbe Stelle im Gewebe. Jeder Puls erzeugt sowohl wärmebedingte Signale als auch schwache, glühähnliche Emissionen, so dass vier unterschiedliche Informationskanäle aus derselben Position gewonnen werden. Eine Wellenlänge ist besonders empfindlich für DNA in Zellkernen, die andere hebt Kollagen, Elastin, rote Blutkörperchen und dunkle Pigmente wie Melanin hervor. Zusammen kartieren sie Kerne, Stützgewebe, Blut und Pigmente auf eine Weise, die dem ähnelt — und sie in manchen Aspekten übertrifft —, was Pathologen mit klassischen Färbungen sehen. 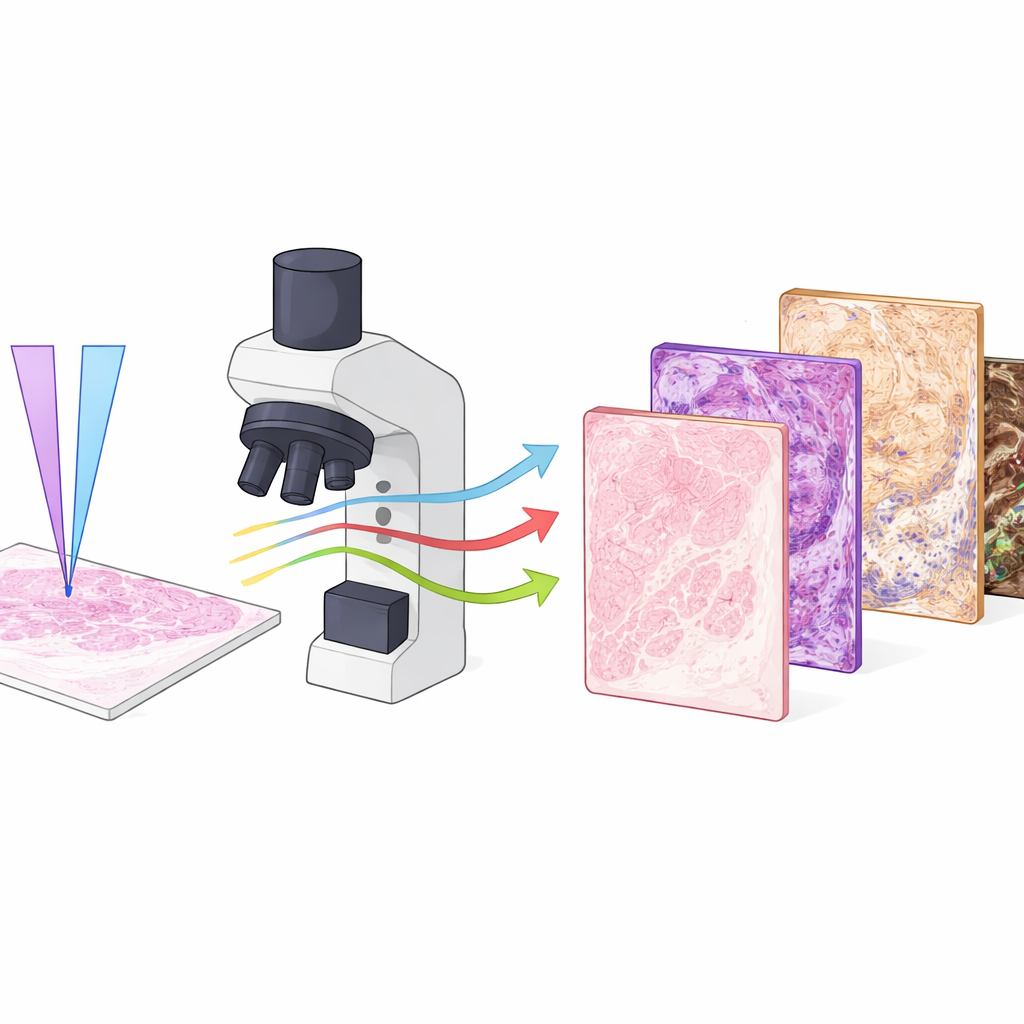
Computern beibringen, virtuelle Färbungen zu malen
Reiche optische Signale zu sammeln ist nur die halbe Miete; die andere Hälfte besteht darin, sie in Bilder zu verwandeln, die wie standardmäßige gefärbte Objektträger aussehen. Dazu nutzte das Team ein tiefes Lernverfahren namens RegGAN. Zuerst bildeten sie unlackierte (ungefärbte) Gewebe mit PARS ab, anschließend färbten sie denselben Objektträger chemisch und scannten ihn mit einem normalen Hellfeldscanner. Nach sorgfältiger Registrierung dieser Bildpaare trainierten sie neuronale Netze, um die mehrkanaligen PARS‑Bilder in Versionen zu transformieren, die bestimmte Färbungen nachahmen — einschließlich Routine‑Hämatoxylin‑Eosin sowie Masson‑Trichrom, PAS und Jones‑Methenamin‑Silber. Für jede Färbung wurden separate Modelle trainiert, sodass ein einzelner, label‑freier Eingangs‑Schnitt später je nach Bedarf auf mehrere Arten „virtuell nachgefärbt“ werden kann.
Was die virtuellen Schnitte zeigen
Über menschliche und Maus‑Gewebe hinweg — einschließlich Nierenkarzinomen, Melanomen, Pilzinfektionen der Haut und normalen Organen — folgten die virtuellen Färbungen ihren chemischen Gegenstücken eng. Tumorränder, Kernformen, kollagenreiche Narben, rote Blutkörperchen, Pilzhyphen und feine Nierenstrukturen erschienen mit hoher Treue, wenn beide UV‑Wellenlängen gemeinsam verwendet wurden. Quantitative Bildqualitätsmaße bestätigten, dass die Kombination der beiden Anregungen bessere Ergebnisse lieferte als die Verwendung einer einzelnen, insbesondere für Strukturen wie Kollagen, Blutkörperchen und Pilze, die vom zusätzlichen Kontrast der längeren Wellenlänge profitieren. In einer kleinen, verblindeten Studie bewerteten drei erfahrene Pathologen sowohl reale als auch virtuelle Bilder überwiegend als gut oder exzellent für visuelle Diagnostikqualität, und sie konnten nicht zuverlässig unterscheiden, welche Bilder chemisch gefärbt und welche virtuell waren.
Stärken, Grenzen und zukünftiges Potenzial
Obwohl vielversprechend, ist die Methode noch nicht bereit, Routinescanner zu ersetzen. Das aktuelle PARS‑System ist langsam und benötigt Stunden, um eine Fläche abzudecken, die ein klinischer Scanner in Minuten erfassen kann, und alle Daten stammten von einem Bildgebungssystem und einem Färbelabor. Die Bewertung konzentrierte sich auf visuelle Ähnlichkeit und ausgewählte messbare Merkmale statt auf umfassende klinische Entscheidungsfindung über viele Patientengruppen und Zentren hinweg. Dennoch bietet der Ansatz einen einzigartigen Vorteil: Da die label‑freie Bildgebung das Gewebe nicht beschädigt, kann derselbe Schnitt später mit traditionellen Farbstoffen gefärbt oder für molekulare Tests verwendet werden, und aus einem einzigen Scan lassen sich mehrere virtuelle Färbungen erzeugen. 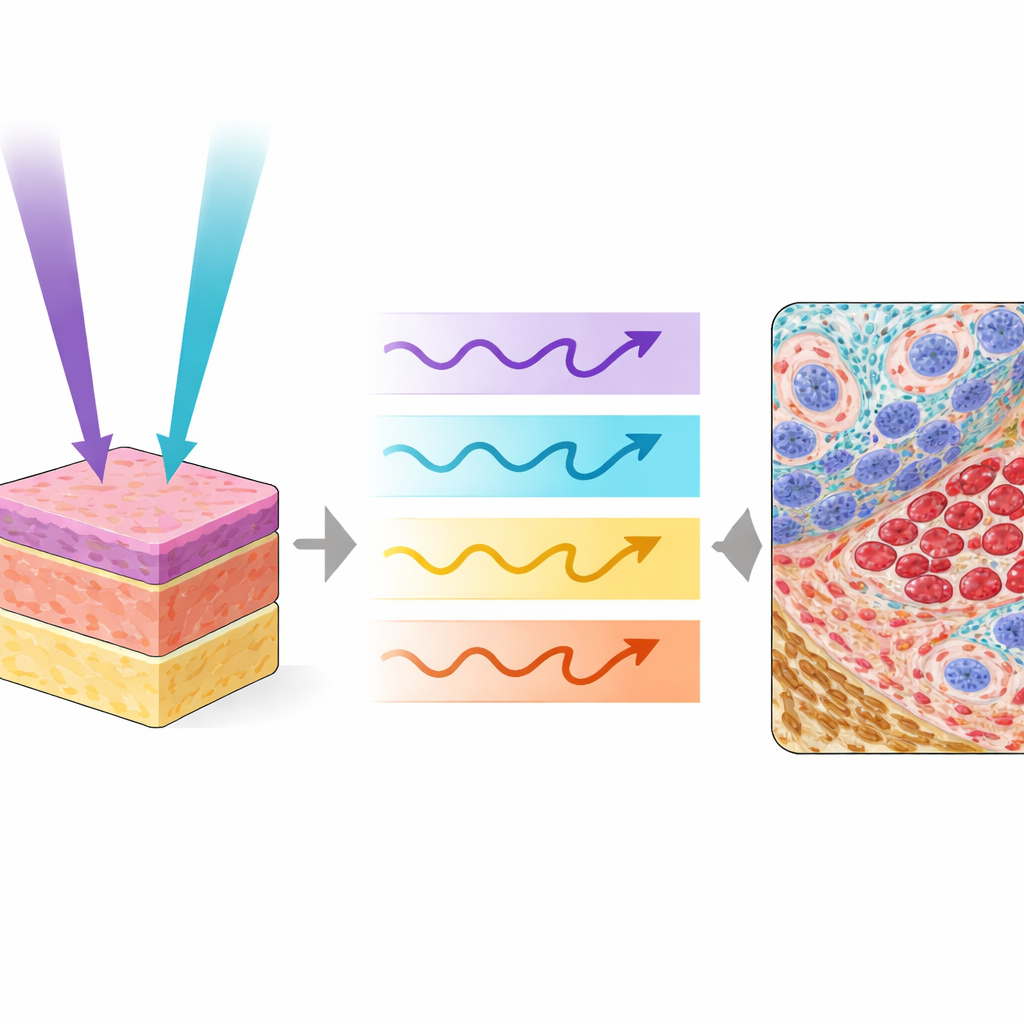
Was das für Patientinnen, Patienten und Ärztinnen und Ärzte bedeutet
Vereinfacht gesagt zeigt diese Studie, dass es möglich ist, Gewebe allein mit Licht „zu lesen“ und anschließend künstliche Intelligenz zu nutzen, um die vertrauten Farben und Muster zu rekonstruieren, denen Pathologen vertrauen — einschließlich mehrerer verschiedener Färbungen aus einem einzigen Schnitt. Das duale PARS‑System liefert genug Informationen, um Kerne, Stützgewebe, Blut, Pigmente und spezialisierte Nierenstrukturen virtuell hervorzuheben, ohne einen Tropfen Farbstoff zu verwenden. Mit schnellerer Hardware und größeren, multizentrischen Studien könnte diese Technologie zu einer leistungsfähigen Ergänzung der Standardpathologie werden, kostbare Biopsien schonen und Pathologen eine reichhaltigere, nicht‑destruktive Sicht auf Erkrankungen bieten.
Zitation: Tweel, J.E.D., Ecclestone, B.R., Tummon Simmons, J.A. et al. Label-free whole slide virtual multi-staining using dual-excitation photon absorption remote sensing microscopy. npj Imaging 4, 22 (2026). https://doi.org/10.1038/s44303-026-00154-x
Schlüsselwörter: virtuelle Färbung, label‑freie Mikroskopie, digitale Pathologie, Ultraviolett‑Bildgebung, Tiefes Lernen in der Histologie