Clear Sky Science · de
Genomische Landschaft der antimikrobiellen Resistenz in Indien: Ergebnisse einer multispezies-Überwachungsstudie
Warum Superkeime in Indien uns alle betreffen
Antibiotikaresistente „Superkeime“ sind ein wachsende globale Sorge, doch wir wissen in vielen Regionen der Welt noch überraschend wenig darüber, wie diese Erreger entstehen und sich ausbreiten. Diese Studie untersucht gefährliche Krankenhausbakterien aus Indien genau und entschlüsselt ihre gesamte DNA, um zu verstehen, wie sie unseren stärksten Medikamenten trotzen. Die Ergebnisse zeigen nicht nur, was diese Mikroben so schwer zu töten macht, sondern prüfen auch, ob schnelle DNA‑basierte Methoden verlässlich langsamere Labortests ersetzen können — eine Frage, die die Behandlung von Infektionen überall beeinflussen könnte.
Blick auf Krankenhausinfektionen
Die Forscher sammelten 266 Bakterienproben von schwer kranken Patienten in großen Krankenhäusern in Nord‑ und Westindien zwischen 2022 und 2024. Die meisten Proben stammten aus Blut, daneben auch aus Urin und Lungeninfektionen; die Mehrheit kam aus Intensivstationen, wo Patienten besonders gefährdet sind. Das Team konzentrierte sich auf bekannte Problemkeime wie Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, methicillinresistente Staphylococcus aureus (MRSA) und vancomycinresistente Enterococcus (VRE). Für jede Probe lagen bereits Standard-Antibiotikaempfindlichkeitstests vor, bei denen Bakterien im Labor Medikamenten ausgesetzt werden, um zu prüfen, welche Wirkstoffe noch wirken. Die Wissenschaftler sequenzierten dann die Genome der Bakterien, um das vollständige Repertoire an Resistenzgenen zu kartieren, und verglichen, was die DNA vorhersagte, mit dem, was tatsächlich in den Testkammern beobachtet wurde.
Wenn Gene und Labortests nicht übereinstimmen
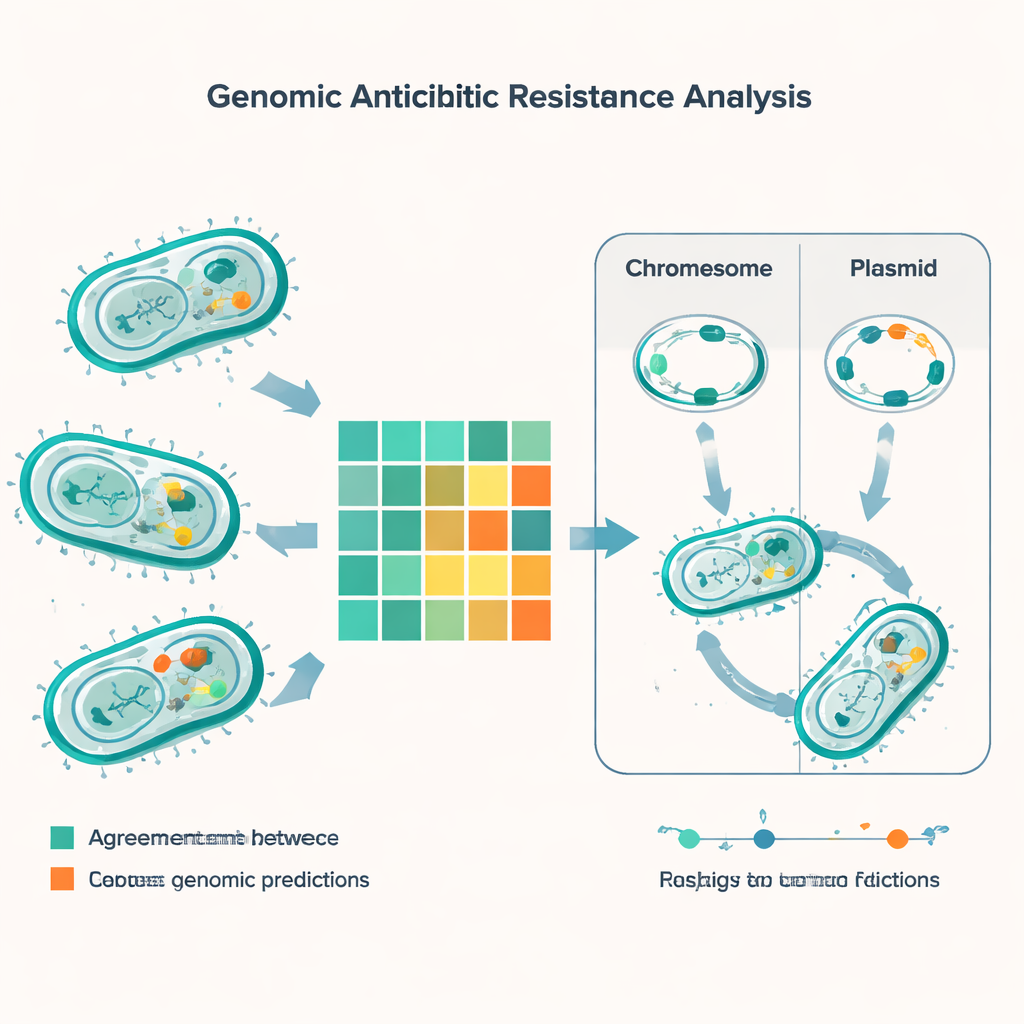
Durch den Abgleich genetischer Vorhersagen mit Labordaten für 56 verschiedene Antibiotika führte die Studie mehr als 5.000 Vergleiche durch. In den meisten Fällen stimmten die DNA‑basierten Methoden und die traditionellen Tests überein, doch fast 600 Unstimmigkeiten traten auf. Die häufigste Fehlerart war, dass das Genom‑Tool Resistenzen vorhersagte, während der Labortest noch Empfindlichkeit anzeigte. Das trat häufig bei Wirkstoffen wie Minocyclin, Colistin und Gentamicin auf, besonders bei E. coli. Die umgekehrte Fehlerart — also wenn der Labortest Resistenz zeigte, die Gene das jedoch nicht eindeutig erklärten — war seltener, aber bedenklicher, weil so Resistenzen übersehen werden könnten. Solche „sehr schweren“ Abweichungen zeigten sich besonders bei darmassoziierten Bakterien, den Enterokokken, vor allem für weit verbreitete penicillinähnliche Medikamente und die Kombination Trimethoprim‑Sulfamethoxazol.
Verborgene Arsenale in bakterieller DNA
Die genomische Untersuchung deckte ein dichtes Arsenal an Resistenzgenen über die wichtigsten Spezies hinweg auf. Jedes der häufigen gramnegativen Pathogene trug mindestens ein Beta‑Laktamasegen, das Penicilline und verwandte Wirkstoffe abbauen kann, und viele Stämme hatten mehrere dieser Gene gleichzeitig. Berüchtigte Ursachen wie NDM‑Typ Carbapenemasen — die Reserveantibiotika neutralisieren — waren weit verbreitet in E. coli, Klebsiella, Acinetobacter und Pseudomonas. Die Studie fand außerdem Gene, die Bakterien das Überleben gegenüber starken „Peptid“‑Antibiotika wie Colistin erleichtern, zusammen mit dem klassischen mecA‑Gen, das MRSA gegen Methicillin resistent macht, sowie Vancomycin‑Resistenzclustern in Enterokokken. Durch den Vergleich von DNA‑Fingerabdrücken, sogenannten Sequenztypen, verband das Team einige dieser Resistenzgene mit bekannten Hochrisikolinien, die sich bereits in Indien und weltweit verbreiten.
Genaustausch über mobile DNA
Ein entscheidender Teil der Geschichte liegt nicht nur darin, welche Gene die Bakterien tragen, sondern wo diese Gene sich befinden. Viele Resistenzgene sitzen auf kleinen DNA‑Kreisen, sogenannten Plasmiden, die Bakterien wie Tauschkarten weitergeben können. Mit spezialisierter Software sagten die Forschenden etwa 1.400 Plasmide in den Proben voraus, mit besonders hoher Vielfalt in E. coli und Klebsiella. In diesen Arten war ein großer Anteil der Resistenzgene — einschließlich mehrerer kritischer Beta‑Laktamasen — plasmidkodiert, was ihren Austausch zwischen Stämmen und sogar zwischen Arten erleichtert. Andere Resistenzmerkmale waren fest im bakteriellen Chromosom verankert, sodass sie bestehen bleiben können, selbst wenn Plasmide verloren gehen. Das Team katalogisierte außerdem mobile genetische Elemente — kurze DNA‑Segmente, die herumspringen und Resistenzgene mit sich tragen können — und hob damit eine weitere Route für die rasche Ausbreitung hervor.
Was das für zukünftige Therapien bedeutet
Für Nichtfachleute ist die Kernbotschaft, dass das Lesen bakterieller DNA den Kampf gegen Superkeime stark unterstützen kann, die Technologie aber noch nicht perfekt ist. Die genomischen Werkzeuge neigten dazu, Resistenzen zu „überdiagnostizieren“, was sicherer ist, als gefährliche Stämme zu übersehen, aber Ärztinnen und Ärzte dazu verleiten könnte, stärkere Medikamente als nötig einzusetzen. Zugleich zeigten einige Fälle, dass Labortests Resistenzen erkannten, die aktuelle Genkataloge nicht vollständig erklärten, was auf wichtige Wissenslücken hinweist. Indem die Studie eine detaillierte Karte von Resistenzgenen, Plasmiden und mobilen Elementen in indischen Krankenhäusern erstellt, legt sie ein Fundament für bessere, schnellere DNA‑basierte Diagnostik und eine informiertere Antibiotikaverwendung — nicht nur in Indien, sondern überall dort, wo Superkeime die moderne Medizin bedrohen.
Zitation: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Schlüsselwörter: antimikrobielle Resistenz, Genomsequenzierung, Krankenhausinfektionen, antibiotikaresistente Bakterien, plasmidvermittelte Resistenz