Clear Sky Science · de
IdentifiHR sagt homologe Rekombinationsdefizienz beim hochgradig serösen Ovarialkarzinom anhand der Genexpression vorher
Warum diese Forschung für Patientinnen mit Eierstockkrebs wichtig ist
Bei Menschen mit hochgradig serösem Eierstockkrebs, einer der tödlichsten Formen von Eierstockkrebs, können Therapieentscheidungen über Leben und Tod entscheiden. Etwa die Hälfte dieser Tumoren weist eine Schwäche in der DNA-Reparatur auf, was sie besonders empfindlich gegenüber bestimmten Wirkstoffen macht, den PARP-Inhibitoren. Die Herausforderung besteht darin, für jede Patientin zu bestimmen, ob ihr Tumor diese Schwäche hat. Diese Studie stellt IdentifiHR vor, ein neues Werkzeug, das Muster der Genaktivität ausliest – nicht nur DNA‑Mutationen – um vorherzusagen, welche Tumoren eine fehlerhafte DNA‑Reparatur aufweisen und am meisten von diesen zielgerichteten Therapien profitieren könnten.
Von DNA‑Narben zu Mustern der Genaktivität
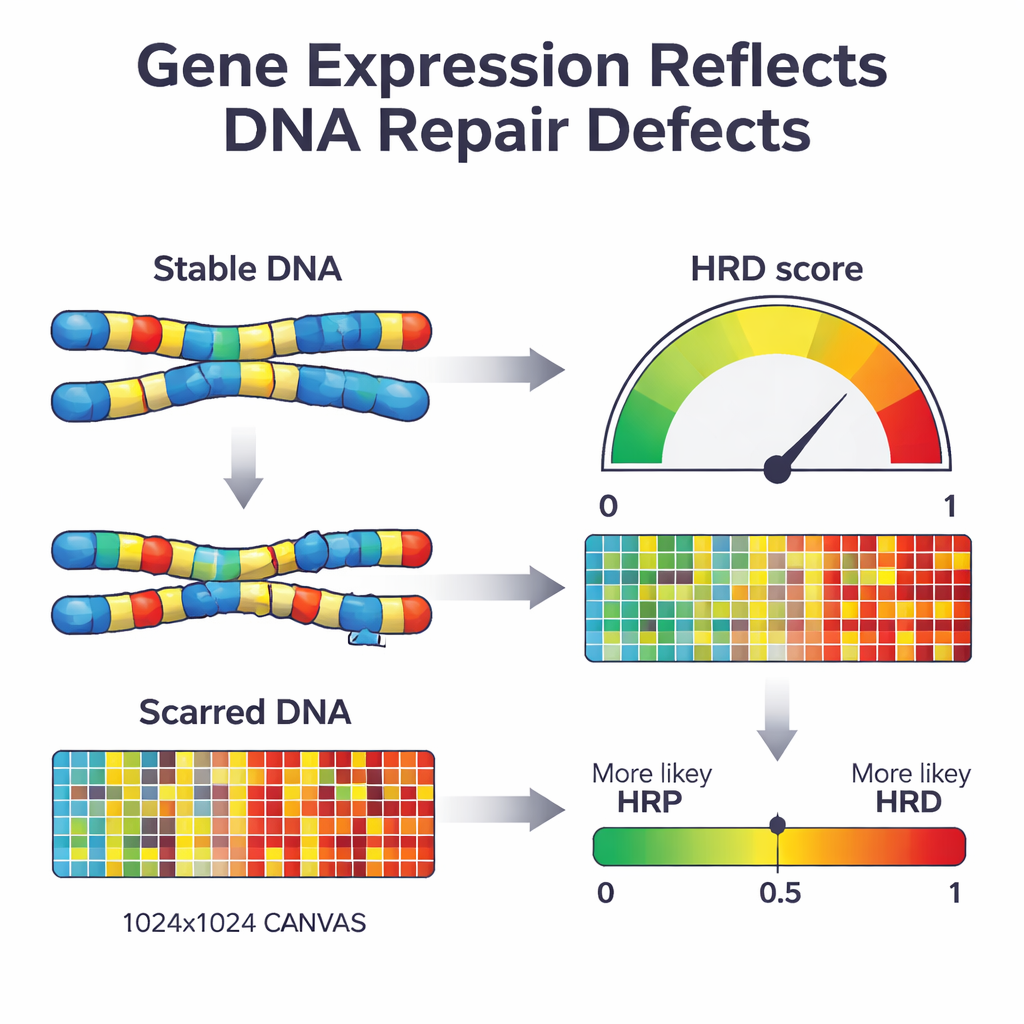
Wenn eine Zelle einen wichtigen Reparaturweg, die homologe Rekombination, verliert, beginnt sie, DNA mit fehleranfälligeren Methoden zu reparieren. Mit der Zeit hinterlässt das charakteristische „Narben“ im Genom – fehlende Abschnitte, zusätzliche Kopien und gebrochene Chromosomenstücke. Bestehende klinische Tests suchen diese Narben direkt in der DNA oder nach spezifischen Mutationen in Schlüsseln, etwa BRCA1 und BRCA2. Obwohl leistungsfähig, erfordern diese Tests umfangreiche DNA-Sequenzierung und erfassen nicht immer den aktuellen Reparaturstatus des Tumors. Die Autorinnen und Autoren fragten, ob eine andere biologische Ebene – das Muster von ein- oder ausgeschalteten Genen im Tumor – als Live‑Anzeiger für diese Schäden dienen und zur Klassifikation in reparaturdefizient oder reparaturkompetent verwendet werden könnte.
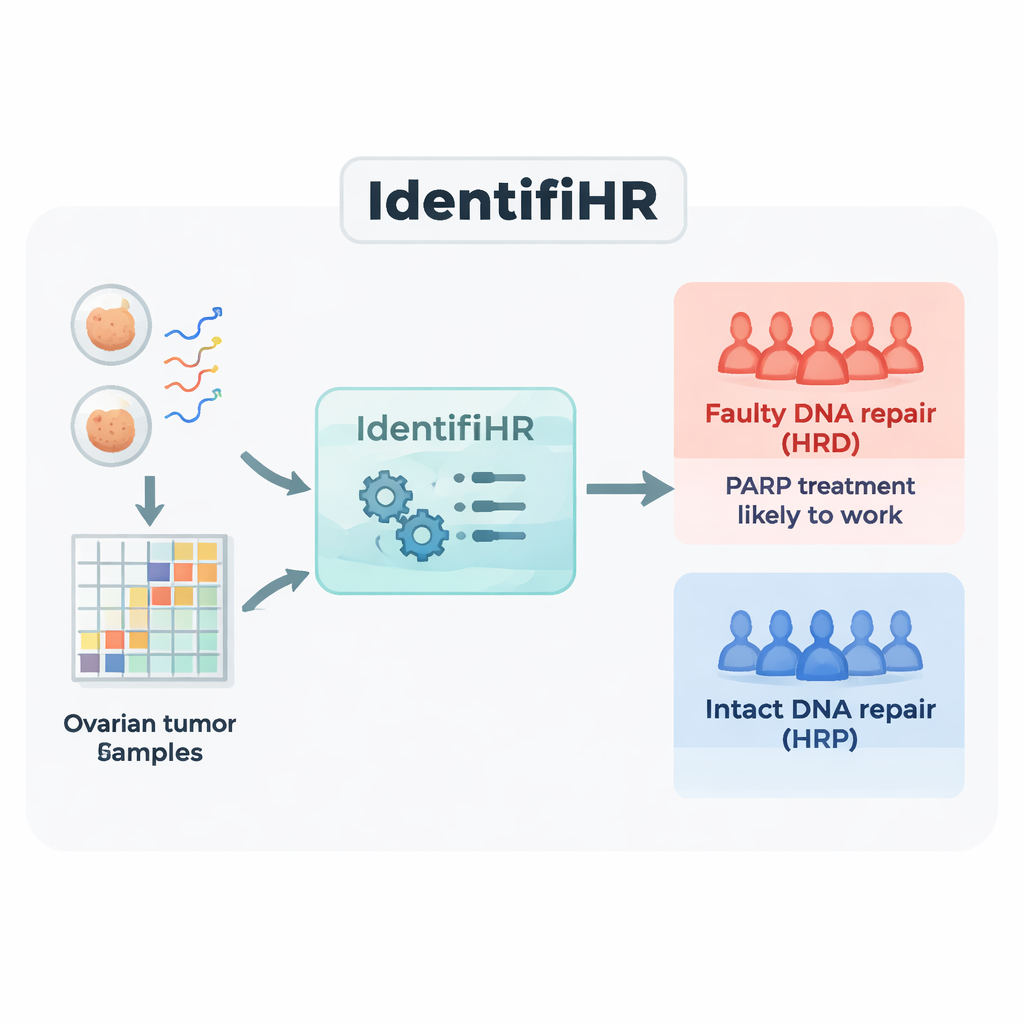
Aufbau eines genbasierten Prädiktors: IdentifiHR
Das Team begann mit RNA‑Sequenzierungsdaten von 361 Ovarialtumoren aus einer großen öffentlichen Ressource, dem Cancer Genome Atlas. RNA‑Sequenzierung misst, welche Gene in jeder Probe aktiv sind und in welchem Ausmaß. Sie teilten die Tumoren in eine Trainingsgruppe und eine Testgruppe ein und klassifizierten jeden Fall als reparaturdefizient (HRD) oder reparaturkompetent (HRP) anhand des aktuellen DNA‑basierten Standards, der mehrere Maße genomischer Narben kombiniert. In den Trainingsproben identifizierten sie 2.604 Gene, deren Aktivität sich konsistent zwischen HRD‑ und HRP‑Krebsen unterschied. Viele dieser Gene lagen in Genomregionen, die bereits dafür bekannt sind, bei reparaturdefekten Tumoren wiederholt verloren oder gewonnen zu werden, was zeigt, dass das Signal der Genaktivität die zugrunde liegenden DNA‑Schäden widerspiegelt.
Eine 209‑Gen‑Signatur, die den Reparaturstatus abbildet
Als Nächstes verwendeten die Forschenden einen maschinellen Lernansatz, die penalised logistic regression, um die Liste der 2.604 Gene auf die informativste Menge zu komprimieren. Das resultierende Modell, das sie IdentifiHR nannten, stützt sich auf die Aktivität von nur 209 Genen, um abzuschätzen, wie wahrscheinlich es ist, dass ein Tumor reparaturdefizient ist. Interessanterweise ist nur eines dieser Gene ein klassisches DNA‑Reparaturgen; die meisten sind gewöhnliche Gene, deren Aktivität durch weiterreichende Veränderungen der Chromosomenstruktur verändert ist. IdentifiHR gibt nicht einfach ein Ja‑oder‑Nein aus – es liefert einen Wahrscheinlichkeitswert, der glatt mit dem zugrunde liegenden DNA‑basierten Schadensscore zusammenläuft und die Idee widerspiegelt, dass Reparaturdefizienz eher ein Kontinuum als ein strikter Ein/Aus‑Zustand ist.
Test des Werkzeugs in mehreren Patientenkohorten
Die Autorinnen und Autoren prüften IdentifiHR sorgfältig in drei unabhängigen Datensätzen, die nie im Training verwendet worden waren. In dem zurückgehaltenen Teil des Cancer Genome Atlas unterschied das Modell HRD‑ von HRP‑Tumoren in etwa 85 % der Fälle korrekt. Es erreichte eine ähnlich gute Leistung – rund 86 % Genauigkeit – in einer separaten australischen Studie, die nicht nur Primärtumoren, sondern auch Proben aus Obduktionen, aus Aszitesflüssigkeit und aus normalen Eileitern enthielt, dem wahrscheinlichen Entstehungsort vieler dieser Krebsarten. In jeder normalen Eileiterprobe sagte IdentifiHR intakte DNA‑Reparatur korrekt voraus. Das Werkzeug funktionierte auch mit „pseudobulked“ Einzelzell‑Daten, bei denen tausende einzelner Krebszellen rechnerisch zu einer Bulk‑Probe zusammengefasst wurden, und erreichte erneut etwa 84 % Genauigkeit. In diesen Tests entsprach oder übertraf IdentifiHR die Leistung mehrerer bestehender genbasierter Methoden, die ursprünglich für andere Krebsarten oder zur Vorhersage verwandter Schadenscores entwickelt worden waren.
Wie sich Forschung und Versorgung dadurch verändern könnten
Da IdentifiHR auf RNA‑Daten läuft, die oft kostengünstiger und leichter zu erheben sind als ganze Genom‑DNA‑Profile, bietet es eine praktische Möglichkeit für Forschende — und möglicherweise künftig auch Klinikern — den DNA‑Reparaturstatus zu schätzen, wenn nur Genexpressionsdaten vorliegen. Das Modell ist als Open‑Source‑R‑Paket veröffentlicht, sodass jede Gruppe mit geeigneten Sequenzierungsdaten es anwenden kann. Zwar ersetzt es noch nicht die Goldstandard‑DNA‑Tests, und seine Fähigkeit, subtilere Veränderungen wie die Wiederherstellung der Reparatur zu erfassen, muss noch untersucht werden, doch IdentifiHR liefert eine starke neue Perspektive darauf, welche Ovarialtumoren am wahrscheinlichsten auf PARP‑Inhibitoren und ähnliche Wirkstoffe ansprechen. Für Patientinnen rückt diese Arbeit das Feld näher an präzisere, biologisch fundierte Therapieentscheidungen, die an das tatsächliche Verhalten ihrer Krebszellen angepasst sind.
Zitation: Weir, A.L., Lee, S.C., Li, M. et al. IdentifiHR predicts homologous recombination deficiency in high-grade serous ovarian carcinoma using gene expression. Commun Med 6, 119 (2026). https://doi.org/10.1038/s43856-026-01387-y
Schlüsselwörter: Eierstockkrebs, DNA-Reparatur, homologe Rekombinationsdefizienz, Genexpression, maschinelles Lernen