Clear Sky Science · de
Analyse der Wirt-Genexpression zur Erkennung bakterieller und viraler Ätiologie bei hospitalisierten Kindern mit vermuteter schwerer Infektion
Warum diese Forschung für Kinder mit schweren Infektionen wichtig ist
Wenn ein Kind mit hohem Fieber und schwerem Krankheitsbild ins Krankenhaus kommt, müssen Ärzte schnell entscheiden, ob die Ursache eine bakterielle Infektion ist, die üblicherweise Antibiotika erfordert, oder eine virale Infektion, die oft von selbst abklingt. Die heute verfügbaren Tests sind weit davon entfernt, perfekt zu sein, und viele Kinder erhalten „vorsorglich“ Antibiotika. In dieser Studie wurde untersucht, ob sich das Ablesen der körpereigenen Signale im Blut – konkret Muster der Genaktivität – dazu eignet, bakterielle und virale Infektionen bei Kindern mit vermuteter schwerer Erkrankung genauer zu unterscheiden.
Das körpereigene Alarmsystem statt des Erregers ansehen
Traditionelle Tests versuchen, den Erreger direkt zu finden, etwa durch Anzucht von Bakterien aus dem Blut oder den Nachweis viraler Nukleinsäuren mittels PCR. Diese Methoden können langsam sein, den tatsächlichen Verursacher übersehen und häufig harmlose „Bystander“-Viren nachweisen, besonders bei Kleinkindern, die oft respiratorische Viren tragen. Die Forscher konzentrierten sich stattdessen auf die Wirtsantwort: welche Gene in den Blutzellen eines Kindes während einer Infektion an- oder abgeschaltet werden. Da das Immunsystem unterschiedlich auf Bakterien und Viren reagiert, kann das Muster aktiver Gene wie ein Fingerabdruck des Infektionstyps wirken, selbst wenn der Erreger schwer zu finden oder zu interpretieren ist.
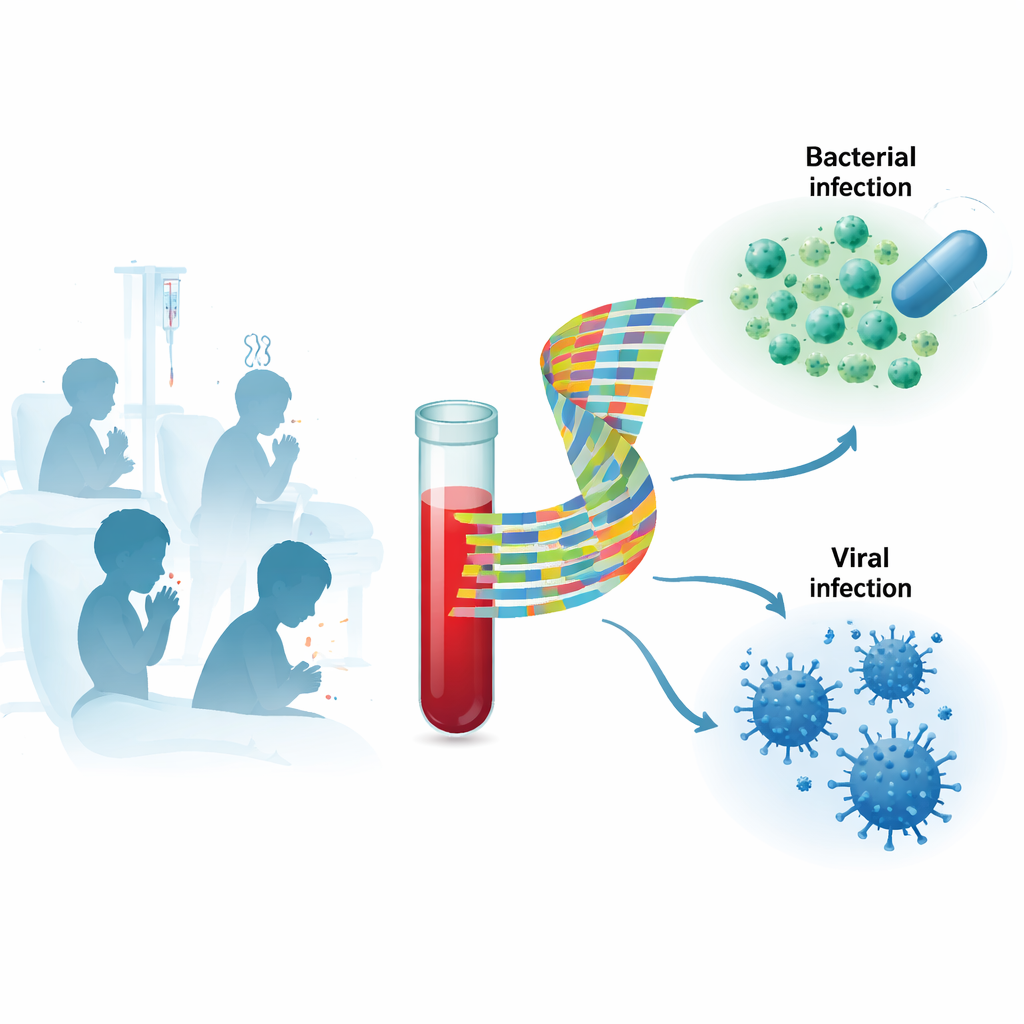
Untersuchung einer realistischen Mischung kranker Kinder
Das Team rekrutierte 268 Kinder im Alter von 4 Wochen bis 16 Jahren in Finnland. Die Mehrheit wurde mit dem Verdacht auf eine schwere Infektion stationär aufgenommen; eine kleinere Gruppe hatte mildere bestätigte Virusinfektionen und wurde ambulant behandelt, und einige waren gesunde Kontrollen. Die Ärzte sammelten detaillierte klinische Daten, standardmäßige Laborwerte wie C-reaktives Protein und Procalcitonin sowie Nasenabstriche auf respiratorische Viren. Blutproben dienten zur Messung der Aktivität von Tausenden Genen mittels RNA-Sequenzierung. Die Erkrankung jedes Kindes wurde sorgfältig als bakteriell, viral, gemischt bakteriell–viral, unklar oder nichtinfektiös klassifiziert und für zentrale Analysen auch vereinfacht in „bakteriell“ oder „viral“ gruppiert.
Entdeckung eines einfachen Signals mit zwei Genen
Als die Wissenschaftler zunächst die Genaktivität im Blut aller Kinder breit untersuchten, stellten sie fest, dass die Proben in mehrere Cluster fielen, die jedoch nicht sauber den Labels „bakteriell“ versus „viral“ entsprachen. Gesunde Kinder unterschieden sich deutlich von solchen mit eindeutigen bakteriellen Infektionen, während die Genmuster bei klaren Virusinfektionen variabler waren. Um diese Komplexität zu durchdringen, teilten die Forscher die Patienten in zwei Gruppen: eine Entdeckungsgruppe mit Atemwegsinfektionen und eine Validierungsgruppe mit anderen Infektionstypen, etwa Nieren- oder Hautinfektionen. In der Entdeckungsgruppe suchten sie nach sehr kleinen Genkombinationen, die bakterielle von viralen Erkrankungen am besten unterscheiden, und testeten dann, wie gut dieselben Kombinationen in der Validierungsgruppe funktionierten.
Sie identifizierten ein besonders vielversprechendes Genpaar, TSPO und SECISBP2. Zusammen konnten die Aktivitätsniveaus dieser beiden Gene bakterielle (einschließlich gemischter bakteriell–viraler) Infektionen von reinen Virusinfektionen mit hoher Genauigkeit trennen. Gemessen als Fläche unter der ROC-Kurve erreichte dieses Zwei‑Gen‑Signal 0,93 in der Entdeckungsgruppe und 0,81 in der Validierungsgruppe; über beide Gruppen zusammen betrug der Wert 0,87, mit einer Sensitivität von etwa 77 % und einer Spezifität von etwa 87 %. Anders ausgedrückt erkannte das Signal die meisten bakteriellen Fälle korrekt, während es selten virale Infektionen fälschlich als bakteriell einstufte. In dieser Studienpopulation schnitt es zudem besser ab als weit verbreitete Blutmarker wie C-reaktives Protein und Procalcitonin.

Welche Rolle diese beiden Gene haben könnten
TSPO ist an der Art und Weise beteiligt, wie Mitochondrien – die Energiezentralen der Zelle – mit Stress umgehen und Entzündungen mitsteuern. Frühere Arbeiten haben eine höhere TSPO-Aktivität mit schwereren bakteriellen Infektionen und Sepsis in Verbindung gebracht, und Experimente deuten darauf hin, dass die Stimulation von Immunzellen mit bakteriellen Komponenten TSPO erhöhen und die Freisetzung entzündungsfördernder Moleküle anregen kann, die beim Abtöten von Erregern helfen. In dieser Studie war TSPO tendenziell bei bakteriellen Infektionen stärker aktiv und bei viralen Infektionen weniger aktiv. SECISBP2 hingegen hilft dem Körper, selenhaltige Proteine zu synthetisieren, die antioxidative, immunologische und antivirale Funktionen haben. Selenium unterstützt bekanntermaßen Immunzellen und kann die Schwere mancher Viruskrankheiten mindern. Hier zeigte SECISBP2‑Aktivität allgemein eine höhere Ausprägung bei Virusinfektionen, was zur Vorstellung passt, dass der Körper selenbezogene Abwehrmechanismen bei Virusbekämpfung hochfährt.
Was das für die zukünftige Versorgung bedeuten könnte
Die Autoren betonen, dass ihre Ergebnisse vorläufig, aber vielversprechend sind. Ein einfacher Test, der nur diese beiden Gene aus einer kleinen Blutprobe abliest, könnte eines Tages Notfallteams dabei helfen, fundierter zu entscheiden, ob ein sehr krankes Kind Antibiotika benötigt. Da das Zwei‑Gen‑Signal nicht nur bei Lungeninfektionen, sondern auch bei anderen schweren Infektionen funktionierte, könnte es in einem breiten Spektrum realer Fälle nützlich sein – einschließlich solcher, in denen bakterielle und virale Erreger gleichzeitig nachgewiesen werden. Die Studie wurde jedoch in einem einzigen Land durchgeführt und beruhte auf den besten verfügbaren, aber nicht perfekten Definitionen von bakterieller versus viraler Erkrankung. Größere Studien in verschiedenen Kliniken und schnell einsetzbare, praxisgerechte Versionen des Tests werden notwendig sein, bevor er den Alltag leiten kann. Dennoch zeigt diese Arbeit, dass die körpereigene Genaktivität der Schlüssel zu klügerem Antibiotikaeinsatz und besserer Versorgung von Kindern mit schweren Infektionen sein könnte.
Zitation: Piri, R., Valta, M., Lempainen, J. et al. Host gene expression analysis in the detection of bacterial and viral etiology in children hospitalized with a suspected severe infection. Commun Med 6, 204 (2026). https://doi.org/10.1038/s43856-025-01370-z
Schlüsselwörter: pädiatrische Infektionen, Genexpression, bakteriell versus viral, Antibiotika-Stewardship, Diagnostik der Wirtsantwort