Clear Sky Science · de
Netzwerk-Hierarchie-Entropie zur Quantifizierung von Graphenunterschieden
Warum winzige Unterschiede in Netzwerken wichtig sind
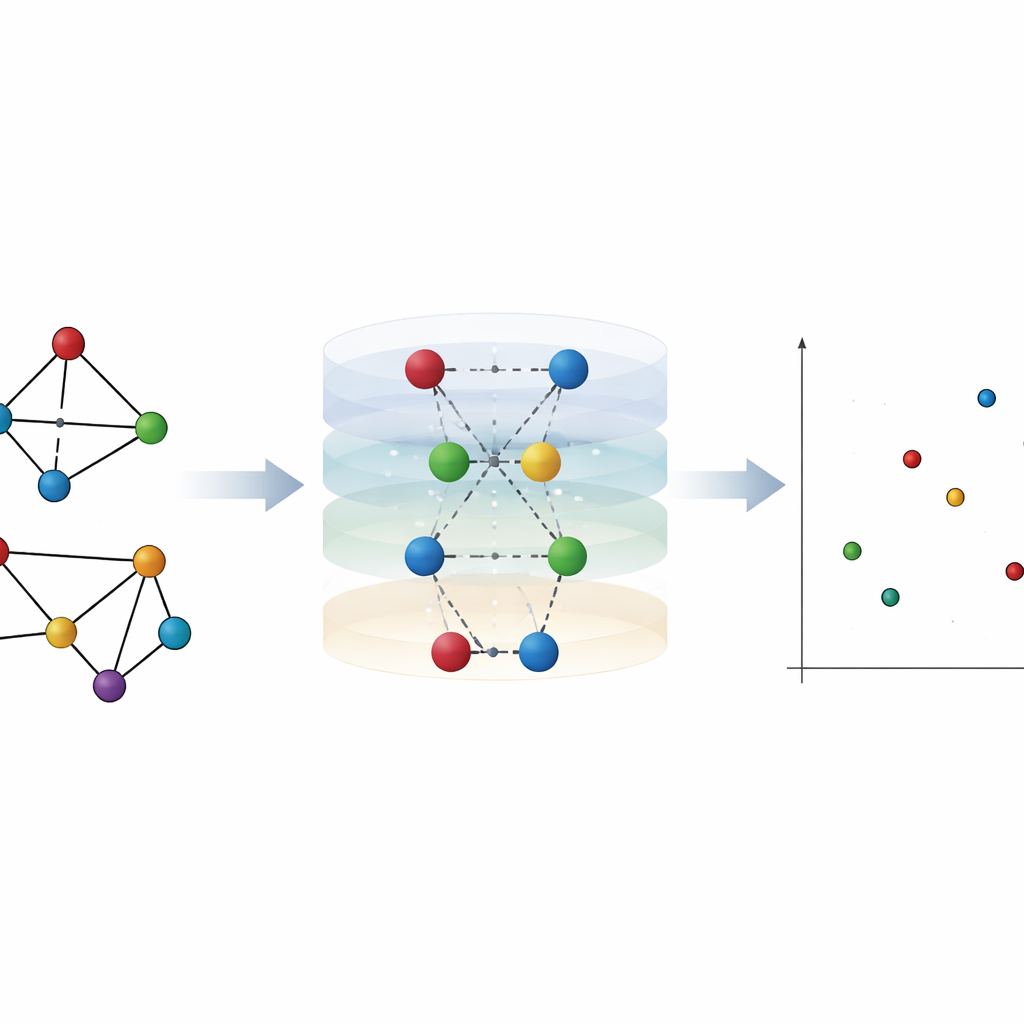
Von Freundschaften in sozialen Medien über Flugrouten bis hin zu Proteinstrukturen lassen sich viele Systeme als Netzwerke aus Knoten und Verbindungen darstellen. Doch zu entscheiden, wann zwei solche Netzwerke wirklich unterschiedlich sind, ist überraschend schwierig — insbesondere, wenn sie auf den ersten Blick ähnlich erscheinen. Diese Arbeit stellt eine neue Methode vor, um zu messen, wie unterschiedlich zwei Netzwerke tatsächlich sind, indem nicht nur einzelne Punkte (Knoten), sondern auch die Verbindungen (Kanten) und deren Zusammenspiel berücksichtigt werden. Die Methode, genannt Netzwerk-Hierarchie-Entropie, erkennt subtile strukturelle Veränderungen, die andere Werkzeuge übersehen, und hilft sogar dabei, Enzym-Proteine von Nicht-Enzymen zu unterscheiden.
Netzwerke Schicht für Schicht betrachten
Um ein Netzwerk zu verstehen, betrachten die Autoren zunächst, wie viele Schritte entlang von Verbindungen jeder Knoten von jedem anderen entfernt ist. Um einen gewählten Knoten herum lassen sich andere Knoten in Schichten gruppieren: unmittelbare Nachbarn, Nachbarn der Nachbarn usw. Diese „Hierarchie“ um einen Knoten beschreibt, wie Einfluss oder eine Infektion sich durch das Netzwerk ausbreiten könnte. Der Haken ist, dass zwei sehr unterschiedliche Netzwerke dieselbe Knoten-Ebenen-Struktur teilen können, sodass diese Sicht allein nicht immer zur Unterscheidung ausreicht. Die Arbeit zeigt klassische Beispiele, wie die Desargues- und die Dodekaeder-Graphen, die identische Knoten-Hierarchien besitzen, obwohl ihre interne Verkabelung verschieden ist.
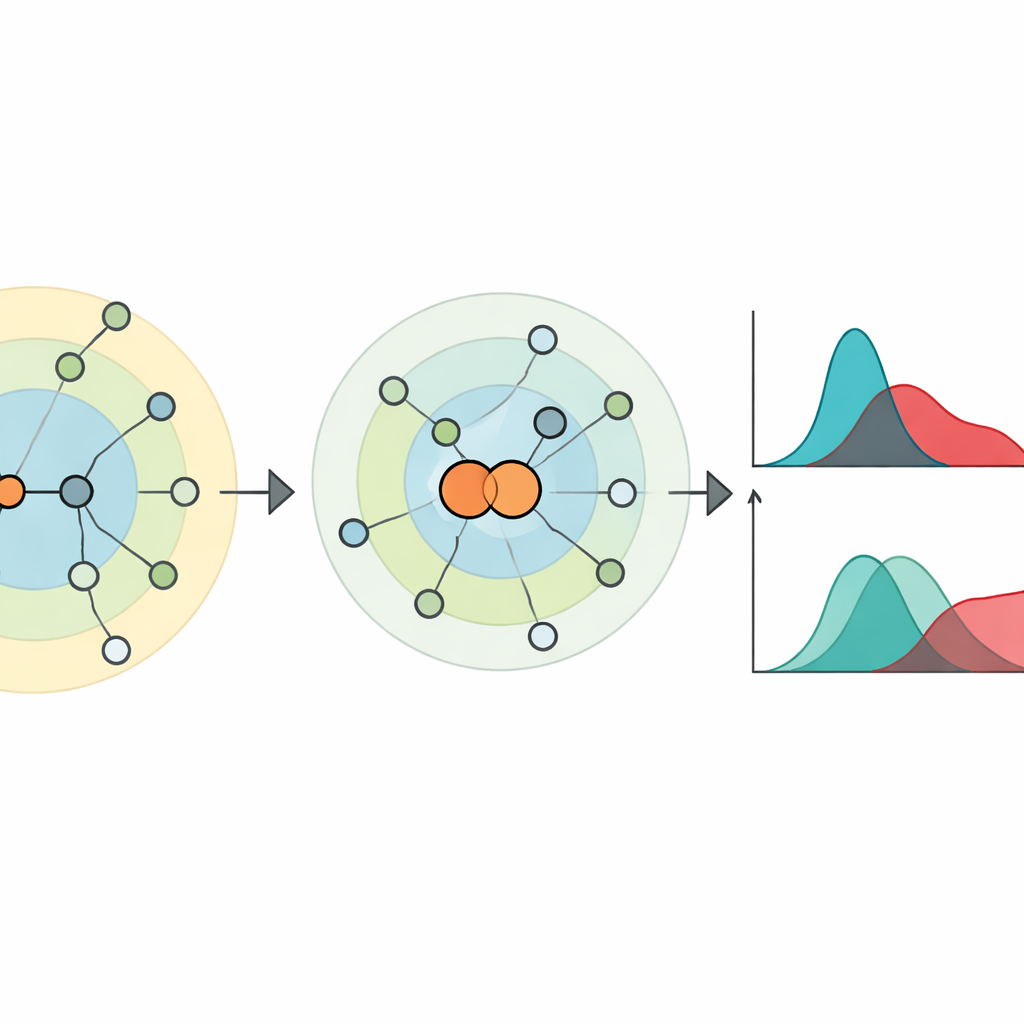
Den Kanten Gehör verschaffen: Knotenpaare zusammenschrumpfen
Um das einzufangen, was die Knoten-Perspektive verpasst, konzentrieren sich die Autoren auf Kanten — die Verbindungen zwischen Knoten — und darauf, wie sie Entfernungen im Netzwerk verändern. Sie führen eine einfache, aber wirkungsvolle Idee ein: das „Schrumpfen von Knotenpaaren“. Dabei werden zwei verbundene Knoten vorübergehend zu einem einzelnen neuen Knoten zusammengeführt, wobei deren kombinierte Nachbarn erhalten bleiben. Das zeigt, wie nah jeder andere Knoten dem Paar im Vergleich zu jedem einzelnen Endpunkt ist. In Ausbreitungsbegriffen ahmt das den Effekt nach, wenn beide Enden einer Verbindung gleichzeitig infiziert werden, statt an einem einzelnen Knoten zu beginnen. Aus diesen geschichteten Distanzmustern definieren sie eine „Hierarchie-Zentralität“ für Knoten und Kanten, die sich als stark korreliert mit der Fähigkeit von Knoten oder Kanten erweist, als Verbreiter in simulierten Epidemien auf realen Netzwerken zu fungieren.
Informationsverlust mit Entropie messen
Aufbauend auf diesen Zentralitäten definieren die Autoren zwei Arten von Hierarchie-Entropie. Die Kanten-Hierarchie-Entropie fragt: Wie viel Information verlieren wir, wenn wir die Bedeutung einer Kante allein dadurch approximieren, dass wir die Bedeutung der beiden verbundenen Knoten mitteln? Die Knoten-Hierarchie-Entropie stellt die umgekehrte Frage für Knoten und ihre umgebenden Kanten. Beide Größen sind normiert, sodass sie nicht von der Gesamtgröße des Netzwerks abhängen. Zusammen bilden sie einen zweidimensionalen Fingerabdruck für jedes Netzwerk. Der Abstand zwischen zwei Netzwerken ist dann einfach die geometrische Distanz zwischen ihren Fingerabdrücken. Dieses neue Maß erfüllt die üblichen Anforderungen an eine Distanz und entspricht intuitiven Erwartungen, etwa indem es größere Strafen vergibt, wenn eine Änderung ein Netzwerk zerteilt.
Feinere Strukturen sehen und zeitliche Veränderungen verfolgen
Die Autoren testen ihr Maß an künstlichen und realen Netzwerken. In synthetischen Benchmarks, die soziale oder technologische Systeme nachbilden, kann das neue Maß verfolgen, wie Netzwerke sich verändern, wenn Modellparameter variieren, und es trennt klar Netzwerke mit starken Gemeinschaften von solchen mit schwächeren Gemeinschaften — selbst wenn konkurrierende Methoden Schwierigkeiten haben. In kontrollierten Experimenten, bei denen Netzwerke gezielt so umsortiert werden, dass viele gemeinsame Statistiken — wie Gradfolgen und sogar Distanzverteilungen — erhalten bleiben, erkennt die Hierarchie-Entropie-Distanz weiterhin Unterschiede, die andere verbreitete Maße als vernachlässigbar behandeln. Sie ist außerdem sehr gut darin, randomisierte Versionen desselben Netzwerks korrekt zu gruppieren, was auf eine scharfe Sensitivität für höherordentliche Strukturen hinweist, die über einfache Zählungen von Kanten und Pfaden hinausgeht.
Anwendungen in der Praxis: Mobilität und Proteine
Um den praktischen Nutzen zu zeigen, wenden die Autoren ihr Distanzmaß auf tägliche Mobilitätsnetzwerke zwischen Hunderten chinesischer Städte während der ersten Monate von COVID-19 an. Unter Verwendung des frühen Januars als Referenz zeigt die Hierarchie-Entropie, wie sich Reisebewegungen durch den Lunar-New-Year-Reisestrom, den Beginn strenger Quarantänen und die anschließende langsame Erholung verschieben — in guter Übereinstimmung mit bekannten politischen Maßnahmen und Mustern in Mobilitätsgemeinschaften. In einer weiteren Anwendung behandeln sie Proteinstrukturen als Netzwerke von Aminosäuren, die miteinander verbunden sind, wenn sie räumlich nahe liegen. Ohne Lernen oder handgefertigte Merkmale erreicht das Clustern von Proteinen mit der neuen Distanz rund 75 % Genauigkeit bei der Trennung von Enzymen und Nicht-Enzymen — konkurrenzfähig zu modernen überwachten neuronalen Netzwerken.
Was das in einfachen Worten bedeutet
Im Kern zeigt diese Arbeit, dass die Berücksichtigung dessen, wie Knoten und Kanten gemeinsam Entfernungen in einem Netzwerk formen, einen deutlich schärferen „Fingerabdruck“ liefert als die Betrachtung von Knoten allein. Indem quantifiziert wird, wie viel verloren geht, wenn man Kanten durch ihre Endpunkte — oder Knoten durch ihre umliegenden Kanten — ersetzt, hebt die vorgeschlagene Hierarchie-Entropie-Distanz subtile strukturelle Unterschiede hervor, die sich stark auf Ausbreitung, Mobilität und biologische Funktion auswirken. Für Wissenschaftler und Analysten, die mit jeglicher Art von Netzdaten arbeiten, bietet dies ein praktisches, allgemeines Werkzeug zum Vergleich komplexer Systeme, das sowohl mathematisch fundiert ist als auch eng mit der Art verbunden ist, wie Prozesse tatsächlich auf diesen Netzwerken ablaufen.
Zitation: Mou, J., Wang, L., Zhang, C. et al. Network hierarchy entropy for quantifying graph dissimilarity. Commun Phys 9, 83 (2026). https://doi.org/10.1038/s42005-026-02523-9
Schlüsselwörter: Netzwerk-Ähnlichkeit, komplexe Netzwerke, Entropie-Maße, epidemische Ausbreitung, Proteinstruktur-Netzwerke