Clear Sky Science · de
Optimierung der CRISPR-Präzision in Maus-Embryonen durch microhomology-vermittelte End-Joining-dominante Zielsteuerung
Warum präziser editierte Mäuse wichtig sind
Werkzeuge zur Genbearbeitung wie CRISPR haben es bemerkenswert einfach gemacht, Mäuse zu erzeugen, die menschliche Krankheiten nachbilden. Es gibt jedoch ein verborgenes Problem: Die genetischen Veränderungen in der ersten Tiergeneration sind häufig unordentlich und gemischt. Das verlangsamt Experimente, senkt die Zuverlässigkeit und erhöht den Tierbedarf. Diese Studie stellt einen Ansatz vor, CRISPR-Schnitte in Maus-Embryonen auf vorhersehbare Ergebnisse zu lenken, sodass die meisten Gründer-Mäuse mit derselben, genau definierten Mutation geboren werden—was sauberere Biologie und bessere ethische Bedingungen für die Geneditierungsforschung bringt.
Die Herausforderung unordentlicher DNA-Reparaturen
Wenn CRISPR die DNA schneidet, muss die Zelle den Bruch mit eigenen Reparatursystemen schließen. Der häufigste Weg, das nicht-homologe End-Joining, ist schnell, aber unpräzise und erzeugt ein Konglomerat kleiner Insertionen und Deletionen an der Schnittstelle. Ein anderer Weg, das microhomology-vermittelte End-Joining, neigt dazu, DNA-Abschnitte in stereotypen Mustern zu löschen, indem kurze übereinstimmende Sequenzen als Leitfaden dienen. Beide Wege sind deutlich effizienter als der präzise, aber langsame homologe Reparaturweg. In standardmäßigen CRISPR-Experimenten konzentrieren sich Forschende meist darauf, wie stark eine Guide-RNA schneiden kann und wie wenige Off-Target-Stellen sie trifft, und schenken der Frage, welcher Reparaturweg bevorzugt wird oder welche exakte Mutation entsteht, weniger Aufmerksamkeit. Das Ergebnis ist, dass viele Gründer-Mäuse ein Flickwerk unterschiedlicher Mutationen in verschiedenen Zellen tragen, weshalb Züchten bis zur nächsten Generation nötig ist, bevor man mit einem sauberen, einheitlichen Genotyp arbeiten kann.
Ein klügerer Weg, CRISPR-Guides auszuwählen
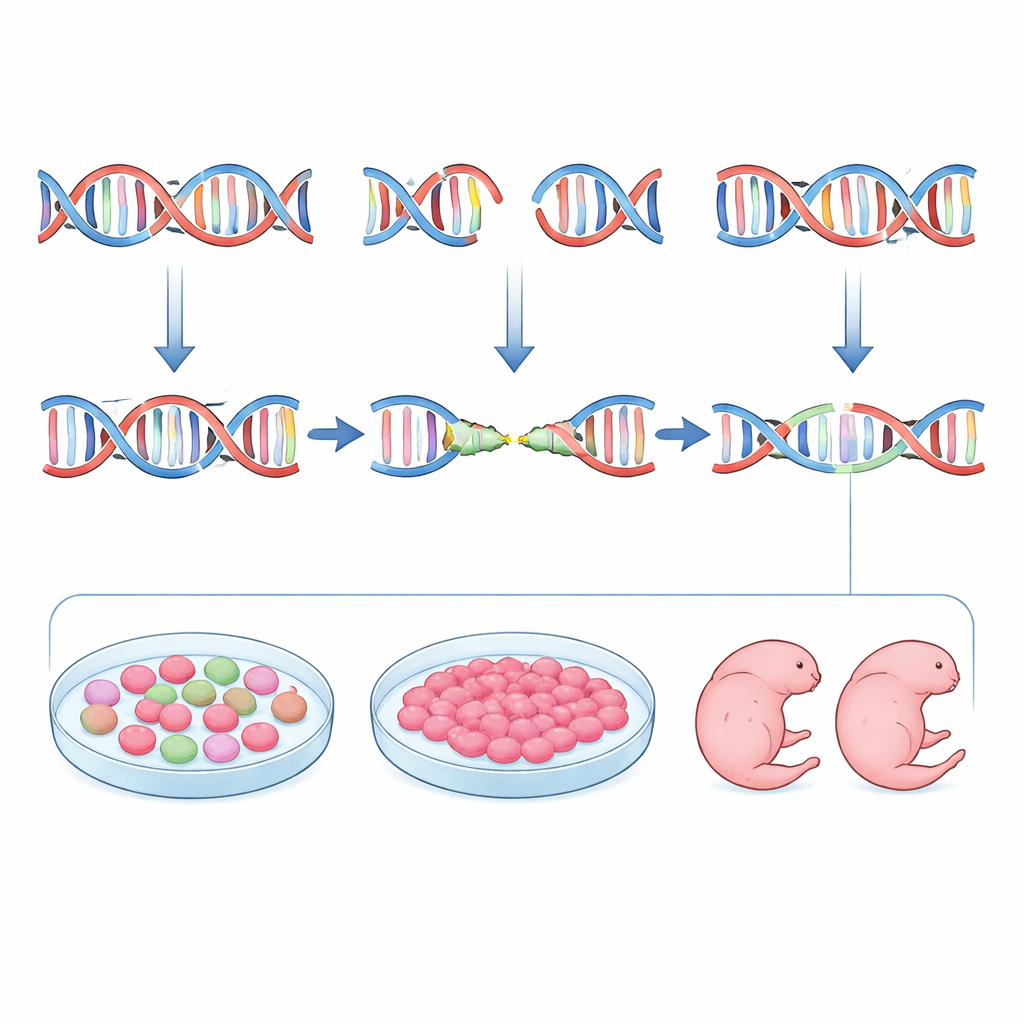
Die Autorinnen und Autoren wollten diesen Ablauf umkehren, indem sie Guides nicht nur nach Stärke und Sicherheit, sondern auch nach Vorhersehbarkeit entwerfen. Sie begannen mit inDelphi, einem Machine-Learning-Tool, das auf großen Datensätzen CRISPR-induzierter Mutationen in Kulturzellen trainiert wurde. inDelphi sagt nicht nur, wie häufig eine Stelle editiert wird; es prognostiziert das volle Spektrum möglicher Insertionen und Deletionen und wie oft jede einzelne auftritt, mit besonderem Blick auf microhomology-getriebene Ereignisse. Das Team durchsuchte das Maus-Tyrosinase-(Tyr)-Gen, dessen Funktionsverlust Tiere albino macht, und wählte Guide-RNAs aus, die voraussichtlich starke, wiederholbare microhomology-vermittelte Deletionen begünstigen und gleichzeitig das Off-Target-Risiko gering halten. Anschließend editierten sie Maus-Embryonen und bestimmten die resultierenden Mutationen mittels Deep-Sequencing. Insgesamt trat inDelphis bevorzugter Genotyp für jeden Guide in Embryonen in ähnlichen Häufigkeiten auf wie vorhergesagt, und Guides mit stärkeren microhomology-Merkmalen erzeugten tatsächlich gleichmäßigere Mutationsmuster.
Stammzellen als Generalprobe nutzen
Allein Vorhersage war jedoch nicht ausreichend. Beim Vergleich von inDelphi-Prognosen mit den tatsächlichen Editierungsmustern ergab sich nur eine moderate Übereinstimmung. Um diese Lücke zu schließen, führten sie einen praktischen Zwischenschritt ein: jeden Guide in murinen embryonalen Stammzellen zu testen, die viele Eigenschaften sehr früher Embryonen teilen. Nach Transfektion dieser Zellen mit CRISPR-Komponenten sortierten sie editierte Zellen und sequenzierten die Zielstellen. Die Mutationsmuster in Stammzellen stimmten deutlich besser mit denen in Embryonen überein als das Computermodell. Guides, die in Stammzellen eine dominante Deletion erzeugten, taten dasselbe typischerweise in Blastozysten und späteren Embryonalstadien. Durch die Kombination von inDelphis Rangfolge mit dieser Stammzell-"Generalprobe" konnten die Forschenden zuverlässig Guides auswählen, die microhomology-vermittelte Reparatur antreiben und die Vielfalt mutantischer Allele minimieren.
Von Augenfarbe bis zu fehlenden Gliedmaßen
Die Autorinnen und Autoren testeten ihre Pipeline an Lebendtieren. Für das Tyr-Gen wählten sie drei Guides, die hohe, mittlere und geringe vorhergesagte Präzision repräsentierten, und setzten editierte Embryonen in Ammenmütter ein. Am Tag 11,5 der Entwicklung untersuchten sie die Augenpigmentierung und sequenzierten jedes Embryo einzeln. Der Guide, der microhomology stark begünstigte, erzeugte überwiegend albinotische Embryonen mit einer dominanten kleinen Deletion, oft in beiden Genkopien und mit sehr geringer Variation. Ein weniger optimierter Guide führte zu einer Mischung aus Pigmentverlust und teilweiser Pigmentierung, verbunden mit einer komplexeren Mutationensammlung. Anschließend wandten sie denselben Ansatz auf das Fgf10-Gen an, dessen Funktionsverlust zu gliedmaßenlosen Embryonen führt. Durch Auswahl eines Guides, der eine spezifische Vier-Basen-Deletion mit hoher Wahrscheinlichkeit zur Geninaktivierung vorhergesagt—und in Stammzellen bestätigt—, erzeugten sie Embryonen am Tag 15,5, die einheitlich gliedmaßenlos waren und eine stark angereicherte Reihe der erwarteten Deletionen trugen. Bei beiden Genen dominierten dieselben wenigen Mutationstypen in inDelphi-Vorhersagen, Stammzellen, frühen Embryonen und späteren Embryonalstadien.
Sauberere Genetik bei weniger Tieren
Praktisch bietet die Studie eine neue Vorlage zur Gestaltung von CRISPR-Experimenten in Mäusen. Statt direkt von einem computerentworfenen Guide zur Embryoneneditierung überzugehen, plädieren die Autorinnen und Autoren für eine integrierte Pipeline: Verwenden Sie inDelphi und Off-Target-Tools, um Guides auszuwählen, die wahrscheinlich microhomology-vermittelte Deletionen und Frameshifts begünstigen; testen Sie diese Guides in embryonalen Stammzellen, um sowohl Effizienz als auch Gleichförmigkeit der Mutationen zu bestätigen; und führen Sie nur die besten Kandidaten in die Embryonenarbeit über. Diese Strategie ergibt Gründer-Mäuse, deren Zellen überwiegend dieselbe, gut charakterisierte Mutation teilen, wodurch sie sofort für die Modellierung menschlicher Erkrankungen nutzbar sind—insbesondere für solche, die durch wiederkehrende Deletionsereignisse verursacht werden—und gleichzeitig die Zahl der zu züchtenden und zu screenenden Tiere reduziert. Das Resultat sind präzisere, reproduzierbarere genetische Modelle und ein ethisch sinnvollerer Weg zu leistungsfähigen Krankheitsmodellen.
Zitation: Lkhagvadorj, K., Okamura, E., Taki, T. et al. Optimizing CRISPR precision in mouse embryos via microhomology-mediated end joining-dominant targeting. Commun Biol 9, 371 (2026). https://doi.org/10.1038/s42003-026-09771-z
Schlüsselwörter: CRISPR, Mausmodelle, Genomeditierung, DNA-Reparatur, Krankheitsmodellierung