Clear Sky Science · de
Aromatischer Fleck in WhiB-ähnlichen Transkriptionsfaktoren erleichtert Wechselwirkung mit dem primären Sigma-Faktor in Mycobacterium tuberculosis
Wie Bakterien Gefahr wahrnehmen
Mycobacterium tuberculosis, der Erreger der Tuberkulose, überlebt im menschlichen Körper, indem es schnell umprogrammiert, welche Gene ein- oder ausgeschaltet werden, wenn sich die Bedingungen ändern — etwa bei Exposition gegenüber Antibiotika oder Immunangriffen. Diese Studie deckt ein winziges Strukturelement auf — einen „aromatischen Fleck“ — in einer Proteinfamilie auf, das diesen Proteinen hilft, an die zentrale Gen-Steuerungsmaschinerie der Zelle anzudocken. Das Verständnis dieses mikroskopischen Händedrucks zeigt, wie Tuberkulose und verwandte Bakterien sich anpassen, und könnte auf neue Wege hinweisen, diesen Erreger zu schwächen.
Eine besondere Familie bakterieller Schaltproteine
Die Arbeit konzentriert sich auf WhiB-ähnliche (Wbl) Proteine, eine Gruppe, die nur in Actinobakterien und ihren Viren vorkommt, einschließlich Mycobacterium tuberculosis. Diese Proteine tragen einen kleinen Eisen–Schwefel-Komplex, einen metallbasierten Cofaktor, der ihnen erlaubt, Änderungen des Sauerstoffangebots und andere Stresssignale zu erkennen. Wbl-Proteine steuern bekannte Schlüsselprozesse wie Zellteilung, Reaktion auf oxidativen Stress und Nährstoffmangel sowie Antibiotikaresistenz. Dennoch fehlt den meisten von ihnen die klassische Struktur, mit der viele Regulatoren direkt an DNA binden — was die lange bestehende Frage aufwirft: Wie kontrollieren sie tatsächlich die Genaktivität?
Anheften an die Haupt-Genlesemaschine
Frühere Arbeiten zeigten, dass mehrere Wbl-Proteine Gene aktivieren, indem sie an eine konservierte Region, genannt Region 4, des primären Sigma-Faktors binden. Der Sigma-Faktor ist der Teil der RNA-Polymerase — des Enzyms, das DNA liest — der erkennt, wo mit dem Abschreiben von Genen begonnen werden soll. In Mycobacterium tuberculosis nutzt dieser primäre Sigma-Faktor dieselbe Region 4, um viele verschiedene Regulatoren anzuheften. Die Autorinnen und Autoren kombinierten Röntgenkristallographie, biochemische Pull-downs und Kalorimetrie und konnten zeigen, dass im Wesentlichen alle getesteten Wbl-Proteine dieses Bakteriums (mit einer speziellen Ausnahme) an genau dieselbe Stelle in der Sigma-Region 4 andocken — und dies mit sehr hoher Bindungsstärke.
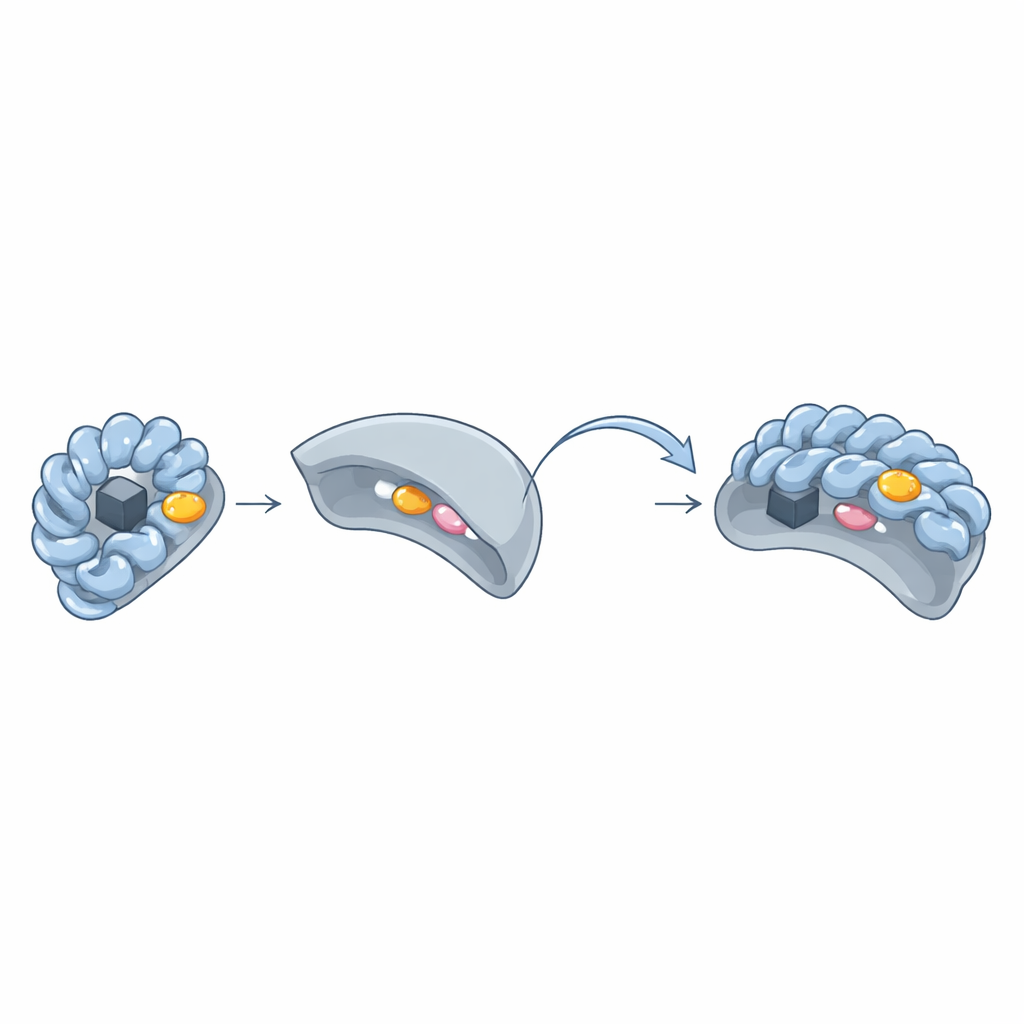
Das verborgene „aromatische Fleck“-Schloss und -Schlüsselprinzip
Durch den Vergleich dreidimensionaler Strukturen von Wbl–Sigma-Paaren entdeckte das Team einen wiederkehrenden Cluster von voluminösen, ringförmigen Aminosäuren — Tryptophan, Phenylalanin, Tyrosin oder Histidin — die auf der Oberfläche der Wbl-Proteine einen „aromatischen Fleck“ bilden. Dieser Fleck liegt in der Nähe des Eisen–Schwefel-Komplexes und drückt direkt gegen zwei Schlüsselaminosäuren in Sigma-Region 4. Wenn die Forschenden diese aromatischen Reste durch einfachere Aminosäuren ersetzten, konnten die Wbl-Proteine keine stabilen Komplexe mit dem Sigma-Faktor mehr bilden, und ihre Eisen–Schwefel-Komplexe wurden oft instabil. Selbst bei ungewöhnlich erscheinenden Wbl-Varianten — etwa WhiB6 oder WhiB5 — kompensierten entweder alternative Reste oder benachbarte aromatische Seitenketten, sodass derselbe Interaktionsstil erhalten blieb.
Ein geteiltes Design bei Bakterien und ihren Viren
Um zu untersuchen, wie verbreitet dieses Merkmal ist, analysierten die Autorinnen und Autoren 995 Wbl-Proteinsequenzen aus vielen actinobakteriellen Arten und ihren infektiösen Viren (Actinobacteriophagen). Sie gruppierten diese Proteine in 29 Unterfamilien und fanden, dass fünf große Zweige, repräsentiert durch fünf Mycobacterium-tuberculosis-Wbl-Proteine, etwa 80 % aller Sequenzen ausmachen. Strukturelle Modellierung mit AlphaFold zeigte, dass fast alle Wbls — mehr als 98 % — mindestens zwei aromatische Reste an Positionen tragen, die dem aromatischen Fleck entsprechen, und nahezu alle weisen mindestens einen Rest in den wichtigsten zentralen Positionen auf. Experimente mit mehreren phagenkodierten Wbl-Proteinen bestätigten, dass auch diese viralen Varianten in einer fleckabhängigen Weise an dieselbe Sigma-Region binden, was darauf hindeutet, dass dasselbe molekulare Design bei Bakterien und ihren Phagen wiederverwendet wird.
Ein evolutionäres Tauziehen um Kontrolle
Der aus diesen 995 Sequenzen aufgebaute phylogenetische Baum zeigt phagische und bakterielle Wbl-Proteine vermischt, mit klaren Hinweisen auf horizontalen Gentransfer in beide Richtungen. Einige virale Wbls stehen an der Basis großer bakterieller Zweige, was darauf hindeutet, dass Phagen diese Regulatoren frühen Bakterien geschenkt haben könnten, die sie dann für eigene Zwecke adaptierten. Andere virale Wbls erscheinen eingebettet in überwiegend bakterielle Cluster und deuten auf spätere Genübertragungen zurück in Phagen hin. Weil Wbl-Proteine Stressantworten, Zellentwicklung und Wirkstoffresistenz durch ihre sigma-bindenden aromatischen Flecken eng steuern, haben diese Hin- und Her-Transfers wahrscheinlich geformt, wie sowohl Bakterien als auch ihre Viren die Transkriptionsmaschinerie des Wirts manipulieren.
Was das für Tuberkulose und darüber hinaus bedeutet
Kurz gesagt zeigt diese Studie, dass viele actinobakterielle Regulatoren einen winzigen, aber entscheidenden klebrigen Punkt teilen — den aromatischen Fleck — der es ihnen erlaubt, an denselben Teil der Genlesemaschine anzudocken und unter Stress fein abzustimmen, welche Gene aktiv sind. In Mycobacterium tuberculosis hilft dieses gemeinsame Andockprinzip, Reaktionen zu koordinieren, die Persistenz, Virulenz und Antibiotikaresistenz unterstützen. Indem gezeigt wird, wie diese mikroskopische Schnittstelle funktioniert und wie weit sie konserviert ist, hebt die Arbeit einen potenziellen Schwachpunkt hervor, der eines Tages gezielt werden könnte, um die Fähigkeit des Erregers zu stören, sich anzupassen und im Wirt zu überleben.
Zitation: Guiza Beltran, D., Wan, T., Seravalli, J. et al. Aromatic patch in whiB-like transcription factors facilitates primary sigma factor interaction in mycobacterium tuberculosis. Commun Biol 9, 424 (2026). https://doi.org/10.1038/s42003-026-09698-5
Schlüsselwörter: Mycobacterium tuberculosis, Transkriptionsfaktoren, Sigma-Faktor, Eisen-Schwefel-Proteine, Bakteriophagen-Evolution