Clear Sky Science · de
Die nächste Ebene: Auffrischung von Foundation-Modellen durch strukturerhaltendes und aufmerksamkeitsgeführtes Lernen für die Verbindung lokaler Flicken mit globalem Kontextbewusstsein in der computergestützten Pathologie
Computern das Lesen von Krebspräparaten beibringen
Wenn ein Pathologe eine Krebsbiopsie unter dem Mikroskop betrachtet, betrachtet er nicht nur einzelne Zellen – er sieht Muster, Nachbarschaften und wie Tumor-, Immun- und normales Gewebe zueinander angeordnet sind. Die heutigen KI-Systeme für die digitale Pathologie sind sehr gut darin, Details in winzigen Bildausschnitten zu erkennen, doch sie übersehen oft das größere Bild. Diese Studie stellt EAGLE-Net vor, einen neuen KI‑Ansatz, der Computern hilft, Gewebeaufnahmen mehr wie menschliche Expertinnen und Experten zu sehen, indem er sowohl lokale Details als auch die Gesamtanordnung des Gewebes auf dem Objektträger berücksichtigt.

Warum die Anordnung von Tumorgewebe wichtig ist
Ein Tumor ist mehr als ein Haufen Krebszellen. Er existiert in einer lebhaften Nachbarschaft aus Blutgefäßen, Immunzellen, Bindegewebe sowie Regionen mit Narbenbildung oder Zelltod. Wie diese Elemente angeordnet sind – ihre Abstände, Grenzen und Mischungsverhältnisse – kann Aufschluss darüber geben, wie aggressiv der Krebs ist und wie eine Patientin oder ein Patient auf eine Behandlung reagieren könnte. Konventionelle KI‑Systeme in der Pathologie zerschneiden Ganzblatt‑Bilder meist in tausende kleine Kacheln und analysieren diese fast isoliert. Anschließend versuchen sie, Diagnose oder Outcome durch das Zusammenfassen der Informationen aller Kacheln vorherzusagen. Diese Strategie vernachlässigt oft, wie Kacheln räumlich zueinander in Beziehung stehen, was Vorhersagen schwächen und KI‑Heatmaps verstreut oder schwer interpretierbar machen kann.
Ein neuer Weg, das größere Bild zu erfassen
EAGLE-Net wurde entwickelt, um die Lücke zwischen lokalem Detail und globaler Struktur zu schließen. Es baut auf leistungsfähigen „Foundation‑Modellen“ auf, die bereits wissen, wie man reichhaltige visuelle Merkmale aus kleinen Präparatsausschnitten extrahiert. Darauf aufbauend fügt es ein neues Modul hinzu, das kodiert, woher jede Kachel auf dem Objektträger stammt und so die echte Geometrie des Gewebes erhält, anstatt sie in ein verzerrtes Raster zu pressen. Mithilfe von Multi‑Scale‑Filtern lernt EAGLE-Net Muster, die von winzigen zellulären Veränderungen bis hin zu breiteren Gewebestrukturen wie Tumorgrenzen und umgebendem Stroma reichen. Anschließend nutzt es einen Aufmerksamkeitsmechanismus – im Wesentlichen eine Methode, um Wichtigkeitspunkte zu vergeben –, um sich auf die Kacheln und Nachbarschaften zu konzentrieren, die für die Vorhersage von Diagnose oder Überleben am relevantesten sind.
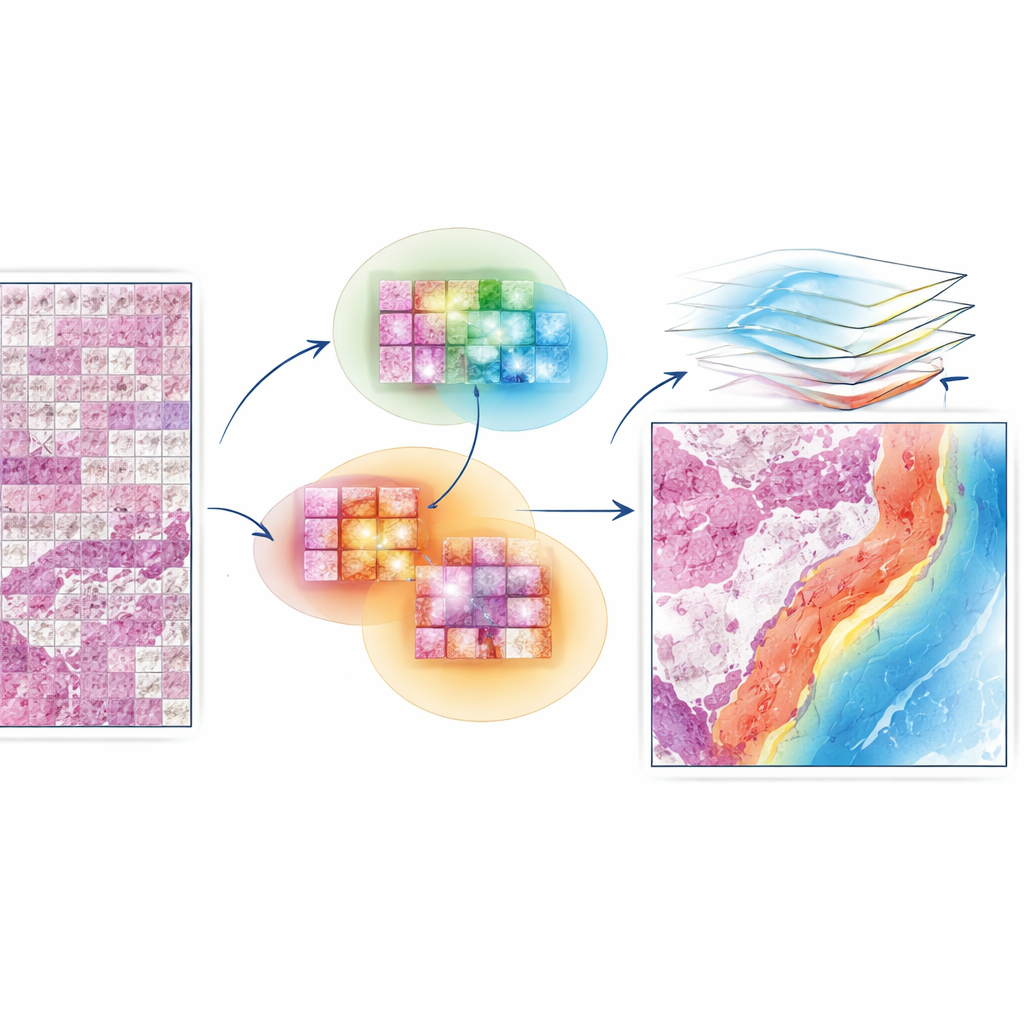
Das Modell aus Nachbarschaften statt nur Punkten lernen lassen
Eine zentrale Innovation von EAGLE-Net ist, wie es das Netzwerk lehrt, nicht nur die wichtigsten Kacheln zu bewerten, sondern auch deren nahegelegene Nachbarn. Während des Trainings identifiziert die Methode wiederholt die Kacheln, die das Modell für am informativsten hält, und ermutigt es dann, die umgebenden Kacheln innerhalb eines kleinen Radius als Teil derselben sinnvollen Region zu betrachten. Dieses „nachbarschaftsbewusste“ Lernen bewegt das Modell dazu, glatte, zusammenhängende Aufmerksamkeitsregionen zu bilden, die mit der Sichtweise von Pathologen auf Tumorfronten, Immuncluster und andere Mikroumgebungen übereinstimmen. Gleichzeitig sorgt ein zusätzlicher Term im Trainingsprozess dafür, dass das Modell Hintergrund‑ oder Leerstellen aktiv ignoriert, wodurch das Risiko falscher Hervorhebungen auf Artefakten oder Weißraum reduziert wird.
Wertbeweis über viele Krebsarten hinweg
Die Forschenden testeten EAGLE-Net an fast 15.000 Ganzblatt‑Bildern aus 10 verschiedenen Krebsarten, darunter Lungen-, Nieren-, Magen-, Uterus-, Schilddrüsen-, Kolorektal‑ und Prostatatumoren. Sie bewerteten zwei Hauptaufgaben: die Vorhersage der Überlebensdauer von Patientinnen und Patienten sowie die Klassifikation von Tumortypen oder -graden. In den meisten Kollektiven erreichte EAGLE-Net gleiche oder bessere Ergebnisse als mehrere führende auf Aufmerksamkeit beruhende Methoden und verbesserte oft Überlebensvorhersagewerte und Klassifikationsgenauigkeit um einige Prozentpunkte – ein auf Bevölkerungsebene bedeutender Zugewinn. Es zeigte zudem starke Leistungen, wenn es mit drei sehr unterschiedlichen zugrunde liegenden Foundation‑Modellen kombiniert wurde, was belegt, dass das Design flexibel ist und nicht an einen einzigen Merkmalextraktor gebunden ist.
Einblick in die Entscheidungsfindung des Modells
Über die bloße Genauigkeit hinaus untersuchten die Autorinnen und Autoren genau, wohin EAGLE-Net auf den Präparaten „sah“. Verglichen mit anderen Methoden bildeten seine Aufmerksamkeitskarten glattere, kohärentere Regionen, die Tumorgrenzen umschlossen und invasive Ränder, nekrotische Bereiche und Immunzell‑Cluster erfassten. Quantitative Vergleiche mit expertengezeichneten Tumormasken zeigten, dass die hervorgehobenen Bereiche von EAGLE-Net besser mit dem tatsächlichen Tumor überlappten, weniger Fehlmarkierungen auf normalem Gewebe aufwiesen und komplexe Tumorformen treuer reproduzierten. Das Modell widmete außerdem einen größeren Anteil seiner Aufmerksamkeit Tumor-, Nekrose‑ und Immunkompartimenten und weniger normalem Lungengewebe oder Blutgefäßen – ein Verhalten, das die Prioritäten eines Pathologen bei der Beurteilung der Prognose widerspiegelt.
Was das für die zukünftige Krebsversorgung bedeutet
Praktisch zeigt EAGLE-Net, dass die Hinzufügung räumlichen Bewusstseins und nachbarschaftlicher Logik auf bestehende Pathologie‑KI sowohl Leistung als auch Interpretierbarkeit verbessern kann. Anstatt ein Präparat als Sammlung unverbundener Kacheln zu behandeln, lernt die Methode, biologisch sinnvolle Nischen zu erkennen – Tumorgrenzen, immunreiche Regionen und Invasionsmuster –, die für Patientenergebnisse relevant sind. Da sie mit vielen verschiedenen Foundation‑Modellen zusammenarbeitet und keine arbeitsintensive pixelgenaue Annotation erfordert, könnte EAGLE-Net breit auf große Archive digitaler Präparate angewendet werden. Mit weiterer Validierung und Integration in klinische Abläufe könnten solche Systeme Pathologen dabei unterstützen, Patientinnen und Patienten präziser zu stratifizieren, neue gewebebasierte Biomarker zu entdecken und letztlich gezieltere Krebsbehandlungen zu lenken.
Zitation: Waqas, M., Bandyopadhyay, R., Showkatian, E. et al. The next layer: augmenting foundation models with structure-preserving and attention-guided learning for local patches to global context awareness in computational pathology. npj Precis. Onc. 10, 109 (2026). https://doi.org/10.1038/s41698-026-01312-5
Schlüsselwörter: computergestützte Pathologie, Krebsprognose, digitale Pathologie KI, Tumormikroumgebung, EAGLE-Net