Clear Sky Science · de
KI-gesteuerte virtuelle Screening-Plattform identifiziert neuartige NSUN2-Inhibitor-Kandidaten für gezielte Krebstherapie: ein computergestützter Ansatz zur Wirkstoffentdeckung
Neue Wege, hartnäckige Krebserkrankungen zu überlisten
Viele Krebserkrankungen werden nicht nur deshalb tödlich, weil sie entstehen, sondern weil sie lernen, unseren besten Medikamenten zu entgehen. Diese Studie untersucht einen vielversprechenden neuen Ansatz, um einen wichtigen Förderer des Tumorwachstums auszuschalten: Mithilfe künstlicher Intelligenz wurden am Computer mehr als einhundert Millionen potenzielle Wirkstoffe durchsucht, bevor irgendeiner davon in einem echten Reagenzglas getestet wurde.
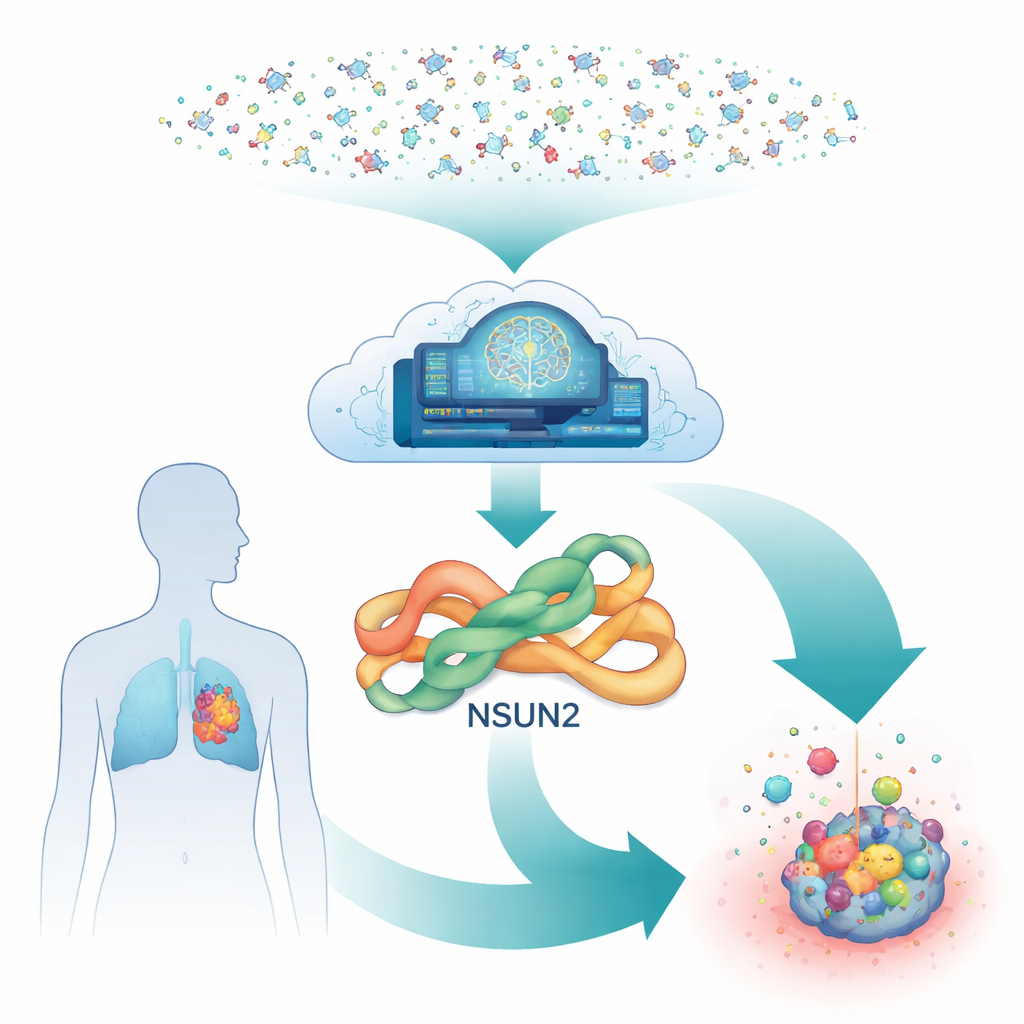
Ein versteckter Schalter in Krebszellen
Tief in unseren Zellen wirkt ein Enzym namens NSUN2 wie ein chemischer Markierer für RNA, das Molekül, das Gene in Proteine übersetzt. Indem es winzige chemische Markierungen an der RNA anbringt, kann NSUN2 wachstumsbezogene Botschaften stabiler und leichter lesbar machen. Viele Tumoren – darunter Lungen-, Magen-, Pankreas- und Brustkrebs – schrauben die NSUN2-Spiegel hoch, was ihre Fähigkeit zu teilen, zu metastasieren und sich gegen zielgerichtete Medikamente zu wehren, erhöht. Trotz seiner Bedeutung gibt es jedoch nur sehr wenige Wirkstoffkandidaten, die NSUN2 sicher herunterregeln können, insbesondere reversible Hemmstoffe, die das Enzym nicht dauerhaft schädigen.
Die KI durchsucht ein Meer von Molekülen
Die traditionelle Wirkstoffsuche käme kaum darum herum, Millionen von Molekülen gegen NSUN2 im Labor zu testen, weil jedes Experiment komplexe RNA-Mischungen und Hilfsstoffe erfordert. Stattdessen bauten die Forschenden eine komplett digitale Pipeline auf. Ausgangspunkt war eine vorhergesagte dreidimensionale Struktur des menschlichen NSUN2, erzeugt von AlphaFold, einem KI-System, das die Strukturvorhersage revolutioniert hat. Um sicherzugehen, dass dieses Modell vertrauenswürdig ist, verglichen sie es mit einem eng verwandten Enzym, dessen Struktur durch Röntgenstudien bekannt ist. Die kritische Tasche, in der NSUN2 sein natürliches Helfermolekül bindet, erwies sich als stark konserviert, was dem Team Zuversicht gab, dass das virtuelle Andocken potenzieller Wirkstoffe an dieser Stelle aussagekräftig sein würde.
Von Hunderten Millionen auf eine Handvoll
Mit der Zieltasche definiert, wandte sich das Team einer umfangreichen öffentlichen Datenbank käuflicher Moleküle zu. Zuerst wurden Trainingssätze von Verbindungen in die NSUN2-Tasche gedockt und die resultierenden Scores genutzt, um ein maschinelles Lernmodell dahingehend zu schulen, welche Formen am vielversprechendsten sind. Dieses Modell durchschaute dann in hoher Geschwindigkeit rund 350 Millionen Moleküle und markierte etwa 101 Millionen als wahrscheinliche »Hits«. Um das Feld weiter einzugrenzen, wurden die besten Kandidaten mit genaueren Berechnungen erneut angedockt; nur die besten 12.000 mit stark vorhergesagter Bindung blieben übrig. Diese durchliefen anschließend eine Reihe computerbasierter Sicherheitsprüfungen, die abschätzten, wie der Körper jedes Kandidaten aufnehmen, verteilen, abbauen und tolerieren könnte. Nach diesen Filtern blieben nur 34 Moleküle übrig, die sowohl potent als auch drug-like erschienen.
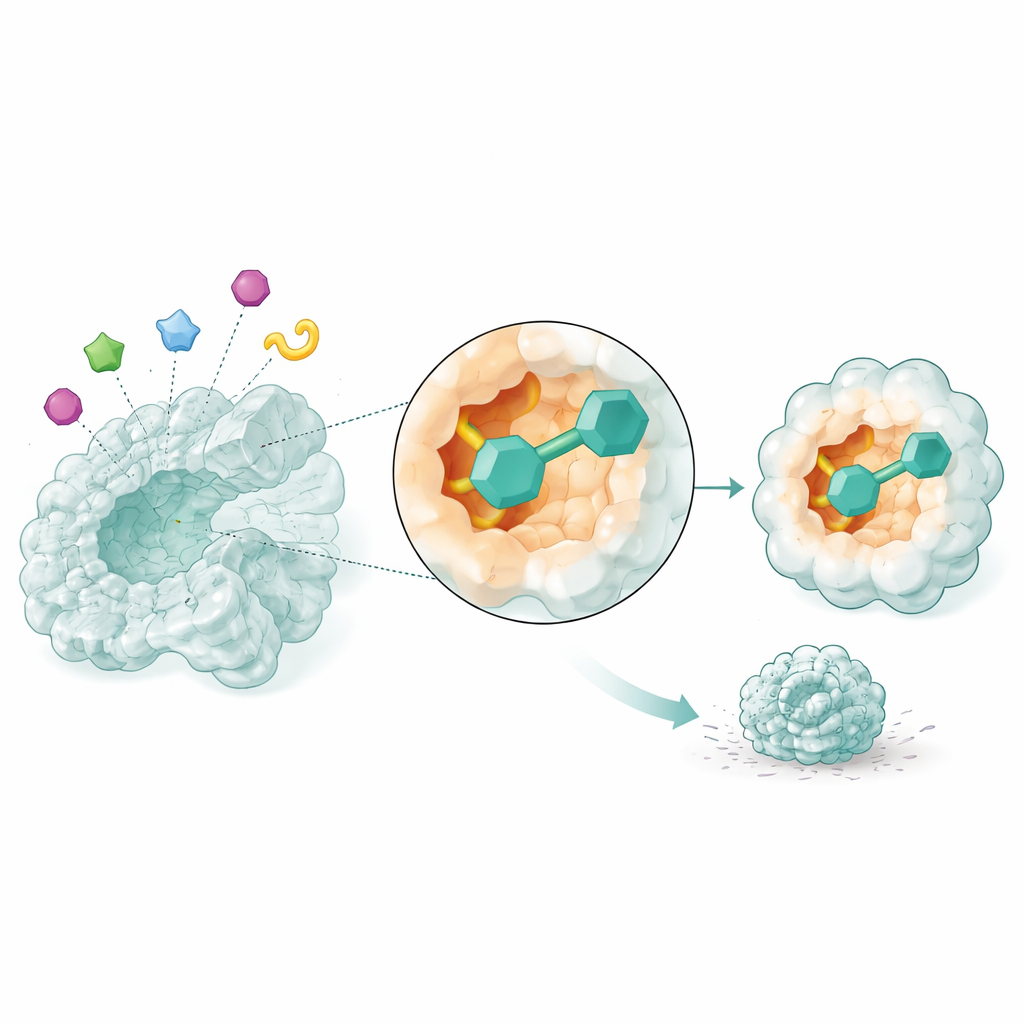
Beobachtung von Wirkstoffkandidaten in Bewegung
Statische Schnappschüsse reichen nicht aus, um zu wissen, ob ein Wirkstoff sein Ziel wirklich festhält. Deshalb nutzten die Forschenden molekulardynamische Simulationen, die modellieren, wie Atome sich im Lauf der Zeit bewegen, um die vielversprechendsten drei Kandidaten über 50 Milliardstel einer Sekunde im Zusammenspiel mit NSUN2 zu beobachten. Zwei Verbindungen, nur durch ihre Datenbank-Codes identifiziert, bildeten besonders stabile Komplexe: Die Enzymstruktur blieb kompakt, ihre Schlüsselregionen verharrten stabil statt schlaff, und die kleinen Moleküle behielten einen engen Sitz in der Tasche bei, während sie persistente Kontakte ausbildeten. Diese Simulationen legen nahe, dass die beiden Verbindungen die Aktivität von NSUN2 in echten Zellen zuverlässig blockieren könnten.
Was das für künftige Behandlungen bedeuten könnte
Auch wenn alle Ergebnisse dieser Arbeit aus Berechnungen stammen und noch im Labor bestätigt werden müssen, liefert die Studie eine Kurzliste realistischer Ausgangspunkte für neue NSUN2-blockierende Wirkstoffe. Da NSUN2 Krebszellen hilft, Wachstums- und Überlebenssignale zu stabilisieren, könnten solche Medikamente Tumoren schwächen und sie möglicherweise wieder empfindlich gegenüber vorhandenen zielgerichteten Therapien machen, insbesondere bei Lungenkrebs, der resistent geworden ist. Ebenso wichtig ist, dass die Studie ein allgemeines Rezept demonstriert, KI und physikbasierte Modellierung zu nutzen, um enorme chemische Räume schnell und kostengünstig zu durchsuchen – ein kraftvoller Shortcut hin zur nächsten Generation präziser Krebstherapien.
Zitation: Yu, S., Peng, Q., Wei, W. et al. AI-driven virtual screening platform identifies novel NSUN2 inhibitor candidates for targeted cancer therapy: a computational drug discovery approach. npj Precis. Onc. 10, 98 (2026). https://doi.org/10.1038/s41698-026-01296-2
Schlüsselwörter: NSUN2, Epitranskriptomik, KI virtuelles Screening, Krebswirkstoffforschung, RNA-Methylierung