Clear Sky Science · de
Genaue Quantifizierung von Krankheitsheterogenität und -verlauf bei MSA und Parkinson mittels maschinellen Lernens
Warum das für Menschen mit Bewegungsstörungen wichtig ist
Menschen mit Parkinson‑Krankheit oder multipler Systematrophie (MSA) leben oft jahrelang in Unsicherheit, weil sich die beiden Erkrankungen klinisch sehr ähnlich zeigen können, dabei aber ganz unterschiedliche Verläufe haben. Diese Studie untersucht, wie fortgeschrittene Computerverfahren auf Basis von Hirnscans Ärzten helfen könnten, die Erkrankungen früher zu unterscheiden, zu verstehen, wie sie von Person zu Person variieren, und zu verfolgen, wie sie sich im Laufe der Zeit verändern.
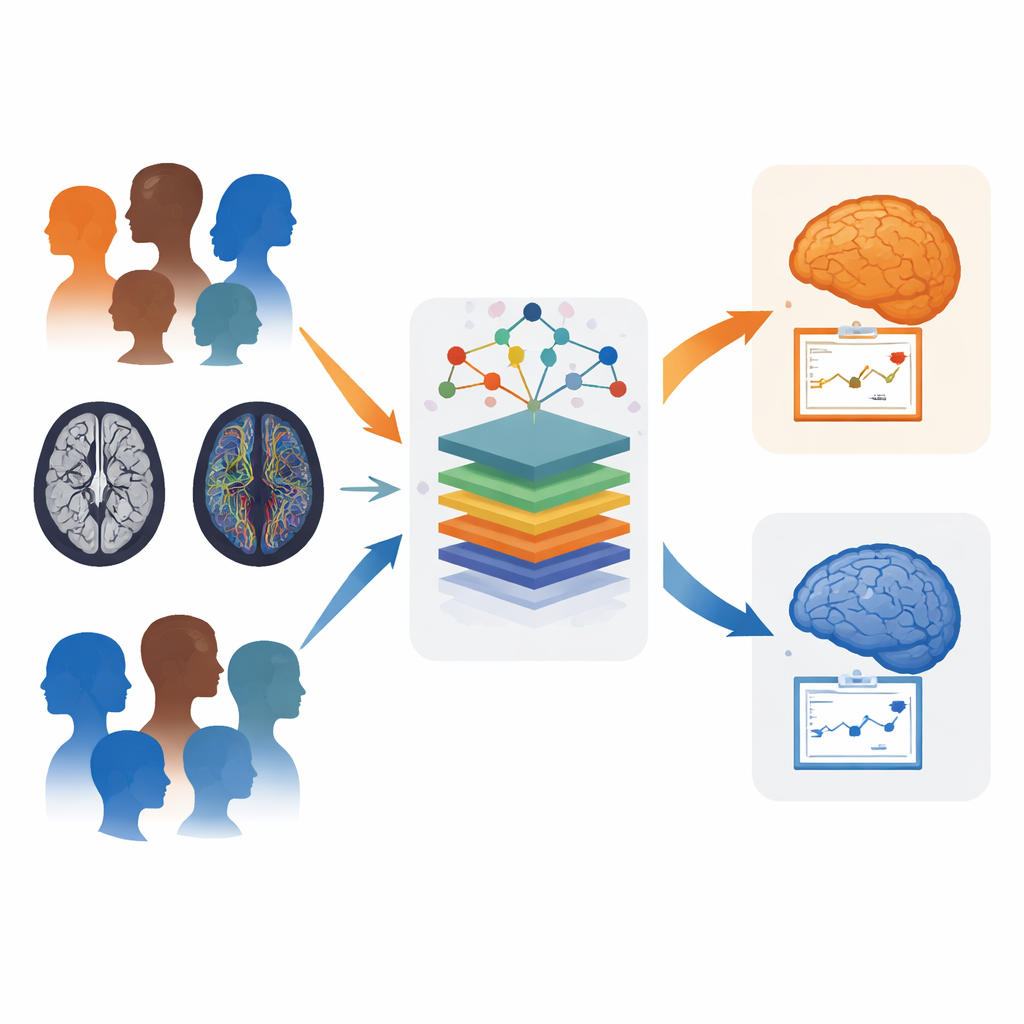
Im Gehirn nach klareren Hinweisen suchen
Bei Parkinson und MSA kommt es beide Male zu einer abnormen Anreicherung des Proteins Alpha‑Synuclein, doch betroffen sind unterschiedliche Hirnregionen. Parkinson betrifft vor allem eine tiefe Region, die Dopamin produziert, während MSA weitere Netzwerke angreift, darunter Kleinhirn, Hirnstamm und Bewegungsbahnen. Auf konventionellen MRTs sind diese Unterschiede besonders im Frühstadium oft subtil, und viele Menschen mit MSA erhalten zunächst die Diagnose Parkinson. Die Forschenden nutzten zwei MRT‑Modalitäten — strukturelle Aufnahmen, die Form und Größe des Gehirns zeigen, und Diffusionsaufnahmen, die die Integrität der weißen Substanz abbilden — um präzisere, patientenspezifische Muster zu finden.
Computern beibringen, verborgene Muster zu erkennen
Das Team untersuchte 17 gesunde Freiwillige, 27 Personen mit MSA (aufgeteilt in zerebelläre und parkinsonische Subtypen) und 15 mit Parkinson, jeweils bis zu vier jährliche Besuche verfolgt. Sie teilten das Gehirn in Dutzende Regionen auf und maßen dort lokales Volumen sowie zwei Diffusionsgrößen, die widerspiegeln, wie sich Wasser entlang von Nervenfasern bewegt. Diese Messwerte flossen in mehrere Maschinenlernmodelle, die darauf trainiert wurden, eine einfache Aufgabe zu erfüllen: entscheiden, ob ein Scan von einer Person mit MSA oder mit Parkinson stammt. Um Overfitting bei einer so seltenen Erkrankung zu vermeiden, verwendeten die Autorinnen und Autoren sorgfältige Kreuzvalidierung, wiederholten das Training viele Male und verglichen fünf verschiedene Algorithmusfamilien, bevor sie die besten Ausführungen auswählten.
Aus komplexen Scans eine einzige persönliche Kennzahl
Anstatt bei einer Ja/Nein‑Computerdiagnose zu stoppen, wollten die Autorinnen und Autoren eine Zahl, die erfasst, wie stark das Hirn einer Person das MSA‑ versus Parkinson‑Muster zeigt. Sie verwendeten eine erklärbare KI‑Methode namens SHAP, die jede Modellentscheidung in Beiträge einzelner Hirnregionen zerlegt. Diese Beiträge dienten als Gewichtungen und betonten, welche Bereiche das Modell als besonders informativ ansah. Durch die Kombination der Gewichtungen mit den tatsächlichen MRT‑Messungen über alle Regionen hinweg erzeugten sie drei „Heterogenitäts“(HET)‑Scores — jeweils einen für das Hirnvolumen und für die beiden Diffusionsmaße. Jeder HET‑Score fasst so ein komplexes Muster von Veränderungen im Gehirn zu einem einzigen Summenwert pro Person und Besuch zusammen.
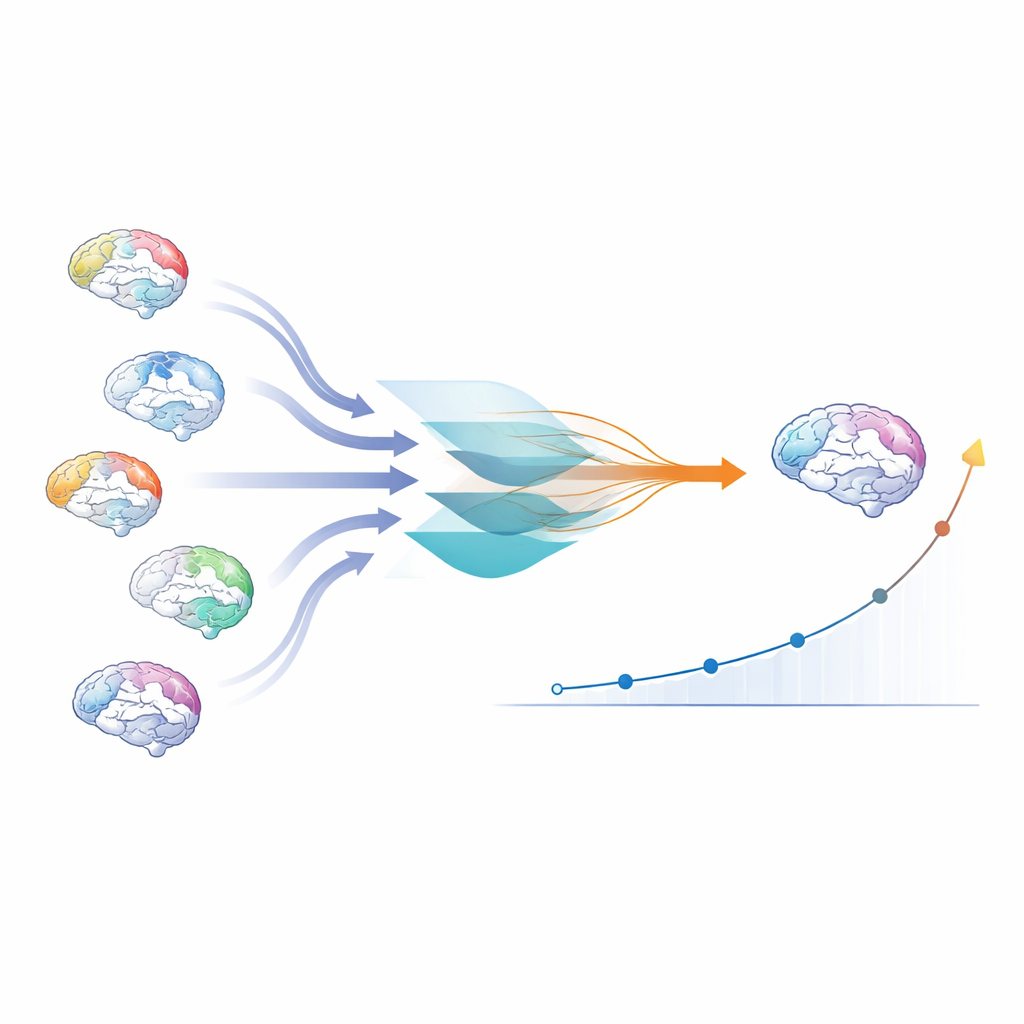
Erkennen des Erkrankungstyps und der Veränderung im Zeitverlauf
Die neuen HET‑Scores lieferten mehr als nur eine Nachbildung vorhandener MRT‑Marker. Sie klassifizierten MSA versus Parkinson mindestens ebenso gut und oft besser als ein weit verbreiteter Atrophie‑Index, der sich auf einige wenige Schlüsselregionen konzentriert. Wichtig ist, dass HET besonders gut darin war, die parkinsonische Form der MSA von der Parkinson‑Krankheit zu trennen — eine Unterscheidung, die auf Standardaufnahmen notorisch schwierig ist. Betrachtete man die Entwicklung über die Zeit, so verfolgten Veränderungen der HET‑Scores über ein Jahr das klinische Fortschreiten, gemessen mit einer standardisierten MSA‑Skala, besser als einfache Maße der Kleinhirn‑Schrumpfung. Regionale HET‑Karten erfassten außerdem bekannte Schädigungsmuster bei MSA, wie Degeneration von Kleinhirn‑ und Hirnstammnetzwerken, und zeigten darüber hinaus eine ausgeweitete Beteiligung frontaler und limbischer weißer Substanzbahnen sowie der Verbindungen zwischen den Gehirnhälften.
Was das für Patientinnen und Patienten sowie die Versorgung bedeuten könnte
Für Nicht‑Spezialisten lautet die Kernbotschaft: Eine intelligentere Auswertung routinemäßiger MRT‑Daten kann verstreute Schäden im Gehirn in eine einzige, verständliche Kennzahl überführen, die widerspiegelt, wie „MSA‑ähnlich“ ein Muster ist und wie schnell es sich verändert. Dieser Ansatz heilt die Erkrankung nicht, und er muss noch in größeren Kohorten bestätigt werden, bietet aber ein vielversprechendes Werkzeug für frühere und genauere Diagnosen, besseres Monitoring des Verlaufs und sensitivere Tests neuer Therapien in klinischen Studien. Indem das HET‑Rahmenwerk anerkennt, dass sich die Gehirne zweier Patientinnen oder Patienten nicht genau gleich verändern, rückt es die Versorgung einen Schritt näher an echte personalisierte Medizin bei Bewegungsstörungen.
Zitation: Gebre, R.K., Raghavan, S., De Tora, M.E.J. et al. Precise disease heterogeneity and progression quantification in MSA and Parkinson’s disease using machine learning. Sci Rep 16, 10579 (2026). https://doi.org/10.1038/s41598-026-45949-5
Schlüsselwörter: multiple Systematrophie, Parkinson-Krankheit, Hirn‑MRT, maschinelles Lernen, Biomarker