Clear Sky Science · de
Morpho-biochemische und molekulare Identifizierung von Bacillus licheniformis- und Bacillus cereus-Isolaten aus der Rhizosphäre von Sorghum (Sorghum bicolor L.)
Freundliche Mikroben an den Wurzeln einer robusten Kultur
Sorghum ist ein widerstandsfähiges Getreide, das Millionen von Menschen ernährt, vor allem dort, wo Hitze und Dürre die Landwirtschaft erschweren. Doch Sorghum steht auf mageren Böden nicht allein: Seine Wurzeln sind von winzigen, im Boden lebenden Partnern umgeben, die ihm helfen können, Nährstoffe zu finden, Krankheiten zu bekämpfen und mit Stress umzugehen. Diese Studie untersucht, welche Bakterien die Wurzeln von Sorghum in Ostindien umgeben, und wirft einen genauen Blick auf zwei wichtige Helfer der Gattung Bacillus. Sie zeigt, wie sorgfältige Detektivarbeit im Labor offenlegen kann, wer sie sind und wie sie mit ihren vielen Verwandten verwandt sind.

Die Lebenswelt um die Wurzeln erkunden
Die Forschenden sammelten Boden, der an den Wurzeln mehrerer Sorghum‑Sorten haftete, die an drei verschiedenen Standorten um Bhubaneswar, Indien, angebaut wurden – darunter ein Stadtpark, eine landwirtschaftliche Versuchsstation und ein Universitätscampus. Aus diesen rhizosphärischen Böden kultivierten sie Bakterien mit standardisierten Kulturverfahren auf nährstoffreichen Platten und wählten dann Kolonien aus, die sich in Farbe, Form und Textur unterschieden. Ein erster Blick unter das Mikroskop und Gram‑Färbung zeigte, dass die meisten der 13 Isolate stäbchenförmige Bakterien mit dicken Zellwänden waren, ein Kennzeichen von Bacillus und nahen Verwandten, daneben einige kugelförmige Formen und ein dünnwandiger, Gram‑negativer Stamm.
Untersuchung der Fähigkeiten der Mikroben
Um über das Aussehen hinauszukommen, führte das Team einfache biochemische Tests durch, die zeigen, wie jeder Mikroorganismus mit Sauerstoff umgeht, bestimmte Moleküle abbaut und Zucker fermentiert. Zum Beispiel zeigt das Hinzufügen von Wasserstoffperoxid, ob Zellen Katalase herstellen, ein Enzym, das sie vor reaktiven Sauerstoffspezies schützt, während andere Tests Säurebildung oder die Fähigkeit zum Abbau der Aminosäure Tryptophan nachweisen. Muster in diesen Reaktionen halfen, die wahrscheinliche Identität jedes Isolats einzugrenzen. Zwei stäbchenförmige Stämme, bezeichnet als AG3 und AG11, stachen hervor: Beide tolerierten Sauerstoff gut, bewältigten schädliche Nebenprodukte effizient und zeigten einen ähnlichen Fermentationsstil, der für Bacillus‑Arten typisch ist, die um Pflanzenwurzeln gedeihen.
Das genetische Barcode der Bakterien lesen
Da viele Bacillus‑Arten ähnlich aussehen und sich ähnlich verhalten, wandten sich die Wissenschaftler der DNA zu, um eine genauere Antwort zu erhalten. Sie konzentrierten sich auf das 16S‑rRNA‑Gen, einen weit verbreiteten genetischen „Barcode“ für Bakterien. Nachdem sie DNA aus AG3 und AG11 extrahiert hatten, vervielfältigten sie dieses Gen mittels Polymerase‑Kettenreaktion und bestätigten auf einem Gel, dass die Fragmente die erwartete Länge hatten. Das Team las dann die Genfolgen mittels Sanger‑Sequenzierung und verglich sie mit Tausenden bekannter Sequenzen in der öffentlichen NCBI‑Datenbank. Die Übereinstimmungen waren eindrucksvoll: AG3 stimmte nahezu perfekt mit Bacillus licheniformis überein, während AG11 eine exakte Übereinstimmung mit Bacillus cereus zeigte. Beide sind in Agrarböden häufig und bekannt dafür, starke Wechselwirkungen mit Pflanzen zu haben – manchmal förderlich für das Wachstum und in anderen Fällen, im Fall von B. cereus, mit gesundheitlichen Bedenken in anderen Kontexten.
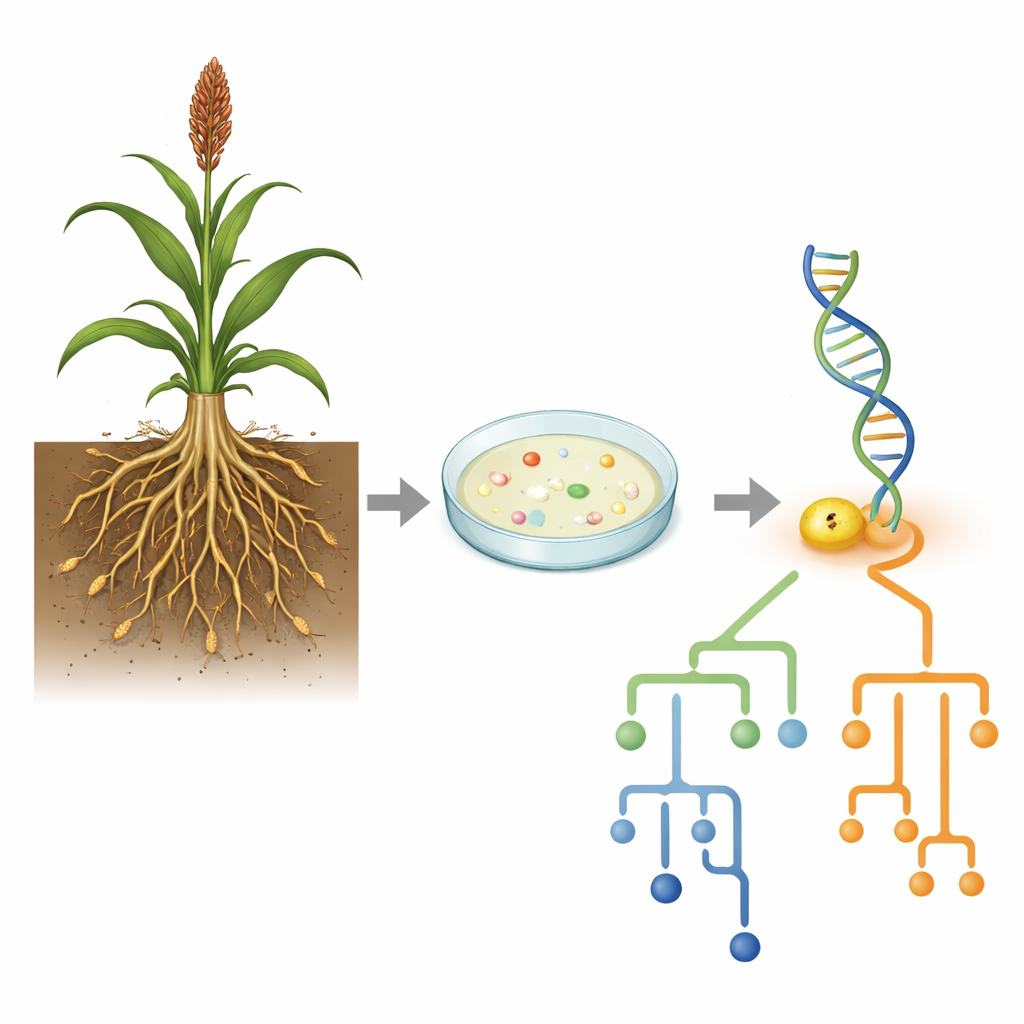
Die neuen Funde im Stammbaum einordnen
Die Kenntnis der nächsten Übereinstimmung ist nur ein Teil der Geschichte; die Autoren wollten auch sehen, wo diese Isolate im größeren bakteriellen Stammbaum sitzen. Sie erstellten Evolutionsbäume, indem sie die 16S‑Sequenzen von AG3 und AG11 mit Dutzenden verwandter Stämme ausrichteten und statistische Modelle verwendeten, um zu schätzen, wie schnell sich verschiedene Positionen im Gen im Laufe der Zeit verändert haben. Bacillus licheniformis AG3 gruppierte sich eng mit einer großen Gruppe ähnlicher Stämme, zeigte jedoch starke Variation in der Evolutionsgeschwindigkeit verschiedener Genabschnitte, was auf Regionen mit unterschiedlichen evolutionären Drücken hinweist. Im Gegensatz dazu fiel Bacillus cereus AG11 in eine eigenständige Untergruppe innerhalb des B. cereus‑Komplexes, mit gleichmäßigeren Änderungsraten der Genpositionen. Diese Muster deuten darauf hin, dass selbst innerhalb einer Gattung verschiedene Linien unterschiedliche evolutionäre Wege einschlagen können, während sie dennoch ähnliche Bodenökologien besetzen.
Was das für die zukünftige Landwirtschaft bedeutet
Die Studie zeigt, dass Sorghumwurzeln in einer einzigen Region eine vielfältige Besetzung von Bakterien beherbergen und dass die Kombination einfacher Mikroskop‑ und chemischer Tests mit DNA‑Sequenzierung ein leistungsfähiger Weg ist, Schlüsselakteure wie B. licheniformis und B. cereus zu identifizieren. Für Nicht‑Spezialisten lautet die Kernbotschaft, dass Gesundheit und Ertrag von Nutzpflanzen nicht nur von Saatgut und Boden abhängen, sondern auch von diesen verborgenen mikrobiellen Partnern. Obwohl diese Arbeit noch nicht direkt getestet hat, wie die identifizierten Stämme das Sorghumwachstum beeinflussen, kartiert sie, welche Mikroben vorhanden sind und wie sie verwandt sind — entscheidende Schritte zur Entwicklung sicherer, gezielter mikrobieller Inokulanzien, die Landwirten helfen könnten, widerstandsfähigeres Sorghum mit weniger chemischen Eingriffen anzubauen.
Zitation: Jurry, A.G., Sahoo, J.P., Sharma, S.S. et al. Morpho-biochemical and molecular identification of Bacillus licheniformis and Bacillus cereus isolates from sorghum (Sorghum bicolor L.) rhizosphere. Sci Rep 16, 8983 (2026). https://doi.org/10.1038/s41598-026-42932-y
Schlüsselwörter: Sorghum, Rhizosphärenbakterien, Bacillus licheniformis, Bacillus cereus, Pflanzenwachstumsförderung