Clear Sky Science · de
Cullin‑3‑Substrat‑Adapterprotein 1 (MtCSP1) beeinflusst die Nodulation durch Interaktion mit der GTPase ARFA1
Wie Bohnen ihren eigenen Dünger herstellen
Die moderne Landwirtschaft setzt stark auf Stickstoffdünger, die die Erträge steigern, aber ökologische Kosten mit sich bringen. Leguminosen wie Klee, Erbsen und Luzerne bieten eine natürliche Alternative: Sie beherbergen nützliche Bodenbakterien in speziellen Wurzelstrukturen, sogenannten Knöllchen, in denen atmosphärischer Stickstoff in pflanzenverfügbaren Dünger umgewandelt wird. Diese Studie zeigt, wie ein bislang wenig charakterisiertes Pflanzenprotein, MtCSP1, die Bildung dieser Knöllchen steuert, indem es den intrazellulären Verkehr und das Recycling wichtiger molekularer Schaltstellen in Wurzelzellen feinjustiert.
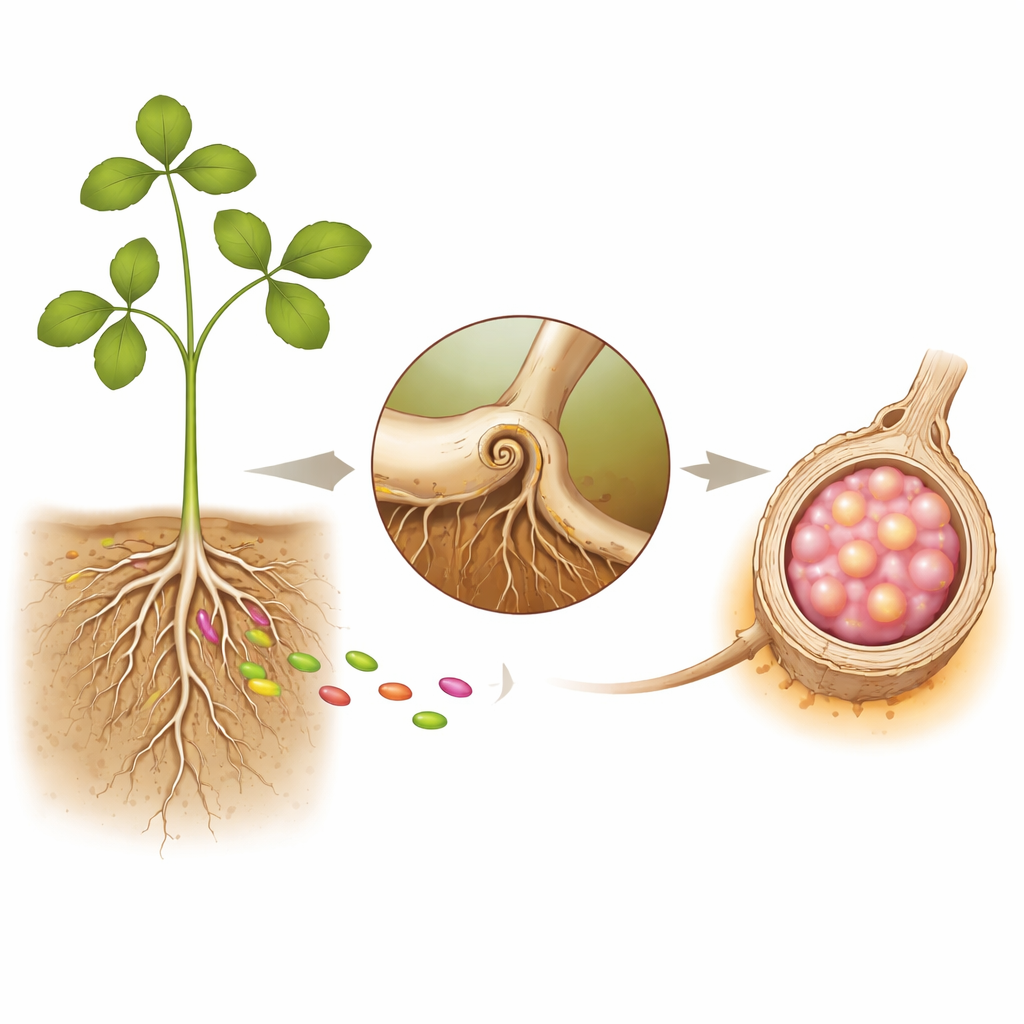
Pflanzenwurzeln und ihre bakteriellen Untermieter
Leguminosen arbeiten mit Rhizobien zusammen, Bodenbakterien, die atmosphärischen Stickstoff in nutzbare Formen wie Ammonium umwandeln können. Um diese Bakterien sicher aufzunehmen, bauen Wurzeln Knöllchen – winzige Fabriken an der Wurzeloberfläche. Der Prozess beginnt, wenn sich Bakterien an Wurzelhaaren festsetzen, die sich einrollen und einen schmalen Tunnel bilden, den Infektionsfaden. Durch diesen Tunnel wandern die Bakterien in tiefere Wurzelschichten, wo ein neues Organ, das Knöllchen, zu wachsen beginnt. Im reifen Knöllchen werden die Bakterien von pflanzlichen Membranen umhüllt und zu spezialisierten „Bakteroiden“, die im Austausch für Zucker und Energie Stickstoff für die Pflanze fixieren.
Intrazelluläre Verkehrspolizei in Wurzelzellen
Der Bau von Infektionsfäden und Knöllchen erfordert umfangreiche Umgestaltung von Pflanzenzellmembranen. Diese Umgestaltung hängt von Vesikeln ab – kleinen Membranbläschen, die Material innerhalb der Zelle transportieren. Ihre Bewegung und ihr Timing werden von kleinen molekularen Schaltern gesteuert, den GTPasen. Eine solche Schaltstelle, ARFA1, hilft in vielen Organismen bei der Formgebung und Lenkung von Vesikeln. Im Kontext stickstofffixierender Knöllchen war jedoch unklar, wie ARFA1 reguliert wird und wie lange es aktiv bleibt, bevor es entfernt wird.
Ein neuer Protein‑Verbindungsglied zwischen Verkehr und Recycling
Die Forschenden suchten nach Pflanzenproteinen, die physisch mit ARFA1 im Modelllegum Medicago truncatula interagieren. Mit Hilfe von Hefe‑Zwei‑Hybrid‑Screens und Proteininteraktionstests in Pflanzenblättern identifizierten sie MtCSP1, ein Protein aus einer Adapterfamilie, die spezifische Zielproteine an das zelluläre „Schredder“-System, das Ubiquitin‑System, anschließt. MtCSP1 trägt eine BTB/POZ‑Domäne, ein charakteristisches Motiv von Proteinen, die ausgewählte Partner an Cullin‑3‑basierte Komplexe rekrutieren, welche Proteine für den Abbau markieren. Fluoreszenzbildgebung zeigte, dass MtCSP1 und ARFA1 auf Vesikeln in späten Endosomen zusammentreffen – zellulären Zwischenstationen, die Cargo häufig in Richtung Abbau lenken.
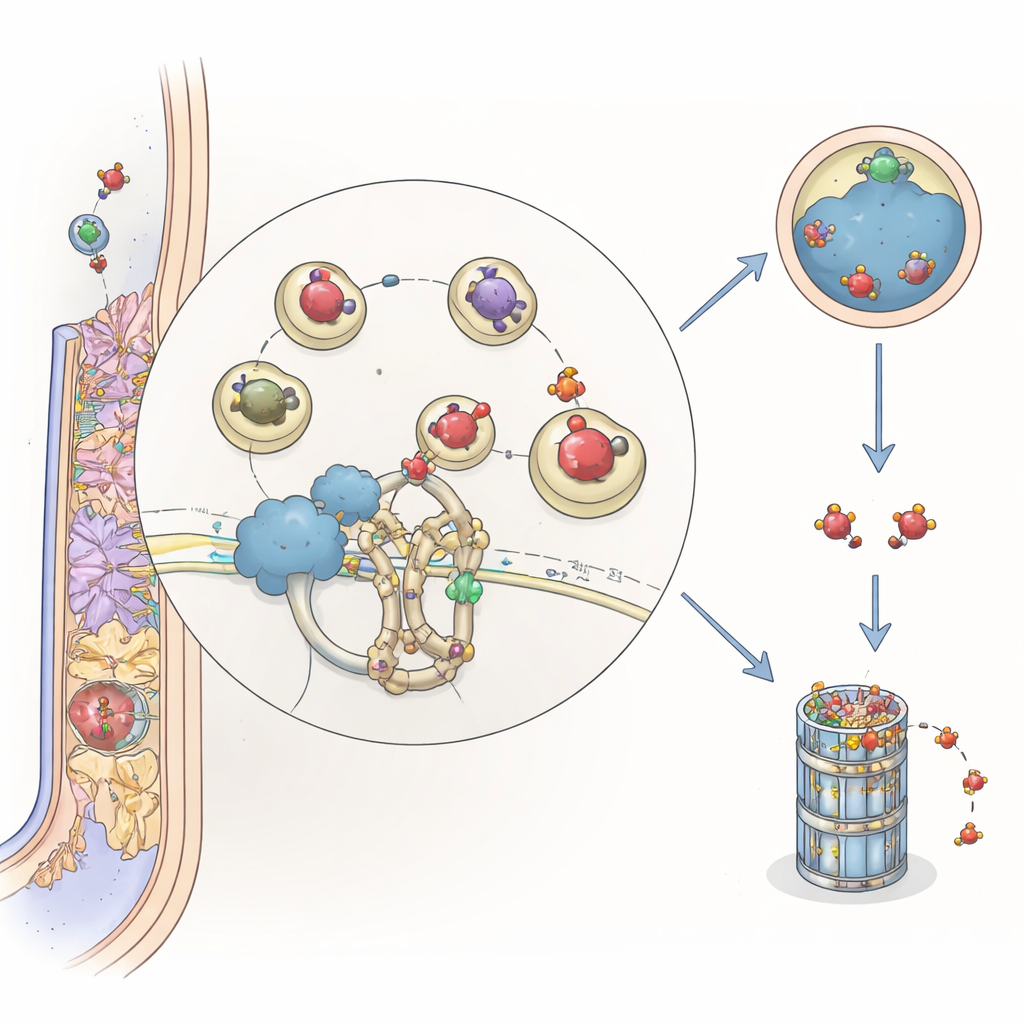
Wann und wo der neue Akteur wirkt
Um herauszufinden, wann MtCSP1 eingesetzt wird, verfolgte das Team die Aktivität seines Promotors, des DNA‑Schalters, der seine Produktion steuert. Sie fanden, dass MtCSP1 in Wurzelspitzen, in entstehenden Seitenwurzeln und in wichtigen Bereichen sich entwickelnder und reifer Knöllchen eingeschaltet wird, insbesondere im Meristem (der Wachstumszone) und in Infektionsregionen. Öffentliche Genexpressionsdatensätze zeigten, dass MtCSP1 und ARFA1 häufig gemeinsam aktiviert sind, was darauf hindeutet, dass die Pflanze die Präsenz des Schalters (ARFA1) und des Adapters (MtCSP1) während der Organbildung in den Wurzeln koordiniert.
Anzahl der Knöllchen und Fortschritt der Infektion feinabstimmen
Die Forschenden veränderten daraufhin die MtCSP1‑Spiegel in Wurzeln. Wurde MtCSP1 durch RNA‑Interferenz stillgelegt, bildeten die Pflanzen im Zeitverlauf weniger Knöllchen, und viele Infektionsfäden blieben in den Wurzelhaaren stecken, statt in die inneren Wurzelschichten vorzudringen. Die Knöllchen, die dennoch entstanden, hatten jedoch normale Größe, was darauf hinweist, dass MtCSP1 hauptsächlich den Beginn und das Voranschreiten der Infektion beeinflusst, weniger das spätere Wachstum. Umgekehrt führten Überexpressionen von MtCSP1 zu mehr Knöllchen und veränderten Abläufen bei Infektionsereignissen, wiederum ohne große Änderungen in Größe oder Form der Knöllchen. Diese Ergebnisse deuten darauf hin, dass MtCSP1 nicht nötig ist, um Infektionsfäden zu initiieren, wohl aber für deren korrektes Voranschreiten und für das erfolgreiche Entstehen neuer Knöllchen.
Schaltstellen recyceln, um die Symbiose zu steuern
In der Zusammenschau schlagen die Autorinnen und Autoren vor, dass MtCSP1 als Lotse wirkt, der ARFA1, in aktiven oder inaktiven Formen, zum Cullin‑3‑Ubiquitin‑Apparat auf späten Endosomenvesikeln bringt. Dort kann ARFA1 markiert und entweder zur Vakuole für den Abbau oder zum Proteasom geschickt werden, wodurch der Vesikelverkehr abgeschaltet oder angepasst werden kann, sobald er seine Funktion erfüllt hat. Indem MtCSP1 steuert, wie lange ARFA1 verfügbar bleibt, ermöglicht das Protein der Pflanze, die fragile Choreographie von Infektionsfäden und Knöllchenbildung fein zu justieren. Für Laien lautet die Botschaft: Leguminosen nutzen ein internes Recycling‑System, um winzige molekulare Ampeln in ihren Wurzeln zu steuern – so werden ihre natürlichen Düngerfabriken effizient und zum richtigen Zeitpunkt aufgebaut.
Zitation: Rípodas, C., Cretton, M., Eylenstein, A. et al. Cullin 3 substrate-adaptor protein 1 (MtCSP1) modulates nodulation through interaction with the GTPase ARFA1. Sci Rep 16, 8938 (2026). https://doi.org/10.1038/s41598-026-41112-2
Schlüsselwörter: Stickstofffixierung, Leguminosenknöllchen, Proteinabbau, Vesikeltransport, Pflanze–Mikroben‑Symbiose