Clear Sky Science · de
Vergleichende Plastid-Genomik von Hippophae enthüllt phylogenetische Beziehungen und liefert Kandidaten für DNA-Marker zur taxonomischen Identifikation
Warum dieser widerstandsfähige Strauch wichtig ist
Sanddorn ist ein zäher Strauch, der dort gedeiht, wo viele andere Pflanzen scheitern: an kalten, trockenen, windigen Hängen des Qinghai-Tibet-Plateaus und darüber hinaus. Seine leuchtend orangefarbenen Beeren werden weltweit als „Superfrüchte“ beworben, und die Pflanze wird vielfach zur Stabilisierung von Böden und zur Renaturierung geschädigter Flächen eingesetzt. Dennoch tun sich selbst Fachleute schwer, die eng verwandten Arten und Unterarten allein nach dem Aussehen zu unterscheiden. Diese Studie stellt eine einfache, aber wichtige Frage: Können wir das interne Gebrauchshandbuch der Pflanze — ihre DNA — lesen, um die Arten zu trennen, und damit Züchtern und Naturschützern ein mächtiges neues Werkzeug zur Verwaltung dieser wertvollen Ressource an die Hand geben?
Ein Blick in die grünen Kraftwerke der Pflanze
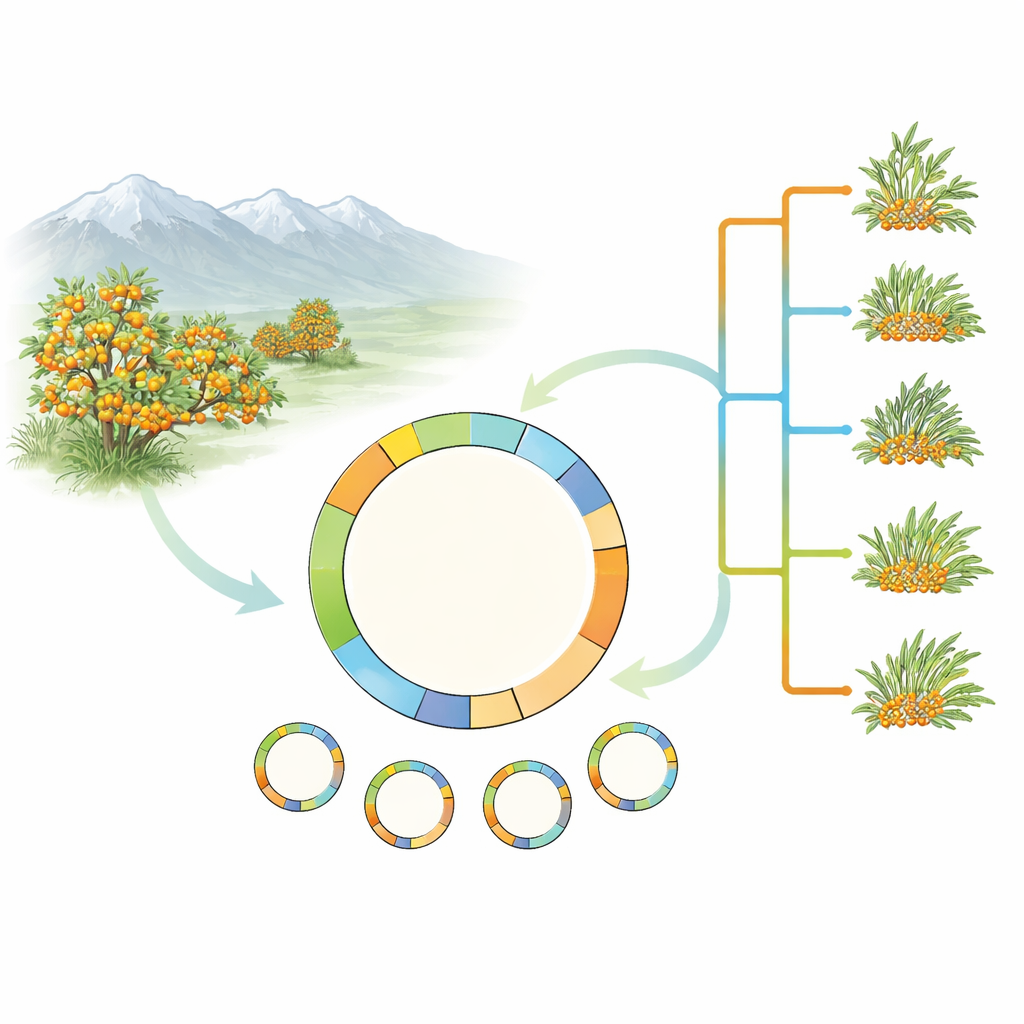
Statt die gesamte Komplexität des Sanddorn-Genoms anzugehen, konzentrierten sich die Forschenden auf die Plastiden der Pflanze — winzige grüne Kompartimente in den Zellen, die die Photosynthese ausführen. Plastiden besitzen ein eigenes kleines, zirkuläres DNA-Molekül, das hauptsächlich maternell vererbt wird und sich als äußerst nützlich zur Rekonstruktion pflanzlicher Stammbäume erwiesen hat. Das Team sammelte und sequenzierte komplette Plastid-Genome von 17 Proben, die fünf Sanddornarten und mehrere Formen des weit verbreiteten Hippophae rhamnoides abdecken. Zusätzlich fügten sie ein neu assemblertes Plastid-Genom einer wichtigen kultivierten Form, H. rhamnoides subsp. mongolica cv. Prevoskhodnaya, hinzu und überprüften frühere Datenbankeinträge sorgfältig auf Fehler.
Ein gemeinsamer Bauplan mit aufschlussreichen Unterschieden
Auf den ersten Blick wirkten die Plastid-DNA aller Sanddornproben bemerkenswert ähnlich. Jedes Genom war etwa 155.000 bis 156.000 „Buchstaben“ lang und folgte dem gleichen vierteiligen Aufbau, den viele Blütenpflanzen zeigen: zwei Einzelkopieregionen, getrennt durch ein Paar duplizierter Segmente. Der gleiche Satz an Genen war vorhanden und in derselben Reihenfolge angeordnet, und selbst die Gesamtverteilung der vier DNA-Buchstaben variierte kaum. Diese strukturelle Stabilität deutet darauf hin, dass der Plastid-Bauplan in Hippophae über die evolutionäre Zeit hinweg konserviert geblieben ist. Wenn die Forschenden jedoch in feinere Details hineinzoomten — etwa wie oft bestimmte Codons verwendet werden, um dieselbe Aminosäure zu verschlüsseln — fanden sie subtile, linien-spezifische Muster, die auf eine langsame, langfristige Prägung des Codes in verschiedenen Zweigen der Gattung hindeuten.
Den Stammbaum entwirren
Anhand von 78 protein-kodierenden Genen aus der Plastid-DNA erstellte das Team Evolutionsbäume, die den Sanddorn in die weitere Rosengewächs-Familie einordnen und danach die Beziehungen innerhalb von Hippophae detaillierter betrachten. Die Analysen bestätigten, dass Sanddorn als Gruppe eine natürliche monophyletische Linie bildet und dass H. rhamnoides und seine Unterarten ebenfalls eng verwandt sind. Interessanterweise fällt eine Art, H. tibetana, im Plastidbaum konstant innerhalb der H. rhamnoides-Gruppe, obwohl frühere Arbeiten auf Basis nuklearer DNA sie näher an der Basis der Gattung platziert hatten. Diese Diskrepanz zwischen nuklearer und plastidärer Geschichte deutet auf vergangene Hybridisierung oder andere komplexe evolutionäre Ereignisse hin und unterstreicht die Notwendigkeit künftiger Studien, die komplette nukleare und plastidäre Datensätze kombinieren.
Die genomischen Hotspots finden, die Identität markieren
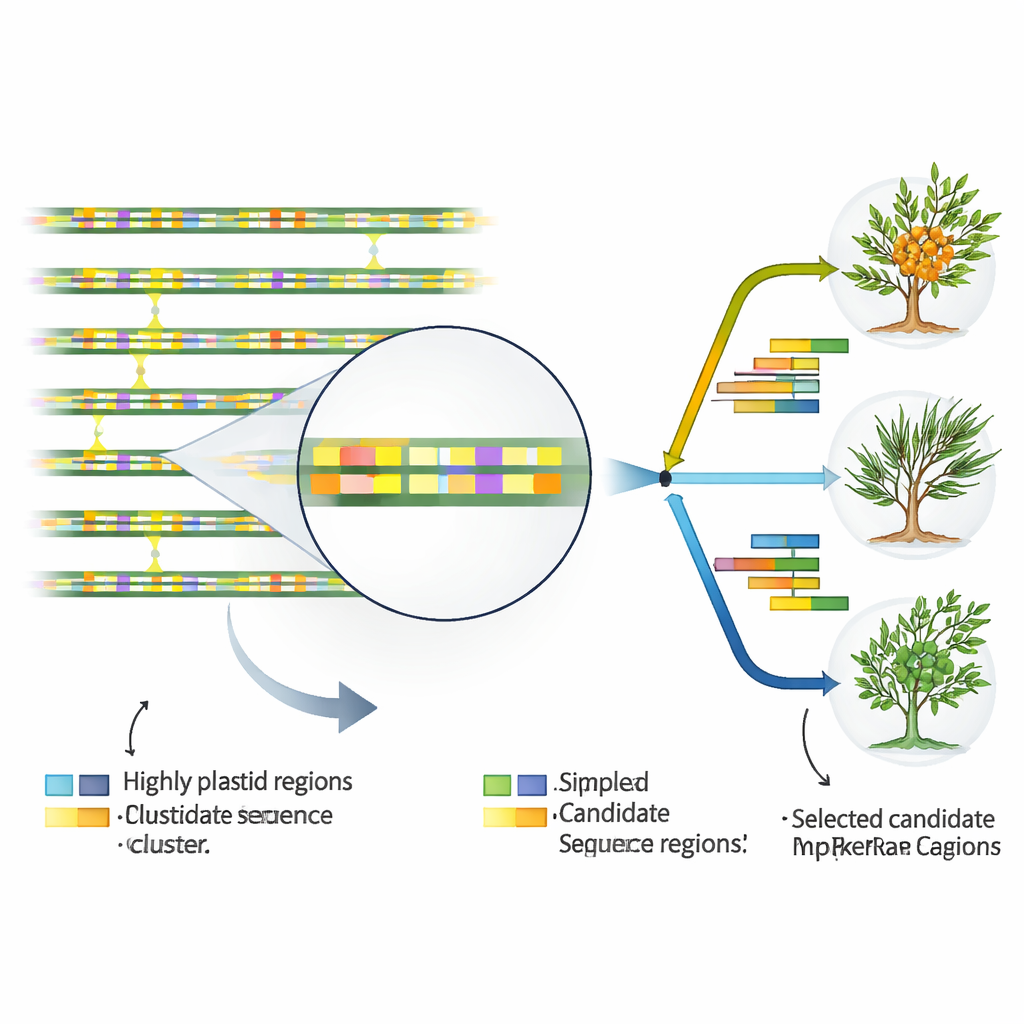
Um Plastid-DNA in alltagspraktische Werkzeuge für Taxonomen und Züchter zu verwandeln, suchten die Autorinnen und Autoren nach Sequenzabschnitten, die sich schneller verändern als der Rest. Beim Vergleich aller 17 Plastid-Genome identifizierten sie 46 besonders variable Regionen, die fast ausnahmslos zwischen Genen oder innerhalb nichtkodierender Introns liegen, statt in den eigentlichen Genbereichen. Sie kartierten zudem Dutzende kleiner, wiederholter Motive, bekannt als Simple Sequence Repeats, die besonders reich an den Basen A und T sind und sich in nichtkodierenden Regionen anhäufen. Einige dieser Wiederholungen und variablen Segmente zeigten klare Unterschiede zwischen Arten und sogar zwischen Unterarten von H. rhamnoides. Einige Regionen stachen sowohl auf Art- als auch auf Unterartenebene als Hotspots hervor und eignen sich damit hervorragend als Kandidaten für praktische DNA-Marker, die mit einfachen Labortests angezielt werden können.
Von DNA-Mustern zu praktischen Anwendungen
Indem die Studie sowohl das stabile Gerüst als auch die kleinen, aber aussagekräftigen Unterschiede in den Plastid-Genomen des Sanddorns kartiert, liefert sie ein Instrumentarium für verlässliche DNA-basierte Identifikation. Die vorgeschlagenen Markerregionen könnten helfen, ähnlich aussehende Arten zu unterscheiden, die Herkunft kommerzieller Beerenprodukte zu verifizieren, die wilde genetische Vielfalt zu schützen und die Auswahl von Zuchteltern in Programmen zu leiten, die auf Ernährung, Medizin und Landwiederherstellung abzielen. Einfach gesagt zeigen die Autorinnen und Autoren, dass ein sorgfältig gelesenes Chloroplasten-Gebrauchshandbuch verraten kann, wer wer in der erweiterten Familie dieses robusten Strauchs ist — und damit den Weg für klügeren Naturschutz und gezieltere Nutzung einer der widerstandsfähigsten Obstarten der Welt ebnen.
Zitation: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
Schlüsselwörter: Sanddorn, Plastid-Genom, DNA-Marker, Pflanzen-Taxonomie, genetische Vielfalt