Clear Sky Science · de
Genomische Charakterisierung multiresistenter Escherichia-coli-Stämme, die bei Patientinnen mit Harnwegsinfektion in Ägypten identifiziert wurden
Warum diese hartnäckigen Infektionen wichtig sind
Harnwegsinfektionen gehören zu den häufigsten Gründen für Arzt‑ und Krankenhausbesuche. Viele werden durch das Bakterium Escherichia coli verursacht und lassen sich in der Regel mit Standardantibiotika behandeln. Doch weltweit, auch in Ägypten, sind einige E.-coli‑Stämme so medikamentenresistent geworden, dass die Behandlungsmöglichkeiten knapp werden. Die vorliegende Studie nimmt zwei solcher schwer zu behandelnden Stämme aus ägyptischen Patientinnen genomisch genau unter die Lupe, um zu verstehen, wie sie mehreren Wirkstoffen entkommen und wie leicht sich ihre Resistenz verbreiten könnte.
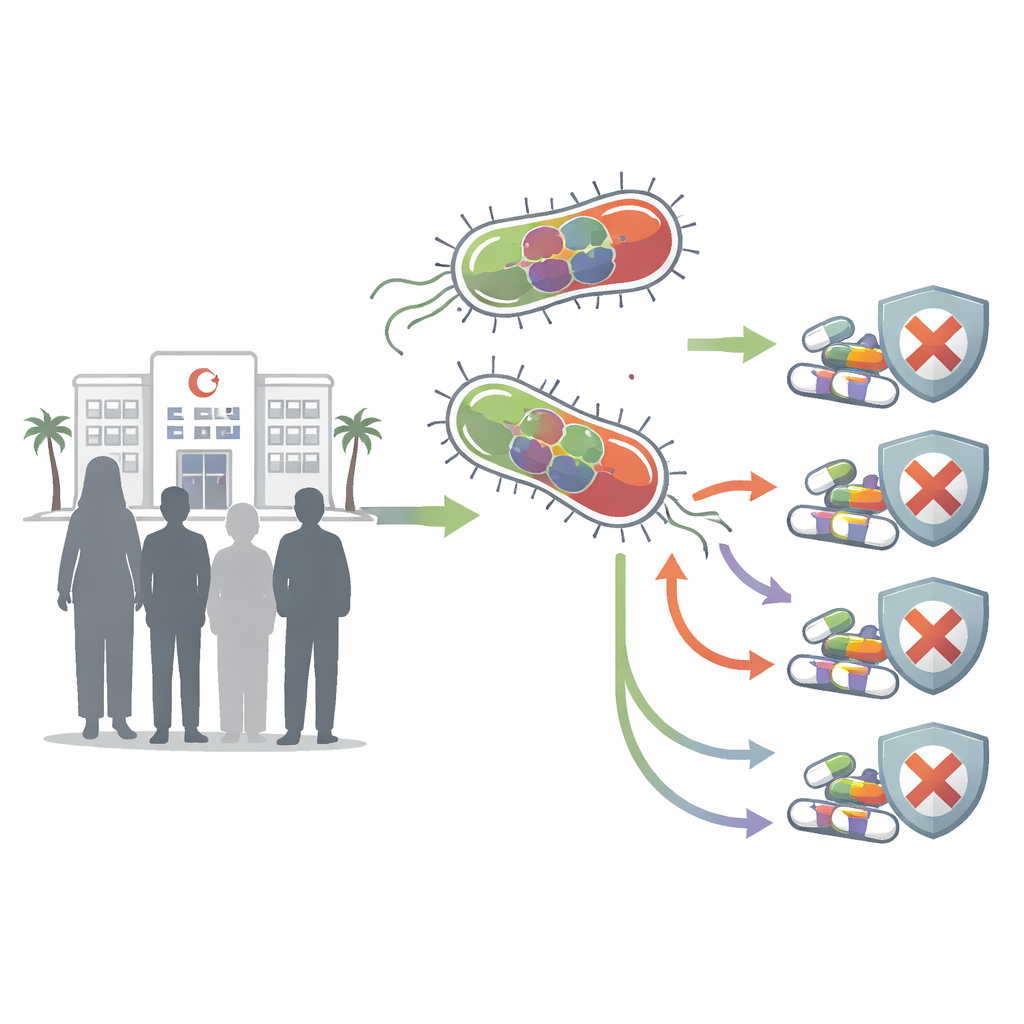
Zwei Patientinnen, zwei gefährliche Erreger
Die Forschenden konzentrierten sich auf zwei E.-coli‑Stämme, bezeichnet als UPE7 und UPE139, isoliert von Frauen mit Harnwegsinfektionen in einem Krankenhaus in Mansoura, Ägypten. In Tests gegen ein breites Spektrum an Antibiotika hielten beide Stämme vielen der normalerweise verschriebenen Wirkstoffe stand, darunter mehrere Reservemedikamente. Sie zeigten Resistenzen gegen gängige Penicilline und Cephalosporine, potente Carbapeneme, weit verbreitete Fluorchinolone und weitere Wirkstoffklassen. Dieses Muster ordnete sie eindeutig in die Gruppe der multiresistenten Bakterien ein, was die Behandlung erschwert, kostenintensiver macht und das Risiko für Komplikationen erhöht.
Das DNA-Spielbuch der Bakterien lesen
Um herauszufinden, wie diese Stämme so widerstandsfähig wurden, sequenzierte das Team ihre gesamten Genome mithilfe moderner DNA‑Sequenzierungstechnologien. Anschließend nutzten sie spezialisierte Computerwerkzeuge, um die Genome nach Genen zu durchsuchen, die mit Antibiotikaresistenz verknüpft sind, sowie nach Merkmalen, die den Bakterien helfen, Krankheit zu verursachen. Beide Stämme trugen zahlreiche Resistenzgene, die ihr Laborverhalten erklärten. So wiesen sie mehrere Beta‑Lactamase‑Gene auf, die wichtige Antibiotika inaktivieren, sowie Gene, die Schutz gegen Aminoglykoside, Tetracycline, Makrolide, Sulfonamide und Trimethoprim vermitteln. Veränderungen in zentralen DNA‑bearbeitenden Enzymen, den Zielstrukturen der Fluorchinolon‑Medikamente, stimmten mit ihrer starken Resistenz gegenüber Levofloxacin überein. Beide Stämme besaßen zudem ein Operon, das ihre Außenhülle so verändert, dass die Wirkung von Polymyxin‑Antibiotika abgeschwächt wird.
Versteckte Helfer, die Resistenz verbreiten
Über einzelne Resistenzgene hinaus beleuchtet die Studie die genetischen Vehikel, die diese Eigenschaften verbreiten. Viele Resistenzgene lagen neben mobilen genetischen Elementen wie Insertionssequenzen und Transposons – kleinen DNA‑Einheiten, die an andere Orte springen können – sowie auf Plasmiden, zirkulären DNA‑Molekülen, die Bakterien untereinander austauschen. Beispielsweise war ein weit verbreitetes Extended‑Spectrum‑Beta‑Lactamase‑Gen, CTX‑M‑15, in beiden Stämmen mit solchen mobilen Elementen verknüpft, während UPE139 zusätzlich OXA‑244 trug, ein Carbapenem‑abbauendes Enzym, das zwischen springenden DNA‑Segmenten im Chromosom eingebettet war. Dieselben Plasmidtypen, die hier gefunden wurden, sind andernorts mit Clustern von Resistenzgenen in Verbindung gebracht worden, was die Befürchtung nährt, dass diese Stämme ihre Abwehrmechanismen an andere Bakterien in Krankenhäusern und der Gemeinschaft weitergeben können.
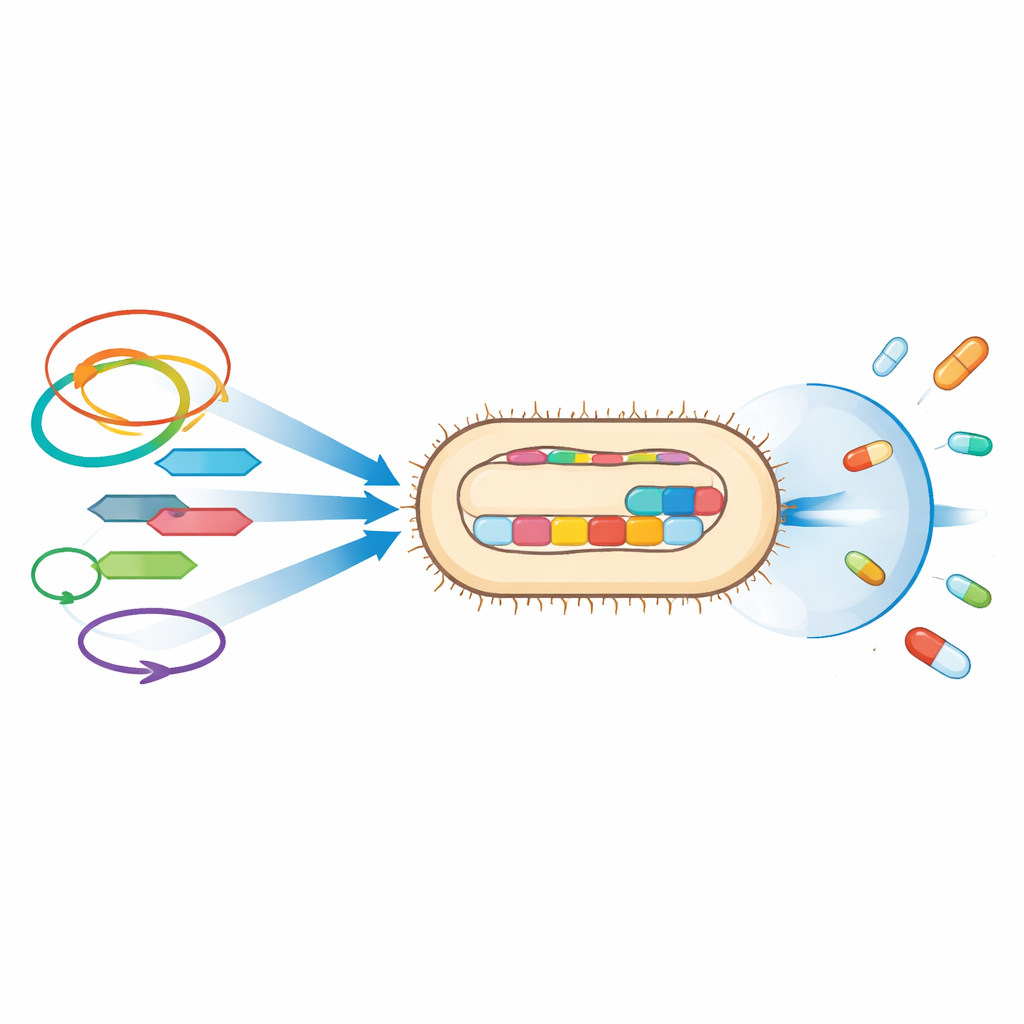
Werkzeuge für Infektion und Überleben
Die genetische Analyse deckte außerdem zahlreiche Eigenschaften auf, die diesen E.-coli‑Stämmen helfen, den Harntrakt zu besiedeln und Gewebe des Wirts zu schädigen. Sowohl UPE7 als auch UPE139 trugen mehrere Adhäsionsstrukturen, die ihnen ermöglichen, an Zellen zu haften und Biofilme zu bilden – schützende Gemeinschaften, die für Medikamente und das Immunsystem schwerer zu beseitigen sind. Sie kodierten Toxine wie Hämolysin, das Wirtszellen schädigen kann, sowie Eisenakquise‑Systeme, die den Bakterien erlauben, im eisenarmen Milieu des Körpers zu gedeihen. UPE139 verfügte insbesondere über zusätzliche Gene, die mit Kapselbildung, Invasion und Immunflucht verknüpft sind und darauf hindeuten, dass dieser Stamm eine besonders ausgeprägte Fähigkeit zur Persistenz und Verbreitung in Patientinnen besitzen könnte.
Was das für Patientinnen und Ärztinnen bedeutet
Durch die Kombination von konventionellen Antibiotikaempfindlichkeitstests mit vollständiger Genomsequenzierung zeigt die Studie, wie eine kleine Anzahl von Genen und mobilen Elementen gewöhnliche Harnwegsbakterien in formidable, multiresistente Krankheitserreger verwandeln kann. Sie macht auch deutlich, dass diese gefährlichen Eigenschaften auf DNA‑Segmenten liegen, die gut für den Transfer an andere Stämme geeignet sind, was das Risiko einer örtlichen und regionalen Ausbreitung erhöht. Für Patientinnen bedeutet das, dass einige häufige Infektionen schwerer zu heilen sein können. Für Klinikerinnen und Gesundheitsbehörden unterstreicht die Arbeit die Notwendigkeit fortlaufender genomischer Überwachung, eines umsichtigeren Antibiotikaeinsatzes und breiter angelegter Studien mit vielen weiteren Isolaten, um Hochrisiko‑Klone zu verfolgen, Behandlungsleitlinien zu verfeinern und die Ausbreitung der Resistenz zu verlangsamen.
Zitation: El Halfawy, N.M., Gouda, M.K., Elgayar, F.A. et al. Genomic characterization of multidrug-resistant Escherichia coli strains identified from patients with urinary tract infection in Egypt. Sci Rep 16, 8958 (2026). https://doi.org/10.1038/s41598-026-40536-0
Schlüsselwörter: Antibiotikaresistenz, Harnwegsinfektion, Escherichia coli, Genomsequenzierung, mobile genetische Elemente