Clear Sky Science · de
Klinisch interpretierbares Modell von extrazellulären Vesikel-Genen zur nichtinvasiven Leberkrebsdiagnose
Warum ein Bluttest für Leberkrebs wichtig ist
Leberkrebs gehört zu den tödlichsten Krebsarten weltweit, vor allem weil er häufig zu spät entdeckt wird, um noch kurativ behandelt werden zu können. Die heute eingesetzten Methoden zur Früherkennung – bildgebende Verfahren und Leberbiopsien – sind teuer, mitunter riskant und nicht immer zuverlässig. Diese Studie untersucht einen anderen Ansatz: Ob eine einfache Blutprobe, ausgewertet mit intelligenten Computermodellen, frühe Anzeichen von Leberkrebs erkennen kann, indem sie winzige genetische Botschaften liest, die erkrankte Zellen ins Blut abgeben.
Kleine Botenstoffe, die in unserem Blut schwimmen
Alle Zellen unseres Körpers setzen regelmäßig mikroskopische Bläschen, so genannte extrazelluläre Vesikel, in Blut und anderen Körperflüssigkeiten frei. Diese Vesikel transportieren Proteine, Lipide und Fragmente genetischen Materials, die den Zustand der Ursprungszellen widerspiegeln. Auch Krebszellen geben solche Vesikel ab, deren Fracht sich von der gesunder Zellen unterscheidet. Da Vesikel im Blutkreislauf zirkulieren, lassen sie sich aus einer einfachen Blutentnahme gewinnen, statt mit einer Nadel in die Leber zu stechen. Die Autorinnen und Autoren nutzten eine große öffentliche Datenbank, exoRBase 3.0, die detaillierte Messwerte des in Vesikeln gefundenen genetischen Materials von Hunderten von Menschen mit und ohne Leberkrebs enthält.
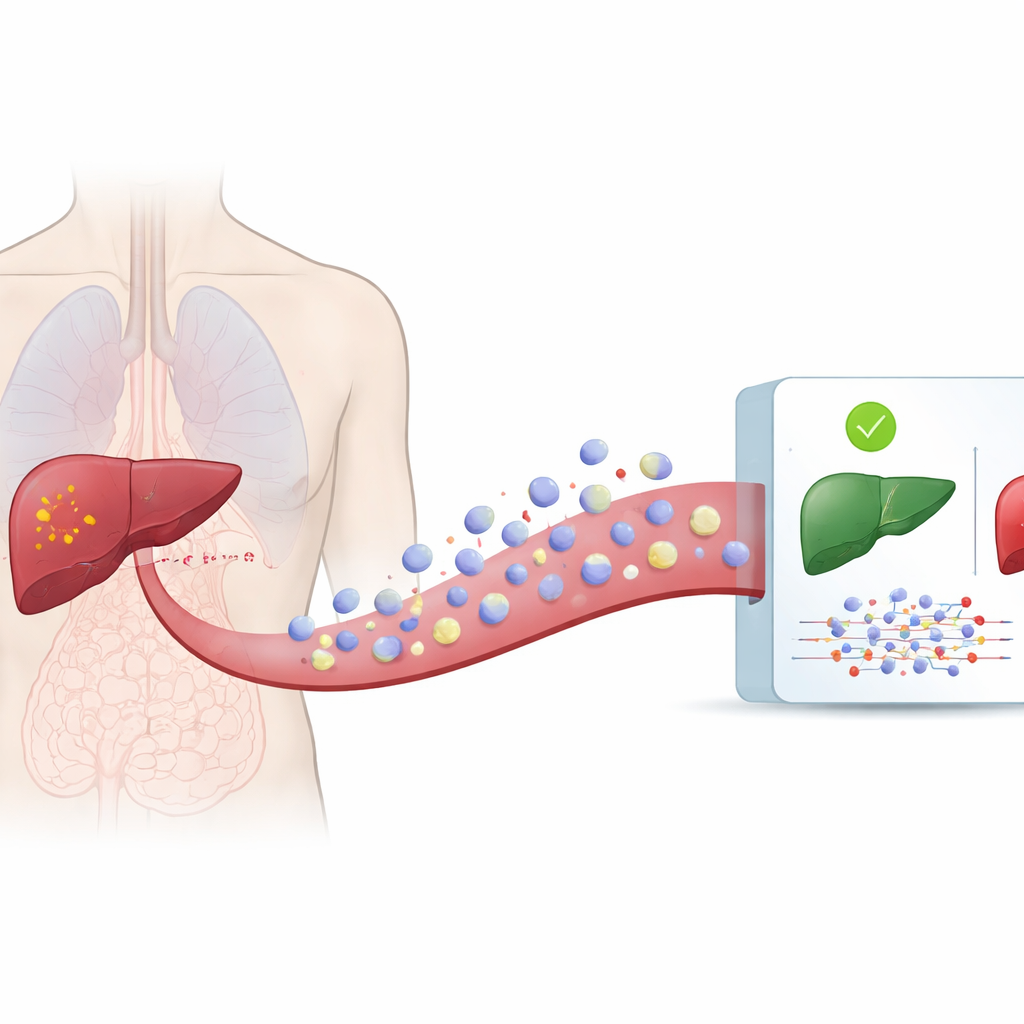
Computern beibringen, Vesikelsignale zu lesen
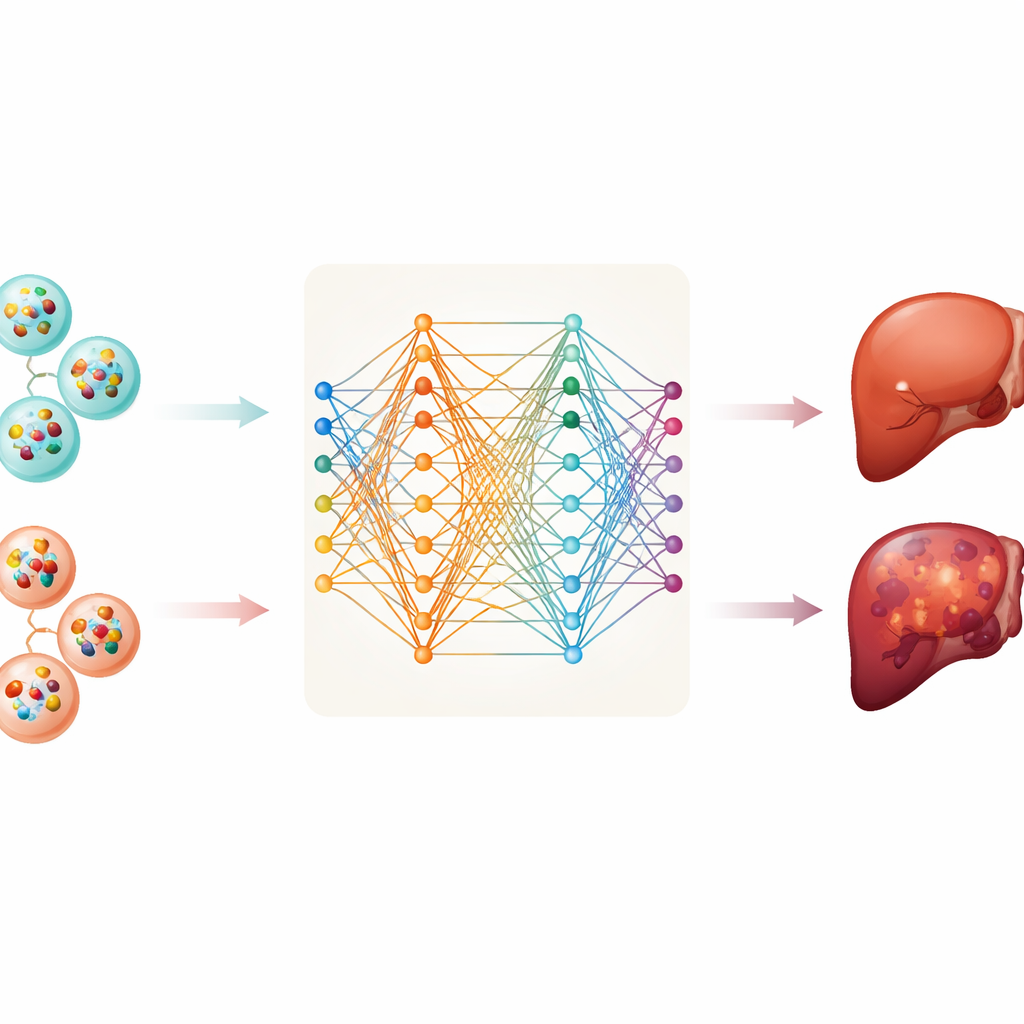
Aus dieser Datenbank sammelte das Team Informationen zu zwei Arten von RNA-Molekülen – Boten-RNA, die Anweisungen zur Proteinsynthese trägt, und lange nicht-kodierende RNA, die das Zellverhalten reguliert. Sie analysierten Proben von 112 Patientinnen und Patienten mit Leberkrebs und 118 gesunden Personen. Nach Bereinigung und Standardisierung der Daten trainierten sie sechs verschiedene Computermodelle, um Krebs- und Nicht-Krebs-Proben anhand von Mustern in Vesikel-RNA zu unterscheiden. Die Methoden reichten von klassischen statistischen Verfahren bis zu flexiblen tiefen neuronalen Netzen, die komplexe Muster aufspüren können.
Ein kleines, aber leistungsfähiges Genpanel finden
Das tiefe neuronale Netz erzielte innerhalb dieses Datensatzes die beste Leistung und trennte Krebs- von gesunden Blutproben in vielen Fällen korrekt. Allerdings ist ein Modell, das auf tausenden Messwerten beruht, schwer zu verstehen und für die Routineuntersuchung unpraktisch. Um dem entgegenzuwirken, wendeten die Forschenden eine Methode namens SHAP an, die hilft zu identifizieren, welche Eingaben für die Entscheidungen eines Modells am wichtigsten sind. Damit konnten sie die Signatur auf nur zehn spezifische Boten-RNAs in Vesikeln reduzieren. Eine davon, MTRNR2L8, hob sich als der stärkste Beitrag zur Vorhersage hervor; weitere wie HBB, PF4, FTL und S100A9 spielten ebenfalls Schlüsselrollen. Selbst mit nur diesen zehn RNAs arbeitete das Modell weiterhin gut, was darauf hindeutet, dass ein relativ kleines, fokussiertes Panel für einen Bluttest ausreichen könnte.
Die "Black Box" der künstlichen Intelligenz öffnen
Ärztinnen und Ärzte stehen Computermodellen, die Antworten ohne erklärbare Gründe liefern, oft skeptisch gegenüber. Um Vertrauen zu schaffen, legte das Team Wert auf Transparenz. SHAP wurde nicht nur genutzt, um die Wichtigkeit jedes Gens insgesamt zu bewerten, sondern auch um für einen bestimmten Patienten zu zeigen, wie jedes Gen die Vorhersage in Richtung „Krebs“ oder „gesund“ verschob. Die Forschenden testeten außerdem einen neueren Netzwerktyp, das Kolmogorov–Arnold-Netzwerk, das Beziehungen zwischen Eingaben und Ausgaben durch explizite mathematische Kurven darstellt. Dieser Ansatz bestätigte, dass dieselben zehn Gene starke Signale tragen und veranschaulichte, wie ihr kombiniertes Verhalten die endgültige Entscheidung prägt, was ein besser interpretierbares Bild des gelernten Modells bietet.
Vom Labor-Konzept zum möglichen klinischen Werkzeug
Als Machbarkeitsnachweis bauten die Autorinnen und Autoren eine Online-Demonstrationsplattform, auf der Nutzer Vesikel-Genmesswerte eingeben und die vom Modell vorhergesagte Wahrscheinlichkeit für Leberkrebs sowie eine visuelle Aufschlüsselung der einflussreichen Gene sehen können. Sie betonen jedoch, dass die Arbeit noch experimentell ist. Das Modell wurde bislang nur an Daten aus derselben öffentlichen Datenbank getestet, und reale Patientengruppen weisen häufig gemischte Lebererkrankungen, unterschiedliche Behandlungen und technische Unterschiede in der Probengewinnung auf. Größere, sorgfältig konzipierte Studien in unabhängigen Patientengruppen – unter Verwendung standardisierter Methoden – werden erforderlich sein, bevor ein solcher Test in Kliniken oder Screeningprogrammen eingesetzt werden kann.
Was das für Patientinnen und Patienten bedeutet
Die Studie zeigt, dass ein kleiner Satz genetischer Marker, transportiert von winzigen Partikeln im Blut, prinzipiell helfen könnte, Leberkrebs ohne invasive Eingriffe zu erkennen. Durch die Kombination dieser Marker mit Computermodellen, die Ärztinnen und Ärzte verstehen und prüfen können, weist die Arbeit in Richtung künftiger Bluttests, die sowohl genau als auch vertrauenswürdig sind. Obwohl vor der klinischen Anwendung noch bedeutende Hürden bestehen – etwa die Bestätigung der Ergebnisse in unterschiedlichen Populationen und die Sicherstellung, dass der Test praktikabel und bezahlbar ist – bietet diese Forschung einen Ausblick darauf, wie Liquid Biopsies und interpretierbare künstliche Intelligenz eines Tages frühere und sicherere Leberkrebsdiagnosen ermöglichen könnten.
Zitation: Zhang, Y., Mo, Z., Zhang, L. et al. Clinically interpretable extracellular vesicle gene model for Non-Invasive liver cancer diagnosis. Sci Rep 16, 9054 (2026). https://doi.org/10.1038/s41598-026-40020-9
Schlüsselwörter: Leberkrebs, Liquid Biopsy, extrazelluläre Vesikel, maschinelles Lernen, Früherkennung