Clear Sky Science · de
Hochsensitives Profiling somatischer Mutationen bei Schilddrüsenkrebs mittels nucleotide-enrichment-basierter MALDI-TOF-MS-Analyse
Warum das für Menschen mit Schilddrüsenknoten wichtig ist
Viele Menschen entdecken eine Schwellung in der Schilddrüse und erleben eine belastende Zeit des Wartens, bis geklärt ist, ob es sich um etwas Harmloses oder um Krebs handelt und wie schwerwiegend dieser gegebenenfalls ist. Ärztinnen und Ärzte stützen sich zunehmend auf Gentests, um winzige Veränderungen in Tumor-DNA zu identifizieren, die Diagnose, Operation und Nachsorge lenken können. Diese Studie stellt einen schnelleren, empfindlicheren und kostengünstigeren Labortest vor, der viele wichtige Schilddrüsenkrebs-Mutationen gleichzeitig nachweisen kann — selbst wenn nur wenige Krebszellen in einer Probe vorhanden sind.
Eine neue Methode zum Lesen von Krebs-DNA
Die Forschenden entwickelten eine Methode namens NE-MS, die einen chemischen Trick namens Nucleotide Enrichment mit einer Massenspektrometrie-Plattform kombiniert, die die Masse von DNA-Fragmenten messen kann. In der Schilddrüsendiagnostik gewinnen Ärztinnen und Ärzte oft nur eine geringe Zellzahl mittels Feinnadelaspiration (FNA), was es mit herkömmlichen Verfahren schwierig macht, seltene Krebsmutationen nachzuweisen. NE-MS ist darauf ausgelegt, auch mit diesen winzigen, teils minderqualitativen Proben gut zu arbeiten und auf 26 bekannte Mutationen in Genen wie BRAF, RAS, TERT, PIK3CA und RET zu testen, die in einschlägigen Leitlinien empfohlen werden.
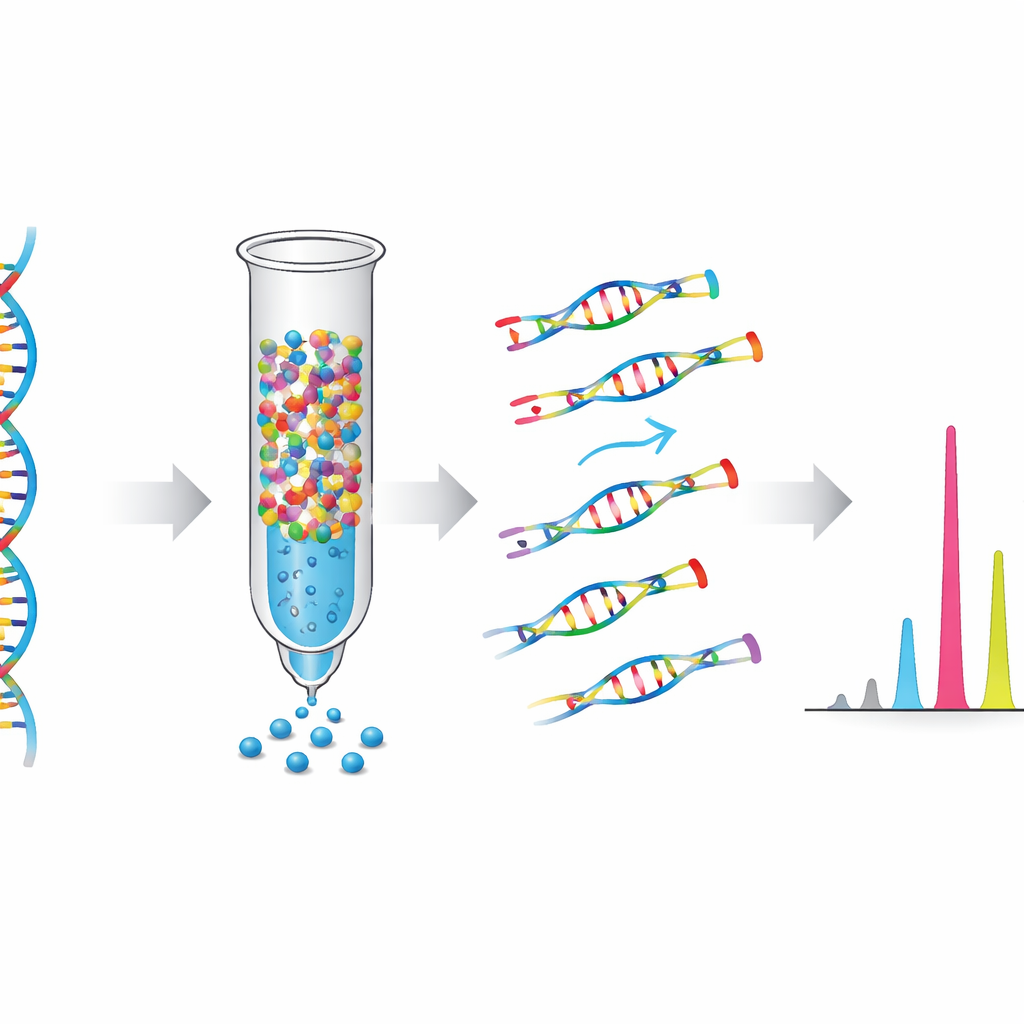
Wie der Test schwache Signale verstärkt
Standard-Massenspektrometrie-Tests verlängern sowohl die normale als auch die mutierte DNA während eines entscheidenden Reaktionsschritts, sodass das starke Signal der normalen DNA das schwache Signal der Krebszellen überdecken kann. NE-MS dreht dieses Problem um. Während des Single-Base-Extension-Schritts wird dem Reaktionsgemisch gezielt das Baustein-Nukleotid entzogen, das zur normalen, also Wildtyp-DNA an jeder Zielposition passen würde. Dadurch lässt sich nur DNA mit einer Mutation verlängern und nachweisen, während die normale DNA weitgehend unberücksichtigt bleibt. Das Team entwickelte außerdem ein automatisiertes Bewertungssystem auf Basis eines robusten Z-Scores, um echte Mutationssignale von Hintergrundrauschen zu unterscheiden, ohne dass eine manuelle Auswertung durch eine Technikerin oder einen Techniker nötig ist.
Nachweis von Empfindlichkeit und Zuverlässigkeit
Um die Leistungsfähigkeit von NE-MS zu prüfen, verwendeten die Wissenschaftler Referenz-DNA-Proben mit bekannten Schilddrüsenkrebs-Mutationen in stufenweise abnehmenden Anteilen, bis hinunter zu weniger als einem mutierten Molekül pro 300. Im Vergleich zur üblichen Massenspektrometrie verringerte NE-MS die Nachweisgrenze um bis zu das Achtfache für Schlüsselmutationen wie NRAS Q61K und TERT C228T und konnte zuverlässig einige Änderungen detektieren, die das ältere Verfahren faktisch verpasste. In Anschlussversuchen mit Patientenproben stimmten die NE-MS-Ergebnisse für die häufige BRAF V600E-Mutation sowohl mit einem hochsensitiven Droplet-Digital-PCR-Test als auch mit Next‑Generation-Sequencing überein und erreichten 100 % Übereinstimmung. Bei Anwendung der Methode auf 466 FNA-Proben zeigte sie eine ausgezeichnete diagnostische Leistung mit einer Fläche unter der ROC-Kurve von 0,99 für die Identifikation von BRAF-Mutationen.
Verknüpfung von Mutationsmustern mit dem Krankheitsverlauf
Über die Diagnostik hinaus untersuchte das Team, wie Mutationsmuster mit dem Verhalten von Schilddrüsenkrebs zusammenhängen. Sie wendeten NE-MS auf mehr als 1.000 operativ entfernte, in Paraffin eingebettete Tumorproben an. Die meisten Tumoren trugen allein BRAF-Mutationen, doch eine kleinere Gruppe wies mehrere Mutationen auf, etwa Kombinationen von BRAF mit TERT oder PIK3CA. Diese Patientinnen und Patienten waren häufiger älter, männlich, hatten größere Tumoren, Fernmetastasen, höhere Tumorstadien und erhielten eher Radiojodtherapie — alles Hinweise auf einen aggressiveren Krankheitsverlauf. Der Test identifizierte außerdem seltene RET-Mutationen, die mit einer besonders schweren Form von Schilddrüsenkrebs assoziiert sind und Patientinnen und Patienten markieren, die von zielgerichteten Medikamenten profitieren könnten.
Was das für die Versorgung bedeuten könnte
Zusammenfassend stellt diese Studie NE-MS als praktikables, hocheffizientes Werkzeug vor, das viele Schilddrüsenkrebs-Mutationen sensitiver in einem einzelnen Durchlauf profilieren kann — sowohl aus Nadelbiopsien als auch aus operativen Proben. Das Verfahren liefert Ergebnisse in etwa sechs Stunden, zu ungefähr einem Drittel der Kosten großer Next‑Generation‑Sequencing-Panels, und mit einem einfacheren Arbeitsablauf, der sich für stark frequentierte klinische Labore eignet. Für Patientinnen und Patienten könnte ein solcher Test klarere Antworten aus kleinen Biopsien, eine bessere Unterscheidung zwischen niedrig- und hochrisikogenen Schilddrüsenkrebsarten und personalisiertere Behandlungsentscheidungen bedeuten. Da die zugrunde liegende Chemie nicht auf Schilddrüsengene beschränkt ist, ließe sich der Ansatz auch auf viele andere Krebsarten ausweiten, um die Versorgung zu leiten.
Zitation: Bai, H., Li, Y., Li, J. et al. Highly sensitive profiling somatic mutations of thyroid cancer by nucleotide-enrichment-based MALDI-TOF MS assay. Sci Rep 16, 8080 (2026). https://doi.org/10.1038/s41598-026-39755-2
Schlüsselwörter: Schilddrüsenkrebs, somatische Mutationen, molekulare Diagnostik, Feinnadelaspiration, Massenspektrometrie