Clear Sky Science · de
Neue Marker-Gene für die gleichzeitige Nachweis von Salmonella, EHEC O157:H7 und Cronobacter
Warum das für die tägliche Lebensmittelsicherheit wichtig ist
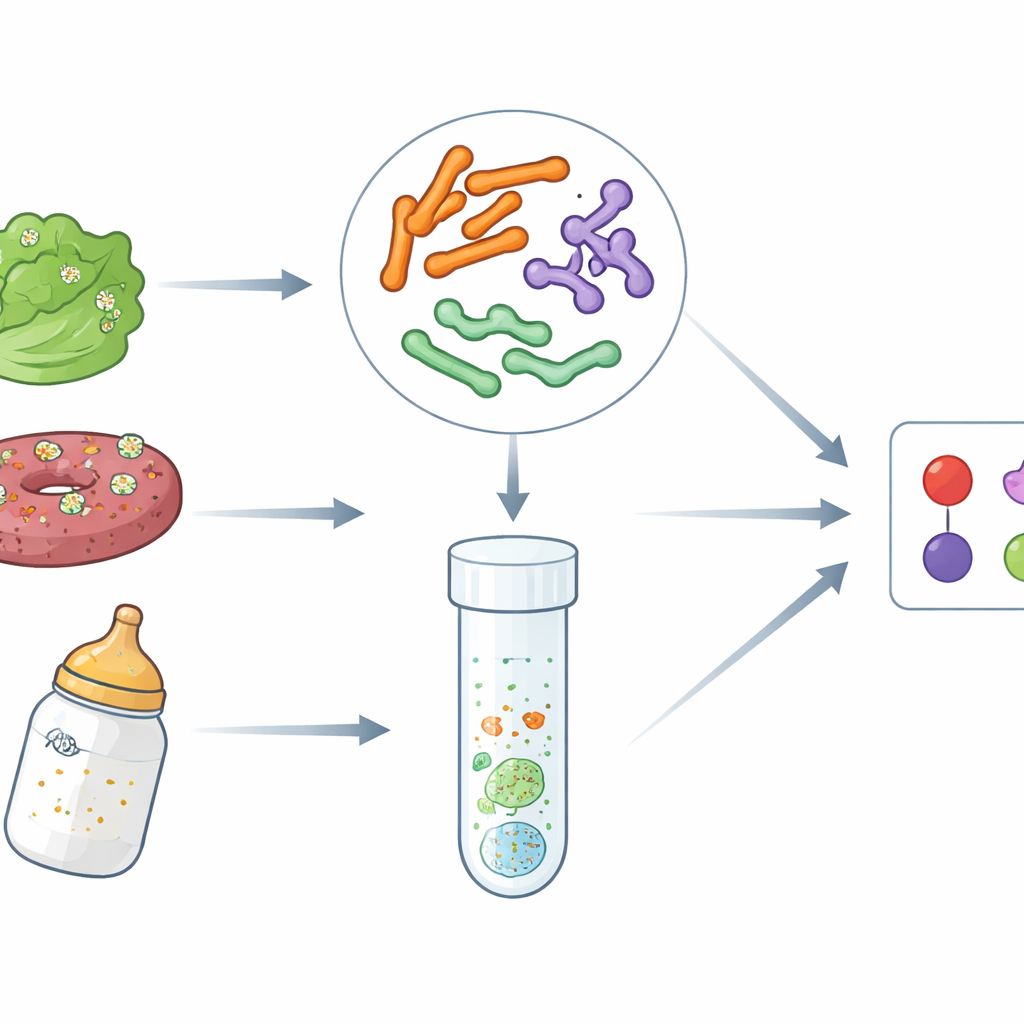
Von Blattgemüse über Burger bis hin zu Babynahrung können die Lebensmittel, denen wir vertrauen, gelegentlich gefährliche Keime enthalten. Drei der besorgniserregendsten Täter — bestimmte Stämme von E. coli, Salmonella und ein weniger bekanntes Bakterium namens Cronobacter — können schwere Erkrankungen auslösen, insbesondere bei Kleinkindern und gefährdeten Erwachsenen. Diese Studie zeigt, wie Wissenschaftler große DNA-Datenbanken und clevere Labortests nutzen, um alle drei Bedrohungen gleichzeitig schnell und zuverlässig zu erkennen, bevor kontaminierte Lebensmittel auf Ihrem Tisch landen.
Verborgene Gefahren in alltäglichen Lebensmitteln
Lebensmittelbedingte Erkrankungen haben im vergangenen Jahrzehnt zugenommen, teilweise bedingt durch globale Lieferketten und die schiere Menge an verarbeiteten und verzehrfertigen Lebensmitteln. EHEC O157:H7, eine hochtoxische Form von E. coli, kann blutigen Durchfall und Nierenversagen auslösen. Salmonella verursacht jährlich Millionen von Fällen von Lebensmittelvergiftungen, und Cronobacter, obwohl weniger bekannt, kann für Neugeborene tödlich sein, besonders in Verbindung mit pulverisierter Säuglingsnahrung. Traditionelle Labormethoden konzentrieren sich oft auf einen Erreger zur Zeit und erfordern Tage der Anzucht, was Ausbruchsuntersuchungen und routinemäßige Prüfungen verlangsamt. Die Autoren wollten schnellere DNA-basierte Tests entwickeln, die diese drei Erreger zusammen in einem einzigen, schlanken Verfahren markieren können.
„Barcodes“ in einem Meer von DNA finden
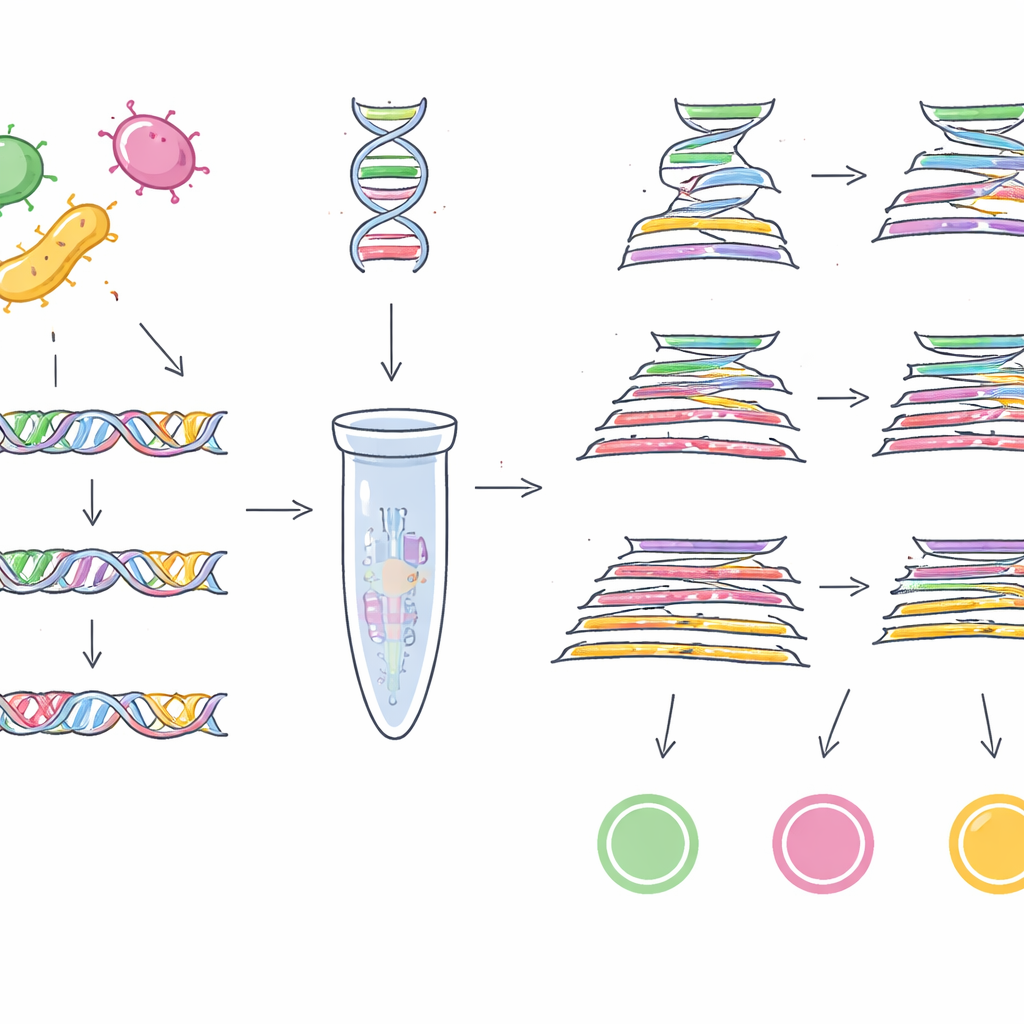
Dazu brauchte das Team zunächst verlässliche genetische „Barcodes“ — kurze DNA-Abschnitte, die in nahezu allen Stämmen eines Zielkeims vorkommen, aber bei anderen fehlen. Anstatt nur eine Handvoll Genome zu durchsuchen, griffen sie auf eine enorme öffentliche Sammlung von 1,46 Millionen bakteriellen Genomen aus 50 verschiedenen Gattungen zurück. Für EHEC O157:H7 verglichen sie Tausende von E. coli-Genomen und durchsuchten mehr als 100.000 Familien von Zusatzgenen, um DNA-Sequenzen zu finden, die für diesen gefährlichen Subtyp einzigartig sind. Nach mehreren Filter- und Abgleichrunden gegen mehr als eine Million Nicht-E.-coli-Genome stießen sie auf ein Gen namens z0340 als hochspezifischen Marker für EHEC O157:H7. Mit einer ähnlichen Strategie an mehr als einer halben Million Salmonella-Genome und nahezu einer Million anderer bakterieller Genome identifizierten sie ein weiteres Gen, sbcC, als zuverlässigen Marker für die Salmonella-Gruppe insgesamt.
Marker in praxistaugliche Tests verwandeln
Mit diesen beiden neuen Barcodes — plus einem Cronobacter-spezifischen Gen, ygcB, das die Gruppe zuvor entdeckt hatte — entwarfen die Forschenden Labortests, die alle drei Erreger auf einmal nachweisen können. Sie entwickelten Multiplex-PCR-Assays, die wie molekulare Kopierer spezifische DNA-Abschnitte anvisieren, sowie eine sensitivere TaqMan-Quantitative-PCR-Version, die in Echtzeit misst, wie viel Ziel-DNA vorhanden ist. Als diese Tests mit 23 Stämmen der drei Erreger und 100 Stämmen anderer häufiger Bakterien konfrontiert wurden, identifizierten sie jedes Mal nur die vorgesehenen Ziele und zeigten damit 100 % Spezifität. Die einfache Multiplex-PCR konnte bereits 1 Pikogramm DNA pro Mikroliter nachweisen, während die TaqMan-Version bis 0,5 Pikogramm reichte, was auf eine hohe Sensitivität hindeutet.
Anwendung der Methoden an Lebensmitteln
Laborgenauigkeit ist nur nützlich, wenn die Tests in unordentlichen, realen Proben funktionieren. Um das zu prüfen, kontaminierten die Wissenschaftler Salat, Hackfleisch und pulverisierte Säuglingsnahrung absichtlich mit bekannten Mengen an EHEC O157:H7, Salmonella oder Cronobacter. Nach standardisierten Anreicherungsphasen, die vorhandene Bakterien vermehren sollten, setzten sie ihre Multiplex-PCR- und TaqMan-qPCR-Assays ein. In allen Fällen detektierten die Methoden den eingesetzten Erreger korrekt und lieferten in negativen Kontrollen keine Fehlalarme. Die Leistung war über alle drei Lebensmitteltypen hinweg konsistent, was darauf hindeutet, dass Fette, Pflanzenbestandteile oder komplexe Zutaten die Detektion nicht merklich stören.
Beschränkungen und mögliche Verbesserungen
Trotz der starken Ergebnisse weisen die Autoren darauf hin, dass ihr Validierungs-Panel nur einen winzigen Bruchteil der in der Natur vorkommenden mikrobiellen Vielfalt repräsentiert. Beispielsweise testeten sie im Labor nur einen EHEC O157:H7-Stamm, obwohl ihr genomischer Screening-Typ Zehntausende solcher Stämme umfasste. Sie arbeiteten außerdem mit relativ hohen Kontaminationsniveaus im Vergleich zu den extrem niedrigen Bakterienzahlen, die dennoch Krankheiten verursachen können. Zukünftige Arbeiten müssen viel mehr reale Isolate testen, natürlich kontaminierte Lebensmittel untersuchen und interne Kontrollen ergänzen, um Substanzen in Lebensmitteln abzufangen, die die DNA-Amplifikation hemmen könnten.
Was das für Verbraucher bedeutet
Alltäglich gesprochen zeigt diese Studie, dass sorgfältig ausgewählte DNA-Barcodes es Lebensmittelsicherheitslabors ermöglichen können, mehrere hochriskante Keime gleichzeitig mit hoher Genauigkeit und in kürzerer Zeit als traditionelle kulturbasierte Methoden zu screenen. Durch das Durchsuchen von Millionen von Genomen identifizierten die Forschenden drei genetische Signaturen — eine für EHEC O157:H7, eine für Salmonella und eine für Cronobacter — die offenbar sowohl hochspezifisch als auch stabil sind. Die resultierenden Tests könnten die routinemäßige Überwachung von Lebensmitteln wie Blattgemüse, Fleisch und Säuglingsnahrung verstärken und Kontaminationen früher und zuverlässiger erfassen. Über diese drei Erreger hinaus könnte derselbe genomische Ansatz verwendet werden, um schnelle Tests für viele andere gefährliche Mikroben zu entwickeln und so ein leistungsfähiges neues Instrument zur Sicherung der globalen Lebensmittelversorgung bereitzustellen.
Zitation: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Schlüsselwörter: Lebensmittelbedingte Krankheitserreger, Multiplex-PCR, genomische Marker, Salmonella und EHEC, Cronobacter-Nachweis