Clear Sky Science · de
Eine Pilotstudie zur Protokollkonsistenz und Reproduzierbarkeit von Graph-Metriken in mikrostruktur-gewichteten Connectomen
Warum die Verdrahtungskarte des Gehirns einen Zuverlässigkeitscheck braucht
Ärztinnen, Ärzte und Wissenschaftler betrachten das Gehirn zunehmend als eine riesige Verdrahtungskarte, in der Regionen über Bündel von Nervenfasern miteinander kommunizieren. Neue, auf MRT basierende Methoden können diese Verdrahtung in mathematische Netzwerke überführen, die frühe Anzeichen von Erkrankungen wie Multipler Sklerose oder Alzheimer aufzeigen könnten. Bevor solche Messungen jedoch für Diagnostik oder Therapieentscheidungen genutzt werden können, muss eine grundlegende Frage beantwortet werden: Wenn wir dasselbe gesunde Gehirn mehrfach scannen oder auf verschiedenen Geräten mit leicht unterschiedlichen Einstellungen, erhalten wir dann im Wesentlichen dasselbe Netzwerk zurück?
Von der Wasserbewegung zu Landkarten der Gehirnautobahnen
Um diese Verdrahtungskarten zu erstellen, verwenden die Autorinnen und Autoren eine Form der MRT, die verfolgt, wie sich Wassermoleküle im Gewebe bewegen. In der weißen Substanz, wo lange, isolierte Nervenfasern zusammenlaufen, bewegt sich Wasser bevorzugt entlang der Fasern statt quer zu ihnen. Durch Messung dieser richtungsabhängigen Bewegung in vielen Orientierungen können Computeralgorithmen Faserbündel rekonstruieren und ein „Connectom“ zusammenstellen – eine Matrix, die festhält, welche grauen Hirnregionen durch welche weißen-materiellen Bahnen verbunden sind. Anstatt nur zu zählen, wie viele virtuelle Fasern zwischen Regionen rekonstruiert wurden, konzentriert sich diese Studie auf „mikrostruktur-gewichtete“ Connectome, bei denen jede Verbindung durch Eigenschaften des Gewebes selbst charakterisiert wird, etwa wie geordnet die Fasern sind oder wie dicht sie erscheinen.
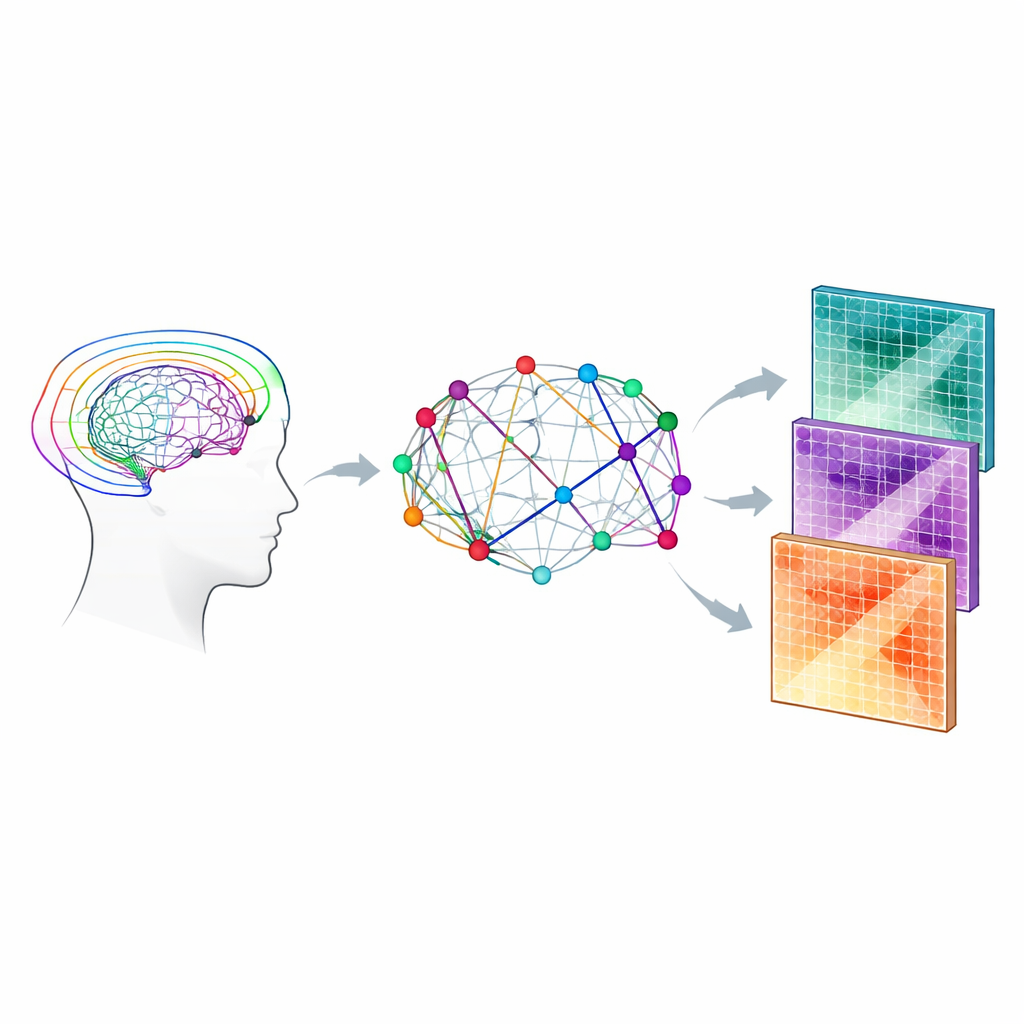
Biologische Details in das Netzwerk einbringen
Das Team kombinierte zwei Modellfamilien, die das Diffusions-MRT-Signal interpretieren. Das erste, die Diffusion Tensor Imaging (DTI), fasst zusammen, wie richtungsabhängig die Wasserbewegung ist und wie schnell sie durchschnittlich diffundiert. Das zweite, Bingham-NODDI genannt, geht einen Schritt weiter, indem es abschätzt, welcher Anteil eines kleinen Gewebevolumens aus Wasser innerhalb von Nervenfasern, außerhalb davon oder in flüssigkeitsgefüllten Räumen besteht. Mit einem relativ umfangreichen „Vier-Shell“-Scanprotokoll, das komplexe Fasergeometrien besser erfassen soll, berechneten sie mehrere mikrostrukturelle Parameter, darunter fraktionelle Anisotropie und mittlere Diffusivität (aus dem Tensormodell) sowie intra-neurite und extra-zelluläre Volumenanteile (aus Bingham-NODDI). Diese Parameter wurden entlang jedes rekonstruierten Faserbündels propagiert und kombiniert, um jeder Verbindung im Netzwerk eine biologisch informierte Gewichtung zu geben.
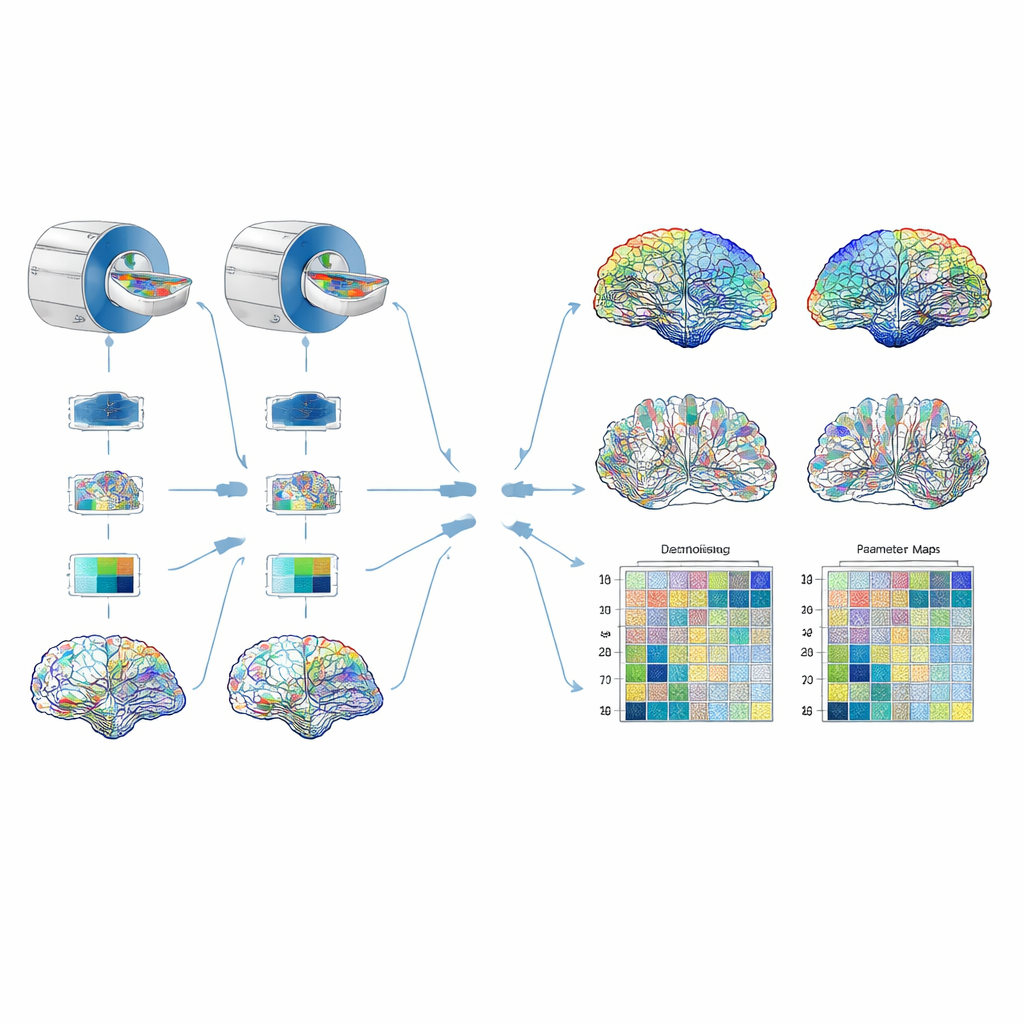
Die Pipeline auf die Probe stellen
Die Zuverlässigkeit wurde auf drei sich ergänzende Weisen bewertet. Zunächst scannten die Forschenden wiederholt einen sorgfältig gestalteten physischen Phantom – ein Geflecht synthetischer Fasern in Salzwasser, das Schlüsselfunktionen des Hirngewebes nachahmt – um zu testen, wie stabil die Parameter über kurze Zeiträume sind. Anschließend untersuchten sie vier gesunde Freiwillige an zwei Krankenhäusern mit derselben Marke und demselben Modell des MRT-Geräts und denselben Einstellungen, um Unterschiede zwischen den Standorten zu ergründen. Schließlich verglichen sie das Vier-Shell-Protokoll mit einem kürzeren, konventionelleren Zwei-Shell-Protokoll, um zu prüfen, ob beide ähnliche Parameterwerte liefern. Für die Hirndaten rekonstruierten sie mehrere Versionen des Connectoms, gewichtet nach unterschiedlichen Parametern, und extrahierten Graph-Maße wie die globale Netzwerkeffizienz, die Clusterung der Verbindungen und die Stärke, mit der jede Region mit dem Rest des Gehirns verbunden ist. Anschließend überprüften sie, wie stark sich diese Maße von Standort zu Standort änderten und wie viel der Variation echte Unterschiede zwischen Personen statt Messrauschen widerspiegelte.
Was sich als vertrauenswürdig erwies
Mehrere zentrale Gewebeparameter zeigten eine bemerkenswerte Konsistenz. Fraktionelle Anisotropie, mittlere Diffusivität sowie die intra-neuritischen und intra-zellulären Volumenanteile variierten bei wiederholten Scans, zwischen Standorten und (für die meisten Regionen) zwischen dem Zwei- und Vier-Shell-Protokoll um weniger als fünf Prozent. Dagegen waren Größen, die beschreiben, wie stark Faserrichtungen gestreut sind – sowie ein verwandter „Konzentrations“-Parameter – unbeständiger und wurden daher aus der Netzwerkbildung ausgeschlossen. Wenn die Forschenden Connectome gewichtet nach den stabilsten Messgrößen erzeugten, waren viele Netzwerkeigenschaften, einschließlich Dichte, globaler Effizienz, mittlerer Clusterung und mittlerer Verbindungsstärke, zwischen den Standorten reproduzierbar. Eine Ausnahme bildete die Modularität, ein Maß dafür, wie klar das Netzwerk in getrennte Gemeinschaften zerfällt; dieses war bemerkenswert empfindlich gegenüber kleinen Änderungen der zugrunde liegenden Gewichtungen. Connectome, die nach extra-zellulärem Volumen gewichtet waren, schnitten insgesamt am schlechtesten ab, wobei mehrere Graph-Maße eine geringe Übereinstimmung zwischen den Standorten zeigten.
Warum das für die Gehirngesundheit wichtig ist
Die Studie zeigt, dass es nicht ausreicht, rekonstruierte Fasern zu zählen, wenn man nach Biomarkern für Erkrankungen der Hirnverdrahtung sucht. Durch die sorgfältige Auswahl stabiler mikrostruktureller Parameter zur Gewichtung jeder Verbindung können Forschende reichhaltigere, biologisch fundierte Netzwerke erstellen, deren Schlüsselfunktionen über Scanner und Protokolle hinweg wiederholbar sind. Unter den getesteten Bedingungen erschienen Connectome, die nach fraktioneller Anisotropie, mittlerer Diffusivität und intra-neuritischem Volumen gewichtet waren, robust genug, dass ihre grundlegenden Netzwerkstatistiken als Kandidaten für Biomarker bei Erkrankungen dienen könnten, die die Gehirnkonnektivität stören. Gleichzeitig weist die Arbeit auf empfindlichere Maße hin, wie Modularität und einige fortgeschrittene mikrostrukturelle Indizes, die mit Vorsicht behandelt werden sollten, bis größere, multizentrische Studien ihre Zuverlässigkeit bestätigen.
Zitation: Cavallo, M., Ricchi, M., Axford, A. et al. A pilot study on protocol consistency and graph metric reproducibility in microstructure-weighted connectomes. Sci Rep 16, 8288 (2026). https://doi.org/10.1038/s41598-026-38964-z
Schlüsselwörter: Gehirnkonnektivität, Diffusions-MRT, Connectom, Netzwerkreproduzierbarkeit, Mikrostruktur-Bildgebung