Clear Sky Science · de
SPCNNet: spiking point cloud neural network für die morphologische Klassifikation von Neuronen
Warum die Form von Gehirnzellen wichtig ist
Jeder Gedanke, jedes Erinnern und jede Wahrnehmung, die Sie erleben, hängt von der Arbeit von Milliarden von Neuronen ab — elektrisch aktiven Zellen mit verzweigten, baumartigen Fortsätzen. Diese Fortsätze sind nicht alle gleich geformt, und die Unterschiede stehen in engem Zusammenhang mit der Funktion der jeweiligen Zelle im Gehirn. Die hier beschriebene Studie stellt eine neue Methode vor, Neuronen anhand ihrer 3D‑Gestalt mit einer vom Gehirn inspirierten Form künstlicher Intelligenz zu klassifizieren, was die Kartierung und das Verständnis neuronaler Schaltkreise verbessern könnte.
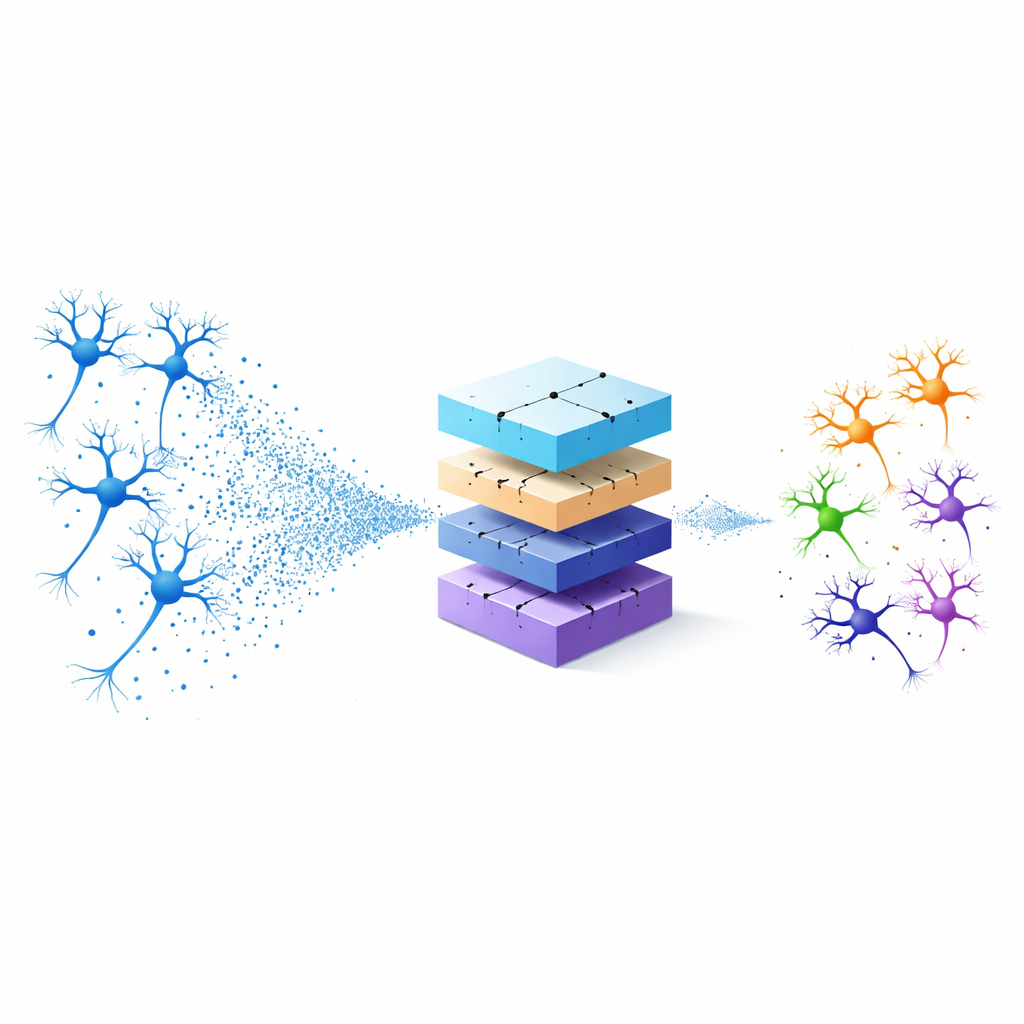
Neuronen als Punktwolken betrachten
Traditionell klassifizieren Wissenschaftler Neuronen entweder durch handgefertigte geometrische Messgrößen — etwa die Anzahl der Zweige — oder durch das Abflachen von 3D‑Zellen zu 2D‑Bildern für Standard‑Bildverarbeitungssoftware. Beide Ansätze werfen Informationen weg: feste Messgrößen können subtile Formmuster übersehen, und 2D‑Projektionen verlieren die Tiefe. Die Autoren behandeln stattdessen jedes Neuron als 3D‑„Punktwolke“, eine Menge von Punkten im Raum, die seine Gesamtgestalt nachzeichnet. Sie beginnen mit einer standardisierten digitalen Beschreibung von Neuronen, den sogenannten SWC‑Dateien, und behalten nur die 3D‑Koordinaten und die Verbindungen jedes kleinen Segments. Mittels einer Technik namens farthest point sampling wählen sie eine Teilmenge von Punkten aus, die die Struktur weiterhin erfasst, dabei aber die zu verarbeitende Datenmenge stark reduziert.
Die Spikes machen die Rechnung
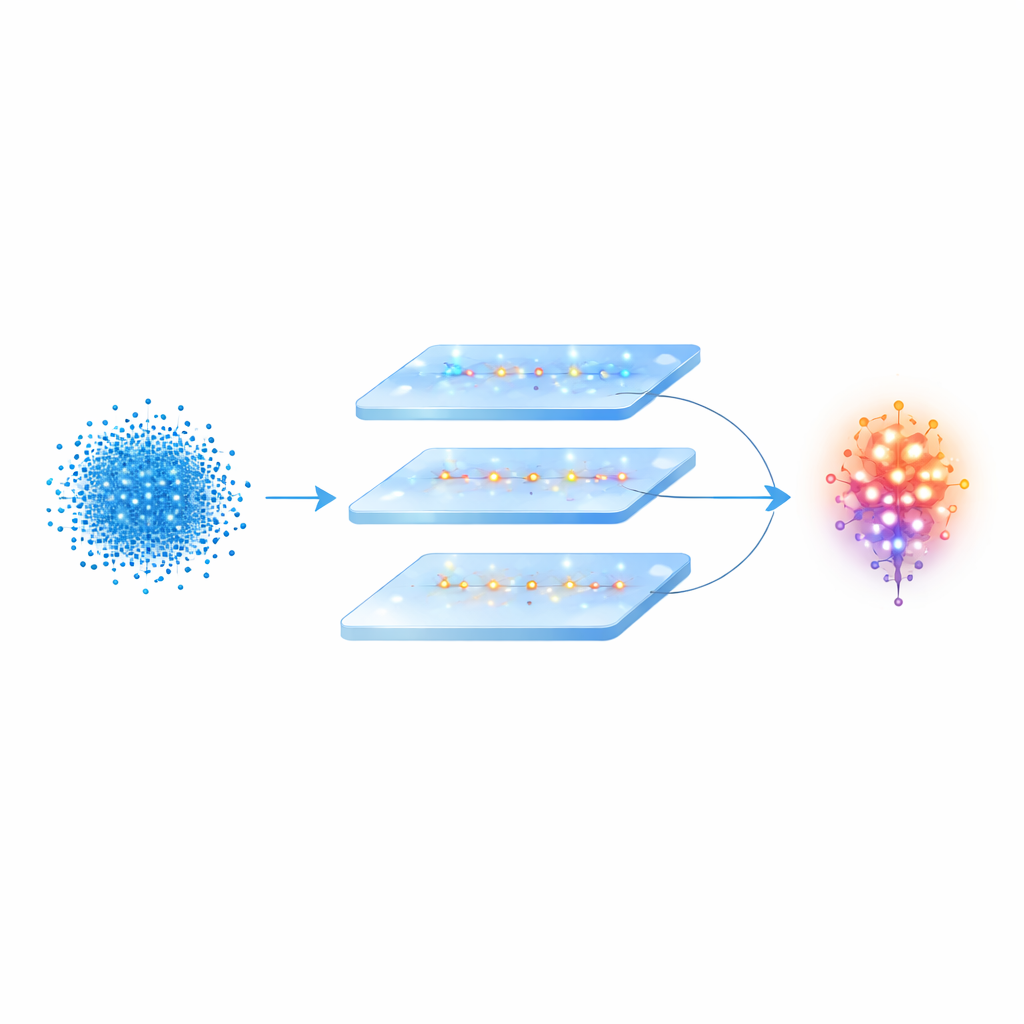
Die meisten künstlichen neuronalen Netze verwenden glatte, kontinuierliche Signale, die sich deutlich von den kurzen elektrischen Spikes unterscheiden, mit denen echte Neuronen miteinander kommunizieren. Im Gegensatz dazu nutzt das hier vorgestellte Modell — das Spiking Point Cloud Neural Network, kurz SPCNNet — künstliche Neuronen, die über die Zeit mit diskreten Spikes kommunizieren. Nachdem die 3D‑Punktwolke jedes biologischen Neurons konstruiert und normalisiert wurde, werden die Koordinaten durch eine Kalibrierungsstufe geführt, die sie räumlich ausrichtet, sodass das System nicht durch Rotation oder die Reihenfolge der Punkte verwirrt wird. Diese ausgerichteten Werte werden dann mithilfe eines vereinfachten Modells elektrischer Aktivität in Spike‑Züge umgewandelt, wodurch räumliche Informationen über die Gestalt des Neurons in Spike‑Muster verwandelt werden, die sich über ein kurzes simuliertes Zeitfenster entfalten.
Das Netzwerk auf Zelltypen trainieren
Sobald die Neuronformen als Spike‑Züge kodiert sind, wendet SPCNNet eine Reihe von Operationen an, um informative Merkmale zu extrahieren. Konvolutionsähnliche Schichten untersuchen alle abgetasteten Punkte und bauen schrittweise höherdimensionale Repräsentationen der Gesamtgestalt des Neurons auf, während ein Pooling‑Schritt diese Informationen zu einer kompakten Zusammenfassung verdichtet. Vollständig verbundene Schichten (fully connected) ordnen diese Zusammenfassung dann einer kleinen Zahl möglicher Neuronentypen zu, und eine abschließende Entscheidungsstufe gibt die wahrscheinlichste Klasse aus. Die Autoren trainierten und testeten ihr Modell an zwei sorgfältig zusammengetragenen Datensätzen aus der öffentlichen NeuroMorpho‑Datenbank: einem mit drei Neurontypen des winzigen Wurms C. elegans und einem weiteren mit vier Neurontypen im Riechkolben des Zebrafischs, sowie an einer größeren und ungleichgewichtigeren Sammlung namens NeuMorph.
Wie gut der neue Ansatz abschneidet
In diesen Datensätzen erwies sich SPCNNet als sowohl genau als auch effizient. Bei den Wurm‑Neuronen erreichte es Testgenauigkeiten von etwa 85 Prozent und lag damit gleichauf oder leicht hinter den besten traditionellen Deep‑Learning‑Methoden, die auf handgefertigten geometrischen Merkmalen beruhen. Bei den anspruchsvolleren Zebrafisch‑Neuronen — größeren Zellen mit Tausenden von Segmenten — übertraf SPCNNet konkurrierende Ansätze deutlich und erreichte ebenfalls rund 85 Prozent Testgenauigkeit, während viele 3D‑bildbasierte oder Punktwolkenmethoden deutlich zurückblieben. Sorgfältige Experimente zeigten, wie die Leistung von entscheidenden Designparametern abhängt, etwa von der Anzahl der aus jedem Neuron abgetasteten Punkte, der Länge der Spike‑Simulation und der Anzahl gleichzeitig verarbeiteter Beispiele. Zusätzliche Ablationstests demonstrierten, dass sowohl das farthest point sampling als auch die spiking Neuronenbausteine wesentlich zum Erfolg des Modells beitrugen.
Was das für die Hirnforschung bedeutet
Indem jedes Neuron als 3D‑Punktwolke behandelt und mit spike‑basierter Rechnung verarbeitet wird, bietet SPCNNet eine Klassifizierungsmethode, die dem entspricht, wie das Gehirn Informationen verarbeitet. Die Methode vermeidet die Notwendigkeit handkonstruierter Messgrößen oder 2D‑Projektionen und lernt stattdessen direkt aus der vollständigen 3D‑Struktur, wobei sie dank ihrer sparsamen Spike‑Aktivität auch einen geringeren Energieverbrauch verspricht. Obwohl die aktuelle Version nur Position und Konnektivität nutzt und andere Details wie Astdicke oder Zelltypkennzeichnungen ausspart, erreicht sie bereits viele etablierte Techniken oder übertrifft sie und skaliert gut auf größere, unausgewogene Datensätze. Mit weiterer Verfeinerung könnte dieser Ansatz ein leistungsfähiges Werkzeug werden, um die vielfältigen Formen von Neuronen automatisch zu katalogisieren und Neurowissenschaftlern zu helfen, reichhaltigere Karten der zellulären Landschaft des Gehirns zu erstellen.
Zitation: Lin, X., Yu, M. & Wang, X. SPCNNet: spiking point cloud neural network for morphological neuron classification. Sci Rep 16, 7989 (2026). https://doi.org/10.1038/s41598-026-38839-3
Schlüsselwörter: Neuronmorphologie, spiking neuronale Netze, 3D-Punktwolken, Zelltyp-Klassifikation, computationale Neurowissenschaft