Clear Sky Science · de
Genomsequenzierung von Bacillus daqingensis und Alkalicoccus luteus liefert taxonomische Einsichten und adaptive Mechanismen
Leben an salzigen Orten
Von Salzseen bis zu alkalischen Böden gedeihen manche Mikroben unter Bedingungen, die die meisten anderen Lebensformen austrocknen und töten würden. Diese Studie taucht in die DNA zweier solcher salzliebenden Bakterien ein, um zu verstehen, wie sie extreme Umgebungen überleben und um zu klären, wo sie wirklich im Stammbaum des Lebens einzuordnen sind. Durch einen detaillierten Vergleich ihrer Genome zeigen die Forschenden, dass Bakterien, die zuvor als unterschiedliche Arten galten, tatsächlich zum gleichen Organismus gehören, und sie enthüllen die molekularen Tricks, mit denen diese Mikroben intensiven Salzstress bewältigen.
Warum diese Salzliebhaber wichtig sind
Im Zentrum dieser Arbeit standen die ursprünglich als Bacillus daqingensis und Alkalicoccus luteus beschriebenen Bakterien. Beide wurden aus salzigen, alkalischen Lebensräumen wie Soda-Seen und salzhaltigen Böden isoliert, in denen die meisten Organismen Probleme haben zu überleben. Wissenschaftler hatten vermutet, dass Bacillus daqingensis tatsächlich zur Gattung Alkalicoccus gehört, aber es fehlte die vollständige Genomsequenz, sodass sein offizieller Status unklar blieb. Durch Sequenzierung und Analyse der kompletten Genome dieser Mikroben und deren Vergleich mit verwandten Arten wollten die Autorinnen und Autoren dieses taxonomische Rätsel lösen und gleichzeitig verstehen, wie Mitglieder der Gattung Alkalicoccus unter so harten Bedingungen überleben können.
Lesen und Vergleichen mikrobieller Genome
Das Team kultivierte die Bakterien im Labor, extrahierte deren DNA und sequenzierte sie mit Hochdurchsatzverfahren. Anschließend setzten sie die Millionen kleiner DNA-Fragmente zu nahezu vollständigen Genomkarten zusammen und überprüften deren Qualität. Sowohl Bacillus daqingensis als auch Alkalicoccus luteus erwiesen sich als ähnlich große Genome von etwa 3,4 bis 3,5 Millionen Basenpaaren, mit nahezu identischem genetischem Inhalt und sehr hoher Vollständigkeit. Ein wichtiger genetischer Marker, das 16S-rRNA-Gen, war in beiden Organismen praktisch gleich: Ein Vergleich ergab 99,8 Prozent Identität zu früheren Laborbefunden, und entscheidend war, dass die 16S-Sequenzen der beiden Stämme untereinander eine perfekte Übereinstimmung von 100 Prozent zeigten.
Entschlüsseln des Überlebens unter Salz und Stress
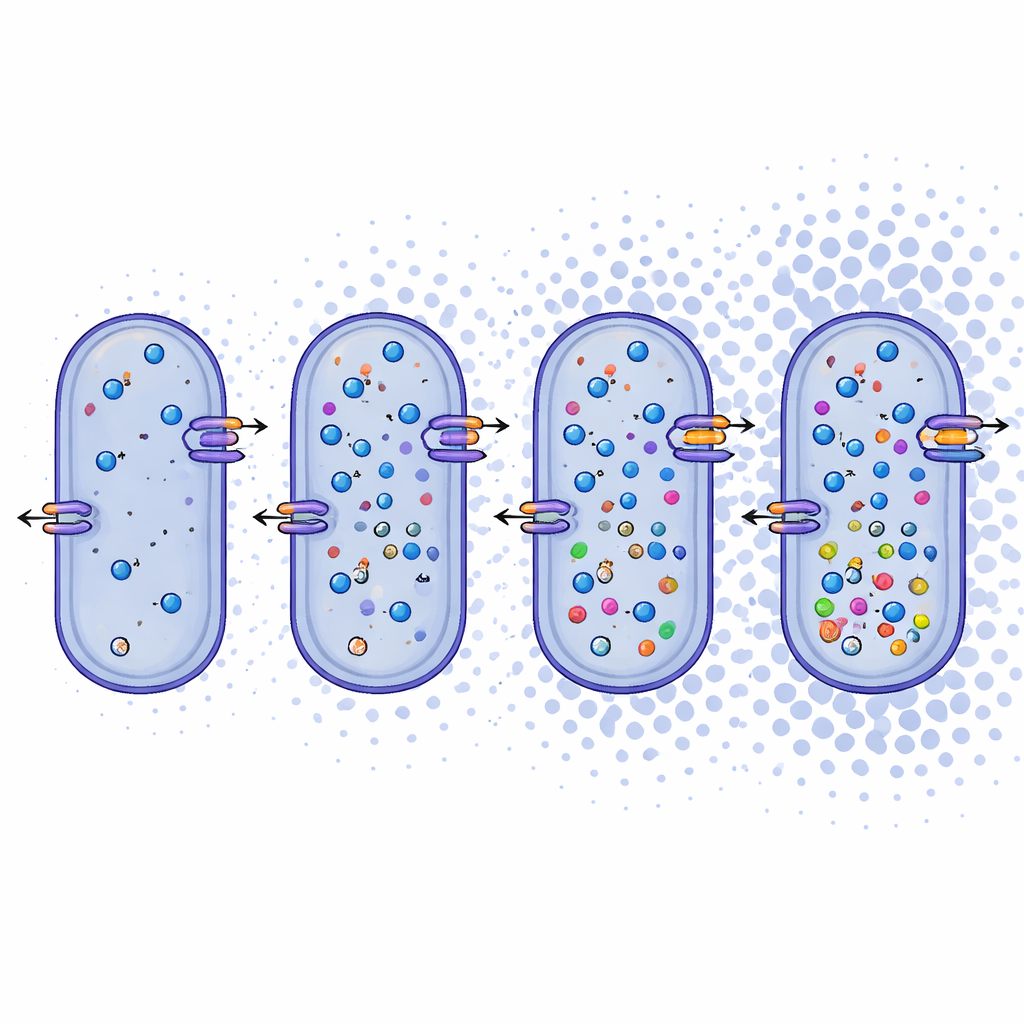
Über die Namen hinaus untersuchten die Forschenden, was die Genome darüber aussagen, wie diese Mikroben ihren Stoffwechsel gestalten. Sie fanden heraus, dass Bacillus daqingensis und alle untersuchten Alkalicoccus-Arten gemeinsame Kernstoffwechselwege teilen, einschließlich gängiger Wege zum Abbau von Zucker und eines modifizierten Zyklus, des Glyoxylat-Shunts, der hilft, unter Stress Kohlenstoff zu sparen. Am auffälligsten war, dass die Genome ein umfangreiches Werkzeugset zur Bewältigung hohen Salzgehalts tragen. Die Bakterien scheinen zwei komplementäre Taktiken zu nutzen: „salt-in“-Systeme, die anorganische Ionen wie Natrium und Kalium über die Zellmembran bewegen, und „salt-out“-Systeme, die kleine organische Moleküle wie Betain, Ectoin und bestimmte Aminosäuren synthetisieren oder aufnehmen — diese wirken als interne Polster gegen Austrocknung. Gene für Ionentransporter, Antiporter und die Biosynthese dieser kompatiblen Solute sind in der gesamten Gattung vorhanden und deuten auf eine robuste, flexible Reaktion auf osmotischen Stress hin.
Belegen, wer wer ist
Um die taxonomische Frage zu klären, verglichen die Autorinnen und Autoren die gesamten Genome mithilfe mehrerer numerischer Kennzahlen, die in der mikrobielle Systematik Standard sind. Die durchschnittliche Nukleotid-Identität (ANI) misst, wie ähnlich die DNA-Sequenzen über das gesamte Genom sind, während die durchschnittliche Aminosäure-Identität (AAI) dasselbe auf Proteinebene bewertet. Zwischen Bacillus daqingensis und Alkalicoccus luteus erreichte die ANI 98,2 Prozent und die AAI 98,5 Prozent — deutlich über den üblichen Schwellenwerten, die zur Definition derselben Art oder sogar Gattung herangezogen werden. Phylogenetische Bäume, die aus vielen Genen erstellt wurden, sowie Vergleiche geteilter Proteinkomplexe zeigten, dass sich diese beiden Stämme fest zusammenschließen und mehr Gencluster miteinander teilen als mit jeder anderen Alkalicoccus-Art. Traditionelle Merkmale wie Zellform, Fettsäureprofile und wichtige biochemische Reaktionen waren zwischen ihnen ebenfalls im Wesentlichen identisch.
Was das für mikrobielle Namen bedeutet
Alle Beweislinien zusammengenommen kommt die Studie zu dem Schluss, dass Bacillus daqingensis keine eigenständige Bakterienart darstellt. Stattdessen gehört sie zur Gattung Alkalicoccus und ist dieselbe Art wie Alkalicoccus luteus, früher bekannt als Bacillus luteus. Die Autorinnen und Autoren schlagen formal die neue Kombination Alkalicoccus daqingensis vor und behandeln diesen Namen zusammen mit dem älteren Bacillus-Namen als spätere Synonyme von Bacillus luteus/Alkalicoccus luteus. Für Nicht-Fachleute ist die zentrale Erkenntnis, dass sorgfältige Genomsequenzierung aufdecken kann, wenn unterschiedliche Bezeichnungen im Grunde dasselbe Mikrobenwesen meinen und so zur Bereinigung des Nomenklatursystems beiträgt. Gleichzeitig zeigt die Arbeit, wie diese salzliebenden Bakterien auf eine Kombination aus Ionenpumpen und schützenden Molekülen setzen, um in Umgebungen zu überleben, die sonst zu salzig für Leben wären.
Zitation: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Schlüsselwörter: halophile Bakterien, Genomsequenzierung, mikrobielle Taxonomie, Anpassung an Salzstress, Alkalicoccus luteus