Clear Sky Science · de
Integrierte Analyse von Transkriptom und Einzelzell-Sequenzierung kombiniert mit experimenteller Validierung identifiziert Biomarker, die mit T‑Zellen und Seneszenz bei Sepsis assoziiert sind
Warum diese Forschung für Patientinnen und Patienten mit schweren Infektionen wichtig ist
Sepsis ist eine lebensbedrohliche Reaktion auf eine Infektion, die aus einer routinemäßigen Erkrankung oder Verletzung innerhalb weniger Stunden einen Notfall machen kann. Ärztinnen und Ärzte fehlt weiterhin ein einfaches, verlässliches Mittel, um früh zu erkennen, welche Patientinnen und Patienten auf dem Weg zu einem Organversagen sind, und es gibt keine Medikamente, die speziell darauf ausgelegt sind, das immunologische Chaos der Sepsis zu korrigieren. Diese Studie untersucht, wie bestimmte Immunzellen, sogenannte T‑Zellen, und das Altern dieser Zellen die Sepsis antreiben könnten – und identifiziert eine kleine Gruppe von Genen, die Ärztinnen und Ärzten helfen könnten, die Erkrankung früher zu diagnostizieren und neue Behandlungsansätze aufzuzeigen.
Sepsis: wenn die Abwehrkräfte außer Kontrolle geraten
Bei Sepsis explodiert das Immunsystem zunächst in einer intensiven Entzündungsreaktion und fährt dann häufig in einen gefährlichen Stillstand herunter. T‑Zellen, die normalerweise bei der Beseitigung von Infektionen helfen und sich an frühere Erreger erinnern, werden seltener und weniger funktionsfähig. Gleichzeitig zeigen viele Immunzellen Anzeichen von „Seneszenz“ – einer Form zellulären Alterns, bei der Zellen nicht mehr teilen, aber weiterhin entzündungsfördernde Signale abgeben. Die Autorinnen und Autoren gingen davon aus, dass sie durch das Identifizieren von Genen, die sowohl mit T‑Zellen als auch mit Seneszenz verknüpft sind, neue Biomarker entdecken könnten, die offenbaren, wer sich einer Sepsis entwickelt und warum manche Patientinnen und Patienten schneller verschlechtern als andere.
Blutuntersuchung auf Einzelzellebene
Das Team kombinierte mehrere Datenebenen aus Blutproben von Personen mit und ohne Sepsis. Zunächst nutzten sie Bulk‑Transkriptomdaten (eine Bestandsaufnahme, welche Gene aktiv sind), um fast 10.000 Gene zu finden, deren Aktivität sich bei Sepsis veränderte. Anschließend untersuchten sie mittels Einzelzell‑RNA‑Sequenzierung Zehntausende einzelner Blutzellen, um mehr als 1.300 Gene zu identifizieren, die speziell in T‑Zellen verändert waren. Durch das Überschneiden dieser Mengen mit einer kuratierten Liste von 866 Genen, die bekanntlich an zellulärem Altern beteiligt sind, gelangten sie auf 45 Kandidaten, die an der Schnittstelle von Sepsis, T‑Zellen und Seneszenz stehen. 
Finden von vier wichtigen genetischen Wegweisern
Um diese Liste weiter einzuschränken, wandten die Forschenden zwei maschinelle Lernverfahren an, die nach den aussagekräftigsten Merkmalen in komplexen Daten suchen. Diese Ansätze führten zu sechs vielversprechenden Genen; beim Überprüfen in zwei unabhängigen Patientendatensätzen hoben sich vier davon konsistent hervor: PATZ1, SIN3B, BLK und MTHFD2. In öffentlichen Datensätzen waren PATZ1, SIN3B und BLK bei Sepsis reduziert, während MTHFD2 erhöht war. In einer kleinen Gruppe klinischer Proben, die mittels der sensitiven Methode RT‑qPCR getestet wurden, zeigten die ersten drei Gene erneut deutlich niedrigere Werte im Blut von Sepsis‑Patientinnen und -Patienten, während MTHFD2 keinen klaren Unterschied aufwies – was andeutet, dass seine Rolle eher mit der Proteinfunktion als mit dessen Menge zusammenhängen könnte.
Wie diese Gene in das Gleichgewicht des Immunsystems und mögliche Medikamente eingebunden sind
Weitere Analysen verbanden jedes Gen mit übergeordneten biologischen Signalwegen. PATZ1 stand in Verbindung mit DNA‑Replikation und T‑Zell‑Rezeptor‑Signalgebung, Prozessen, die für die Vermehrung und Reaktionsfähigkeit von T‑Zellen essenziell sind. SIN3B wurde mit einem fettbasierten Signalsystem assoziiert, das Zellüberleben und Entzündung beeinflusst. BLK, das besser aus Autoimmunerkrankungen bekannt ist, war mit der Blutbildung und der Immunabwehr im Darm verknüpft, einschließlich der Produktion von IgA‑Antikörpern, die die Darmbarriere schützen. MTHFD2 hing mit der Proteinsynthese‑ und Abbau‑Maschinerie zusammen, zentral dafür, wie Immunzellen ihren Stoffwechsel unter Stress anpassen. Beim Untersuchungen der Muster von Immunzell‑„Infiltration“ im Blut ging ein höherer PATZ1‑Spiegel mit mehr CD8‑T‑Zellen und weniger Neutrophilen einher – ein Gleichgewicht, das eine bessere Infektionskontrolle begünstigen könnte. Mit diesen vier Genen bauten die Forschenden ein künstliches neuronales Netzwerk – ein einfaches KI‑Modell –, das Sepsis in zwei externen Datensätzen mit nahezu perfekter Genauigkeit von Nicht‑Sepsis unterscheidet. Außerdem nutzten sie eine Wirkstoff‑Gen‑Datenbank und molekulare Docking‑Simulationen, um mehrere vorhandene Verbindungen vorzuschlagen, darunter das Antibiotikum Latamoxef sowie die Moleküle Emetin und Dihydroergotamin, als Kandidaten, die stark an diese Ziele binden könnten. 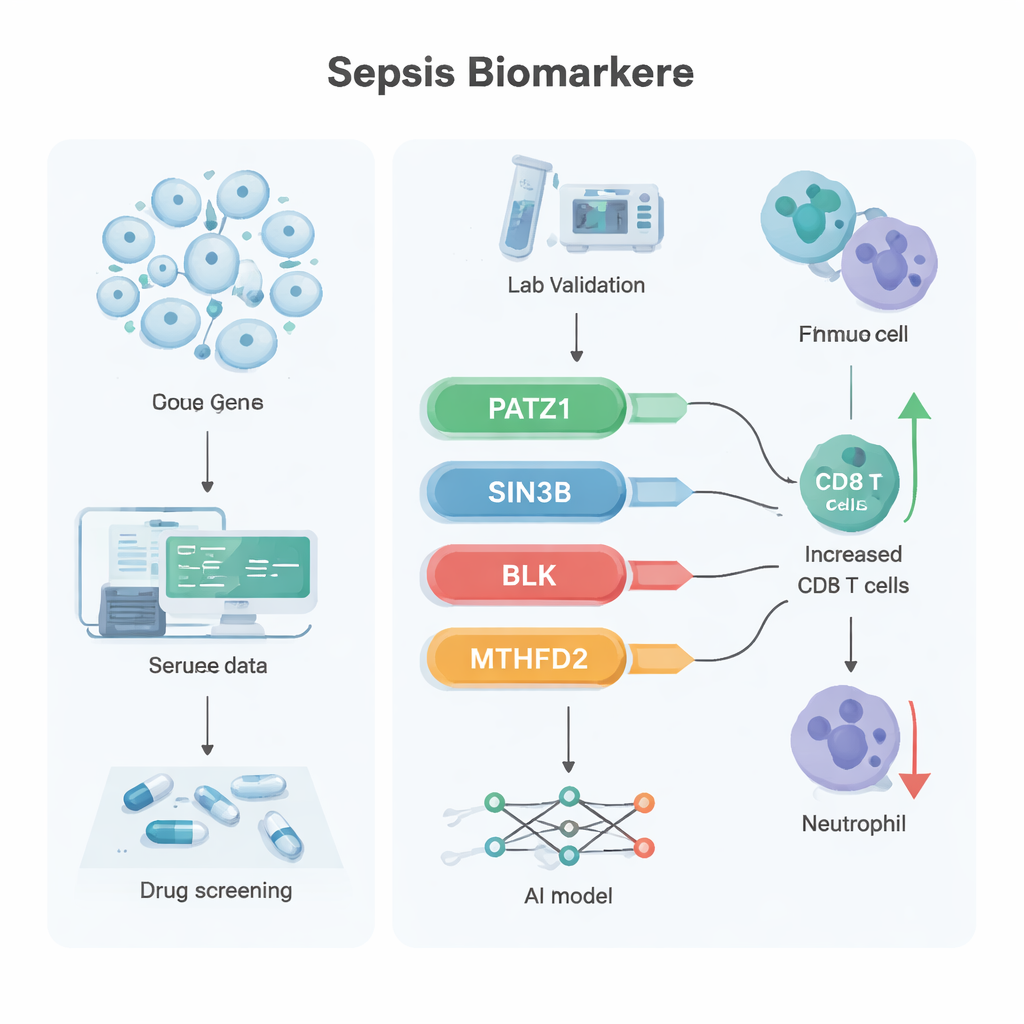
Was das für die künftige Versorgung bedeuten könnte
Für Laien ist die zentrale Erkenntnis, dass diese Studie vier Gene identifiziert, die als Warnleuchten auf T‑Zellen fungieren, die während einer Sepsis fehlregulieren und vorzeitig altern. Zusammen bilden diese Gene ein potenzielles Bluttest‑Panel, das Ärzten eines Tages helfen könnte, Sepsis früher und genauer zu diagnostizieren als mit den derzeitigen Mitteln. Sie liefern auch Hinweise darauf, wie der Energiehaushalt und die Reparatursysteme des Immunsystems versagen, und schlagen neue Ansätze für Medikamente vor, die darauf abzielen, die gesunde Funktion von T‑Zellen wiederherzustellen, statt lediglich die Entzündung zu dämpfen. Obwohl größere Studien und Laborversuche notwendig sind, bevor diese Ergebnisse in die Klinik gelangen, weist diese Arbeit einen vielversprechenden Weg hin zu einer präziseren, biologisch fundierten Diagnose und Behandlung der Sepsis.
Zitation: Yang, K., Hu, Y., Ma, C. et al. Integrative analysis of transcriptome and single-cell sequencing combined with experimental validation identifies biomarkers associated with T cell and senescence in sepsis. Sci Rep 16, 7109 (2026). https://doi.org/10.1038/s41598-026-38559-8
Schlüsselwörter: Sepsis-Biomarker, T‑Zellen, Immun‑Seneszenz, Einzelzell-Sequenzierung, Immunometabolismus