Clear Sky Science · de
Automatisierte und robuste nicht-rigide Registrierung serieller mikroskopischer Schnitte mit PiCNoR
Gewebe in 3D sehen, ohne Details zu verlieren
Die moderne Biologie baut häufig dünne Gewebeschnitte zu vollständigen 3D-Bildern von Organen und Gehirnen zusammen. Beim Schneiden, Färben und Abbilden jedes mikroskopischen Schnitts können diese aber dehnen, reißen oder verrutschen. Werden die Schnitte nicht korrekt ausgerichtet, kann das resultierende 3D-Bild irreführend sein. Diese Arbeit stellt eine neue Rechenmethode namens PiCNoR vor, die Forschenden dabei hilft, solche Bilder genauer und automatisch auszurichten, sodass feine Strukturen in Embryonen und Gehirnen in 3D-Rekonstruktionen erhalten bleiben.
Warum das Ausrichten von Schnitten so schwierig ist
Für eine 3D-Darstellung nehmen Forschende lange Reihen von ultradünnen Schnitten desselben Gewebestücks auf. Theoretisch sollte jeder Schnitt perfekt auf dem vorherigen liegen, wie Karten in einem ordentlich gestapelten Kartenstapel. In der Praxis kann sich jedoch jeder Schnitt beim Schneiden und Färben auf leicht unterschiedliche Weise verziehen. Farben können variieren, Teile können sich dehnen und Strukturen können verschieben. Traditionelle „rigide“ Ausrichtungsverfahren nehmen an, dass sich ein ganzer Schnitt nur verschiebt oder dreht, was oft nicht ausreicht. Flexiblere, „elastische“ Methoden existieren zwar, sind aber manchmal langsam, erfordern sorgfältige Abstimmung durch Expertinnen und Experten oder sind stark abhängig von der Bildhelligkeit, die von Schnitt zu Schnitt schwanken kann.
Ein neuer Ansatz: lokale Teile, die zusammenarbeiten
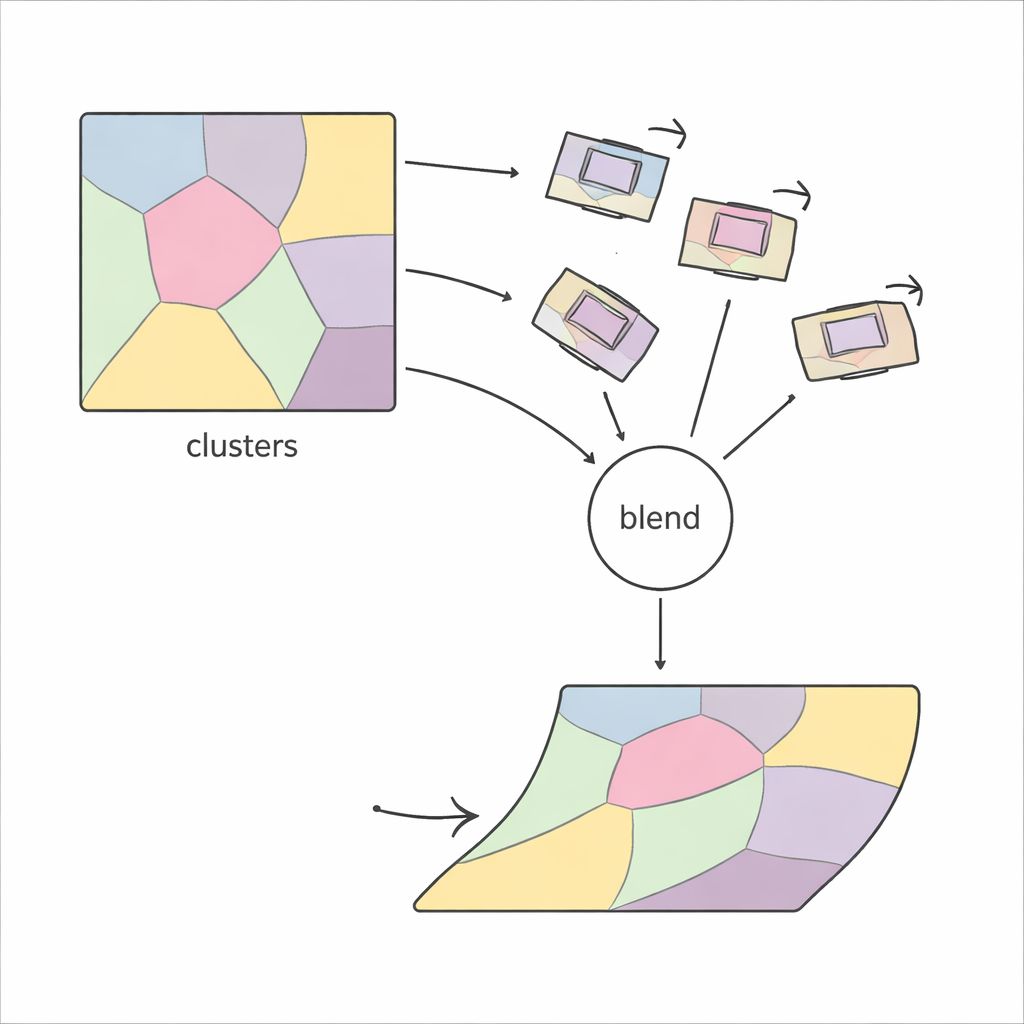
PiCNoR nimmt das Problem aus einer anderen, lokaler abgestimmten Perspektive. Statt zu versuchen, ein ganzes Bild auf einmal zu verformen, teilt die Methode zuerst jeden Schnitt in viele Regionen ein, basierend auf dem Muster der Bildmerkmale. Innerhalb jeder Region findet das Verfahren passende Punkte zwischen zwei benachbarten Schnitten mit robusten Merkmalserkennern und schätzt, wie sich diese Region drehen und verschieben muss, um übereinzustimmen. Diese lokalen Bewegungen werden dann auf Plausibilität geprüft und behutsam kombiniert, sodass jeder Pixel im Schnitt eine Bewegung erhält, die Informationen aus den umliegenden Regionen glatt überblendet. Das Ergebnis ist eine flexible, „nicht-rigide“ Ausrichtung, die dennoch kontrolliert und realitätsnah bleibt.
Die Daten die richtige Komplexität wählen lassen
Eine zentrale Herausforderung bei regionenbasierten Methoden ist die Entscheidung, wie viele Regionen verwendet werden sollen: Sind es zu wenige, können feine Verformungen nicht korrigiert werden; sind es zu viele, wird die Methode instabil und langsam. Frühere Ansätze beruhten oft auf Trial-and-Error und wiederholter visueller Prüfung der Ergebnisse. PiCNoR vermeidet diese manuelle Feinabstimmung durch den Einsatz eines statistischen Werkzeugs, des Bayesschen Informationskriteriums, das automatisch die Detailtiefe gegen das Risiko des Überanpassens abwägt. In der Praxis bedeutet das, dass der Algorithmus selbst entscheiden kann, wie viele Regionen für einen gegebenen Datensatz nötig sind, ganz ohne menschliche Aufsicht — was Zeit spart und Verzerrungen reduziert.
Ergebnisse zuverlässig und effizient halten
Nicht jede geschätzte lokale Bewegung ist vertrauenswürdig — manche können durch Rauschen oder schlechte Übereinstimmungen verfälscht sein. PiCNoR begegnet diesem Problem, indem jede Region als Knoten in einem Graphen dargestellt wird, in dem benachbarte Regionen einander beeinflussen. Bewegungen, die in Bezug auf Rotation oder Verschiebung unrealistisch erscheinen, werden durch einen gewichteten Durchschnitt der zuverlässigeren Bewegungen der Nachbarn ersetzt. Eine kompakte mathematische Repräsentation hilft, diese Bewegungen effizient zu kombinieren. Schließlich wird die Bewegung jedes Pixels als wahrscheinlichkeitsgewichtete Mischung der regionalen Bewegungen berechnet, sodass Übergänge zwischen Regionen glatt bleiben, ohne plötzliche Knicke oder Falten im Gewebe.
Bewiesen an realen biologischen Daten
Die Forschenden testeten PiCNoR an drei sehr unterschiedlichen Datensätzen: menschliche Embryonalschnitte aus der Kyoto-Sammlung, ein Elektronenmikroskopie-Stack eines Fruchtfliegen-Nervenstrangs und einen neuen Lichtmikroskop-Stack aus dem Hippocampus eines Rattengehirns. In all diesen Beispielen lieferte PiCNoR durchgängig bessere Überlappungen zwischen Schnitten als Standard-rigide und weit verbreitete nicht-rigide Methoden. Es bewahrte die Kontinuität empfindlicher Strukturen in 3D-Ansichten und vermied die übertriebenen Verformungen, die bei anderen Werkzeugen mitunter auftreten. Wichtig ist, dass dies gelang, während weniger lokale Regionen verwendet wurden als bei manchen Wettbewerbern und die Rechenkosten praktisch für große Stapel blieben.
Was das für die zukünftige 3D-Mikroskopie bedeutet
Für Nicht-Spezialisten lautet die Quintessenz: PiCNoR bietet einen verlässlicheren Weg, Stapel zweidimensionaler Mikroskopbilder in getreue 3D-Rekonstruktionen zu überführen. Indem die Methode automatisch bestimmt, wie detailliert die Ausrichtung sein soll, und sich gegen fehlerhafte lokale Korrekturen absichert, bewahrt sie die tatsächlichen Formen des Gewebes und hält gleichzeitig die Verarbeitungszeit überschaubar. Das macht es für Biologinnen, Biologen und Pathologinnen und Pathologen leichter, dem zu vertrauen, was sie in 3D sehen — sei es bei der Untersuchung der Embryonalentwicklung oder der Anordnung von Gehirnzellen — und legt die Grundlage für genauere, automatisierte Analysen komplexer mikroskopischer Datensätze.
Zitation: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Schlüsselwörter: 3D-Mikroskopie, Bildregistrierung, Gehirnbildgebung, Histologie, nicht-rigide Ausrichtung