Clear Sky Science · de
Robuste Imputationsmethode zur Vorhersage von Augen-, Haar- und Hautfarbe aus niedrigabdeckender alter DNA
Die Gesichter hinter antiker DNA sichtbar machen
Wenn Archäologen alte Knochen ausgraben, wissen sie selten, wie die Menschen zu Lebzeiten aussahen — welche Augenfarbe sie hatten, wie dunkel ihre Haut war oder ob ihr Haar schwarz, blond oder rot war. Diese Studie stellt eine neue Methode vor, um diese sichtbaren Merkmale aus extrem beschädigter DNA abzulesen. Damit können Wissenschaftler ein menschlicheres Bild einzelner Personen aus der fernen Vergangenheit zeichnen und dieselben Ideen heute auf degradierte forensische Proben anwenden.
Warum alte DNA so schwer zu lesen ist
DNA aus lange begrabenen Überresten ist ein biologisches Wrack. Die Zeit zerlegt sie in winzige Fragmente und fügt chemische Schäden hinzu, die einen genetischen Buchstaben in einen anderen verwandeln. Die meisten antiken Genome werden nur mit „niedriger Abdeckung“ sequenziert, das heißt, viele Positionen werden nur einmal oder gar nicht gelesen. Bestehende forensische Werkzeuge wie HIrisPlex-S, das Augen-, Haar- und Hautfarbe aus 41 wichtigen DNA-Markern vorhersagen kann, wurden für moderne, hochwertige DNA entwickelt und erwarten verlässliche Informationen über beide Kopien jedes Markers. Bei antigem Material fehlen diese Informationen oft oder sind unsicher, sodass traditionelle Methoden entweder ganz versagen oder sehr wackelige Vorhersagen liefern.
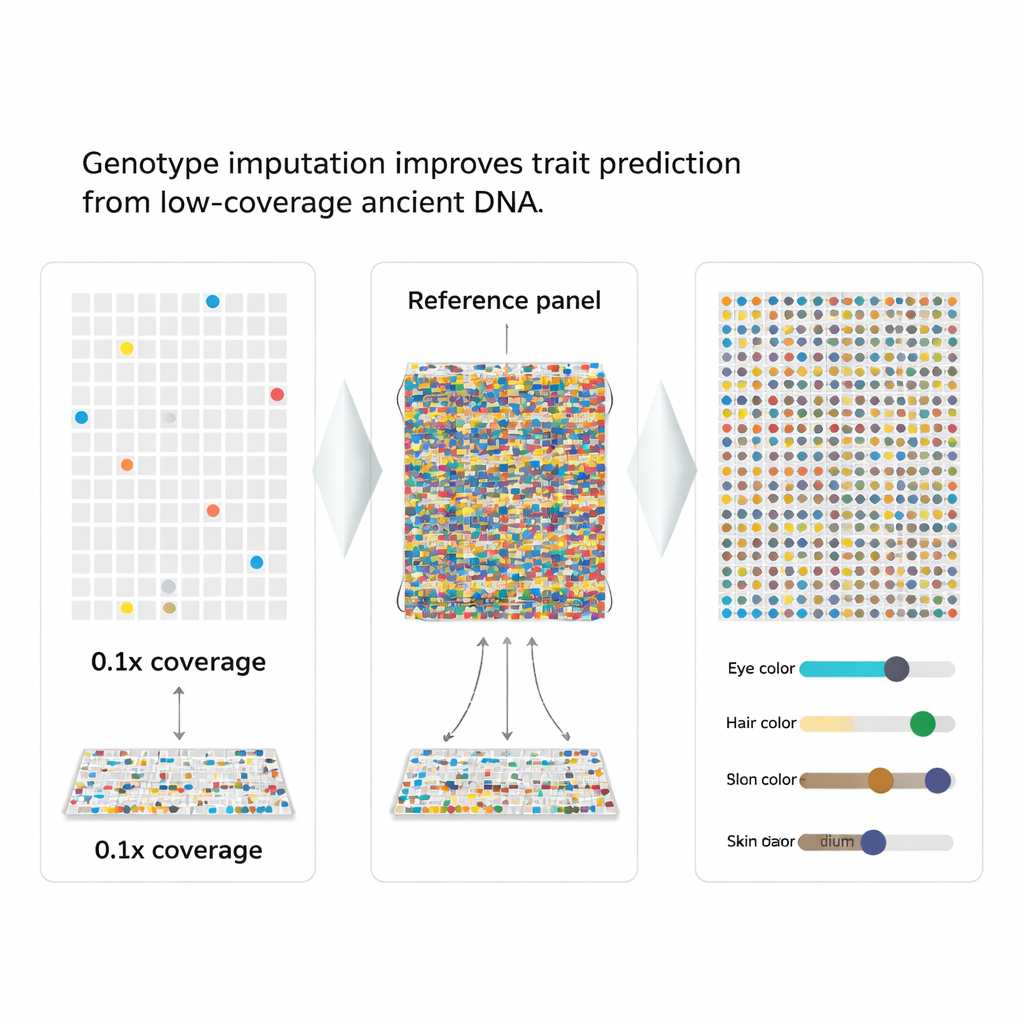
Die Lücken mit kluger Schätzung füllen
Die Autoren griffen zu einer Strategie namens Genotyp-Imputation, die Muster in einem großen Referenzpanel moderner Genome nutzt, um fehlende Teile in einem beschädigten Genom „aufzufüllen“. Da benachbarte genetische Marker in Stücken gemeinsam vererbt werden, kann ein teilweise beobachtetes Muster stark auf die wahrscheinlichsten fehlenden Buchstaben hinweisen. Das Team bündelte diese Idee in einen neuen Arbeitsablauf, aHISplex, der bei ausgerichteten DNA-Reads beginnt, moderne Imputationssoftware laufen lässt, die Ergebnisse in das von HIrisPlex-S exakt geforderte Format konvertiert und dann automatisch die vorhergesagten Wahrscheinlichkeiten in klare Merkmalskategorien für Augen-, Haar- und Hautfarbe übersetzt.
Genauigkeit testen an modernen und antiken Personen
Um die Leistungsfähigkeit der Methode zu prüfen, nahmen die Forscher 93 moderne Genome mit bekannten Merkmalen und „downgesampelt“ sie künstlich, um sehr niedrige Abdeckung zu simulieren, bis hinunter zu einem Zehntel eines vollständigen Durchlaufs. Anschließend imputierten sie die fehlenden Marker und verglichen die Ergebnisse mit den echten Daten. Selbst bei nur 0,5× Abdeckung blieb die Gesamtfehlerrate für die 41 Marker unter etwa 2 %, und die schwerwiegendsten Fehler — das komplette Vertauschen eines Markers von einem homozygoten Zustand in den gegenteiligen — waren extrem selten. Die meisten Vorhersagen zu Augen- und Haarfarbe stimmten mit den bekannten Merkmalen überein, und Hautfarbenvorhersagen verschoben sich nur leicht zwischen benachbarten Schattierungen.
Herausforderungen bei seltenen Merkmalen und alter Diversität
Nicht alle Merkmale lassen sich gleichermaßen gut rekonstruieren. Rotes Haar, das weitgehend durch seltene Varianten im MC1R-Gen bestimmt wird, erwies sich als schwieriger: Die Methode erfand praktisch nie rotes Haar, wo keines vorhanden war, verpasste aber manchmal tatsächlich rote Individuen und klassifizierte sie stattdessen als blond oder dunkelblond. Das Team wendete seinen Workflow außerdem auf 31 echt antike Individuen mit hochwertigen Genomen an und tat so, als wären diese Genome nur niedrig abgedeckt, um sie dann wieder zu imputieren. Auch hier war die Gesamtgenauigkeit hoch: Bei 0,5× Abdeckung wurden etwa 95 % der Schlüsselmarker korrekt imputiert. Allerdings zeigte eine kleine Menge von Marker–Probe-Kombinationen, insbesondere bei Individuen deren genetische Hintergründe in modernen Referenzpanels schlecht repräsentiert sind, systematisch höhere Fehlerquoten. Dieser „Referenzbias“ könnte zum Beispiel in einem Bruchteil der Durchläufe ein blauäugiges Genotyp in eine braunäugige Vorhersage verwandeln.
Antike Menschen schärfer in den Fokus rücken
Trotz dieser Einschränkungen zeigt die Studie, dass es jetzt praktikabel ist, Augen-, Haar- und Hautfarbe für viele antike Individuen vorherzusagen, selbst wenn ihre DNA extrem spärlich ist, bei nur 0,1–0,5× Abdeckung. Die neue aHISplex-Pipeline automatisiert die komplexen Schritte zwischen Roh-Sequenzierdateien und benutzerfreundlichen Merkmalangaben und macht sie damit für Archäogenetik-Labore und potenziell für forensische Teams, die mit degradierten Proben arbeiten, zugänglich. Mit wachsenden Referenzpanels, die vielfältigere und ältere Genome einschließen, und mit der Entdeckung zusätzlicher merkmalsassoziierter Marker sollte dieser Ansatz noch präziser werden — und uns helfen, von anonymen Knochen und DNA-Sequenzen zu lebendigen, ethisch bedachten Porträts von Menschen zu gelangen, die vor langer Zeit gelebt haben.
Zitation: Maróti, Z., Nyerki, E., Török, T. et al. Robust imputation-based method for eye, hair, and skin colour prediction from low-coverage ancient DNA. Sci Rep 16, 7371 (2026). https://doi.org/10.1038/s41598-026-38372-3
Schlüsselwörter: antike DNA, forensische Phänotypisierung, Augen Haar Hautfarbe, Genotyp-Imputation, Archäogenetik