Clear Sky Science · de
Darmmikrobiota und Resistom‑Profile von Schweizer Expatriates in Afrika aufgedeckt durch Nanopore‑Metagenomik
Warum sich Ihre Darmmikroben verändern, wenn Sie im Ausland leben
Viele Menschen verbringen Monate oder Jahre im Ausland, oft an Orten, an denen antibiotikaresistente Bakterien verbreitet sind. Diese Studie stellt eine einfache, aber wichtige Frage: Verändert sich die Gemeinschaft von Mikroben und Resistenzgenen im Darm Schweizer Expatriates, die in afrikanischen Ländern mit hoher Belastung durch medikamentenresistente Infektionen leben, auf eine Weise, die ihre Gesundheit und die weitere Verbreitung antimikrobieller Resistenzen beeinflussen könnte?
Die unsichtbare Gemeinschaft in uns
Unser Darm beherbergt Billionen von Mikroben, überwiegend Bakterien, die bei der Verdauung helfen, das Immunsystem trainieren und schädliche Keime in Schach halten. Neben diesen nützlichen Mikroben existiert das „Resistom“ – die Gesamtheit der Gene, die Bakterien resistent gegen Antibiotika machen. Selbst gesunde Menschen tragen viele dieser Gene. Wenn Personen in Regionen ziehen oder dort reisen, in denen multiresistente Bakterien häufig sind, können sie still neue Resistenzgene und die mobilen DNA‑Elemente, sogenannte Plasmide, die diese verbreiten, aufnehmen. Zu verstehen, wie das geschieht, ist entscheidend, um die globale Antibiotikaresistenz zu kontrollieren.
Vergleich von Expatriates in Europa und Afrika
Die Forschenden analysierten Stuhlproben von 72 gesunden Schweizer Expatriates bei ihrer Rückkehr in die Schweiz: 39 hatten in afrikanischen Ländern gelebt und 33 in anderen europäischen Ländern. Anstatt Bakterien im Labor anzuzüchten, nutzten sie eine Langlese‑DNA‑Sequenzierungstechnologie namens Nanopore‑Shotgun‑Metagenomik, die das komplette genetische Material einer Probe auf einmal liest. Dadurch konnten sie kartieren, welche Bakterien vorhanden waren (die Mikrobiota) und welche Antibiotikaresistenzgene und Plasmide sie trugen (das Resistom und Plasmidom). Jede Probe wurde zweimal sequenziert, um die Zuverlässigkeit zu erhöhen, und ausgefeilte Software identifizierte bakterielle Gruppen und Resistenzgene und setzte aus der gemischten DNA längere Genomfragmente zusammen.
Überraschende Stabilität der Darmmikroben
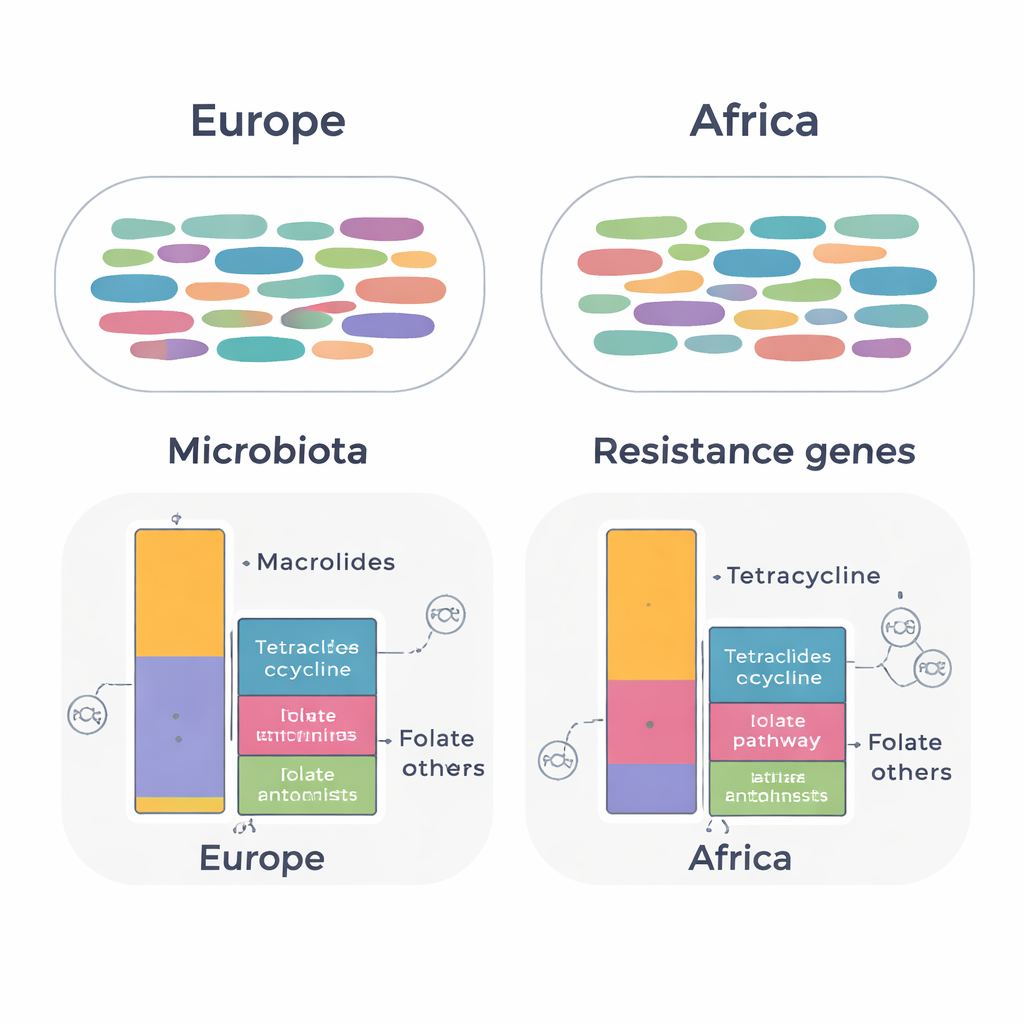
Trotz der Tatsache, dass in früheren kulturabhängigen Tests mehr Personen aus der Afrika‑Gruppe mit multiresistenten Darmbakterien kolonisiert waren, ähnelte die Gesamtzusammensetzung ihrer Darmmikrobiota auffallend derjenigen von Expatriates, die in Europa gelebt hatten. Diversitätsmaße – wie viele verschiedene Bakterienarten vorhanden sind und wie gleichmäßig sie verteilt sind – unterschieden sich nicht nach Kontinent, und statistische Analysen zeigten kein klares Clustering der Proben aus Afrika gegenüber Europa. In beiden Gruppen dominierten vertraute Darmbewohner wie Blautia, Faecalibacterium und Bacteroides, was darauf hindeutet, dass ein längerer Aufenthalt im Ausland bei gesunden Erwachsenen nicht zwangsläufig die Kernbakteriengemeinschaft grundlegend verändert.
Resistenzgene und mobile DNA erzählen eine andere Geschichte
Wenn das Team seinen Fokus auf Resistenzgene richtete, traten subtilere, aber wichtige Unterschiede zutage. In allen Proben fanden sie 134 verschiedene Resistenzgene aus 14 Antibiotikaklassen. Das Gesamtmuster der Gene war zwischen den Kontinenten weitgehend ähnlich, doch Expatriates, die in Afrika gelebt hatten, trugen höhere Mengen an Genen, die Bakterien gegen Tetrazykline und gegen das Folsäurestoffwechselzielsystem (wie Trimethoprim‑Sulfamethoxazol) schützen. Im Gegensatz dazu zeigten Expatriates aus europäischen Ländern höhere Mengen an Genen, die Resistenz gegen Makrolidantibiotika vermitteln. Viele dieser Gene waren mit verbreiteten Darmbakterien verknüpft, darunter Ruminococcoides, Bifidobacterium und Bacteroides. Klinisch relevante Gene, wie blaCTX‑M‑15, das fortgeschrittene Cephalosporin‑Antibiotika inaktivieren kann, wurden in Escherichia coli aus beiden Gruppen nachgewiesen.
Plasmide als globale Shuttle für Resistenz
Die Studie verfolgte auch Plasmide – kleine, oft übertragbare DNA‑Kreise, die Resistenzgene zwischen Bakterien und Umweltbereichen transportieren. Mithilfe der langen DNA‑Reads konnten die Forschenden manchmal Resistenzgene und Plasmid‑„Replikon“‑Marker auf demselben zusammengebauten DNA‑Fragment sehen und damit bestätigen, dass sie gemeinsam unterwegs sind. Sie identifizierten 46 verschiedene Plasmidtypen, von denen einige auf je einen Kontinent beschränkt und andere geteilt waren. Bemerkenswert ist, dass bestimmte Plasmide mehrere Resistenzgene trugen und Plasmiden ähnelten, die aus menschlichen, tierischen, Lebensmittel‑ und Abwasserquellen in verschiedenen Teilen der Welt bekannt sind. Ein Plasmidtyp, der häufig mit Enterococcus‑Bakterien in Verbindung gebracht wird und in Hühnern und Abwasser gefunden wurde, war in Stuhlproben von Expatriates in Afrika häufiger anzutreffen, was unterstreicht, wie Nahrung, Tiere und Umwelt dazu beitragen können, was letztlich in unseren Darm gelangt.
Was das für den Alltag und die öffentliche Gesundheit bedeutet
Für eine interessierte Leserschaft ist die Kernbotschaft, dass das bloße Leben in einer Hochrisikoregion offenbar nicht grundlegend bestimmt, welche Darmbakterien Sie beherbergen, wohl aber das Verhältnis von Antibiotikaresistenzgenen und mobilen DNA‑Elementen verändern kann. Diese verborgenen Veränderungen, mitgeprägt durch lokale Antibiotikagebrauchsmuster, können für zukünftige Infektionen und dafür relevant sein, wie Resistenzeigenschaften zwischen Menschen, Tieren und der Umwelt zirkulieren. Die Arbeit zeigt außerdem, dass tragbare Langlese‑Sequenzierung als Frühwarninstrument dienen kann, indem sie offenlegt, wie Resistenzgene und Plasmide in gesunden Reisenden und Expatriates zirkulieren, bevor sie Erkrankungen verursachen.
Zitation: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Schlüsselwörter: Darmmikrobiom, Antibiotikaresistenz, Expatriates, Plasmide, Metagenomik