Clear Sky Science · de
Das erste mitochondriale Genom für Sterictiphorinae (Hymenoptera: Argidae) und Einblicke in die Phylogenie der Argidae
Warum winzige Blattfresser wichtig sind
Sägespinner der Familie Argidae wirken unscheinbar, doch ihre raupenähnlichen Jungstadien können Blätter von Kulturpflanzen und Bäumen kahlfressen und sind damit bedeutende landwirtschaftliche Schädlinge. Auf der Ebene ihrer DNA, insbesondere in den energieerzeugenden Mitochondrien in ihren Zellen, sind diese Insekten jedoch bisher wenig untersucht. Dieser Artikel berichtet das erste vollständige mitochondriale Genom einer koreanischen Sägespinne, Sterictiphora koreana, und nutzt es, um zu erforschen, wie sich diese schädlingsanfällige Familie über mehr als 160 Millionen Jahre entwickelt hat.
Ein Blick in die Kraftwerke einer Sägespinne
Die Autoren entzifferten die gesamte mitochondriale DNA eines einzelnen Weibchens von S. koreana. Wie bei den meisten Tieren ist dieses winzige „Kraftwerks“-Genom ein Ring aus DNA mit 37 Genen, die der Zelle bei der Energiegewinnung helfen. Bei S. koreana ist der Ring ungewöhnlich lang – etwa 17.900 Basen im Vergleich zu rund 15.600 bei drei verwandten Argidae‑Arten – vor allem, weil ein nicht‑kodierender, A‑ und T‑reicher Abschnitt stark vergrößert ist. Trotz dieser Größenabweichung entspricht die Gesamtanordnung der Gene weitgehend dem typischen Muster anderer Sägespinnen: die meisten Gene liegen auf einem DNA‑Strang, eine kleinere Gruppe auf dem gegenüberliegenden Strang, und die Transfer‑RNA‑Gene falten sich zu klassischen Kleeblattstrukturen mit einigen Besonderheiten.

Buchstabenmuster, die Familienbindungen verraten
Mitochondriale DNA ist bei vielen Insekten stark zugunsten der Basen A und T verschoben, und diese Sägespinnen bilden keine Ausnahme. Alle vier untersuchten Argidae‑Arten haben Genome, die zu etwa 80 Prozent aus A oder T bestehen, aber das Verhältnis ist nicht identisch. Die drei zuvor bekannten Arten, alle aus der Unterfamilie Arginae, sind sogar noch A+T‑reicher als S. koreana, die zur Unterfamilie Sterictiphorinae gehört. Feine Ungleichgewichte darin, wie häufig A gegenüber T bzw. G gegenüber C vorkommt, unterscheiden sich zwischen Arten und innerhalb verschiedener Bereiche des Genoms. Eine Art, Arge aurora, kehrt einige dieser Schieflagen sogar um und hebt sich damit von ihren Verwandten ab. Die Forscher zeigen außerdem, dass bestimmte Aminosäuren wie Leucin, Isoleucin, Methionin und Phenylalanin häufiger kodiert werden als andere, was widerspiegelt, wie dieses verzerrte Basenalphabet die genetischen „Wörter“ der Sägespinnen prägt.
Verschobene Gene und langsam sich verändernder Code
Obwohl der mitochondriale Bauplan insgesamt konservativ ist, neigen kleine Gene, die tRNAs, dazu, umgelagert zu werden; ihre neuen Positionen können große Verzweigungen im Stammbaum der Sägespinnen markieren. Bei Arginae‑Arten ist ein tRNA‑Gen (trnW) an eine neue Stelle in der Nähe der A+T‑reichen Region gesprungen. Bei S. koreana wurde ein anderes Set von tRNAs (trnK, trnD, trnI und trnM) in einem konsistenten Muster umgeordnet. Diese unterschiedlichen Umlagerungen markieren wahrscheinlich die zwei Unterfamilien als getrennte Linien. Als das Team untersuchte, wie schnell sich die proteinkodierenden Gene verändern, stellten sie fest, dass die meisten Änderungen durch natürliche Selektion entfernt werden, ein Muster, das als reinigende Selektion bezeichnet wird. Ein Gen, cox1, verändert sich besonders langsam, was seine Nützlichkeit als DNA‑„Barcode“ zur Artunterscheidung unterstreicht.
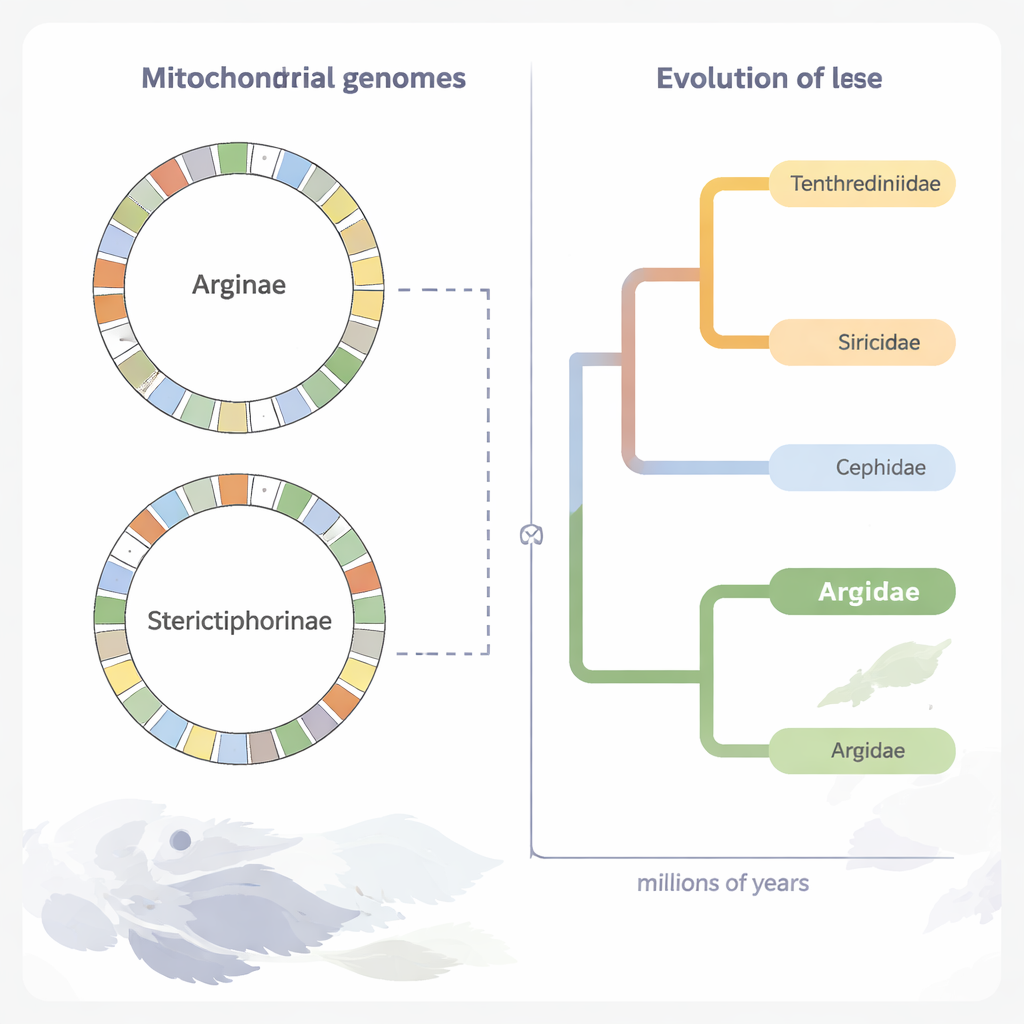
Den alten Stammbaum der Sägespinnen neu aufbauen
Mithilfe der proteinkodierenden Anteile der mitochondrialen DNA von 70 Sägespinnenarten rekonstruierten die Forschenden einen detaillierten Evolutionsbaum. Ihre Analysen bestätigen, dass Argidae eine natürliche Gruppe bildet und eng mit einer anderen Familie, den Pergidae, innerhalb der größeren Superfamilie Tenthredinoidea verwandt ist. Unter Einbeziehung fossiler Daten schätzen sie, dass sich die Linie Argidae–Pergidae vor etwa 206 Millionen Jahren von anderen Sägespinnenfamilien abspaltete und dass die Argidae selbst vor ungefähr 166 Millionen Jahren, im Mittleren Jura, entstanden sind. Die beiden großen Unterfamilien der Argidae, Arginae und Sterictiphorinae, trennten sich offenbar bereits im Unteren Kreidezeitalter, vor etwa 126 Millionen Jahren, einer Zeit, in der sich auch die Blütenpflanzen diversifizierten.
Was das für Wissenschaft und Schädlingsbekämpfung bedeutet
Dieses erste mitochondriale Genom aus Sterictiphorinae schließt eine wichtige Lücke in unserem genetischen Bild der Argidae. Es zeigt, dass feinere Merkmale – etwa Genomlänge, Genordnung und Basenbias – zuverlässig große Gruppen innerhalb dieser schädlingsbehafteten Familie trennen und sie im breiteren Stammbaum der Sägespinnen verankern können. Für Nicht‑Spezialisten lautet die Kernaussage: Indem Wissenschaftler die kleinen DNA‑Ringe in den Zellkraftwerken von Insekten lesen und vergleichen, können sie nachverfolgen, wie zerstörerische blattfressende Sägespinnen miteinander verwandt sind, abschätzen, wann ihre Linien entstanden sind, und so eine bessere Grundlage für die Artbestimmung und das Verständnis ihrer Ausbreitung in Feld und Wald schaffen.
Zitation: Park, B., Hwang, U.W. The first mitochondrial genome for Sterictiphorinae (Hymenoptera: Argidae) and insights into argid phylogeny. Sci Rep 16, 7154 (2026). https://doi.org/10.1038/s41598-026-38021-9
Schlüsselwörter: Sägemehlwespen‑Evolution, mitochondriales Genom, Insekten‑Phylogenie, Forst‑ und Feldschädlinge, DNA‑Barcoding