Clear Sky Science · de
Ein genom‑Struktur‑adaptives Rahmenwerk zur ROH‑basierten Abschätzung von Inzucht bei Penaeus vannamei
Warum Garnelen‑Familienstammbäume für Ihr Abendessen wichtig sind
Moderne Garnelenfarmen beliefern einen großen Teil der weltweiten Meeresfrüchte, doch das wiederholte Züchten derselben Familienlinien kann deren Gesundheit schleichend untergraben. Wenn nahe Verwandte paaren, können schädliche, versteckte Gene kombiniert werden, was Wachstum, Überleben und Krankheitsresistenz verringert. Diese Studie stellt eine auf den ersten Blick einfache, aber weitreichende Frage für die globale Aquakultur: Wie lässt sich Inzucht bei Zuchtgarnelen so genau messen, dass Bestände gesund und produktiv bleiben?
Versteckte genetische Spuren der Inzucht
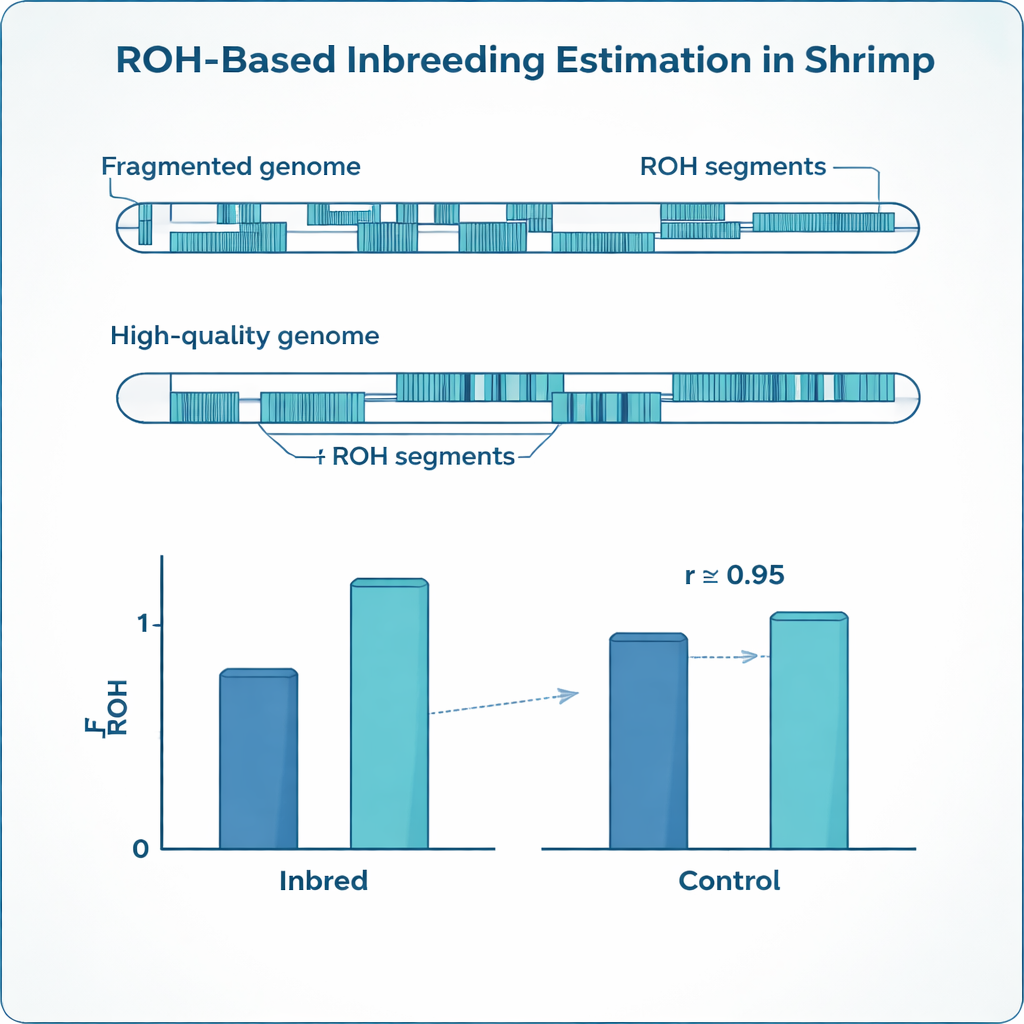
Inzucht hinterlässt charakteristische Fingerabdrücke in der DNA. Anstatt zwei leicht unterschiedliche Versionen vieler Gene zu tragen, haben inzüchtige Tiere häufig lange Abschnitte, in denen beide Kopien identisch sind. Genetiker bezeichnen diese Abschnitte als „Runs of Homozygosity“ (ROH). Indem man aufsummiert, welcher Anteil des Genoms eines Tiers in solchen Abschnitten liegt, lässt sich der Inzuchtgrad genauer schätzen als über Papierreihen, die oft lückenhaft oder fehlerhaft sind. Dieses ROH‑basierte Maß, bekannt als FROH, ist bei Rindern, Schweinen und anderem Nutzvieh inzwischen Standard, doch Garnelen‑Genome stellen besondere Herausforderungen, die Standardmethoden unzuverlässig machen können.
Warum Garnelen‑Genome besonders knifflig sind
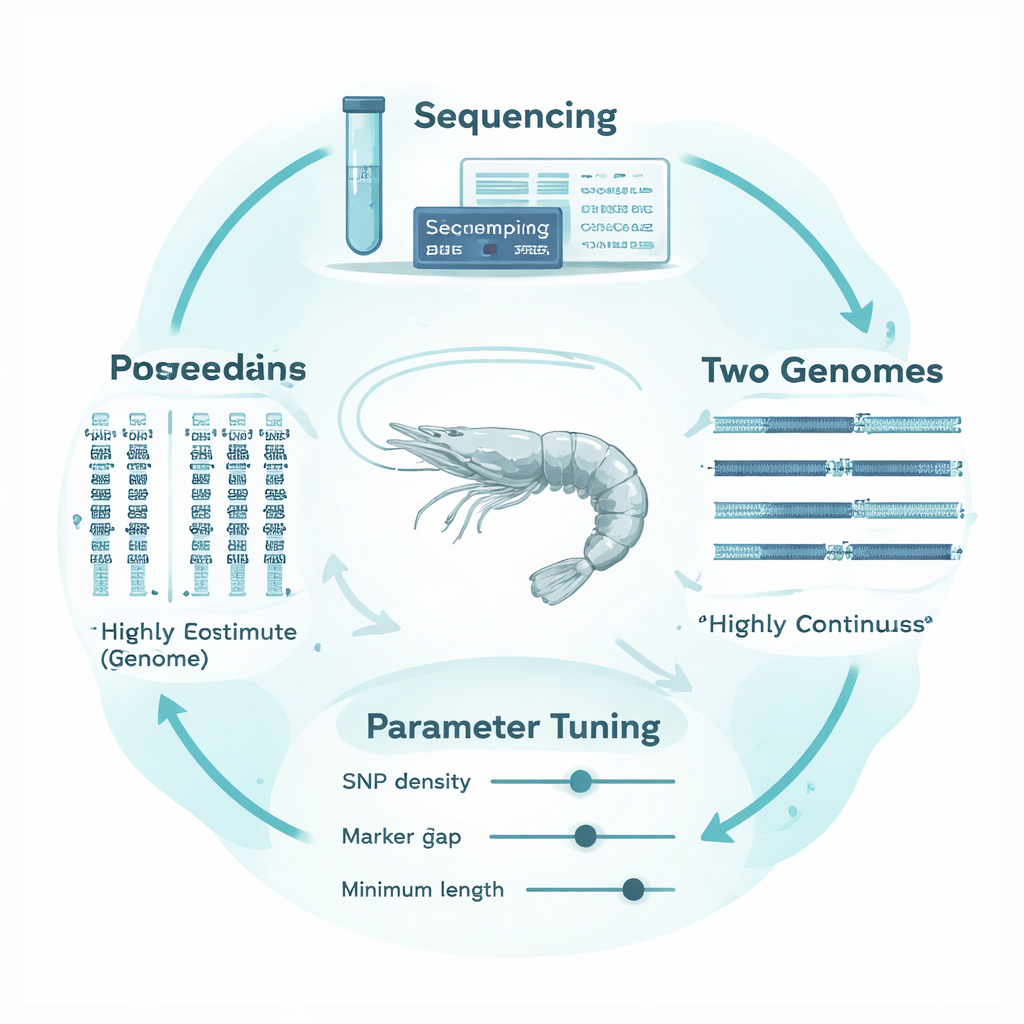
Die Weißbein‑Garnele (Penaeus vannamei), die weltweit am meisten gezüchtete Garnelenart, besitzt ein stark fragmentiertes und komplexes Genom. Anstatt langer, durchgehender Chromosomensequenzen sind viele verfügbare Genomassemblies in Tausende kleinere Fragmente mit Lücken und repetitiven Regionen aufgeteilt. Genetische Marker sind ungleichmäßig über dieses Mosaik verteilt, und die Art weist eine sehr hohe genetische Diversität auf. Methoden und Programmvoreinstellungen, die ursprünglich für gut kartierte Säugetier‑Genome optimiert wurden, können deshalb technische Lücken für echte Unterbrechungen von ROH halten oder kurze, zufällige Ähnlichkeiten mit echten Inzuchtsignalen verwechseln. Das Ergebnis ist ein hohes Risiko, den Inzuchtgrad einer Garnele falsch zu schätzen.
Ein genom‑bewährter Messstab
Um das Problem zu lösen, entwickelten die Autoren ein „genom‑struktur‑adaptives“ Rahmenwerk, das die ROH‑Analyse an die Besonderheiten der Garnelen‑DNA anpasst. Sie erzeugten dreizehn stark inzüchtige Garnelenfamilien durch kontrollierte Paarungen und sequenzierten dann die Genome von fünf dieser Familien plus deren Eltern tiefgehend. Entscheidend war, dass dieselben Sequenzdaten an zwei sehr unterschiedliche Referenzgenome angelegt wurden: eine ältere, fragmentierte Assembly und eine neuere, stark zusammenhängende Version. Mit dem weit verbreiteten Analysewerkzeug PLINK prüften sie systematisch, wie acht zentrale Parameter die ROH‑Erkennung beeinflussen, und konzentrierten sich auf drei, die besonders sensibel gegenüber der Genomstruktur sind: wie dicht Marker liegen müssen, wie groß eine Lücke zwischen Markern innerhalb eines Runs sein darf und wie lang ein Run mindestens sein muss, um zu zählen. Sie bauten empirische, nicht überlappende genomische Fenster, um lokale Markerabstände und fehlende Daten zu verfolgen, und nutzten die „genomische Abdeckung“ dieser Fenster zusammen mit der Stabilität von FROH und ROH‑Längen als objektive Leitlinien für sinnvolle Schwellenwerte.
Verschiedene Einstellräder, ein einheitliches Inzuchtbild
Die optimierten Einstellungen erwiesen sich für die beiden Referenzen als sehr unterschiedlich. Die fragmentierte Assembly erforderte deutlich dichtere Marker, kürzere zulässige Lücken und kürzere minimale Run‑Längen als das hochwertigere Genom, um echte ROH nicht in viele kleine Stücke zu zerlegen. Nach separater Feinabstimmung dieser Parameter konvergierten die Inzuchtschätzungen jedoch: Der durchschnittliche FROH in den inzüchtigen Garnelen lag in beiden Fällen bei etwa 0,24, was gut mit dem aus den geplanten Paarungen erwarteten Wert übereinstimmte und stark miteinander korrespondierte. Gleichzeitig zeigte das kontinuierlichere Genom weniger, dafür deutlich längere ROH‑Segmente, während die fragmentierte Karte viele davon in kurze Abschnitte zerschnitt. Die Studie offenbarte außerdem auffällige Unterschiede zwischen Vollgeschwistern: Selbst innerhalb derselben Familie variierten die Inzuchtgrade stark — etwas, das einfache Stammbaumunterlagen nicht erfassen können.
Präzisere Werkzeuge für gesündere Garnelenbestände
Für Nicht‑Fachleute lautet die Kernbotschaft schlicht: Die Messung von Inzucht anhand von DNA kann bei Zuchtgarnelen sehr genau sein — vorausgesetzt, die Methode berücksichtigt die zugrunde liegende Genomstruktur. Indem diese Arbeit ein praktisches Vorgehen zur Anpassung der ROH‑Analyse an fragmentierte Krustentier‑Genome liefert, können Züchter Inzucht Tier für Tier überwachen statt sich auf unvollständige Familientafeln zu verlassen. Das wiederum hilft, Paarungspläne zu entwerfen, die die genetische Vielfalt erhalten und gleichzeitig Wachstum und Widerstandsfähigkeit verbessern — ein Beitrag zu nachhaltigerer Garnelenzucht und ein Vorbild für andere Aquakulturarten mit ähnlichen genomischen Herausforderungen.
Zitation: Zou, X., Zhou, H., Liu, M. et al. A genome-structure adaptive framework for ROH-based inbreeding estimation in Penaeus vannamei. Sci Rep 16, 6769 (2026). https://doi.org/10.1038/s41598-026-37622-8
Schlüsselwörter: Garnelenzucht, Inzucht, genomische Selektion, Runs of Homozygosity, Aquakulturgenetik