Clear Sky Science · de
Schnelle, lernfreie Organoid-Quantifizierung und -Verfolgung mit OrganoSeg2
Warum winzige, im Labor gezüchtete Gewebe wichtig sind
In Laboren weltweit züchten Forschende inzwischen Miniaturversionen menschlicher Gewebe, sogenannte Organoide. Diese winzigen, dreidimensionalen Zellverbände können das Verhalten von Organen oder Tumoren nachbilden und sind deshalb mächtige Werkzeuge zur Erforschung von Krankheiten und zur Prüfung von Therapien. Es gibt jedoch einen Engpass: Forschende sammeln oft tausende von Mikroskopaufnahmen bei niedriger Vergrößerung und haben Schwierigkeiten, für jedes einzelne Organoid zu messen, wie es wächst, seine Form verändert oder im Laufe der Zeit abstirbt. Diese Arbeit stellt OrganoSeg2 vor, eine neu entwickelte Software, die diese einfachen, grauen Bilder in aussagekräftige, verlässliche Messdaten für jedes einzelne Organoid verwandelt — ganz ohne künstliche Intelligenz-Training oder teure Bildgebungsausstattung.
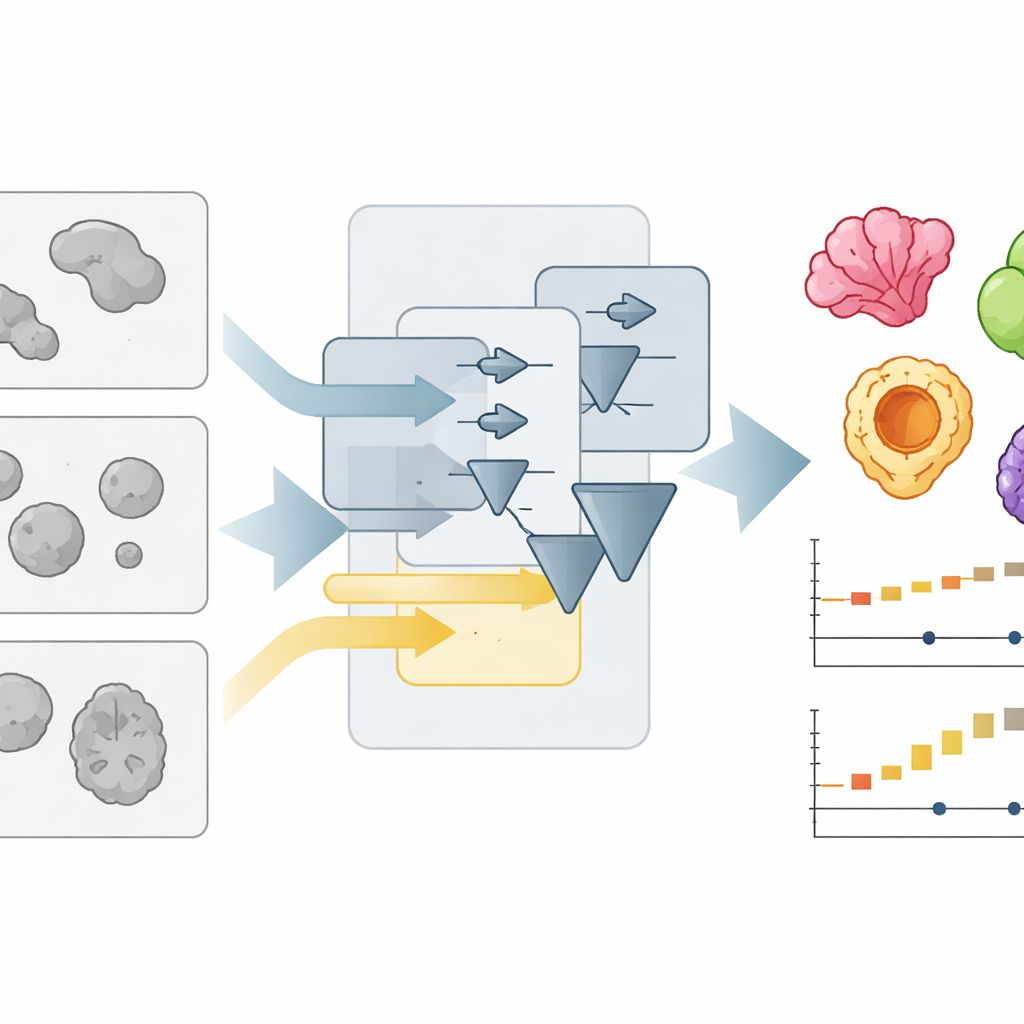
Ein neuer Weg, überfüllte Mikroskopbilder zu lesen
Organoide werden üblicherweise mit einfachen Hellfeldmikroskopen aufgenommen, die sie als schwache, überlappende Flecken zeigen. Jedes dieser Flecken automatisch zu umreißen — also das Bild zu segmentieren — ist schwieriger, als es scheint, besonders wenn Labore unterschiedliche Kulturformate, Beleuchtung oder Objektive verwenden. Die Autor:innen hatten bereits OrganoSeg entwickelt, ein Programm, das grundlegende Segmentierungsaufgaben bewältigen konnte, aber bei größeren Bildsammlungen langsam und unhandlich wurde. Mit OrganoSeg2 wurde die Software von Grund auf neu aufgebaut: moderne Oberfläche, gestraffter interner Code und mehrere bisher versteckte Einstellungen sichtbar gemacht, damit Nutzer:innen genau einstellen können, wie Organoide vom Hintergrund getrennt, benachbarte, aneinandergrenzende Objekte geteilt und Artefakte am Bildrand ignoriert werden. Die App speichert diese Einstellungen jetzt als Metadaten, sodass Analysen reproduzierbar und teilbar sind.
Beschleunigung der Arbeit ohne Verlust an Details
Neben der Flexibilität legte das Team großen Wert auf Geschwindigkeit und Benutzerfreundlichkeit. In früheren Versionen berechnete die Software automatisch jede mögliche Messgröße für jedes Organoid, selbst wenn nur wenige benötigt wurden. OrganoSeg2 berechnet stattdessen nur, was die Nutzer:innen auswählen, und organisiert verwandte Berechnungen so, dass zeitaufwändige Schritte effizient wiederverwendet werden. Es reduziert zudem die Informationsüberflutung auf dem Bildschirm, zeigt Beschriftungen nur bei Bedarf und ergänzt Tastenkürzel sowie interaktive Werkzeuge zum schnellen Entfernen von Schmutz oder Nicht‑Organoid‑Objekten. Diese Designentscheidungen verkürzen häufige Arbeitsabläufe — wie das Segmentieren von Bildern, das Anzeigen von Konturen und das Exportieren von Daten — um etwa das Zehnfache und machen es praktikabel, große, gekachelte Bilder und lange Zeitrafferexperimente auf einem gewöhnlichen Computer zu bearbeiten.
Leistungsstärker als Hightech-Rivalen bei realen Daten
Um die Leistungsfähigkeit von OrganoSeg2 zu prüfen, verglichen die Autor:innen es mit mehreren anderen Segmentierungstools, darunter Deep‑Learning‑Systeme, die auf manuell gelabelten Beispielen trainiert werden müssen. Sie stellten Bildsets aus sechs verschiedenen Quellen zusammen — etwa Kolon-, Lungen-, Pankreas-, Gehirn- und Brust‑Organoide sowie Embryoidkörper — bei denen menschliche Expert:innen die Organoid‑Grenzen bereits nachgezeichnet hatten. Anhand eines Standard‑Genauigkeitsscores, der misst, wie stark die automatischen Umrisse mit den manuellen übereinstimmen, erreichte OrganoSeg2 in den meisten Datensätzen ähnliche oder bessere Werte als spezialisierte Werkzeuge und führte die Rangliste besonders deutlich bei schwierigen Brustkrebsaufnahmen an, die viel Fremdmaterial und ungewöhnlich geformte Organoide enthielten. Bemerkenswert ist, dass OrganoSeg2 diese Leistung ohne zehntausende Trainingsbeispiele erzielte und mindestens so schnell lief wie seine Konkurrenten, selbst solche auf KI‑Basis.
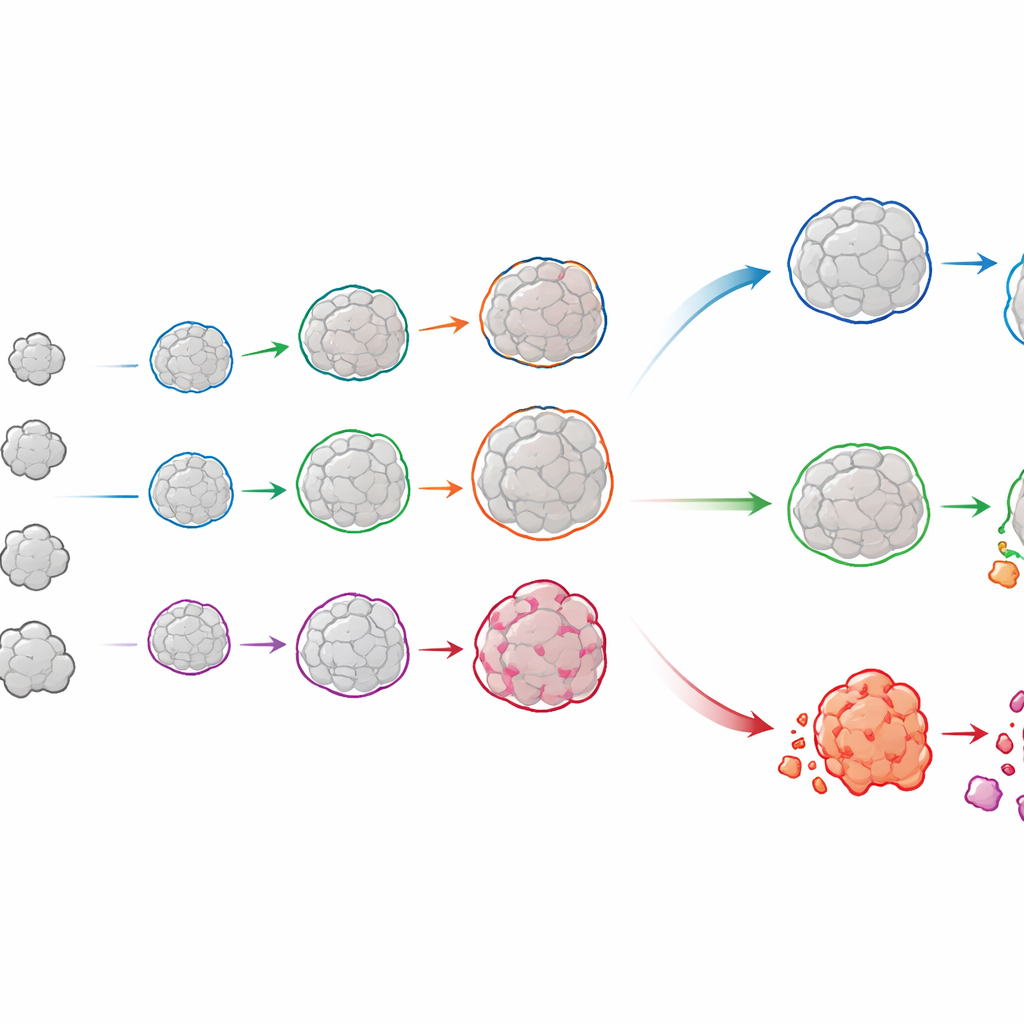
Die Lebensgeschichte jedes Organoids nachverfolgen
OrganoSeg2 kann mehr als einzelne Organoide in Einzelbildern umreißen. Es kann Bilder aus verschiedenen Tagen ausrichten und dasselbe Organoid über die Zeit verbinden und so eine Wachstumshistorie für jedes Objekt aufbauen. Als die Autor:innen dies auf Organoide anwandten, die direkt aus luminalen Brusttumoren von Patientinnen gezogen wurden, stellten sie fest, dass einzelne Organoide selten gleichmäßig wuchsen; viele verlangsamten sich oder erreichten Plateaus — ein Spiegelbild der Tatsache, dass reale Tumoren aus einer Mischung schnell‑ und langsam wachsender Regionen bestehen. Durch das Anpassen dieser Verläufe an ein einfaches Wachstumsmodell konnte das Team sowohl die Wachstumsrate jedes Organoids als auch seine zu erwartende Endgröße quantifizieren. Der Vergleich dieser Muster zwischen Patientinnen zeigte, dass Tumoren mit ähnlichem Gesamtwachstum sehr unterschiedliche Zusammensetzungen zugrundeliegender Verhaltensweisen verbergen können — Unterschiede, die für die Vorhersage der Therapieantwort wichtig sein könnten.
Krebszellen beim Leben und Sterben unter Strahlung beobachten
Die Software verknüpft auch Hellfeldaufnahmen mit fluoreszenten Farbstoffen, die den Zellzustand anzeigen. In neuen Experimenten setzten die Autor:innen Brustkrebs‑Organoide Strahlendosen aus, die denen in der Klinik ähneln, und färbten sie mit einem Vitalitätsmarker, der während des programmierten Zelltods aufleuchtet, sowie mit einem zweiten Farbstoff, der tote Zellen am Endzeitpunkt sichtbar macht. OrganoSeg2 nutzte das Hellfeldbild, um die Organoid‑Form zu definieren, und maß dann die fluoreszenten Signale innerhalb jedes Organoids über viele Tage. So konnte das Team Organoid für Organoid nachverfolgen, wann die Strahlung den Zelltod auslöste und wie stark. Einige Patient:innen‑Organoide zeigten kaum Reaktion, andere hohe Empfindlichkeit bereits bei niedrigeren Dosen — ein Hinweis auf die große Variabilität von Tumorantworten.
Was das für Forschung und Versorgung bedeutet
In der Summe zeigt die Arbeit, dass sorgfältige, einstellbare Bildverarbeitung komplexe Deep‑Learning‑Methoden für eine breite Palette von Organoidbildern Konkurrenz machen oder übertreffen kann, dabei transparent bleibt und sich leicht anpassen lässt. OrganoSeg2 verwandelt einfache, niedrig‑vergrößerte Filme von Organoiden in detaillierte Aufzeichnungen darüber, wie jedes winzige Gewebe unter verschiedenen Bedingungen wächst und überlebt. Für Grundlagenforscher:innen bietet es einen robusten Weg, die verborgene Vielfalt in Organoidkulturen aufzuschlüsseln. Insbesondere für die Krebsforschung eröffnet es die Möglichkeit, patientenabgeleitete Organoide nicht nur für Ja‑/Nein‑Screens zu verwenden, sondern für reichhaltige, zeitlich aufgelöste Messungen von Wachstum und Zelltod, die eines Tages helfen könnten, Behandlungen präziser zu gestalten.
Zitation: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Schlüsselwörter: Organoide, Bildanalyse, Krebsforschung, Mikroskopie, Strahlenreaktion