Clear Sky Science · de
Aufdeckung potenzieller MTA, Kandidatengene und mikroRNA-Regulationsnetzwerke, die an der durch Salinität ausgelösten Stressverträglichkeit in der iranischen Aegilops tauschii beteiligt sind
Warum salzige Böden unser tägliches Brot bedrohen
Mit dem Klimawandel nehmen Dürren zu und Bewässerungswasser wird salzhaltiger, wodurch große Ackerflächen für gewöhnlichen Weizen zu salzig werden. Das betrifft alle, die Brot als Grundnahrungsmittel nutzen. Die hier zusammengefasste Studie richtet den Blick auf eine wilde Grasart, Aegilops tauschii, einen direkten Vorfahren des modernen Brotweizens, um die verborgenen genetischen Werkzeuge — und kleine regulatorische Moleküle — aufzuspüren, die Pflanzen helfen, mit Salinität fertigzuwerden. Durch die Kartierung dieser natürlichen Schutzmechanismen wollen die Forschenden Züchtern neue Wege aufzeigen, Weizensorten zu entwickeln, die produktiv bleiben, auch wenn der Boden brackig wird.
Ein wilder Weizenverwandter als verborgene Ressource
Aegilops tauschii wächst natürlich im Fruchtbaren Halbmond, einschließlich Iran, wo sie sich über Jahrtausende an raue, trockene und oft salzhaltige Umgebungen angepasst hat. Diese Art lieferte den „D“-Anteil des Genoms, den der moderne Brotweizen heute trägt. Da die heutigen ertragsstarken Weizensorten aus einer relativ engen genetischen Basis gezüchtet wurden, fehlt ihnen oft die volle Bandbreite an Stressverträglichkeitseigenschaften, die noch in ihren wilden Verwandten vorhanden sind. Die Autorinnen und Autoren stellten 77 iranische Aegilops tauschii-Ekotypen (lokale Formen) zusammen und zogen sie im Sämlingsstadium unter normalen und salzhaltigen Bedingungen, wobei sie Merkmale wie Wurzel- und Sprosslänge, Frisch- und Trockengewicht sowie Blatt- und Wurzeloberfläche maßen. Salinität reduzierte all diese Merkmale deutlich und bestätigte, dass hohe Salzkonzentrationen junge Pflanzen schädigen.
Die DNA-Fingerabdrücke der Salzverträglichkeit lesen
Um zu verstehen, warum einige wilde Pflanzen besser mit Salz zurechtkamen als andere, griff das Team auf DNA-Marker zurück — kurze, leicht messbare Sequenzen über das Genom verteilt, die wie Barcodes für nahegelegene Gene wirken. Mit einer Kombination aus „zufälligen“ Markern und halbzufälligen RAMP-Markern bewerteten sie Hunderte von DNA-Banden und untersuchten die tatsächliche Diversität der Sammlung. Sie fanden hohe genetische Variation, wobei bestimmte Markersysteme, etwa ISJ9 und OPE03-Xgwm44-7DF, besonders große Unterscheidungskraft zwischen Ekotypen boten. Diese reiche Vielfalt bedeutet, dass die iranische Aegilops tauschii weiterhin viele einzigartige genetische Varianten birgt, die Züchter nutzen können. Durch statistische Verknüpfung bestimmter DNA-Banden mit Sämlingsmerkmalen unter Salzstress identifizierten die Forschenden 115 Marker–Merkmals-Assoziationen, die auf genomische Regionen hinweisen, welche die Entwicklung von Wurzeln, Sprossen und Blättern in salzhaltiger Umgebung beeinflussen.
Von Markern zu funktionellen Stressabwehrgenen
Das Auffinden eines nützlichen DNA-Markers ist nur der erste Schritt; als Nächstes fragten die Autorinnen und Autoren, welche tatsächlichen Gene in der Nähe dieser Marker liegen und die Arbeit verrichten könnten. Mithilfe des Weizen-Referenzgenoms suchten sie 500.000 Basenpaare um jeden assoziierten Marker und entdeckten 254 Kandidatengene. Viele dieser Gene wurden unabhängig durch umfangreiche RNA-Sequenzierungsdatensätze bestätigt, dass sie ihre Aktivität hoch- oder herunterregulieren, wenn Pflanzen Umweltstress ausgesetzt sind, einschließlich Kälte, Hitze, Nährstoffmangel und Krankheit. Die Kandidatengene waren gehäuft für Funktionen in Abwehrreaktionen sowie Schutz vor Hitze- und oxidativen Schäden vertreten. Mehrere kodieren Proteine wie Krankheitsresistenzrezeptoren, Hitzeschock-Chaperone und sogenannte Thaumatin- und Osmotin-ähnliche Proteine, die helfen, Zellen zu stabilisieren, wenn Salz Wasser entzieht und schädliche reaktive Sauerstoffmoleküle ansteigen. Die Pfadanalyse hob den Glutathionstoffwechsel hervor, ein zentrales chemisches System, das Pflanzen zur Entgiftung stressbedingter Nebenprodukte nutzen.
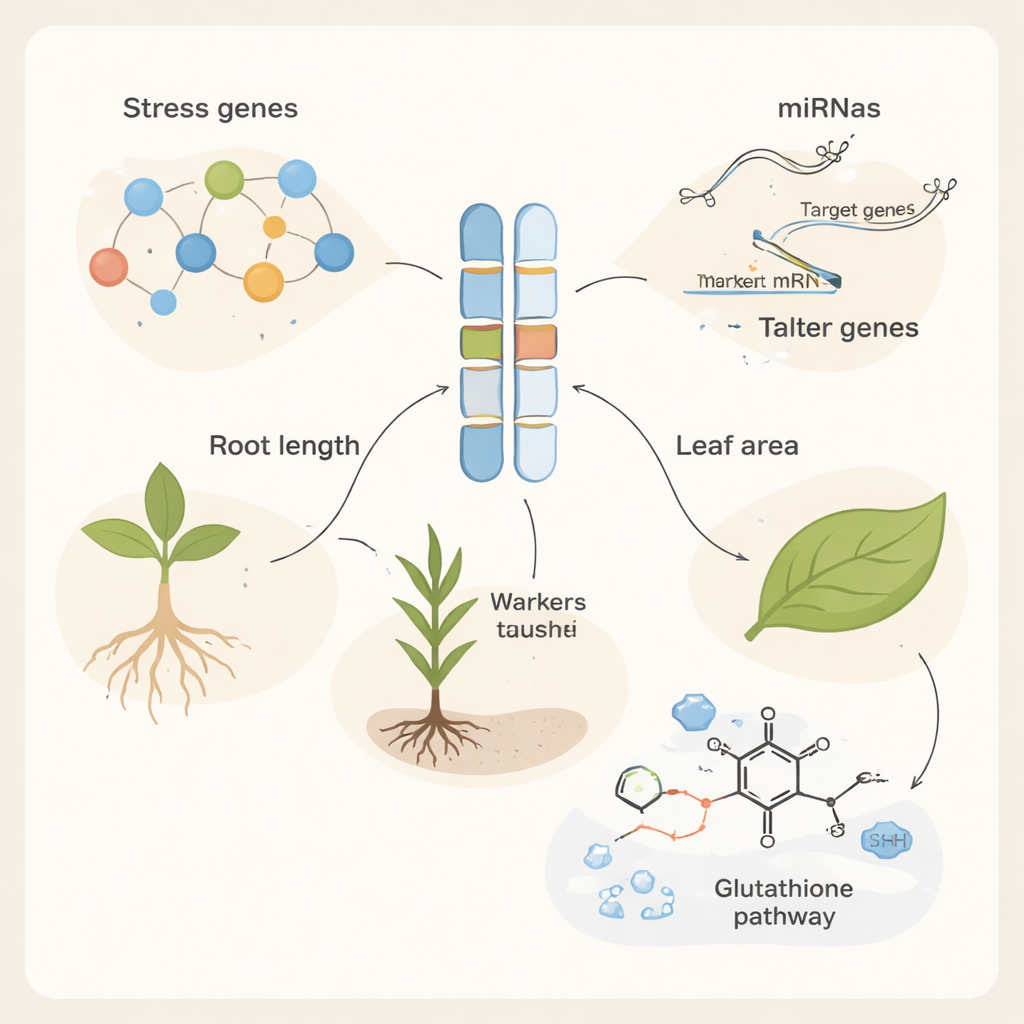
Kleine RNA-Schalter, die Stressreaktionen feinjustieren
Gene wirken nicht allein; sie werden von mikroRNAs gesteuert, sehr kurzen RNA-Molekülen, die Genaktivität abschalten oder dämpfen können. Die Forschenden sagten voraus, welche Weizen-mikroRNAs ihre Kandidatengene anvisieren könnten, und entdeckten 107 verschiedene mikroRNAs, die dichte Regulationsnetzwerke bilden. Viele dieser kleinen Regulatoren waren bereits bekannt dafür, auf Dürre, Hitze, Metalle oder Salinität zu reagieren. Zum Beispiel wurden spezifische mikroRNAs, die zuvor mit Salz- oder Hitzetoleranz oder „Stressgedächtnis“ in Verbindung gebracht wurden, als Regulatoren zentraler Abwehr- und Entgiftungsgene identifiziert, die in dieser Studie gefunden wurden. Einige Gene wurden von mehreren mikroRNAs angegriffen, was darauf hindeutet, dass Pflanzen mehrere regulatorische Schalter übereinanderlegen, um ihre Reaktion je nach Stressintensität fein abzustimmen.
Die wilde Belastbarkeit in die Felder der Landwirte bringen
Zusammen bieten der Katalog vielfältiger DNA-Marker, 254 Kandidatengene und 107 regulatorische mikroRNAs eine Landkarte zur Verbesserung der Weizenleistung auf salzhaltigen Böden. Züchter können die aussagekräftigsten Marker in einfache Labortests überführen, um große Pflanzenzahlen auf verborgene Salzverträglichkeitsmerkmale zu screenen — eine Strategie, die als markergestützte Selektion bekannt ist. Langfristig könnten die vielversprechendsten Gene und deren mikroRNA-Regulatoren gezielt in empfindliche Weizensorten eingebracht oder editiert werden, um deren natürliche Abwehrkräfte zu stärken. Obwohl die Studie weiterhin experimentelle Validierung unter Salinität in lebenden Pflanzen fordert, zeigt sie deutlich, dass der wilde Verwandte Aegilops tauschii mächtige genetische Werkzeuge birgt, die, wenn sie bedacht eingesetzt werden, dazu beitragen können, Weizenerträge angesichts zunehmender Salinität und Klimabelastung zu sichern.
Zitation: Sabouri, H., Nikkhah, N., Kazerani, B. et al. Uncovering the potential MTAs, candidate genes and microRNAs regulatory networks involved in salinity stress tolerance triggered in Iranian Aegilops tauschii. Sci Rep 16, 6877 (2026). https://doi.org/10.1038/s41598-026-37365-6
Schlüsselwörter: Salzresistenz, Weizenzüchtung, Aegilops tauschii, stressresponsible Gene, Pflanzen-mikroRNAs