Clear Sky Science · de
Vergleichende Karyotypanalyse von elf Lilium-Arten aus China mittels FISH mit rDNA-Oligo-Sonden
Warum Lilienchromosomen über das Labor hinaus wichtig sind
Gartenlilien sind mehr als nur schöne Blumen und traditionelle Heilmittel: Sie sind auch genetische Modellorganismen, die Forschern helfen zu verstehen, wie neue Pflanzenarten entstehen und wie man sie korrekt klassifiziert. Diese Studie untersucht die Zellen von elf chinesischen Lilienarten, von denen viele als Nahrungs- oder Heilpflanzen genutzt werden, um zu sehen, wie ihre Chromosomen angeordnet und markiert sind. Durch den Vergleich dieser verborgenen Strukturen klären die Autorinnen und Autoren, welche Lilien wirklich nahe verwandt sind, und liefern Belege, die langjährige Streitfragen zur Stammesgeschichte der Lilien beantworten können.
Entwirrung eines verwirrenden Lilienstammbaums
Die Gattung Lilium umfasst etwa 125 Arten, die auf der Nordhalbkugel verbreitet sind, wobei China eines der Hauptzentren der Vielfalt darstellt. Seit mehr als einem Jahrhundert versuchen Botanikerinnen und Botaniker, diese Arten auf der Grundlage überwiegend sichtbarer Merkmale wie Blütenform in natürliche Sektionen zu gliedern. Ähnliche Blüten bedeuten jedoch nicht immer nahe Verwandtschaft, und genetische Studien an Chloroplasten und Kernen haben teils widersprüchliche Ergebnisse geliefert, wie die Arten zueinander stehen. Insbesondere eine Gruppe namens Leucolirion und ihre zwei Untersektionen (6a und 6b) sowie mehrere Arten aus Südwest- und Zentralchina waren schwer eindeutig einzuordnen.
Barcodes auf Chromosomen lesen
Um dieses Problem anzugehen, wandte sich das Team der Zytogenetik zu, der Studie der Chromosomen. Alle elf untersuchten Arten teilen denselben grundlegenden Chromosomensatz von zwölf Chromosomen, der bei Diploiden üblicherweise als 24 vorliegt; zwei Populationen von Lilium lancifolium waren triploid mit 36 Chromosomen. Unter dem Mikroskop zeigt jede Art zwei größere und zehn kleinere Chromosomen, doch subtile Unterschiede in Form und Länge sind mit bloßem Auge schwer zu erkennen. Die Forschenden maßen daher Chromosomengrößen präzise und verwendeten eine Technik namens Fluoreszenz-in-situ-Hybridisierung (FISH), um leuchtende DNA-Marker an spezifische ribosomale DNA-Regionen (rDNA) zu binden, die wie helle Barcodes entlang der Chromosomen fungieren.
Mustern in Liliengenomen auf die Spur kommen
Die Autorinnen und Autoren kartierten zwei rDNA-Typen — 5S und 35S — auf den Chromosomen jeder Art. Die meisten Lilien wiesen eine 5S-Position und zwischen zwei und sechs 35S-Positionen auf, oft an charakteristischen Stellen. Zum Beispiel teilten vier Arten, die traditionell in die Untersektion Leucolirion 6a eingeordnet werden (L. leucanthum, L. sargentiae, L. sulphureum und L. regale), sehr ähnliche Muster von rDNA-Markierungen auf denselben Chromosomenpaaren, was auf eine enge Verwandtschaft hinweist, obwohl L. regale einige zusätzliche Veränderungen zeigte. Im Gegensatz dazu zeigten Arten der Schwesteruntersektion 6b und einige Sinomartagon-Lilien deutlich andere rDNA-Anordnungen, was eine echte Trennung dieser beiden Gruppen unterstreicht. Außerhalb von Leucolirion verbanden stark geteilte Muster die weit kultivierte L. lancifolium mit L. pumilum und L. davidii, was frühere DNA-Sequenzstudien bestätigt, die sie zusammengruppiert hatten.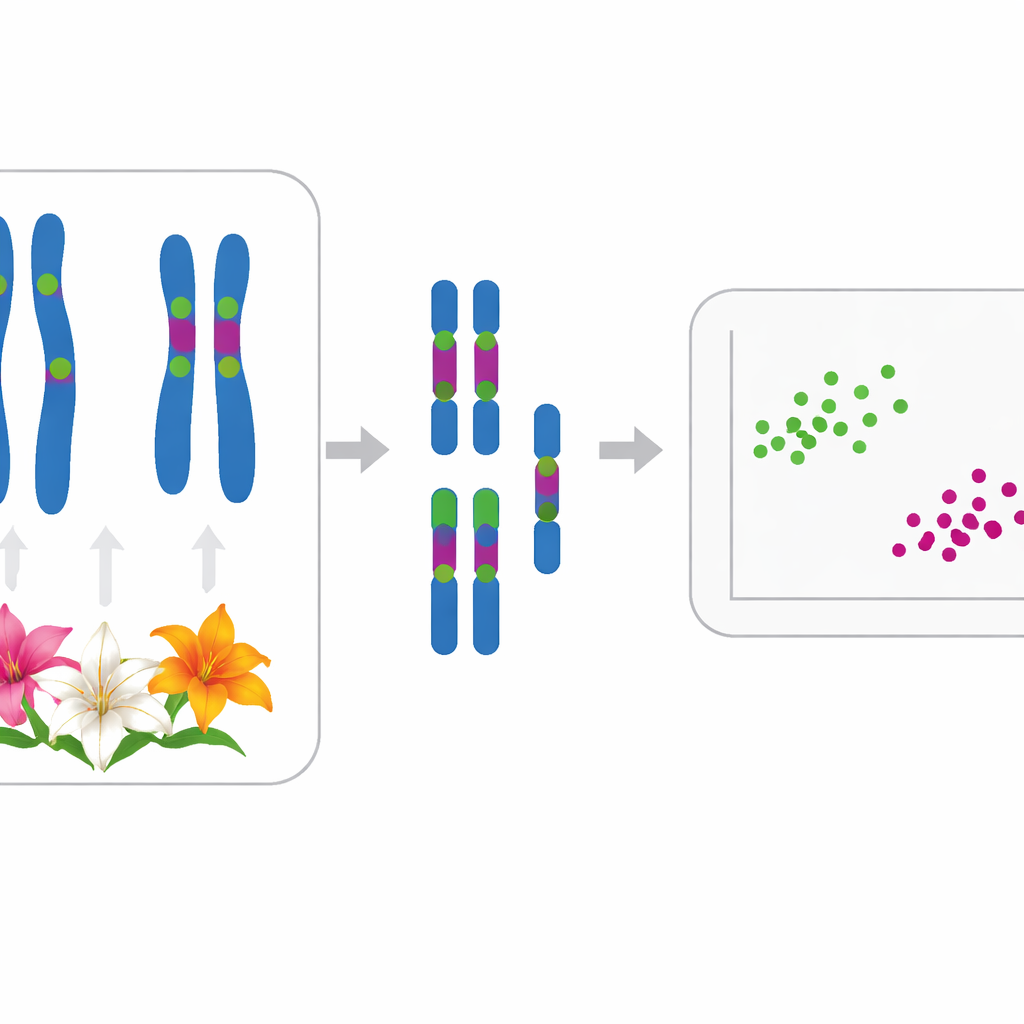
Messwerte in eine Beziehungslandkarte umwandeln
Über die Barcode-Positionen hinaus quantifizierte das Team, wie ungleichmäßig jeder Karyotyp war — sowohl in den Positionen der Zentromere (der „Taille“ des Chromosoms) als auch in den Chromosomenlängen. Sie verwendeten zwei statistische Indizes, MCA und CVCL, um diese Merkmale zu erfassen, und trugen die elf Arten in ein zweidimensionales Diagramm ein. Jede Art nahm einen eigenen, von den anderen unterscheidbaren Punkt ein, was zeigt, dass selbst scheinbar ähnliche Karyotypen bei sorgfältiger Messung voneinander zu unterscheiden sind. Eine weitergehende statistische Analyse (Hauptkoordinatenanalyse) gruppierte die Lilien dann in zwei Hauptcluster, die gut mit ihrer vermuteten Evolutionsgeschichte übereinstimmen. Ein Cluster enthielt L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale sowie die Formen von L. lancifolium und L. davidii; das andere gruppierte L. leucanthum, L. sargentiae, L. sulphureum, L. henryi und L. rosthornii.
Was das für die Benennung und Nutzung von Lilien bedeutet
Durch die Kombination detaillierter Chromosomenmessungen mit rDNA-Barcode-Karten zeigt diese Studie, dass sich Lilienarten in ihren Karyotypen stärker unterscheiden, als bisher angenommen, und dass diese Unterschiede ein deutliches evolutives Signal tragen. Praktisch ergibt sich daraus Unterstützung dafür, die Untersektion Leucolirion 6a als natürliche, klar abgegrenzte Gruppe innerhalb der Gattung Lilium zu behandeln, im Einklang mit jüngeren Klassifizierungsvorschlägen. Für Züchter, Kräuterpraktiker und Naturschutzplaner kann ein genaueres Bild der Verwandtschaftsverhältnisse zwischen Lilien die Kreuzungsauswahl leiten, die genetische Vielfalt sichern und sicherstellen, dass medizinische und essbare Sorten korrekt identifiziert und verwendet werden.
Zitation: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Schlüsselwörter: Lilium, Chromosomen, Fluoreszenz-in-situ-Hybridisierung, Pflanzenentwicklung, Zytotaxonomie