Clear Sky Science · de
Entwicklung und vorläufige Bewertung von Real‑Time‑PCR‑Assays für sechs Milchsäurebakterien
Hilfreiche Keime hinter Alltagslebensmitteln
Viele der Lebensmittel im Supermarktregal – von Joghurt und Käse bis zu Gurken und fermentiertem Gemüse – verdanken Geschmack und mögliche gesundheitliche Vorteile freundlichen Bakterien, die als Probiotika bekannt sind. Damit Hersteller diese „guten“ Mikroben sicher und zuverlässig nutzen können, müssen sie jedoch genau wissen, welche Bakterienarten tatsächlich in ihren Produkten vorkommen. Diese Studie beschreibt neue Labortests, die schnell und präzise sechs vielversprechende probiotische Bakterien aus Lebensmitteln identifizieren können und so eine Brücke zwischen moderner Mikrobiologie und den Lebensmitteln des Alltags schlagen.
Warum diese probiotischen Bakterien wichtig sind
Die sechs im Mittelpunkt stehenden Bakterien gehören alle zu einer größeren Gruppe, den Milchsäurebakterien, die seit langem in Fermentationen verwendet werden. Neuere Forschung deutet darauf hin, dass sie mehr können als nur Milch oder Kohl zu säuern. Einige Stämme von Ligilactobacillus agilis und Ligilactobacillus salivarius könnten helfen, schädliche Darmkeime abzuwehren, Entzündungen zu dämpfen und die Integrität der Darmbarriere zu unterstützen. Limosilactobacillus fermentum wurde in Tierstudien mit besserer Blutdruckkontrolle und antioxidativen Effekten in Verbindung gebracht. Lactobacillus johnsonii scheint das Mikrobiom so zu beeinflussen, dass verschiedene Organe geschützt werden könnten. Pediococcus pentosaceus und Weissella cibaria zeigen Potenzial zur Senkung des Cholesterins, zur Bekämpfung von Verderb und sogar zur Unterstützung der Mundgesundheit. Angesichts dieser Bandbreite möglicher Vorteile ist die Lebensmittelindustrie daran interessiert, diese Arten häufiger einzusetzen – jedoch nur, wenn sie mit Zuversicht identifiziert werden können.
Die Herausforderung, ähnlich aussehende Mikroben zu unterscheiden
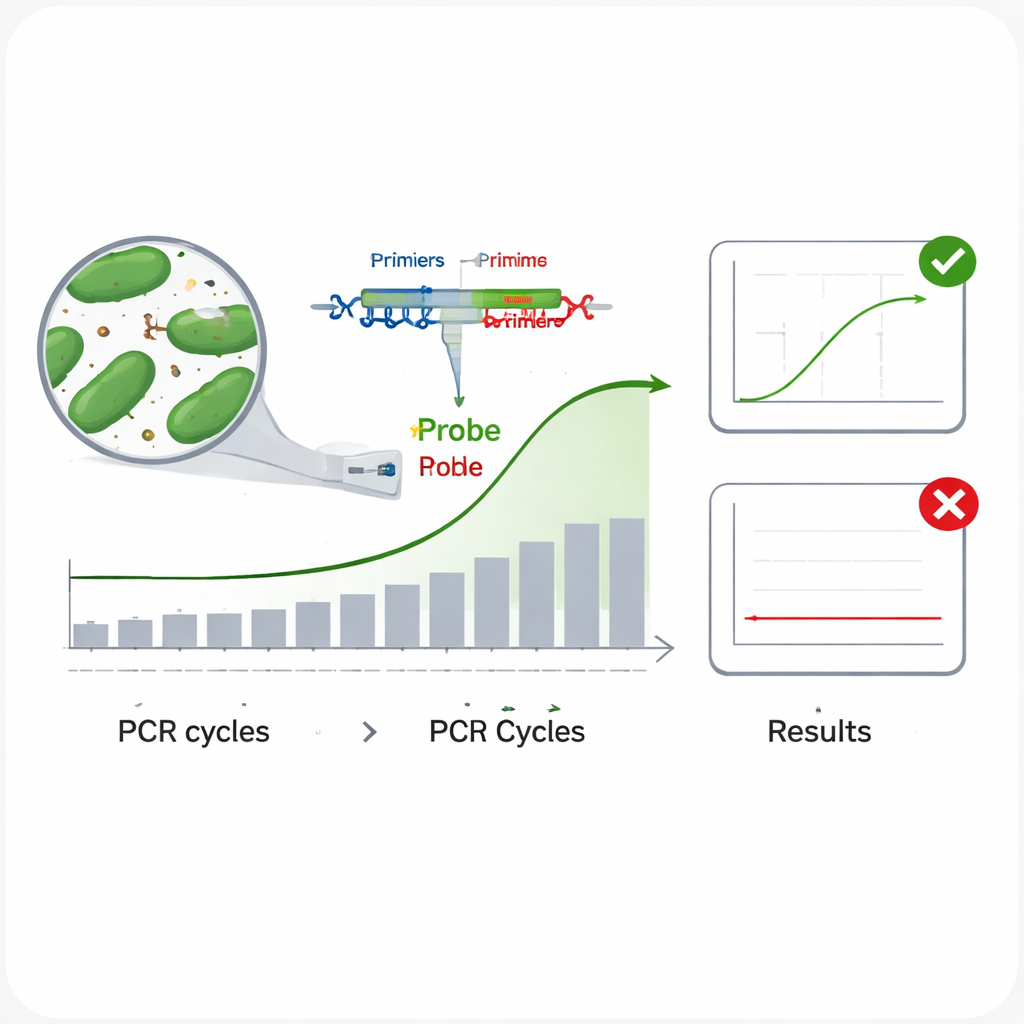
Traditionelle Methoden zur Identifizierung von Bakterien – Anzucht im Labor und biochemische Tests – sind langsam und arbeitsintensiv. Moderne DNA‑basierte Verfahren, insbesondere Real‑Time‑PCR, sind deutlich schneller. Bei der Real‑Time‑PCR richten kurze DNA‑Abschnitte, sogenannte Primer, und eine fluoreszierende Sonde sich auf eine charakteristische Stelle im genetischen Code eines Mikros aus; ist das richtige Mikroorganismus vorhanden, erkennt das Gerät ein aufleuchtendes Signal, während die DNA Zyklus für Zyklus vervielfältigt wird. Das Problem ist, dass eng verwandte Bakterien sehr ähnliche DNA teilen können, sodass häufig verwendete Regionen wie das 16S‑rRNA‑Gen manchmal nicht zwischen Arten unterscheiden. Das kann zu Tests führen, die das Ziel verfehlen (falsch negative) oder für falsche Arten anschlagen (falsch positive) – beides inakzeptabel bei Kennzeichnung und Sicherheit von Produkten.
Entwicklung schärferer molekularer „Barcodes“
Um dem zu begegnen, durchforsteten die Forscher vollständige Genomsequenzen nach kurzen DNA‑Abschnitten, die innerhalb jeder Zielart stark konserviert und gleichzeitig klar von anderen Bakterien unterscheidbar sind. Für jede der sechs Probiotika entwarfen sie passende Primer und eine Sonde mit sorgfältig abgestimmter Länge, Basenzusammensetzung, Schmelztemperatur und minimaler Neigung zur Bildung sekundärer Strukturen oder zur gegenseitigen Anlagerung. Computergestützte Prüfungen mithilfe der BLAST‑Datenbank und Sequenzalignments bestätigten, dass die ausgewählten DNA‑Regionen innerhalb der Art stabil, aber gegenüber Nicht‑Zielen differenziert sind. Das Team entwickelte außerdem eine Standard‑Reaktionsmischung und ein Temperaturprogramm, sodass alle Tests unter konsistenten und praktischen Bedingungen auf demselben Typ von Real‑Time‑PCR‑Gerät laufen konnten.
Prüfung der neuen Tests unter Realbedingungen
Anschließend bewerteten die Wissenschaftler die praktische Leistungsfähigkeit jedes Assays. Um die Inklusivität zu testen – also ob ein Test viele verschiedene Stämme derselben Art erkennt – führten sie jeden Assay an mehreren DNA‑Proben der Zielbakterie durch. In allen Fällen erzeugten alle getesteten Stämme eine deutliche Amplifikationskurve, was auf ein geringes Risiko hinweist, echte Ziele zu übersehen. Um die Spezifität zu prüfen – ob der Assay Nicht‑Zielarten ignoriert – konfrontierten sie jeden Test mit DNA von 13 anderen Darmbakterien, einschließlich verwandter Milchsäurebakterien und häufiger Darmmikroben wie Escherichia coli. Keine dieser Proben zeigte ein Signal, was ein sehr geringes Risiko für Fehlalarmen anzeigt. Das Team untersuchte zudem die Amplifikationseffizienz mittels einer Reihe von zehnfachen DNA‑Verdünnungen und bestätigte, dass alle sechs Assays ihre Ziele mit etwa 95–100 % Effizienz kopierten, nahe am Ideal. Schließlich bestimmten sie die Präzision durch wiederholte Durchläufe auf zwei DNA‑Niveaus und stellten fest, dass die geringen Schwankungen zwischen Wiederholungen und zwischen getrennten Experimenten deutlich unter den akzeptierten Grenzwerten blieben.
Was das für zukünftige Lebensmittel bedeutet
Vereinfacht gesagt haben die Autoren sechs fein abgestimmte DNA‑„Fingerabdruck“‑Tests entwickelt, die zentrale probiotische Arten schnell, genau und zuverlässig unterscheiden können. Sie warnen zwar, dass vor einer routinemäßigen industriellen Einführung noch breitere Tests an mehr Stämmen, weiteren Nicht‑Zielarten und zusätzlichen PCR‑Instrumenten nötig sind, doch die ersten Ergebnisse sind vielversprechend. Für Verbraucher tragen solche Fortschritte dazu bei, sicherzustellen, dass Lebensmittel, die mit bestimmten Probiotika beworben werden, tatsächlich die richtigen Mikroben enthalten – was zu ehrlicher Kennzeichnung, besserer Qualitätskontrolle und vertrauenswürdigeren Untersuchungen darüber führt, wie diese winzigen Partner unsere Gesundheit beeinflussen.
Zitation: Li, SJ., Cui, B., Li, W. et al. Development and preliminary evaluation of real-time PCR assays for six lactic acid bacteria. Sci Rep 16, 6165 (2026). https://doi.org/10.1038/s41598-026-37047-3
Schlüsselwörter: Probiotika, Milchsäurebakterien, Real‑Time‑PCR, Lebensmittelmikrobiologie, Mikrobielle Identifizierung