Clear Sky Science · de
Ein Multiomics-Profil koordinierter Abwehr und wichtiger Kandidatengene gegen bakteriellen Welke bei Tabak
Warum Landwirte und Züchter das beachten sollten
Bakterielle Welke ist eine gefürchtete Pflanzenkrankheit, die Tabakfelder und viele andere Kulturen vernichten kann. Sobald der Erreger den Boden verunreinigt hat, können Pflanzen plötzlich welken und absterben, was für Landwirte schwere Verluste bedeutet. Diese Studie stellt eine praktische Frage und nutzt moderne Methoden: Was macht einige Tabaksorten widerstandsfähiger gegen diese Krankheit als andere? Indem die Forschenden Tausende von Molekülen und Genen der Pflanzen gleichzeitig verfolgen, zeigen sie, wie eine mittelmäßig resistente Tabaksorte eine gestufte Abwehr aufbaut, und identifizieren ein zentrales Gen, auf das Züchter abzielen können, um stärker welkresistente Sorten zu entwickeln.
Zwei Tabaksorten, zwei sehr unterschiedliche Schicksale
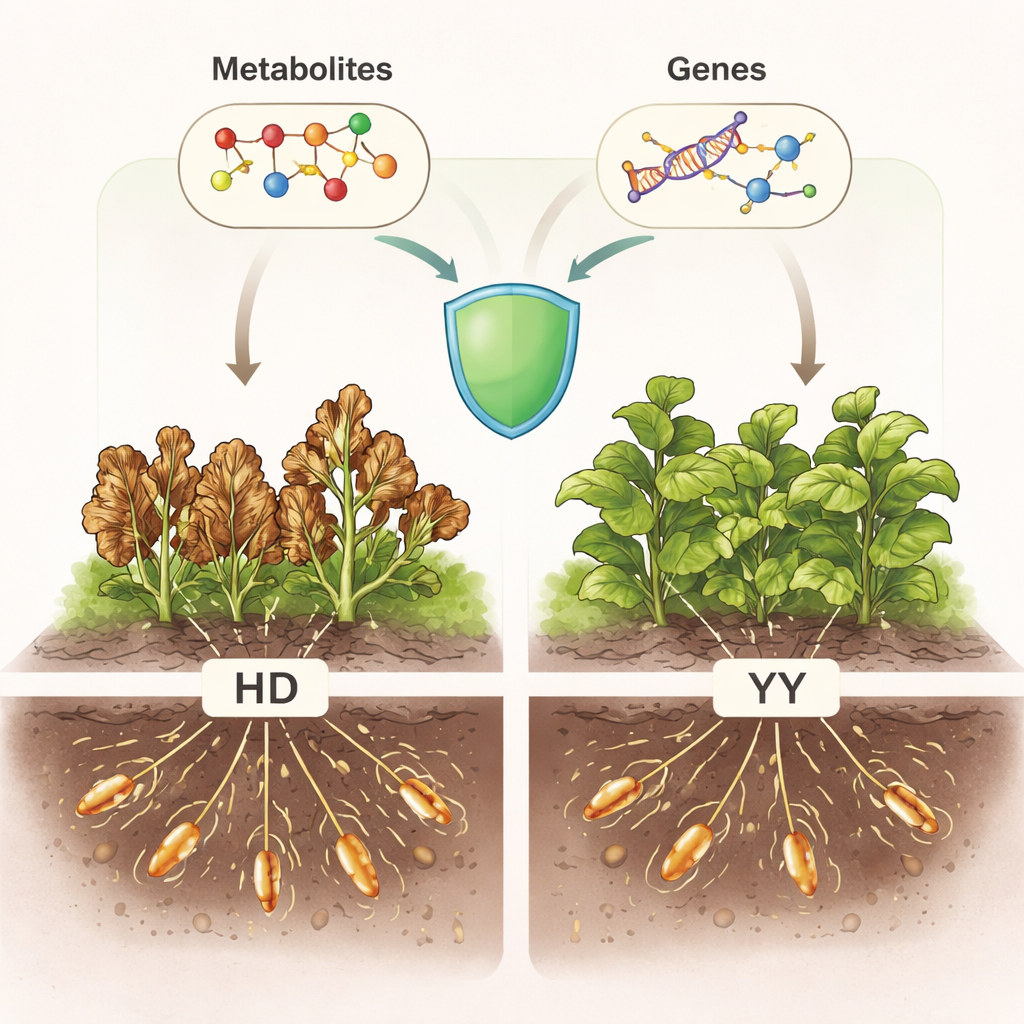
Das Team verglich eine anfällige Tabaksorte namens Honghua Dajinyuan (HD) mit einer mäßig resistenten Sorte namens Yanyan 97 (YY). Auf einem befallenen Feld waren die HD-Pflanzen bis Ende Juni nahezu vollständig erkrankt, während YY-Pflanzen langsamer krank wurden und nie denselben Schädigungsgrad erreichten. Dieser Kontrast im Feld legte den Grundstein für eine genauere Untersuchung dessen, was sich in den Pflanzen abspielte. Die Wissenschaftler sammelten Blätter von jeweils gesund aussehenden und infizierten Pflanzen beider Sorten auf dem Höhepunkt des Ausbruchs, um zu sehen, wie sich ihre interne Chemie und Genaktivität unterschieden.
Tausende kleiner Moleküle im Blick
Mithilfe fortschrittlicher chemischer Profilierung bestimmten die Forschenden nahezu 1.500 verschiedene kleine Moleküle in den Blättern, von fetthaltigen Substanzen bis zu Aminosäuren und anderen Metaboliten. Schon vor der Infektion zeigten YY und HD klar unterschiedliche metabolische "Hintergründe", was darauf hindeutet, dass ein Teil der Resistenz in der Basischemie der Pflanze verankert ist. Als das Welke-Bakterium zuschlug, reorganisierte YY Hunderte von Metaboliten. Viele Veränderungen konzentrierten sich auf Verbindungen wie Prenol-Lipide und organische Sauerstoff-Moleküle, die oft mit Signalgebung und Abwehr verknüpft sind. Die Weganalyse zeigte, dass bei YY die Infektion insbesondere Stoffwechselwege verstärkte, die in die Pflanzenhormone Jasmoninsäure (JA) und Abscisinsäure (ABA) münden, die beide dafür bekannt sind, Pflanzen bei Angriff und Stress zu unterstützen.
In die Gene der Pflanze hineinhören
Parallel dazu sequenzierte das Team RNA, um zu erfassen, welche Gene während der Infektion ein- oder ausgeschaltet wurden. Tausende Gene reagierten in den jeweiligen Vergleichen, doch 818 Gene stachen als eine gemeinsame "Kern"-Gruppe hervor, die mit der Resistenz von YY verbunden war. Viele dieser Gene sind an der Verstärkung der Zellwände, dem Umgang mit oxidativem Stress und der Verarbeitung von Signalen durch Hormone und andere Botenstoffe beteiligt. Netzwerk-Analysen ordneten Gene in Cluster ein, die koordiniert reagierten; zwei große Cluster korrelierten stark mit Anfälligkeit beziehungsweise Widerstand. Innerhalb dieser Cluster konzentrierten sich die Forschenden auf ein einzelnes herausragendes Gen, Nta17g05760, das in einer genomischen Region liegt, die in früheren genetischen Kartierungsstudien bereits mit Welke-Resistenz in Verbindung gebracht wurde.
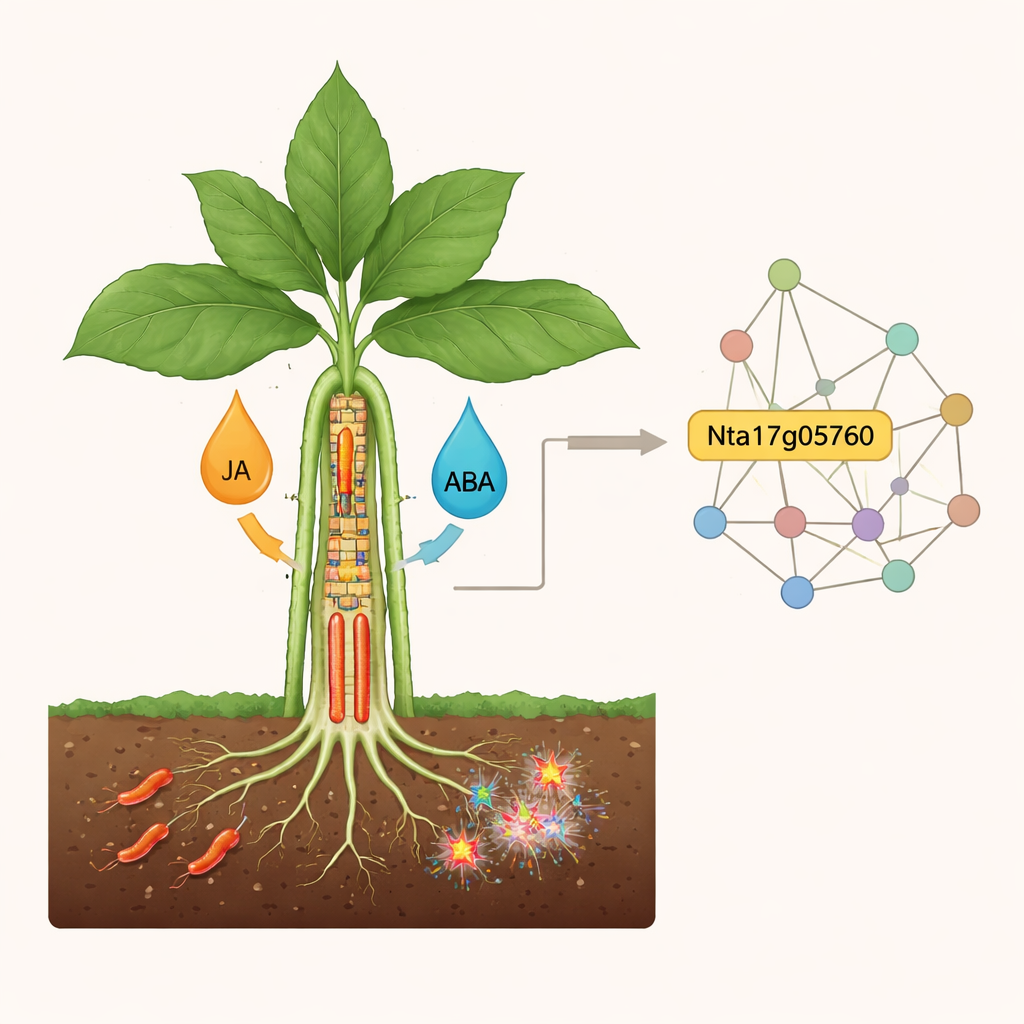
Ein verdächtiges Gen in der Abwehrkette
Nta17g05760 zeigte ein aussagekräftiges Expressionsmuster. In gesunden Pflanzen war es in der anfälligen HD höher exprimiert als in der resistenten YY. Nach der Infektion fiel seine Expression in HD stark ab, blieb jedoch in YY niedrig und relativ stabil. Dieses Verhalten, zusammen mit seiner Lage in einer resistenzassoziierten Region, legt nahe, dass Nta17g05760 eher wie eine Bremse als ein Beschleuniger der Abwehr wirkt: Pflanzen mit natürlicherweise geringerer Aktivität dieses Gens könnten freier starke Immunantworten ausbilden. Indem die Studie Genaktivität mit Metabolitveränderungen korrelierte, hob sie zudem gemeinsame Wege hervor — etwa solche, die auf die Produktion spezialisierter antimikrobieller Verbindungen wie Diterpenoide zielen — die YY wahrscheinlich helfen, das eindringende Bakterium in Schach zu halten.
Was das für künftige Kulturen bedeutet
Für Nicht‑Spezialisten ist die Kernbotschaft: Welke‑Resistenz beim Tabak wird nicht von einem einzigen Schalter gesteuert, sondern von einem fein abgestimmten Netzwerk aus chemischer Abwehr und Genaktivität. Die resistente Sorte YY bereitet schützende Moleküle vor und setzt sie ein, stärkt ihre Zellwände und aktiviert Hormonabwehrmechanismen effektiver als die anfällige HD. Unter den vielen beteiligten Genen rückt Nta17g05760 als vielversprechender Kandidat in den Vordergrund, auf den Züchter und Molekularbiologen abzielen können, um neue, welkresistente Tabaklinien zu entwickeln. Weitere Experimente sind nötig, um seine genaue Rolle zu bestätigen, doch diese Arbeit liefert eine Roadmap und konkrete genetische Ziele, um Pflanzen vor einer kostspieligen und hartnäckigen Krankheit zu schützen.
Zitation: Qing, Y., Wei, L., Yong, L. et al. A multiomics profile of coordinated defense and key candidate genes against bacterial wilt in tobacco. Sci Rep 16, 6043 (2026). https://doi.org/10.1038/s41598-026-36889-1
Schlüsselwörter: bakterielle Welke, Tabakresistenz, Pflanzenimmunität, Multiomics, Pflanzenzüchtung