Clear Sky Science · de
QSPR-Analyse von Krebsmedikamenten unter Verwendung des Euler–Sombor-Index und theoretische Einsichten in dessen Minimalwert für unizyklische Graphen
Warum die Form eines Moleküls für Krebsmedikamente wichtig ist
Krebsmedikamente bestehen aus Atomen, die in komplexen Mustern verbunden sind, und schon kleine Änderungen in diesen Mustern können das Verhalten eines Medikaments im Körper verändern. Die genaue Messung solcher Unterschiede erfordert oft langsame und kostspielige Laborarbeit. Diese Studie untersucht eine mathematische Abkürzung: die Verwendung einer einzelnen Zahl, des Euler–Sombor-Index, die aus der Struktur eines Moleküls gewonnen wird, um wichtige physikalische Eigenschaften von Krebsmedikamenten abzuschätzen – was Chemikern helfen könnte, Kandidaten schneller zu sichten und zu verstehen, welche Formen am besten wirken.
Wie man Moleküle in einfache Landkarten verwandelt
Chemiker beschreiben Moleküle oft als Graphen, wobei Atome Punkte und Bindungen Linien sind, die sie verbinden. Aus diesen Graphen berechnen Forschende „topologische Indizes“ – wohlüberlegte Zahlen, die erfassen, wie gut vernetzt und wie dicht ein Molekül ist, ohne auf 3D-Geometrie oder Quantenmechanik Bezug zu nehmen. Der Euler–Sombor-Index ist ein neues Mitglied dieser Familie. Er kombiniert Informationen darüber, wie viele Bindungen jedes Atom hat und wie diese Atome verknüpft sind, und erzeugt so einen einzelnen numerischen Fingerabdruck für jedes Molekül. Da er, einmal die Struktur bekannt ist, leicht zu berechnen ist, eignet sich dieser Index besonders für großangelegte Screenings von Wirkstoffkandidaten.
Vorhersage wesentlicher Eigenschaften von Krebsmedikamenten
Die Autoren berechneten den Euler–Sombor-Index für 17 bekannte Krebsmedikamente, darunter Wirkstoffe wie Carmustin, Melatonin und Daunorubicin. Für jedes Medikament sammelten sie vier grundlegende, aber wichtige physikalische Eigenschaften aus einer chemischen Datenbank: Siedepunkt, Schmelzpunkt, Enthalpie (bezogen auf die Wärme, die bei Zustandsänderungen beteiligt ist) und molare Brechung (die widerspiegelt, wie das Molekül mit Licht interagiert und indirekt wie „voluminös“ seine Elektronen sind). Anschließend verwendeten sie Standardstatistikwerkzeuge, sogenannte Regressionsmodelle, um zu prüfen, wie gut sich jede dieser Eigenschaften allein aus dem strukturellen Fingerabdruck vorhersagen ließ.
Wie gut schlägt sich der Index?
Das Team verglich drei Regressionsarten: linear (ein geradliniger Trend), quadratisch (eine sanft gekrümmte Beziehung) und logarithmisch (eine Kurve, die anfangs schnell ansteigt und sich dann abflacht). Für Siedepunkt und Enthalpie zeigten alle drei Ansätze einigermaßen starke Zusammenhänge zwischen dem Euler–Sombor-Index und den gemessenen Werten, wobei die Vorhersagen für den Siedepunkt weniger präzise waren und größere Abweichungen zwischen vorhergesagten und tatsächlichen Temperaturen aufwiesen. Für den Schmelzpunkt waren die Zusammenhänge etwas schwächer, aber immer noch bedeutsam. Besonders auffällig war die molare Brechung: Hier folgte der Index den Daten sehr genau und lieferte über alle Modelle hinweg geringe Vorhersagefehler und hohe statistische Zuverlässigkeit.
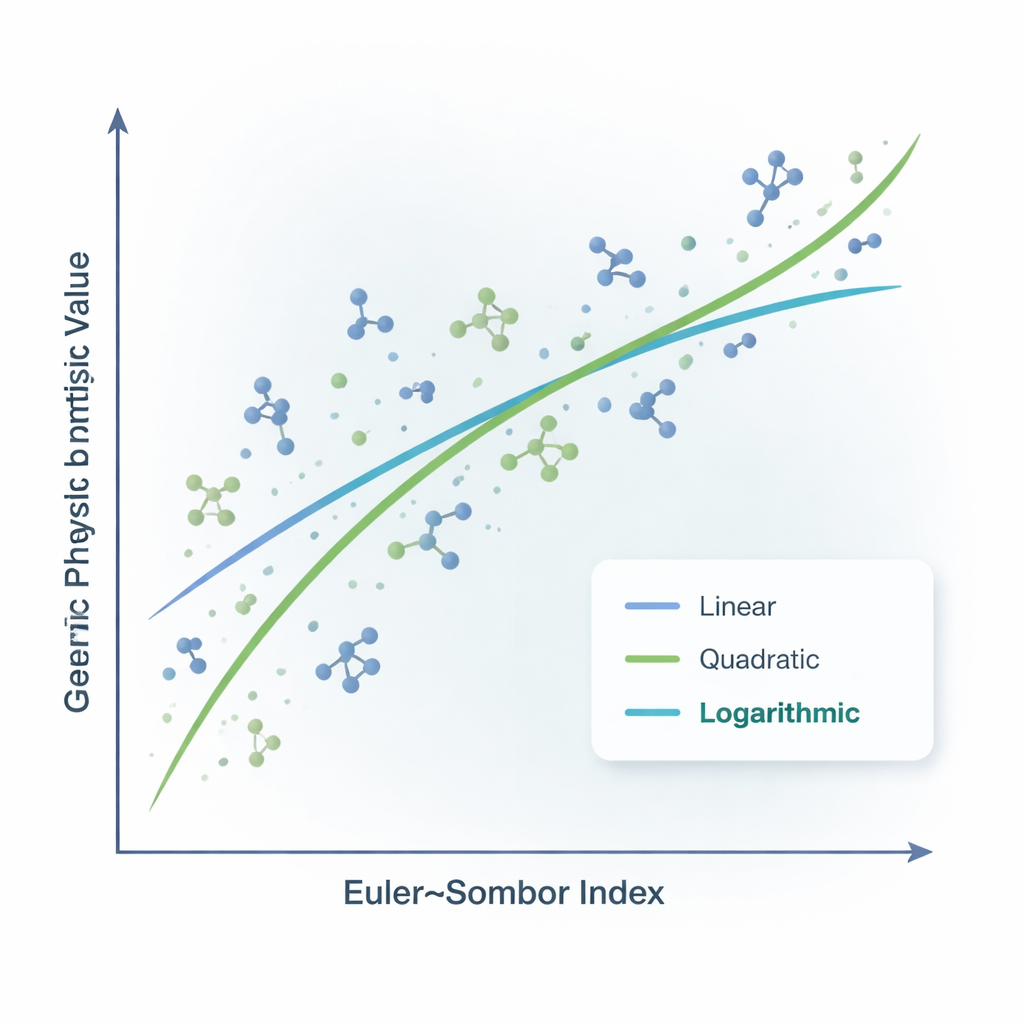
Die beste mathematische Anpassung finden
Bei genauerer Betrachtung der Statistik stellten die Autoren fest, dass das logarithmische Modell allgemein am besten für Siedepunkt, Schmelzpunkt und molare Brechung abschnitt und hohe Korrelationswerte sowie sehr geringe Wahrscheinlichkeiten für zufällige Ergebnisse lieferte. Für die Enthalpie funktionierte ein einfaches Geradenmodell etwas besser als die gekrümmten Modelle. In der Praxis bedeutet dies: Kennt ein Chemiker den Euler–Sombor-Index eines Kandidatenmoleküls, kann er ihn in diese angepassten Gleichungen einsetzen, um eine vernünftige Schätzung mehrerer physikalischer Eigenschaften zu erhalten – bevor die Verbindung jemals im Labor synthetisiert wird. Die Studie weist jedoch darauf hin, dass der Datensatz überschaubar ist und die Vorhersagen für den Siedepunkt relativ verrauscht bleiben; diese Modelle sind also vielversprechende Wegweiser, aber keine endgültigen Antworten.
Was die Formen einfacher Graphen enthüllen
Über praktische Vorhersagen hinaus geht das Papier in die Mathematik des Euler–Sombor-Index. Die Autoren untersuchen „unizyklische“ Graphen – einfache, ringartige Strukturen mit genau einem Ring – und bestimmen, welche von ihnen die kleinsten und drittkleinsten möglichen Indexwerte für eine gegebene Größe liefern. Durch sorgfältige Umformungen und Vergleiche verschiedener Graphenfamilien identifizieren sie spezifische Muster, wie kurze Verzweigungen an einem Einzelring angeordnet sein müssen, um den Index zu minimieren. Diese Ergebnisse helfen zu erklären, wie bestimmte strukturelle Motive den Euler–Sombor-Wert nach oben oder unten treiben und verbinden reine Graphentheorie mit potenziellem molekularem Verhalten.
Was das für das zukünftige Wirkstoffdesign bedeutet
Für Nicht-Fachleute ist die Kernbotschaft, dass eine geschickt gewählte Zahl, die aus der Art stammt, wie Atome in einem Molekül verbunden sind, überraschend viel über das Verhalten dieses Moleküls aussagen kann. Der Euler–Sombor-Index zeigt großes Potenzial als kompakter, informativer Deskriptor für Krebsmedikamente, insbesondere für Eigenschaften wie molare Brechung und Enthalpie. Zugleich vertieft die mathematische Analyse einfacher ringförmiger Graphen unser Verständnis dafür, warum bestimmte Strukturmuster zu niedrigeren oder höheren Indexwerten führen. Zusammengenommen deuten diese Einsichten darauf hin, dass Werkzeuge aus der Graphentheorie Chemikern helfen können, effizientere und gezieltere Suchstrategien für künftige Krebstherapien zu entwickeln.
Zitation: Shetty, S., Rakshith, B.R. & Udupa, N.V.S. QSPR analysis of anticancer drugs using the Euler–Sombor index and theoretical insights on its minimum value for unicyclic graphs. Sci Rep 16, 6924 (2026). https://doi.org/10.1038/s41598-026-36855-x
Schlüsselwörter: Krebsmedikamente, Euler–Sombor-Index, QSPR-Modellierung, molekulare Topologie, Graphentheorie in der Chemie